peptides
spectra
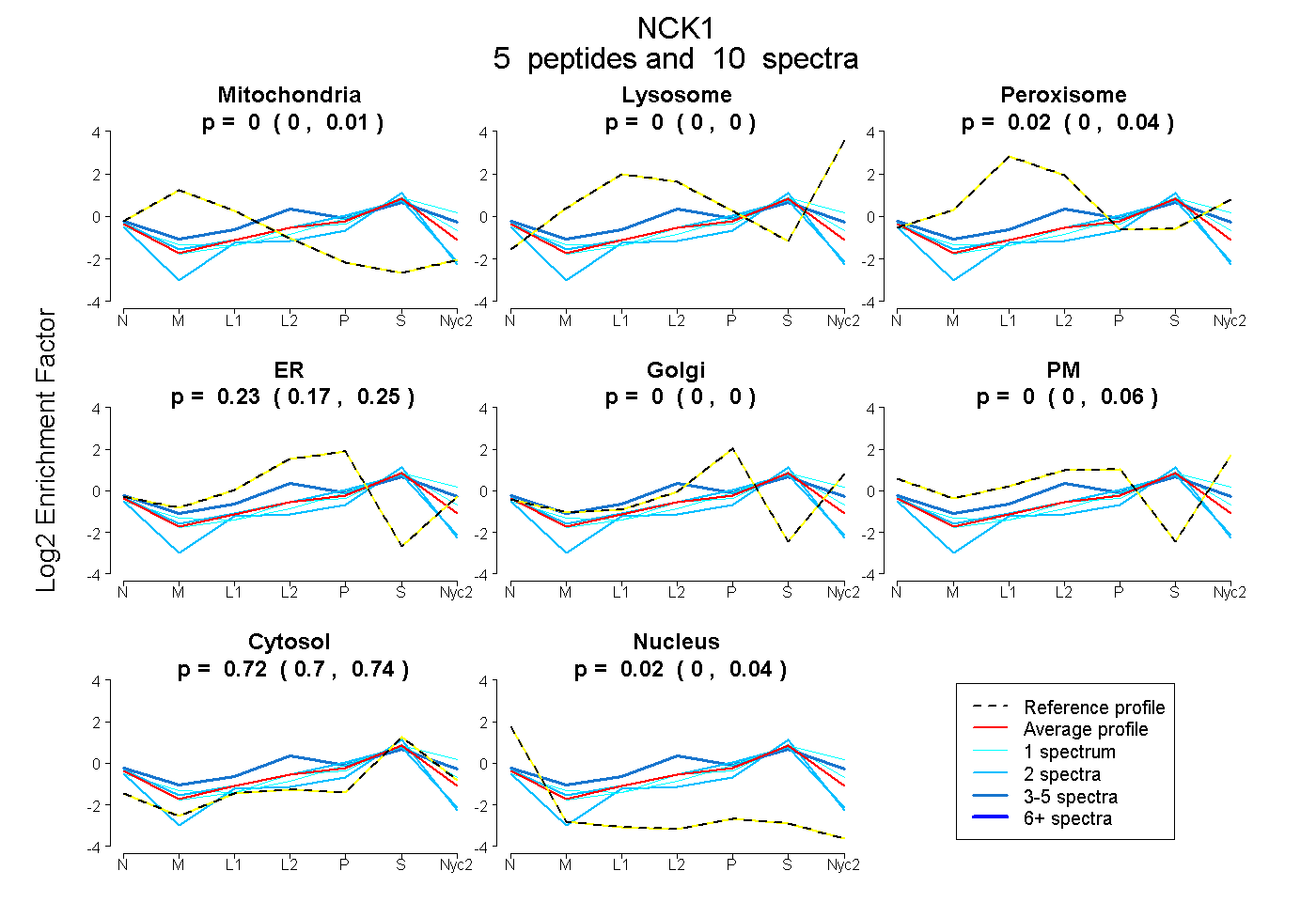
0.000 | 0.008
0.000 | 0.000
0.000 | 0.042
0.173 | 0.252
0.000 | 0.000
0.000 | 0.058
0.699 | 0.740
0.000 | 0.042
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
10 spectra |
 |
0.000 0.000 | 0.008 |
0.000 0.000 | 0.000 |
0.021 0.000 | 0.042 |
0.235 0.173 | 0.252 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.058 |
0.721 0.699 | 0.740 |
0.023 0.000 | 0.042 |
| 1 spectrum, KPSVPDTASPADDSFVDPGER | 0.000 | 0.000 | 0.000 | 0.000 | 0.096 | 0.204 | 0.700 | 0.000 | ||
| 4 spectra, HQAEMALNER | 0.000 | 0.000 | 0.175 | 0.135 | 0.000 | 0.141 | 0.549 | 0.000 | ||
| 2 spectra, LYDLNMPAFVK | 0.017 | 0.000 | 0.000 | 0.261 | 0.000 | 0.000 | 0.646 | 0.077 | ||
| 2 spectra, ETVYCIGQR | 0.000 | 0.000 | 0.000 | 0.055 | 0.000 | 0.000 | 0.808 | 0.137 | ||
| 1 spectrum, EDELSLIK | 0.022 | 0.000 | 0.000 | 0.110 | 0.000 | 0.132 | 0.736 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
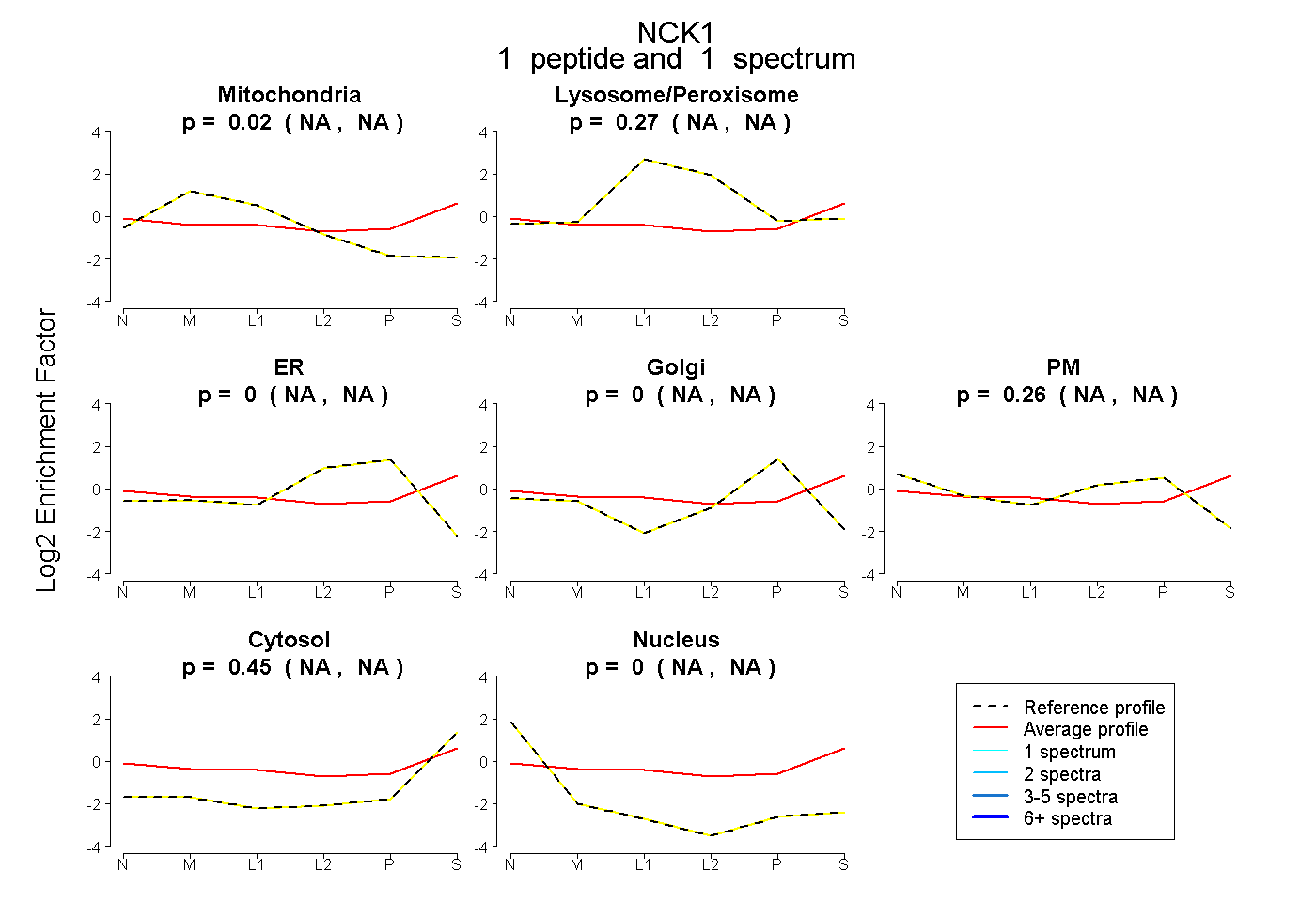 |
0.023 NA | NA |
0.266 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.262 NA | NA |
0.447 NA | NA |
0.003 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
10 spectra |
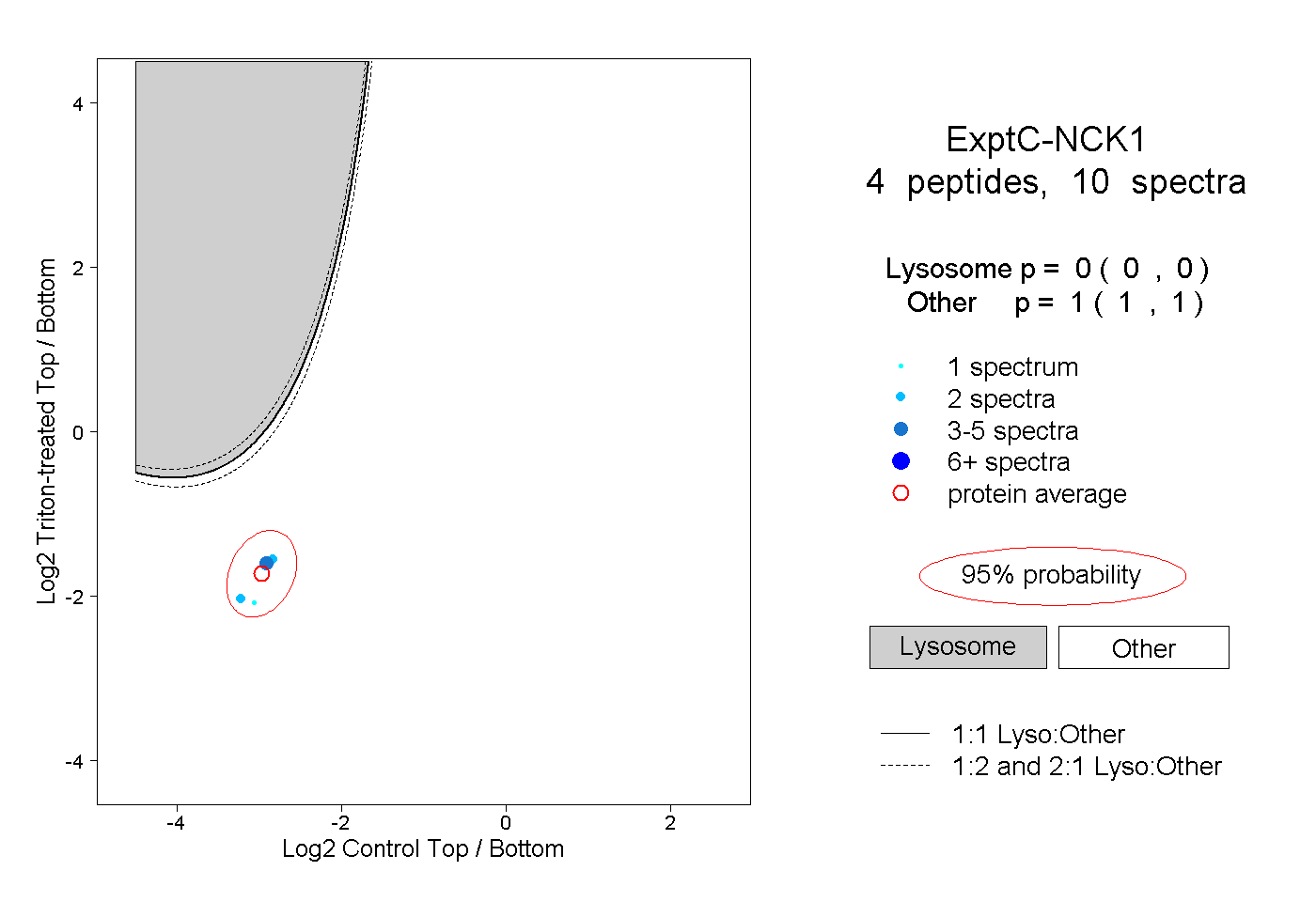 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |