peptides
spectra
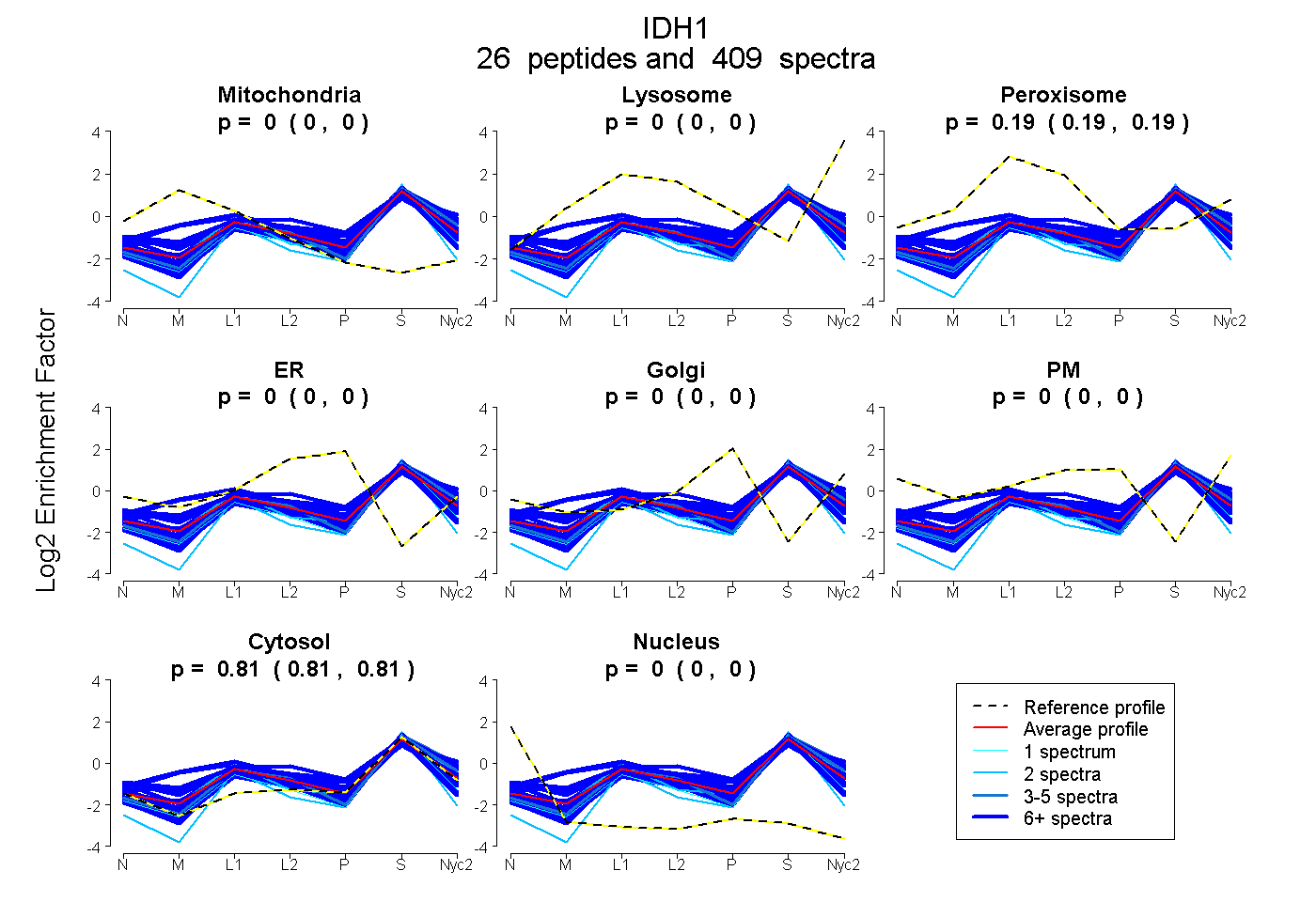
0.000 | 0.000
0.000 | 0.000
0.188 | 0.190
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.810 | 0.812
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
409 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.189 0.188 | 0.190 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.811 0.810 | 0.812 |
0.000 0.000 | 0.000 |
| 11 spectra, DLAACIK | 0.048 | 0.000 | 0.049 | 0.000 | 0.000 | 0.000 | 0.902 | 0.000 | ||
| 4 spectra, VTYLVHDFEEGGGVAMGMYNQDK | 0.000 | 0.000 | 0.153 | 0.000 | 0.000 | 0.000 | 0.847 | 0.000 | ||
| 8 spectra, LILPYVELDLHSYDLGIENR | 0.000 | 0.000 | 0.105 | 0.000 | 0.000 | 0.000 | 0.895 | 0.000 | ||
| 5 spectra, ATDFVVPGPGK | 0.000 | 0.079 | 0.072 | 0.000 | 0.000 | 0.000 | 0.849 | 0.000 | ||
| 9 spectra, DIFQEIYDK | 0.000 | 0.000 | 0.067 | 0.000 | 0.000 | 0.000 | 0.933 | 0.000 | ||
| 7 spectra, GWPLYLSTK | 0.000 | 0.033 | 0.175 | 0.000 | 0.000 | 0.000 | 0.792 | 0.000 | ||
| 62 spectra, GLPNVQR | 0.000 | 0.000 | 0.081 | 0.000 | 0.000 | 0.000 | 0.919 | 0.000 | ||
| 15 spectra, TVEAEAAHGTVTR | 0.017 | 0.000 | 0.287 | 0.000 | 0.004 | 0.000 | 0.692 | 0.000 | ||
| 23 spectra, IHGGSVVEMQGDEMTR | 0.000 | 0.086 | 0.251 | 0.000 | 0.000 | 0.029 | 0.634 | 0.000 | ||
| 10 spectra, LGENLK | 0.016 | 0.000 | 0.102 | 0.000 | 0.000 | 0.000 | 0.881 | 0.000 | ||
| 30 spectra, IWYEHR | 0.160 | 0.000 | 0.262 | 0.000 | 0.000 | 0.000 | 0.578 | 0.000 | ||
| 46 spectra, IIWELIK | 0.000 | 0.000 | 0.065 | 0.000 | 0.000 | 0.000 | 0.935 | 0.000 | ||
| 6 spectra, SPNGTIR | 0.190 | 0.000 | 0.242 | 0.000 | 0.000 | 0.000 | 0.568 | 0.000 | ||
| 7 spectra, DAAEAIK | 0.000 | 0.000 | 0.184 | 0.029 | 0.000 | 0.000 | 0.787 | 0.000 | ||
| 10 spectra, CATITPDEK | 0.069 | 0.000 | 0.222 | 0.000 | 0.000 | 0.000 | 0.709 | 0.000 | ||
| 11 spectra, EAIICK | 0.000 | 0.000 | 0.122 | 0.000 | 0.000 | 0.000 | 0.852 | 0.026 | ||
| 29 spectra, LIDDMVAQAMK | 0.000 | 0.064 | 0.181 | 0.000 | 0.000 | 0.000 | 0.756 | 0.000 | ||
| 2 spectra, GQETSTNPIASIFAWSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 19 spectra, YNVGVK | 0.000 | 0.000 | 0.177 | 0.000 | 0.000 | 0.000 | 0.823 | 0.000 | ||
| 18 spectra, SDYLNTFEFMDK | 0.000 | 0.000 | 0.170 | 0.000 | 0.000 | 0.000 | 0.830 | 0.000 | ||
| 13 spectra, SEGGFIWACK | 0.092 | 0.000 | 0.095 | 0.000 | 0.000 | 0.000 | 0.812 | 0.000 | ||
| 1 spectrum, VEITYTPK | 0.020 | 0.000 | 0.030 | 0.000 | 0.000 | 0.000 | 0.950 | 0.000 | ||
| 24 spectra, NILGGTVFR | 0.134 | 0.015 | 0.258 | 0.000 | 0.000 | 0.000 | 0.593 | 0.000 | ||
| 2 spectra, SIEDFAHSSFQMALSK | 0.000 | 0.000 | 0.184 | 0.000 | 0.000 | 0.000 | 0.816 | 0.000 | ||
| 6 spectra, DATNDQVTK | 0.000 | 0.000 | 0.208 | 0.019 | 0.000 | 0.000 | 0.773 | 0.000 | ||
| 31 spectra, HAYGDQYR | 0.034 | 0.000 | 0.242 | 0.000 | 0.000 | 0.000 | 0.724 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
94 spectra |
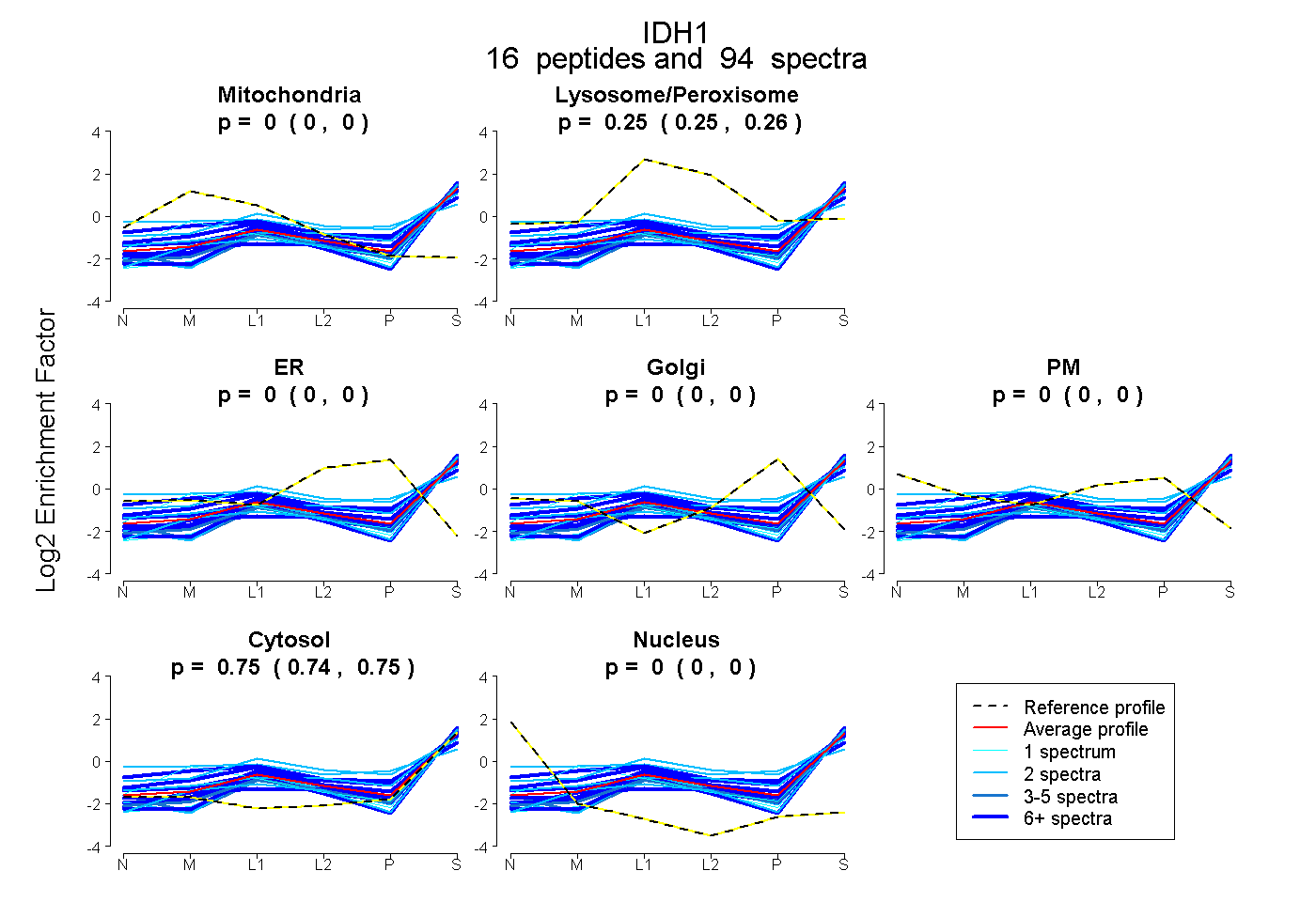 |
0.000 0.000 | 0.000 |
0.253 0.250 | 0.255 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.747 0.744 | 0.749 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
808 spectra |
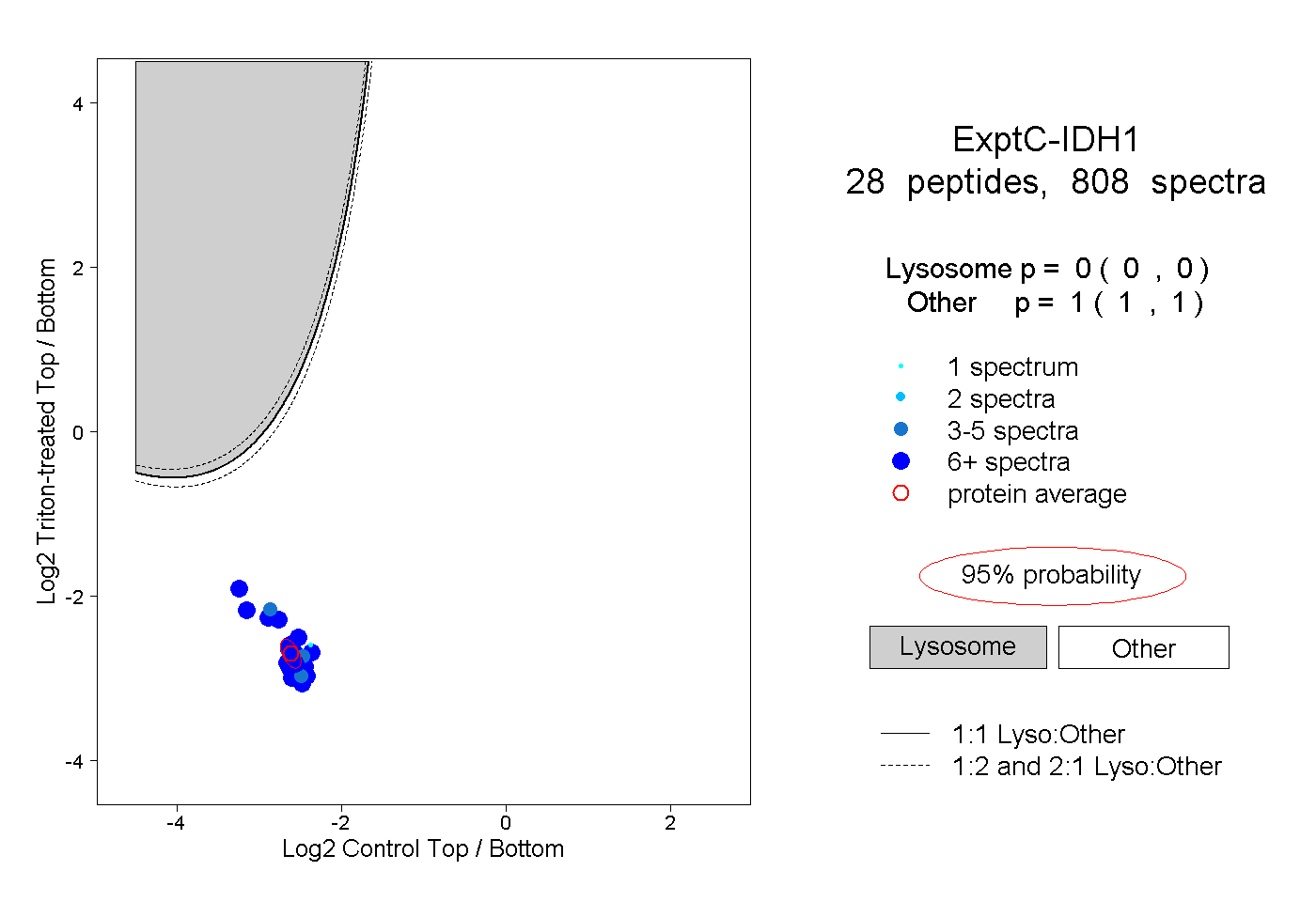 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
76 spectra |
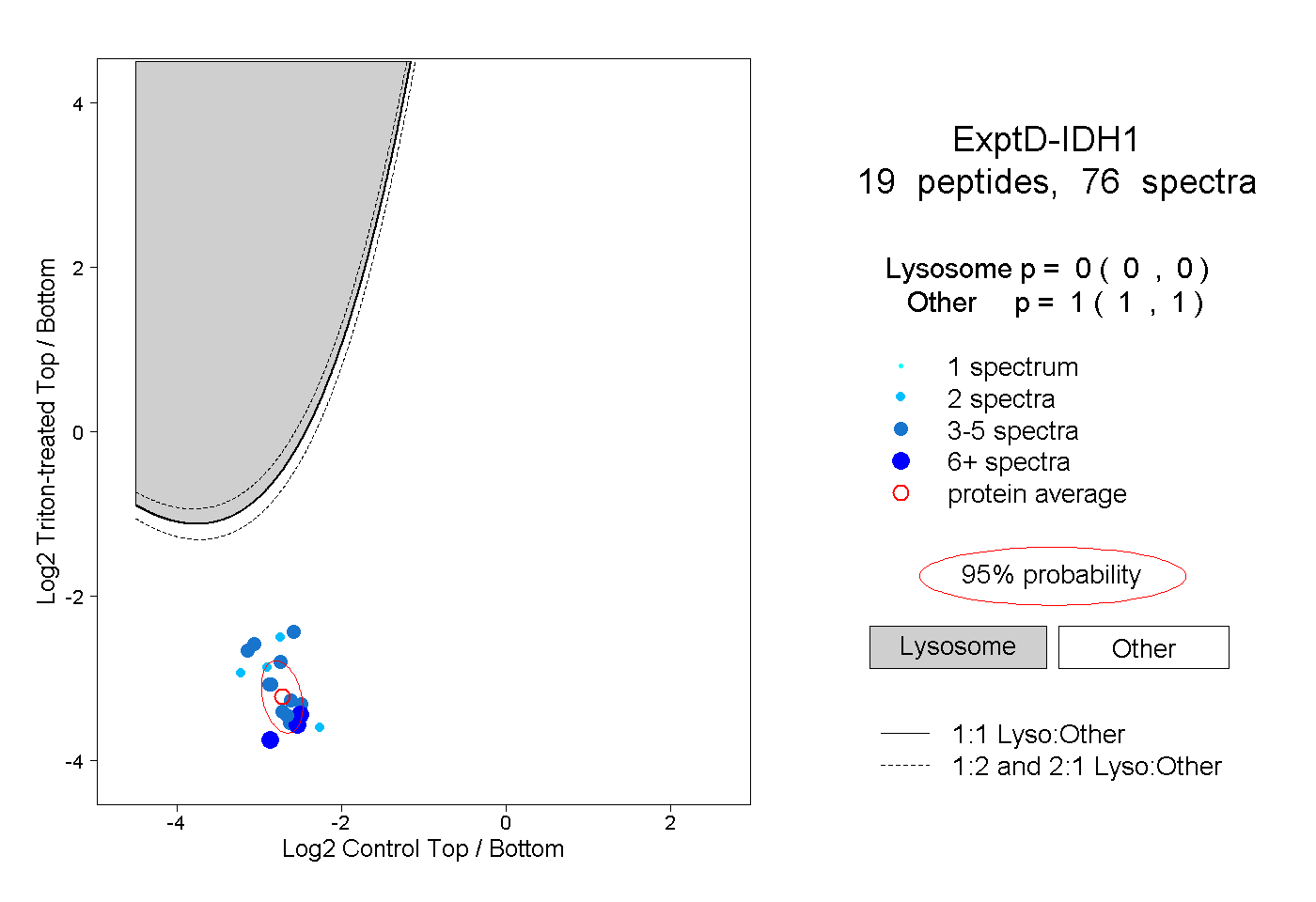 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |