peptides
spectra
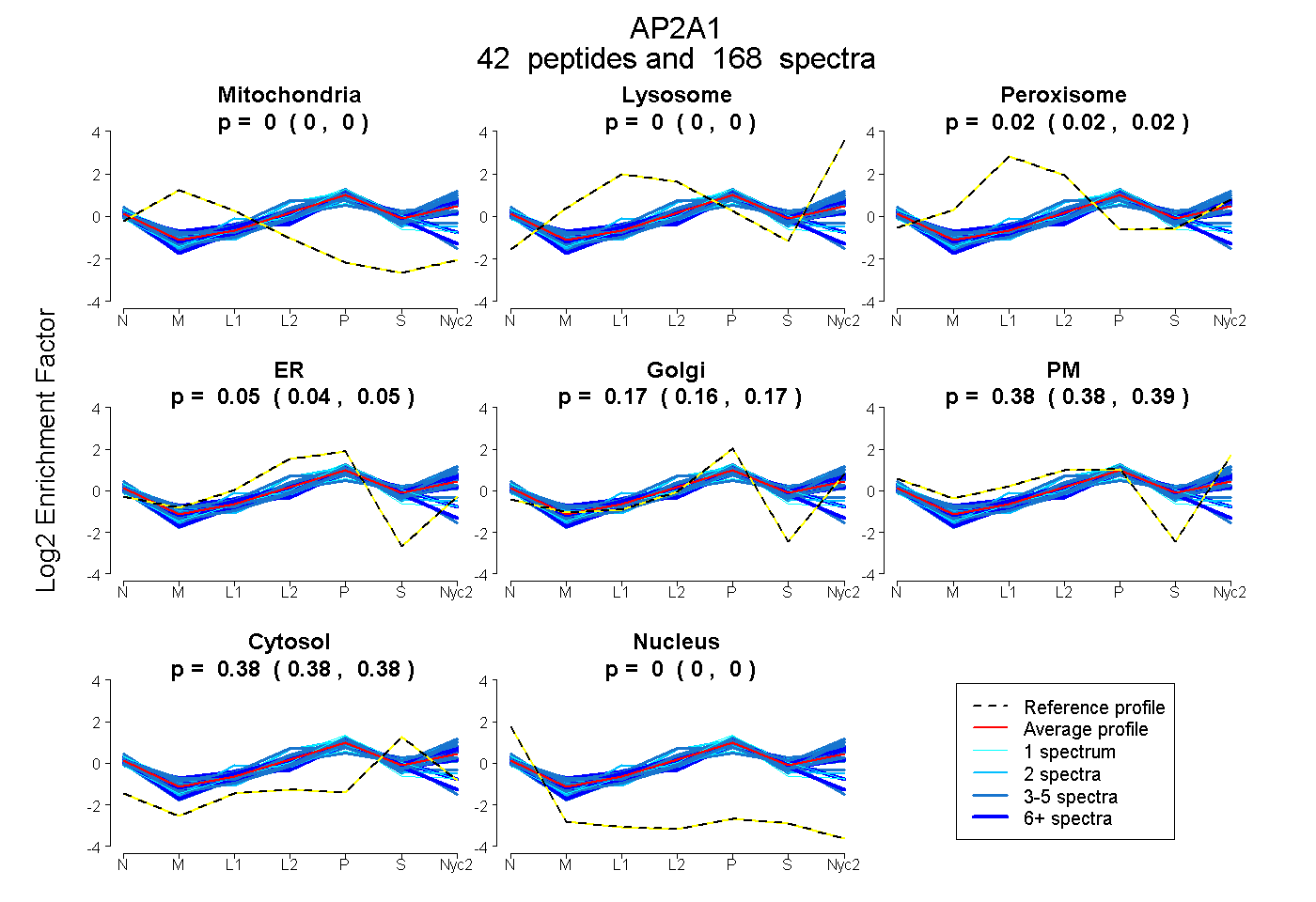
0.000 | 0.000
0.000 | 0.000
0.018 | 0.021
0.041 | 0.054
0.163 | 0.173
0.380 | 0.388
0.378 | 0.381
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
168 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.020 0.018 | 0.021 |
0.048 0.041 | 0.054 |
0.169 0.163 | 0.173 |
0.384 0.380 | 0.388 |
0.379 0.378 | 0.381 |
0.000 0.000 | 0.000 |
| 11 spectra, FHLCSVATR | 0.000 | 0.000 | 0.071 | 0.309 | 0.163 | 0.000 | 0.440 | 0.018 | ||
| 3 spectra, HLCELLAQQF | 0.000 | 0.000 | 0.001 | 0.055 | 0.000 | 0.480 | 0.464 | 0.000 | ||
| 4 spectra, AQEPPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.225 | 0.404 | 0.370 | 0.000 | ||
| 6 spectra, QSAALCLLR | 0.062 | 0.000 | 0.000 | 0.537 | 0.000 | 0.000 | 0.398 | 0.003 | ||
| 8 spectra, VAILAEK | 0.000 | 0.032 | 0.037 | 0.000 | 0.220 | 0.367 | 0.343 | 0.000 | ||
| 2 spectra, SSPPVQFSLLHSK | 0.000 | 0.018 | 0.060 | 0.000 | 0.101 | 0.399 | 0.421 | 0.000 | ||
| 3 spectra, ESSILAK | 0.000 | 0.000 | 0.005 | 0.000 | 0.126 | 0.465 | 0.404 | 0.000 | ||
| 2 spectra, ATIQGVLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.160 | 0.482 | 0.358 | 0.000 | ||
| 1 spectrum, NPTFMCLALHCIANVGSR | 0.000 | 0.000 | 0.011 | 0.600 | 0.000 | 0.064 | 0.305 | 0.019 | ||
| 1 spectrum, AGSQLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.273 | 0.453 | 0.274 | 0.000 | ||
| 2 spectra, LVECLETVLNK | 0.000 | 0.000 | 0.000 | 0.363 | 0.205 | 0.055 | 0.359 | 0.019 | ||
| 2 spectra, ASPDLVPMGEWTAR | 0.000 | 0.047 | 0.000 | 0.000 | 0.152 | 0.432 | 0.369 | 0.000 | ||
| 5 spectra, LPVTINK | 0.000 | 0.000 | 0.000 | 0.028 | 0.152 | 0.476 | 0.343 | 0.000 | ||
| 3 spectra, ALQVGCLLR | 0.000 | 0.000 | 0.000 | 0.491 | 0.000 | 0.000 | 0.467 | 0.042 | ||
| 4 spectra, VQHSNAK | 0.000 | 0.000 | 0.000 | 0.028 | 0.429 | 0.180 | 0.363 | 0.000 | ||
| 3 spectra, NPDDFK | 0.000 | 0.049 | 0.000 | 0.000 | 0.204 | 0.419 | 0.327 | 0.000 | ||
| 3 spectra, ILVAGDSMDSVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.173 | 0.500 | 0.328 | 0.000 | ||
| 4 spectra, ALLLSTYIK | 0.000 | 0.101 | 0.000 | 0.000 | 0.074 | 0.455 | 0.369 | 0.000 | ||
| 2 spectra, GPGAASALDDSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.183 | 0.418 | 0.399 | 0.000 | ||
| 7 spectra, GLAVFISDIR | 0.000 | 0.000 | 0.020 | 0.000 | 0.207 | 0.424 | 0.349 | 0.000 | ||
| 5 spectra, ACNQLGQFLQHR | 0.000 | 0.000 | 0.129 | 0.101 | 0.264 | 0.150 | 0.357 | 0.000 | ||
| 1 spectrum, QIVSEMLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.562 | 0.438 | 0.000 | ||
| 4 spectra, AADLLYAMCDR | 0.000 | 0.000 | 0.091 | 0.334 | 0.187 | 0.044 | 0.343 | 0.000 | ||
| 1 spectrum, YLALESMCTLASSEFSHEAVK | 0.000 | 0.000 | 0.000 | 0.478 | 0.066 | 0.000 | 0.456 | 0.000 | ||
| 4 spectra, THIDTVINALK | 0.000 | 0.083 | 0.004 | 0.000 | 0.000 | 0.583 | 0.330 | 0.000 | ||
| 3 spectra, ALDGYSK | 0.000 | 0.003 | 0.114 | 0.000 | 0.286 | 0.264 | 0.333 | 0.000 | ||
| 6 spectra, LEPNAQAQMYR | 0.000 | 0.000 | 0.000 | 0.000 | 0.241 | 0.318 | 0.441 | 0.000 | ||
| 2 spectra, FINLFPETK | 0.000 | 0.001 | 0.000 | 0.000 | 0.203 | 0.415 | 0.381 | 0.000 | ||
| 4 spectra, IAGDYVSEEVWYR | 0.000 | 0.062 | 0.000 | 0.000 | 0.172 | 0.400 | 0.366 | 0.000 | ||
| 5 spectra, FFQPTEMAAQDFFQR | 0.000 | 0.008 | 0.058 | 0.000 | 0.137 | 0.449 | 0.347 | 0.000 | ||
| 4 spectra, YLETADYAIR | 0.000 | 0.069 | 0.000 | 0.000 | 0.197 | 0.326 | 0.408 | 0.000 | ||
| 5 spectra, VLQIVTNR | 0.000 | 0.046 | 0.000 | 0.000 | 0.164 | 0.479 | 0.311 | 0.000 | ||
| 4 spectra, NADVELQQR | 0.000 | 0.000 | 0.000 | 0.028 | 0.112 | 0.506 | 0.353 | 0.000 | ||
| 2 spectra, ELANIR | 0.000 | 0.001 | 0.000 | 0.000 | 0.186 | 0.433 | 0.380 | 0.000 | ||
| 4 spectra, DFLTPPLLSVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.229 | 0.392 | 0.379 | 0.000 | ||
| 5 spectra, DDVQGYAAK | 0.000 | 0.021 | 0.000 | 0.000 | 0.182 | 0.340 | 0.457 | 0.000 | ||
| 5 spectra, ANHPMDAEVTK | 0.000 | 0.000 | 0.010 | 0.063 | 0.127 | 0.438 | 0.363 | 0.000 | ||
| 8 spectra, MYLFYGNK | 0.000 | 0.000 | 0.141 | 0.105 | 0.257 | 0.176 | 0.320 | 0.000 | ||
| 3 spectra, NDLASR | 0.000 | 0.000 | 0.000 | 0.000 | 0.134 | 0.539 | 0.327 | 0.000 | ||
| 8 spectra, EMGEAFAADIPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.117 | 0.482 | 0.402 | 0.000 | ||
| 7 spectra, SELVLK | 0.000 | 0.002 | 0.000 | 0.000 | 0.129 | 0.456 | 0.414 | 0.000 | ||
| 2 spectra, LINNAIK | 0.000 | 0.027 | 0.000 | 0.000 | 0.160 | 0.526 | 0.288 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
9 spectra |
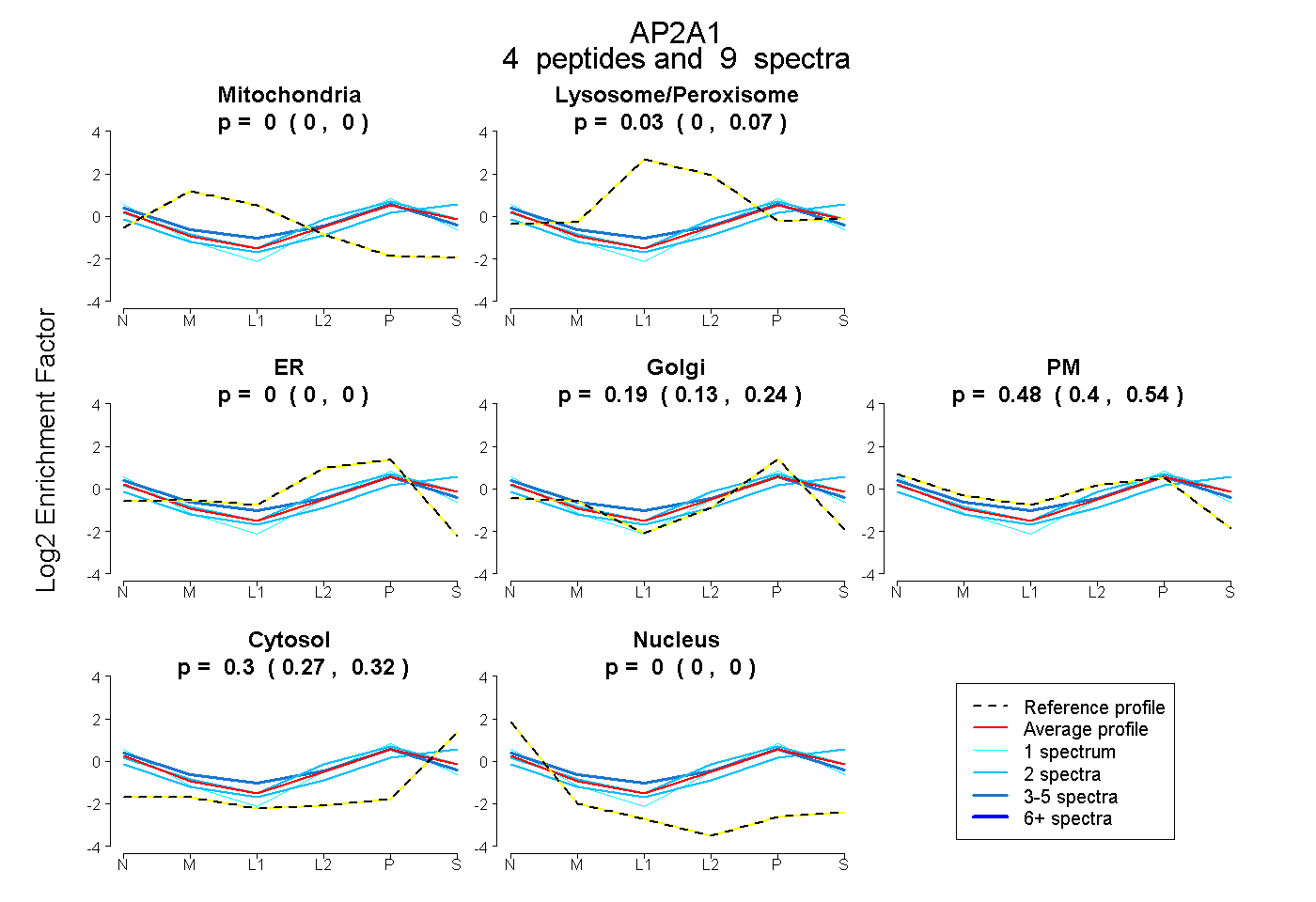 |
0.000 0.000 | 0.000 |
0.034 0.000 | 0.065 |
0.000 0.000 | 0.000 |
0.188 0.128 | 0.239 |
0.480 0.401 | 0.544 |
0.297 0.273 | 0.319 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
86 spectra |
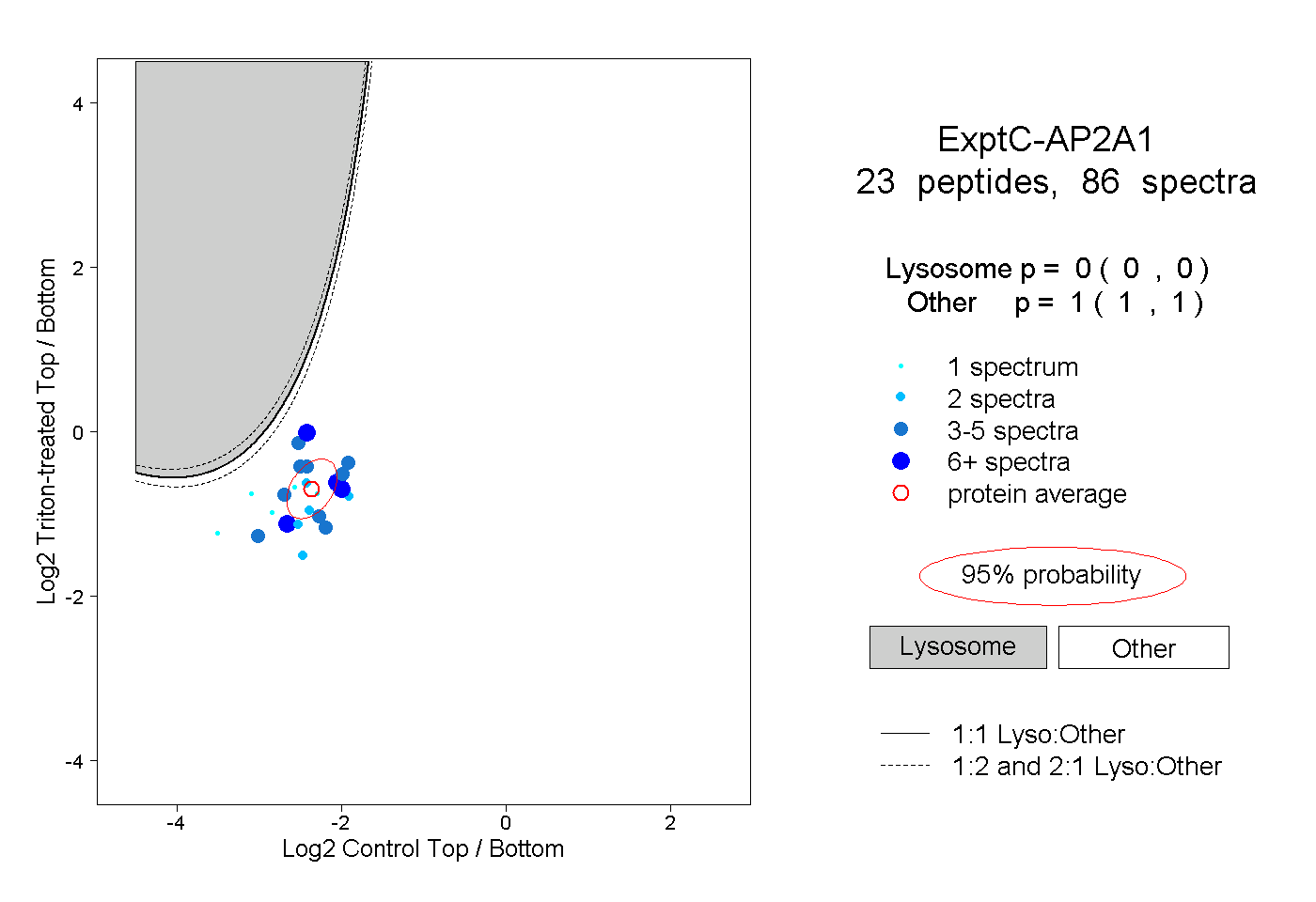 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
10 spectra |
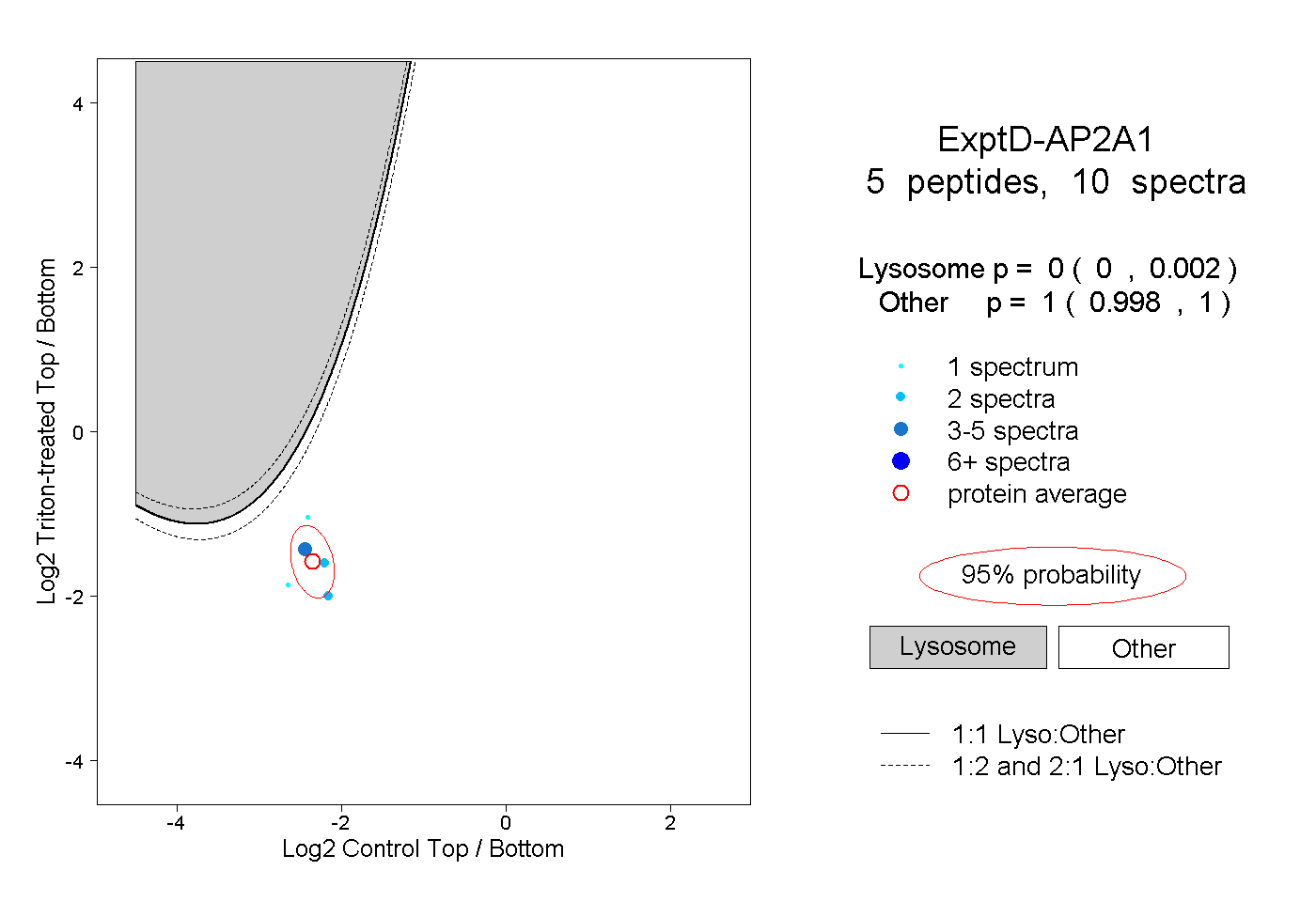 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |