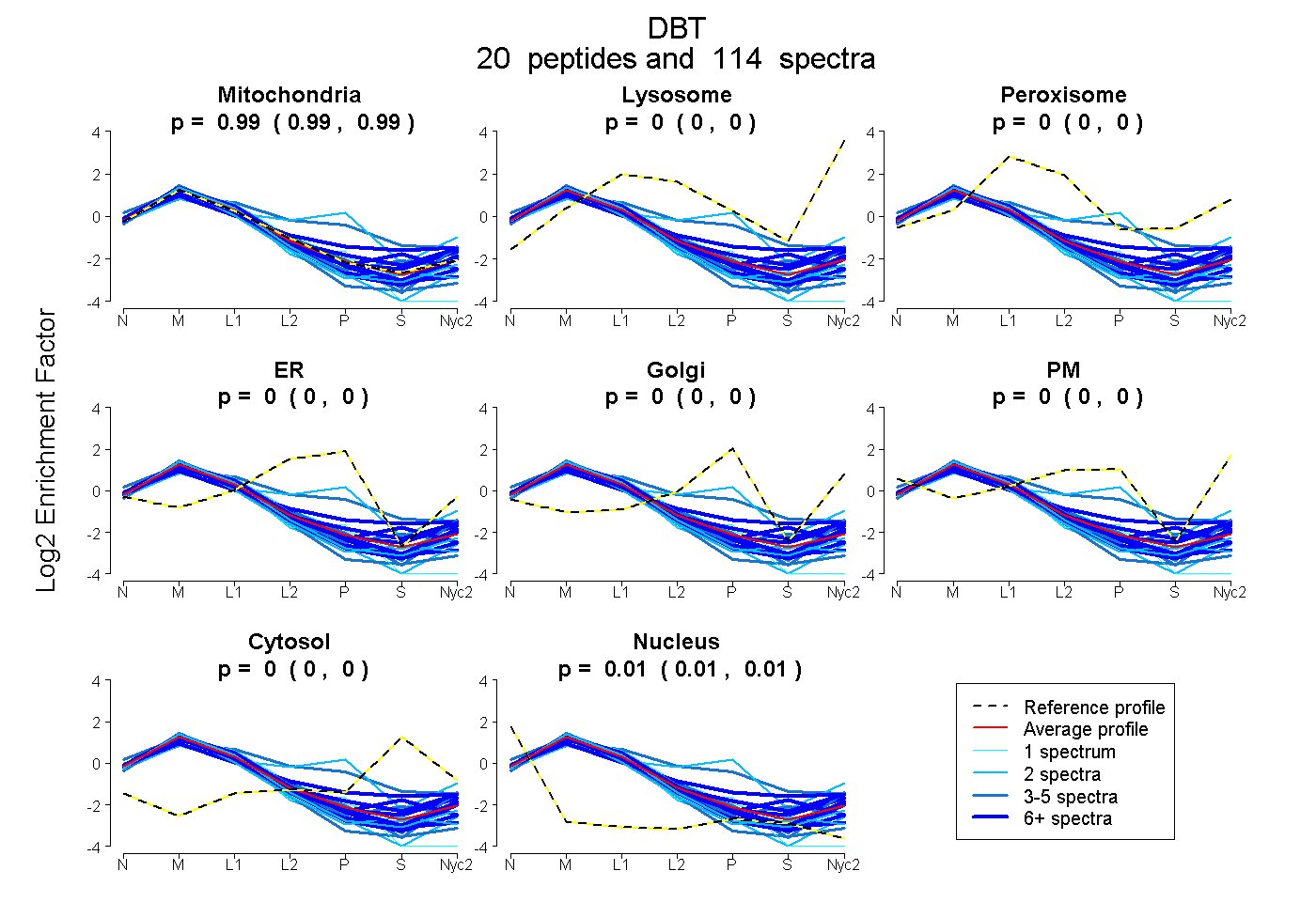
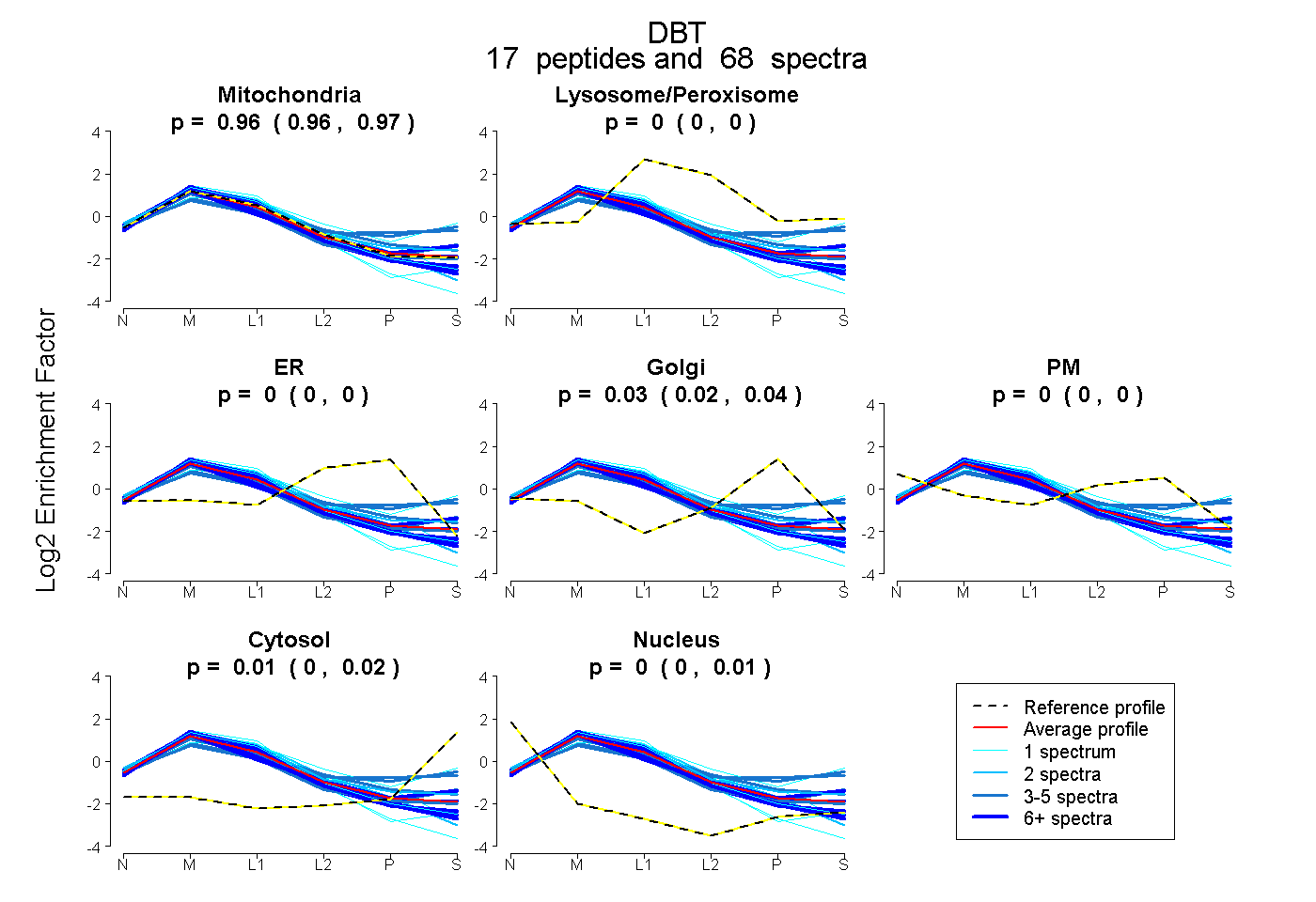
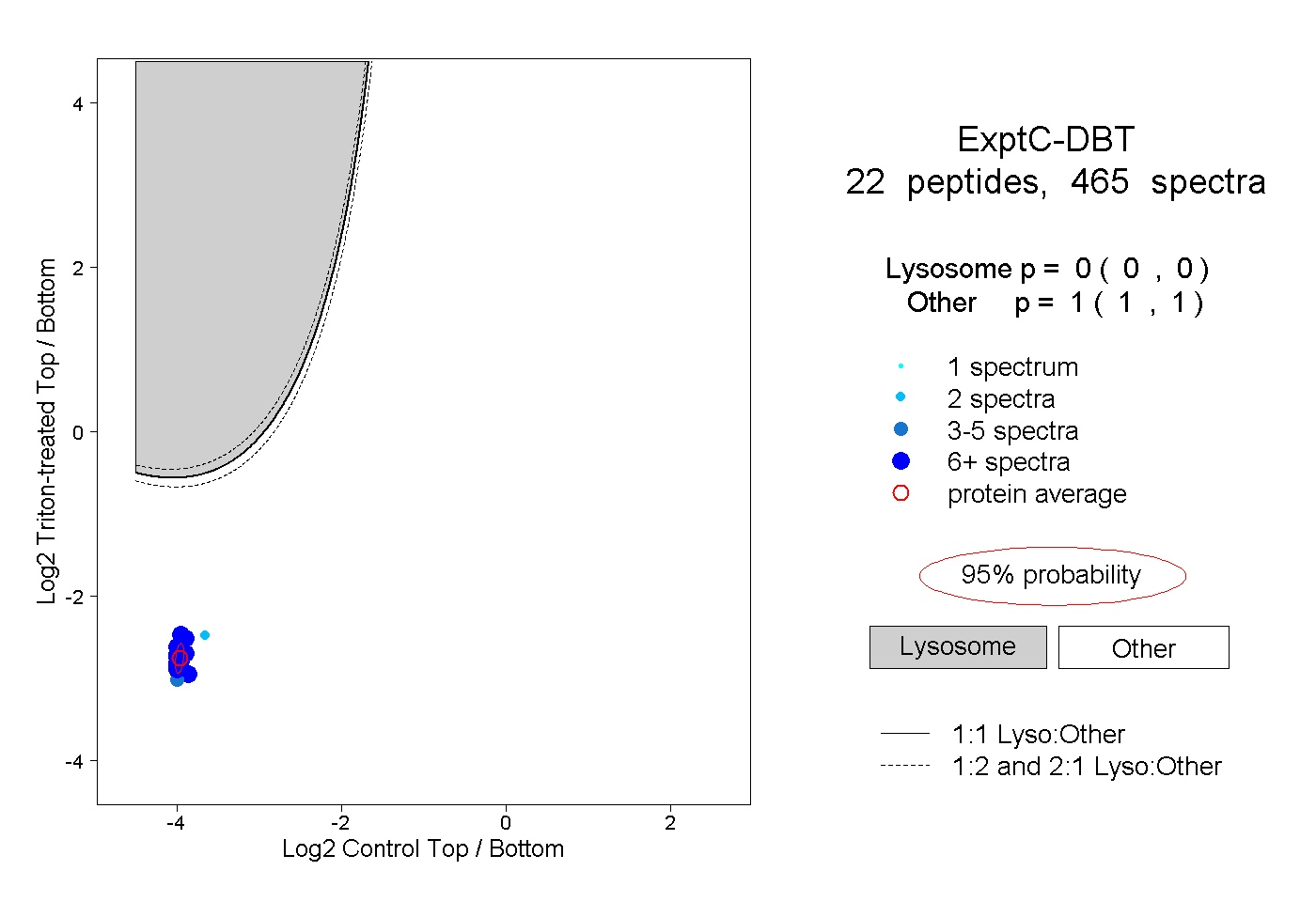
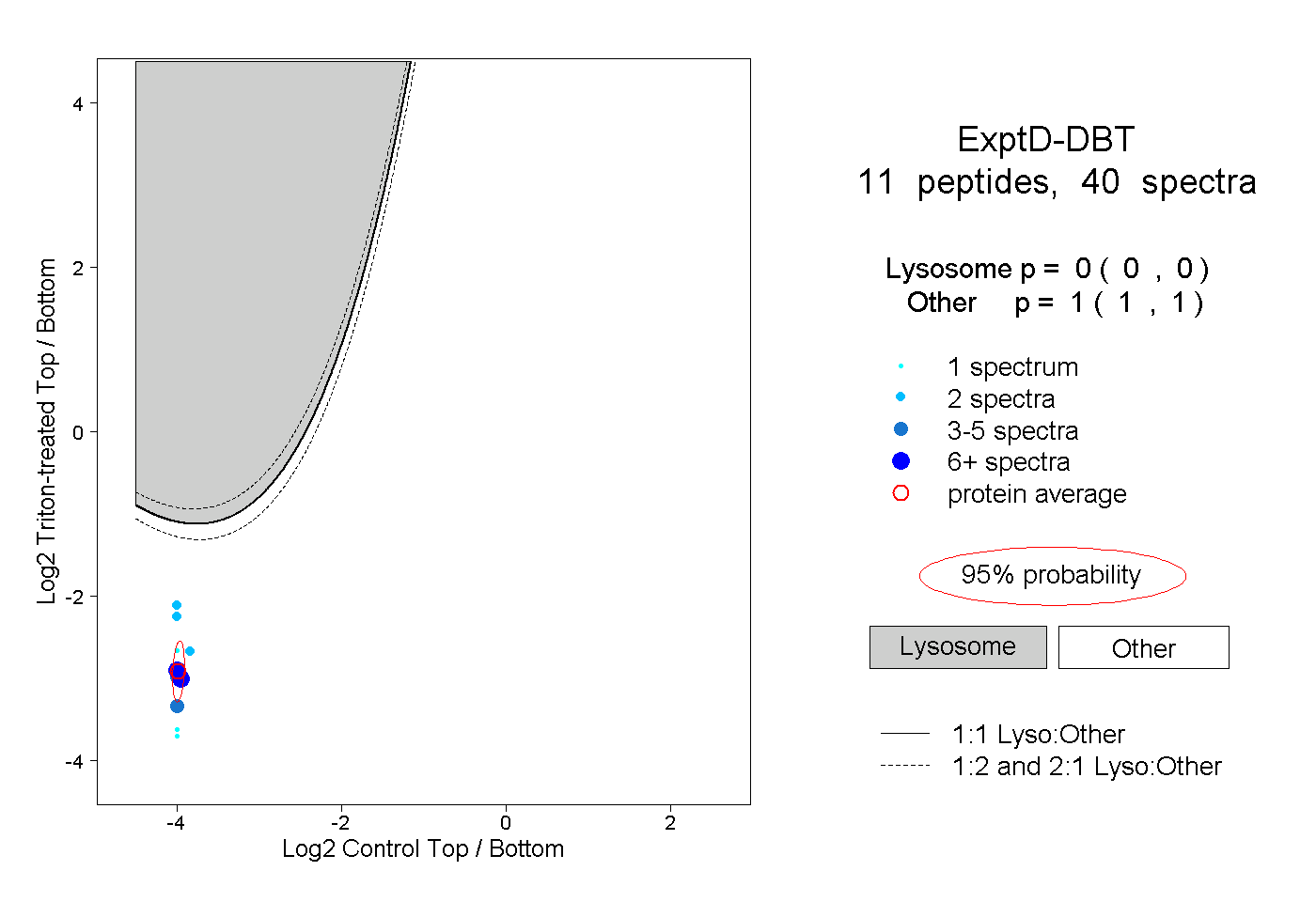
| 15 spectra, IPHFGYCDEVDLTELVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, SEITPPPPQPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 26 spectra, LSFMPFFLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, QTGAILPPSPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ASVTITSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 22 spectra, LAMENNIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, ASHNIGIAMDTER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 32 spectra, LSDIGEGIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, EELKPVALAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, SYLENPAFMLLDLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, AQIMNVSWSADHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 26 spectra, DRPFPTPVSKPPVFLGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, TLATPAVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, TEPVTGFQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 29 spectra, SVFEIAMELNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, LSEVVGSGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 37 spectra, TMSAALK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 25 spectra, YDGVIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, FSNLWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 40 spectra, GLIVPNVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, EDILNFLEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 68 spectra, VIDGATMSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |