peptides
spectra
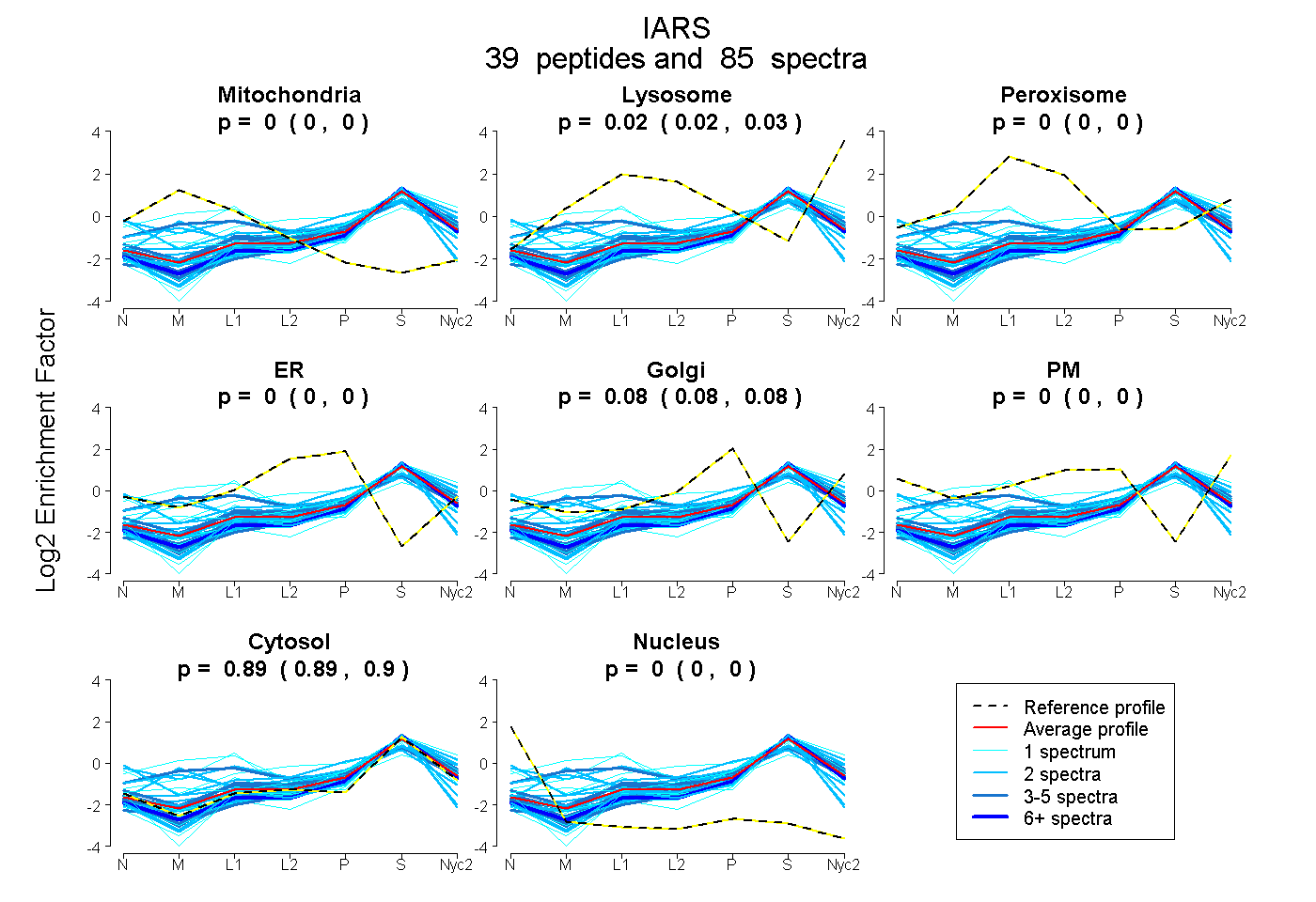
0.000 | 0.000
0.021 | 0.027
0.000 | 0.000
0.000 | 0.000
0.078 | 0.084
0.000 | 0.000
0.892 | 0.896
0.000 | 0.000
peptides
spectra
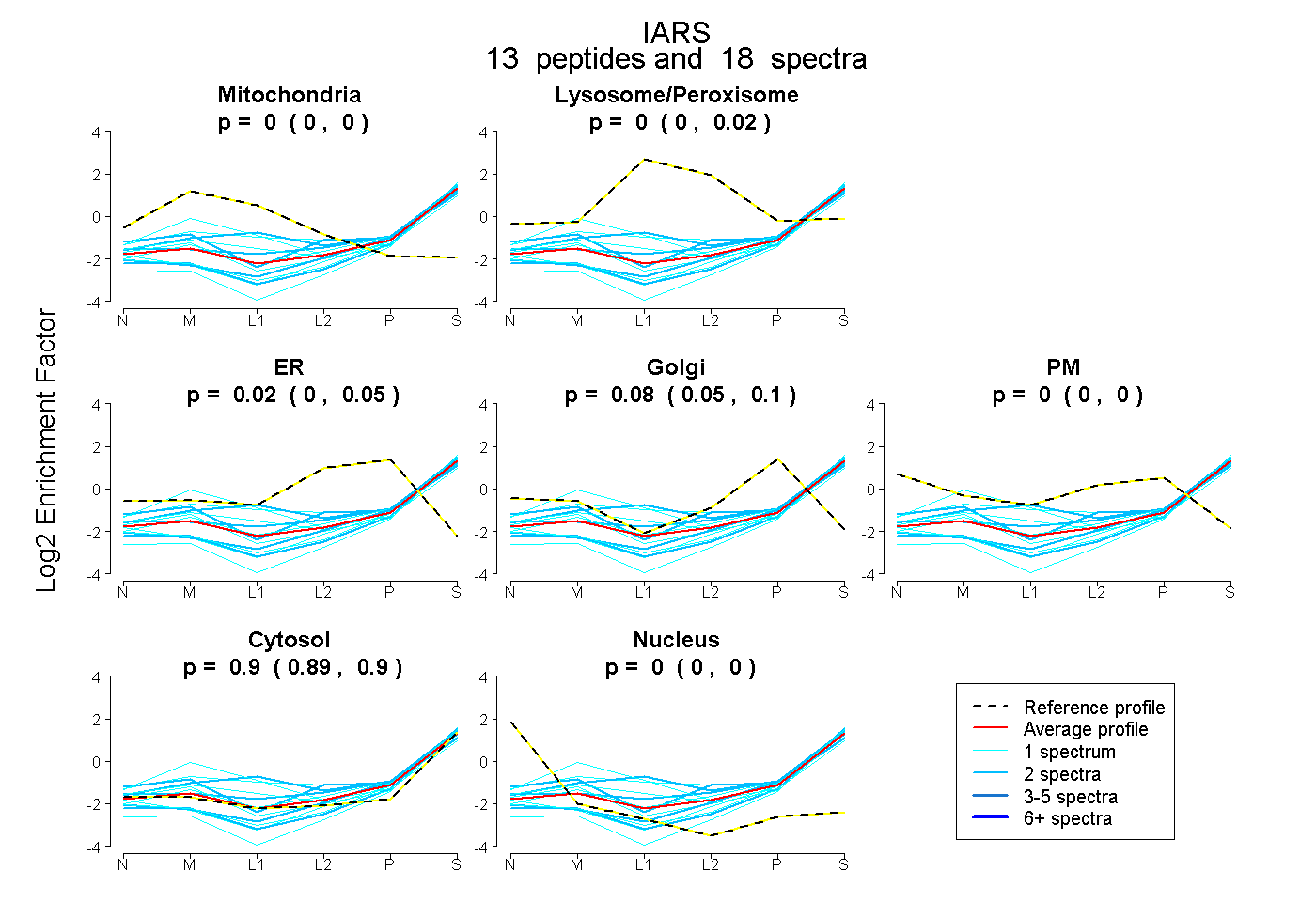
0.000 | 0.000
0.000 | 0.019
0.000 | 0.047
0.046 | 0.105
0.000 | 0.000
0.886 | 0.904
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
85 spectra |
 |
0.000 0.000 | 0.000 |
0.025 0.021 | 0.027 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.081 0.078 | 0.084 |
0.000 0.000 | 0.000 |
0.894 0.892 | 0.896 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
18 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.019 |
0.025 0.000 | 0.047 |
0.076 0.046 | 0.105 |
0.000 0.000 | 0.000 |
0.899 0.886 | 0.904 |
0.000 0.000 | 0.000 |
| 2 spectra, YGADALR | 0.000 | 0.000 | 0.000 | 0.049 | 0.000 | 0.951 | 0.000 | |||
| 2 spectra, QLSNEELEQFQK | 0.000 | 0.255 | 0.000 | 0.008 | 0.000 | 0.736 | 0.000 | |||
| 2 spectra, LYLINSPVVR | 0.000 | 0.000 | 0.097 | 0.018 | 0.108 | 0.777 | 0.000 | |||
| 1 spectrum, ISDLHR | 0.000 | 0.000 | 0.000 | 0.019 | 0.000 | 0.981 | 0.000 | |||
| 1 spectrum, SGSIVVEGHELHEEDIR | 0.000 | 0.000 | 0.094 | 0.022 | 0.000 | 0.884 | 0.000 | |||
| 1 spectrum, LFILMEAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, VQQVPENISFPAEEEK | 0.000 | 0.000 | 0.000 | 0.072 | 0.000 | 0.928 | 0.000 | |||
| 1 spectrum, SVPSWFVR | 0.271 | 0.079 | 0.000 | 0.000 | 0.000 | 0.651 | 0.000 | |||
| 2 spectra, FFIQNVFR | 0.000 | 0.102 | 0.000 | 0.079 | 0.000 | 0.819 | 0.000 | |||
| 1 spectrum, YIIEELNVR | 0.000 | 0.000 | 0.000 | 0.004 | 0.000 | 0.996 | 0.000 | |||
| 1 spectrum, SVITSIFGVK | 0.000 | 0.105 | 0.000 | 0.068 | 0.000 | 0.826 | 0.000 | |||
| 2 spectra, LLIDPASIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, ESIDHLTIPSR | 0.018 | 0.246 | 0.000 | 0.049 | 0.000 | 0.687 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
68 spectra |
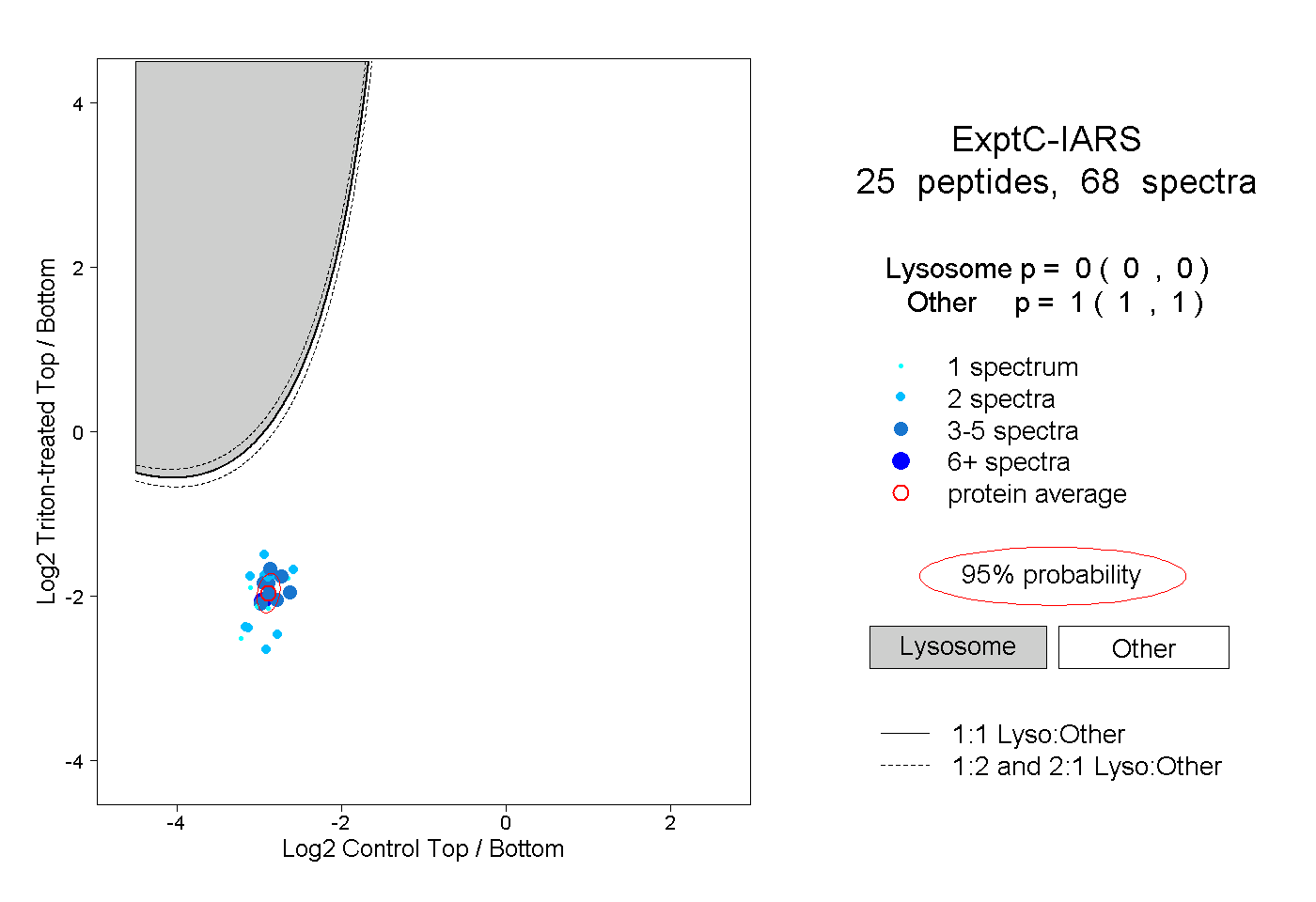 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
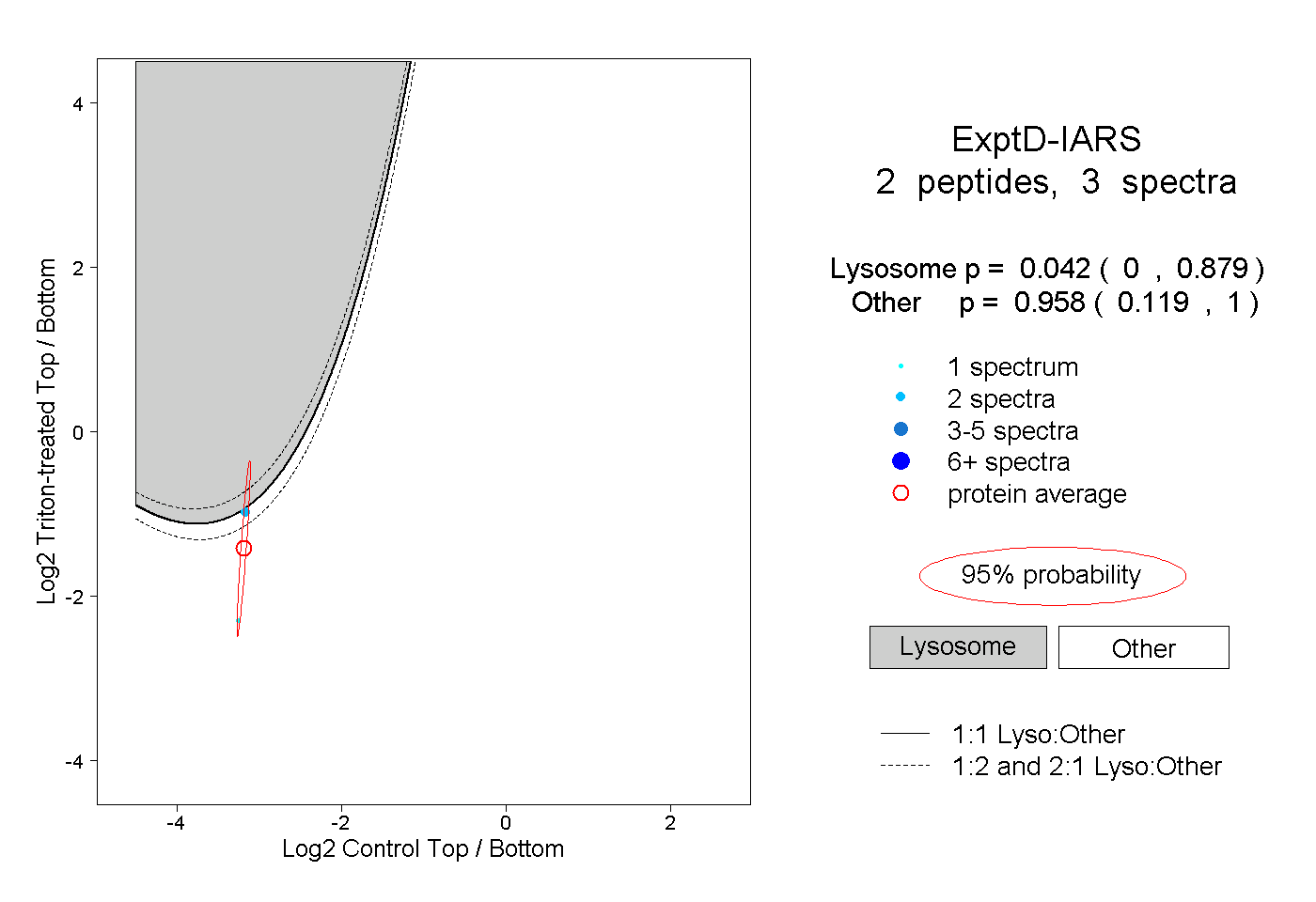 |
0.042 0.000 | 0.879 |
0.958 0.119 | 1.000 |