peptides
spectra
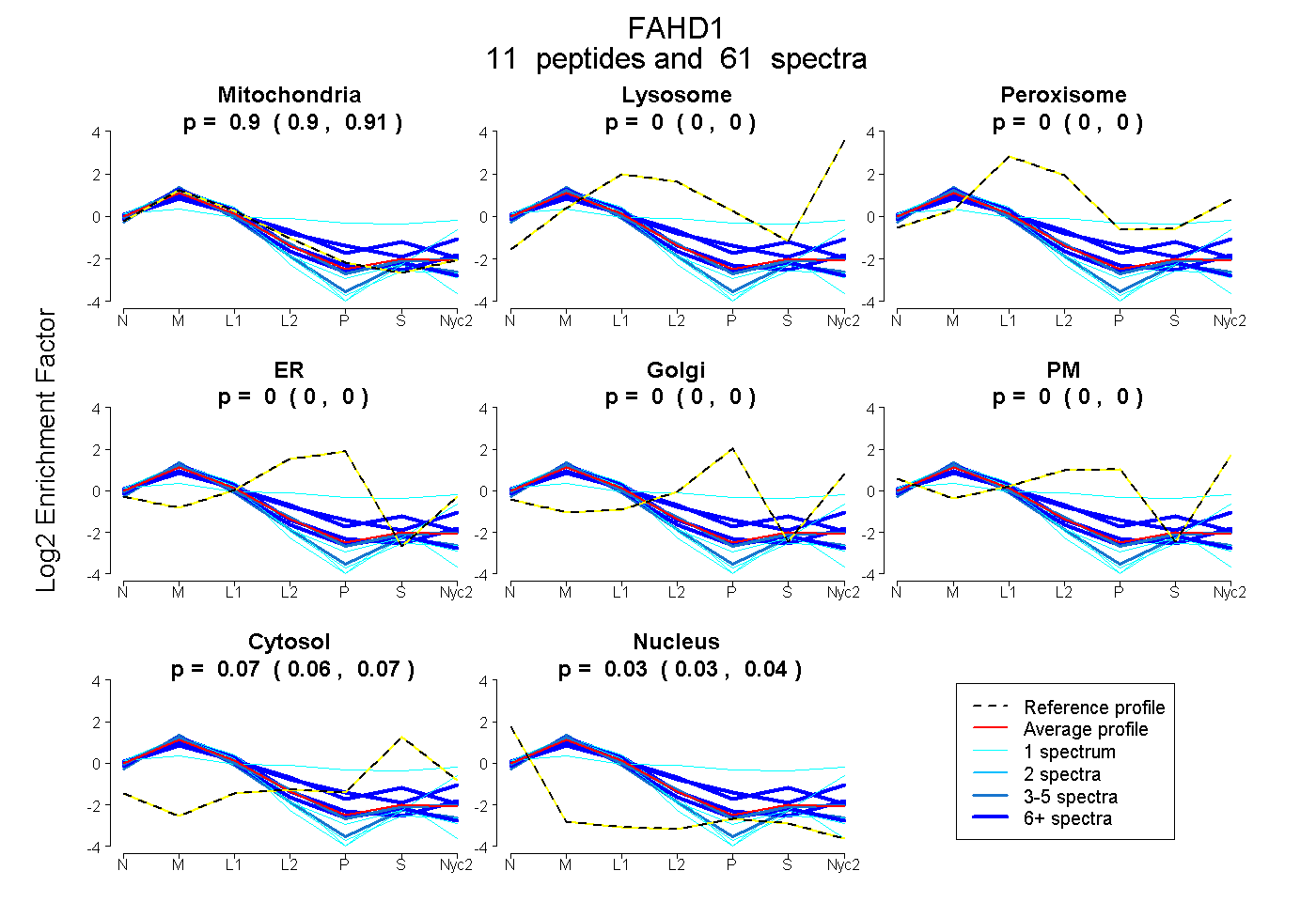
0.898 | 0.907
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.058 | 0.072
0.025 | 0.037
peptides
spectra
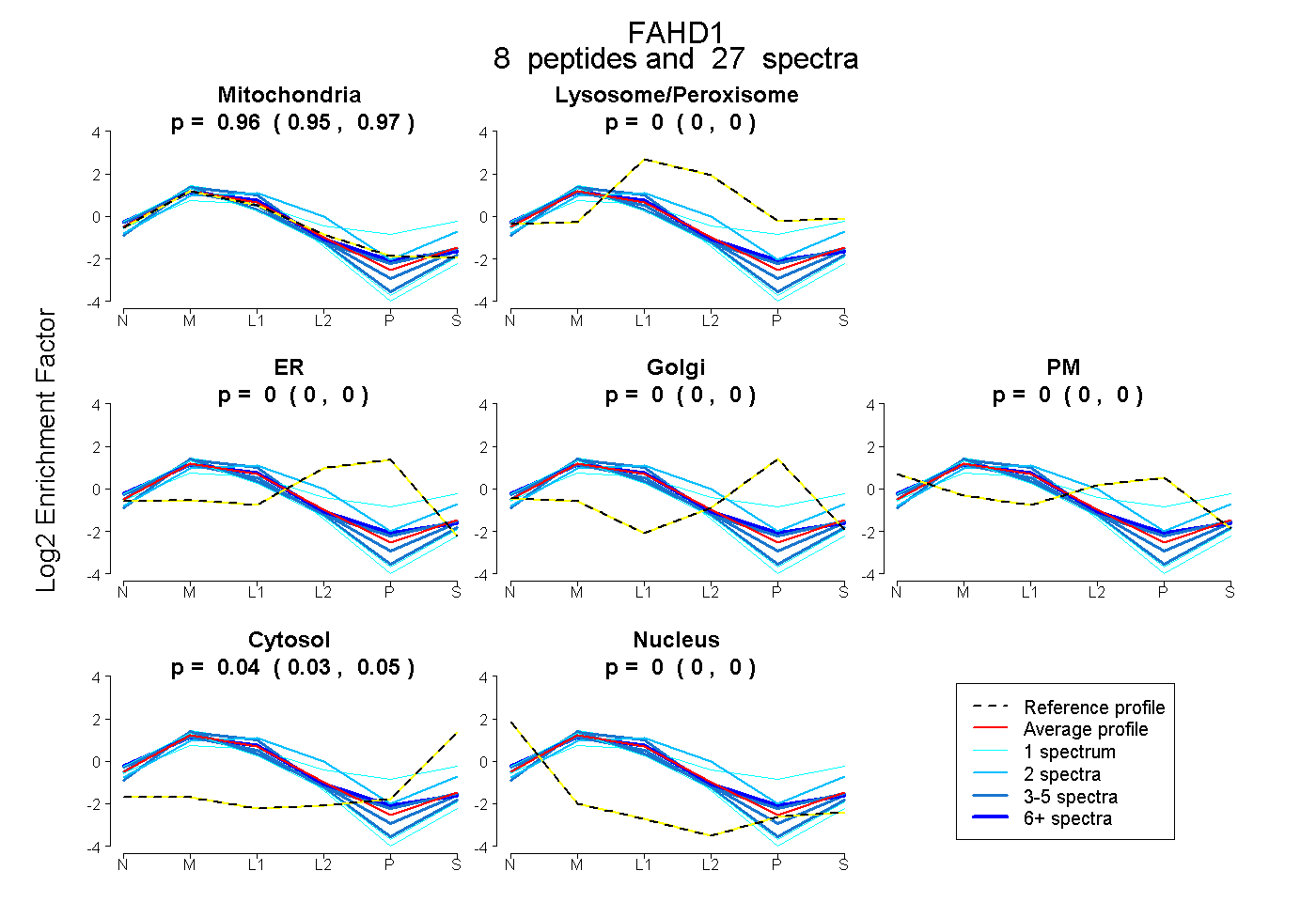
0.947 | 0.966
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.032 | 0.051
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
61 spectra |
 |
0.903 0.898 | 0.907 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.065 0.058 | 0.072 |
0.032 0.025 | 0.037 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
27 spectra |
 |
0.958 0.947 | 0.966 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.042 0.032 | 0.051 |
0.000 0.000 | 0.000 |
| 3 spectra, FWEWGK | 0.990 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.010 | |||
| 3 spectra, NYADHVK | 0.923 | 0.000 | 0.000 | 0.000 | 0.000 | 0.041 | 0.036 | |||
| 11 spectra, NIVCVGR | 0.948 | 0.023 | 0.000 | 0.000 | 0.000 | 0.001 | 0.028 | |||
| 1 spectrum, DVQDECK | 0.973 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.027 | |||
| 5 spectra, IPDPHALR | 0.936 | 0.000 | 0.000 | 0.000 | 0.000 | 0.064 | 0.000 | |||
| 1 spectrum, GLPWTLAK | 0.457 | 0.307 | 0.000 | 0.046 | 0.000 | 0.190 | 0.000 | |||
| 1 spectrum, SFTSSCPVSAFVPK | 0.887 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.113 | |||
| 2 spectra, NLHHEVELGVLLGR | 0.646 | 0.278 | 0.000 | 0.000 | 0.000 | 0.076 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
263 spectra |
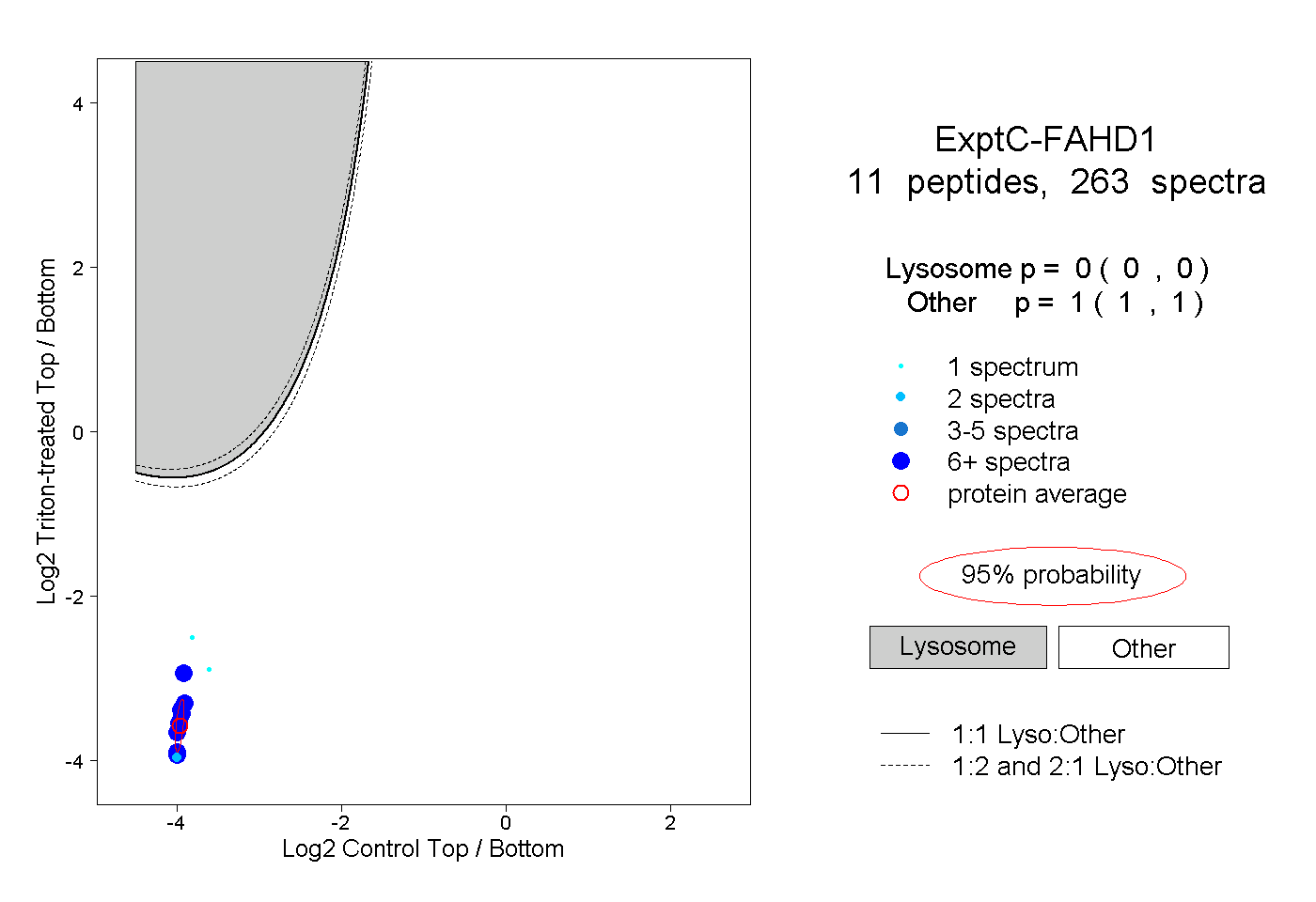 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
33 spectra |
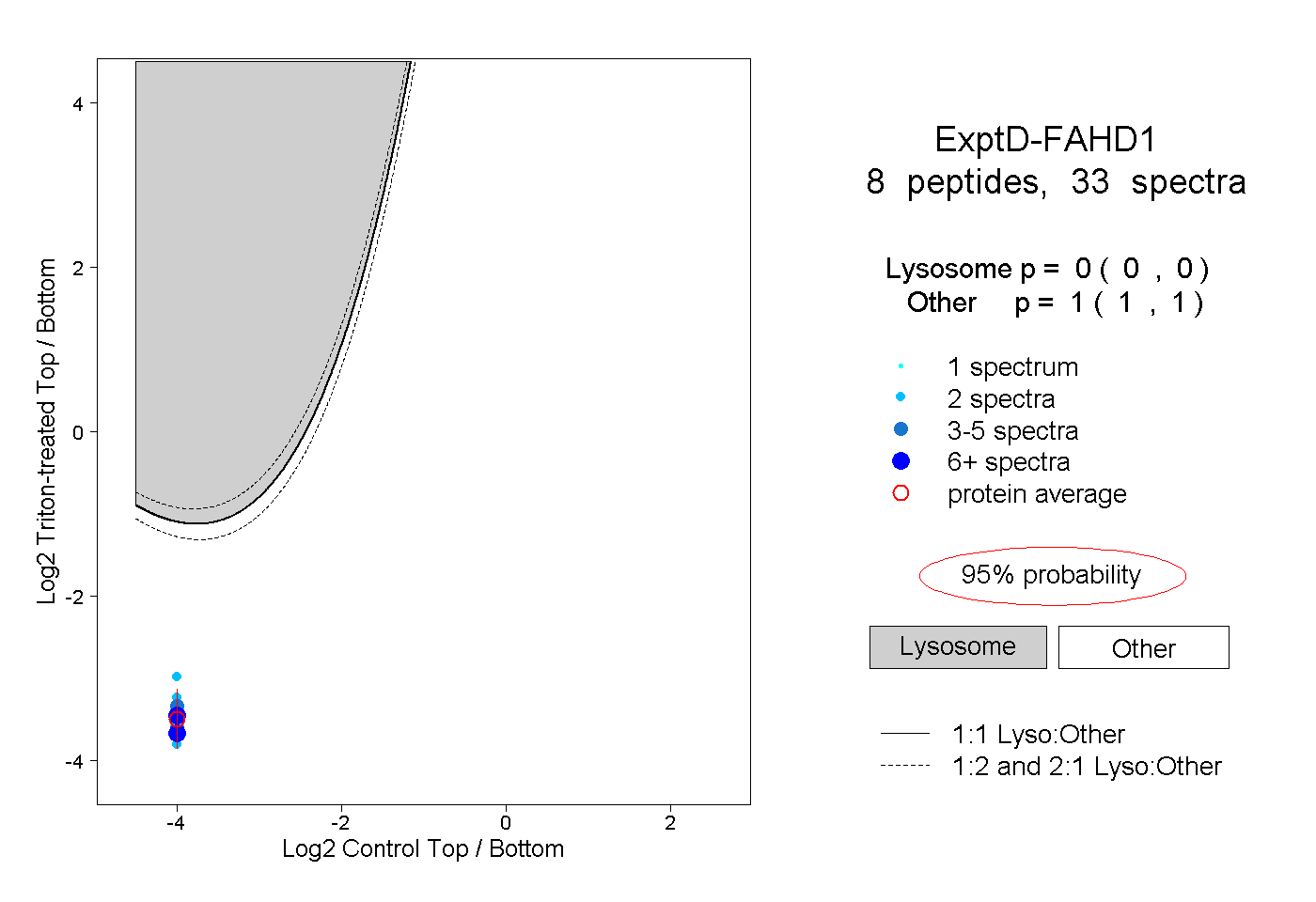 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |