peptides
spectra
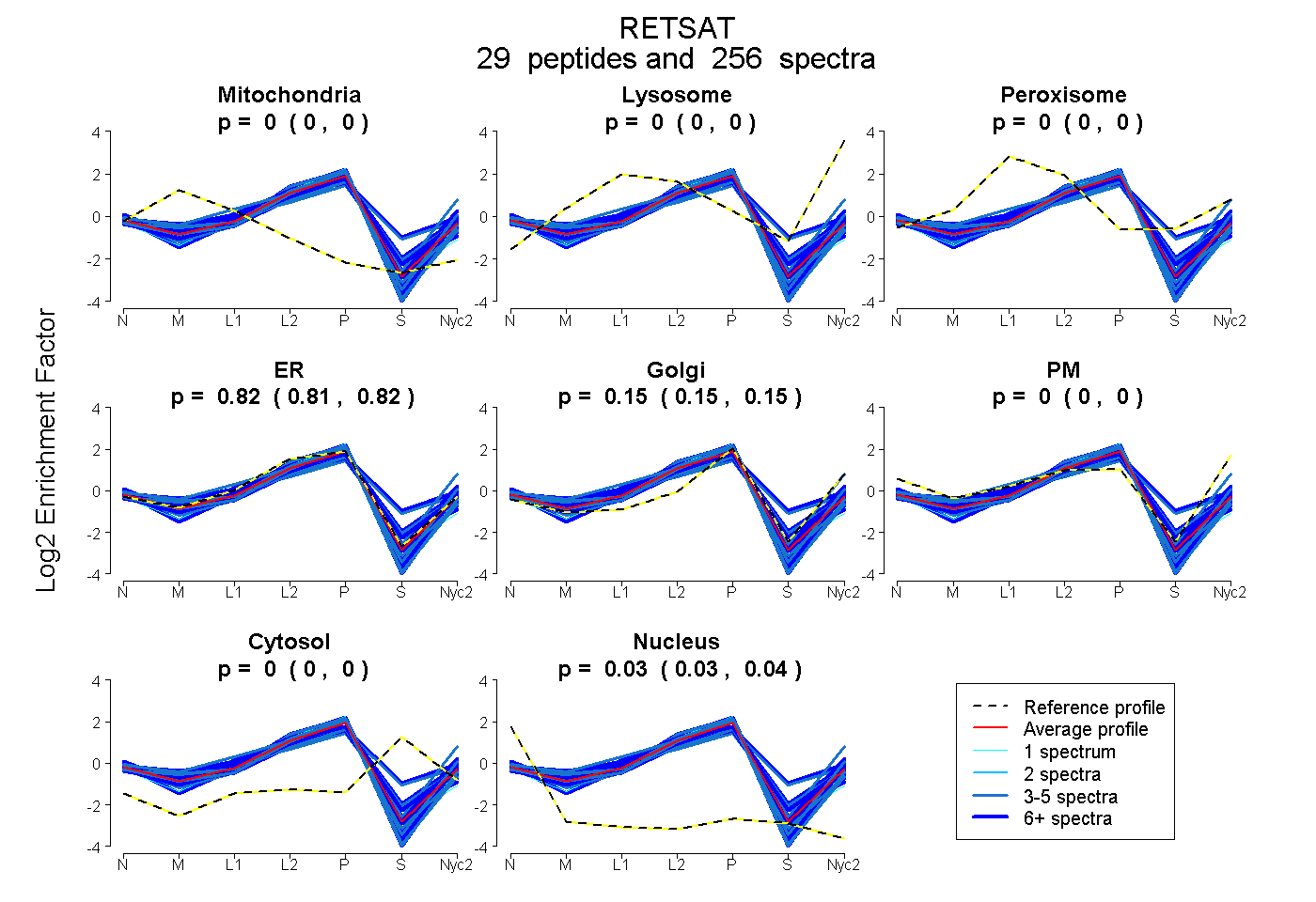
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.813 | 0.818
0.146 | 0.152
0.000 | 0.000
0.000 | 0.000
0.034 | 0.035
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
256 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.816 0.813 | 0.818 |
0.149 0.146 | 0.152 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.034 0.034 | 0.035 |
| 3 spectra, NLYSDLQALGSK | 0.000 | 0.000 | 0.000 | 0.946 | 0.000 | 0.000 | 0.000 | 0.054 | ||
| 29 spectra, AGGAVLTR | 0.000 | 0.000 | 0.000 | 0.945 | 0.021 | 0.000 | 0.000 | 0.034 | ||
| 8 spectra, ACGVSVK | 0.033 | 0.000 | 0.000 | 0.868 | 0.000 | 0.000 | 0.032 | 0.066 | ||
| 3 spectra, FLPLPLTQLLNK | 0.141 | 0.000 | 0.030 | 0.611 | 0.183 | 0.000 | 0.036 | 0.000 | ||
| 1 spectrum, AGGCCHTFGENGLEFDTGIHYIGR | 0.015 | 0.000 | 0.000 | 0.922 | 0.000 | 0.000 | 0.000 | 0.063 | ||
| 5 spectra, VESVTGGSPLTNQYYLAAHR | 0.084 | 0.000 | 0.000 | 0.606 | 0.217 | 0.035 | 0.057 | 0.000 | ||
| 6 spectra, LFPQLEGK | 0.000 | 0.000 | 0.000 | 0.918 | 0.039 | 0.000 | 0.000 | 0.043 | ||
| 18 spectra, FGLLTR | 0.000 | 0.000 | 0.000 | 0.924 | 0.060 | 0.000 | 0.000 | 0.016 | ||
| 3 spectra, ASTQSLAEVLK | 0.000 | 0.000 | 0.000 | 0.947 | 0.010 | 0.000 | 0.000 | 0.043 | ||
| 4 spectra, DPTWEDR | 0.000 | 0.000 | 0.000 | 0.782 | 0.211 | 0.000 | 0.000 | 0.007 | ||
| 6 spectra, EYIQGLK | 0.020 | 0.000 | 0.000 | 0.864 | 0.094 | 0.000 | 0.000 | 0.022 | ||
| 6 spectra, NTFLEASMSVIMK | 0.000 | 0.000 | 0.000 | 0.683 | 0.175 | 0.033 | 0.106 | 0.003 | ||
| 11 spectra, GGSSEIAFHTIPLIQR | 0.000 | 0.000 | 0.067 | 0.663 | 0.170 | 0.059 | 0.005 | 0.036 | ||
| 14 spectra, QAFSVSR | 0.020 | 0.005 | 0.000 | 0.691 | 0.068 | 0.216 | 0.000 | 0.000 | ||
| 1 spectrum, LQSTNYYVYFDTDMDK | 0.000 | 0.000 | 0.000 | 0.875 | 0.106 | 0.000 | 0.000 | 0.019 | ||
| 22 spectra, FSPFCR | 0.000 | 0.000 | 0.000 | 0.942 | 0.000 | 0.000 | 0.000 | 0.058 | ||
| 9 spectra, VVAHGVSHAILLK | 0.029 | 0.000 | 0.000 | 0.776 | 0.142 | 0.000 | 0.052 | 0.000 | ||
| 16 spectra, GVDYETLK | 0.078 | 0.000 | 0.000 | 0.573 | 0.292 | 0.058 | 0.000 | 0.000 | ||
| 6 spectra, EFPMYSGR | 0.000 | 0.000 | 0.000 | 0.791 | 0.205 | 0.000 | 0.000 | 0.005 | ||
| 7 spectra, YLPDVK | 0.000 | 0.000 | 0.000 | 0.747 | 0.213 | 0.000 | 0.000 | 0.041 | ||
| 5 spectra, GATYGADHDLAR | 0.000 | 0.000 | 0.000 | 0.655 | 0.019 | 0.096 | 0.230 | 0.000 | ||
| 5 spectra, YMELVK | 0.000 | 0.000 | 0.000 | 0.682 | 0.318 | 0.000 | 0.000 | 0.000 | ||
| 9 spectra, EGNIGR | 0.000 | 0.000 | 0.000 | 0.777 | 0.207 | 0.000 | 0.000 | 0.017 | ||
| 21 spectra, LHPHAMASLR | 0.109 | 0.000 | 0.019 | 0.734 | 0.112 | 0.000 | 0.026 | 0.000 | ||
| 11 spectra, EEAVIDK | 0.000 | 0.006 | 0.056 | 0.505 | 0.229 | 0.000 | 0.203 | 0.000 | ||
| 4 spectra, YVSMPK | 0.005 | 0.000 | 0.000 | 0.917 | 0.054 | 0.000 | 0.000 | 0.024 | ||
| 3 spectra, RPPEPLVTDK | 0.000 | 0.073 | 0.000 | 0.485 | 0.099 | 0.344 | 0.000 | 0.000 | ||
| 5 spectra, VLVLEQHTK | 0.000 | 0.000 | 0.000 | 0.857 | 0.095 | 0.000 | 0.000 | 0.048 | ||
| 15 spectra, ATVQSVLLDSAGR | 0.000 | 0.000 | 0.000 | 0.907 | 0.060 | 0.000 | 0.000 | 0.033 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
73 spectra |
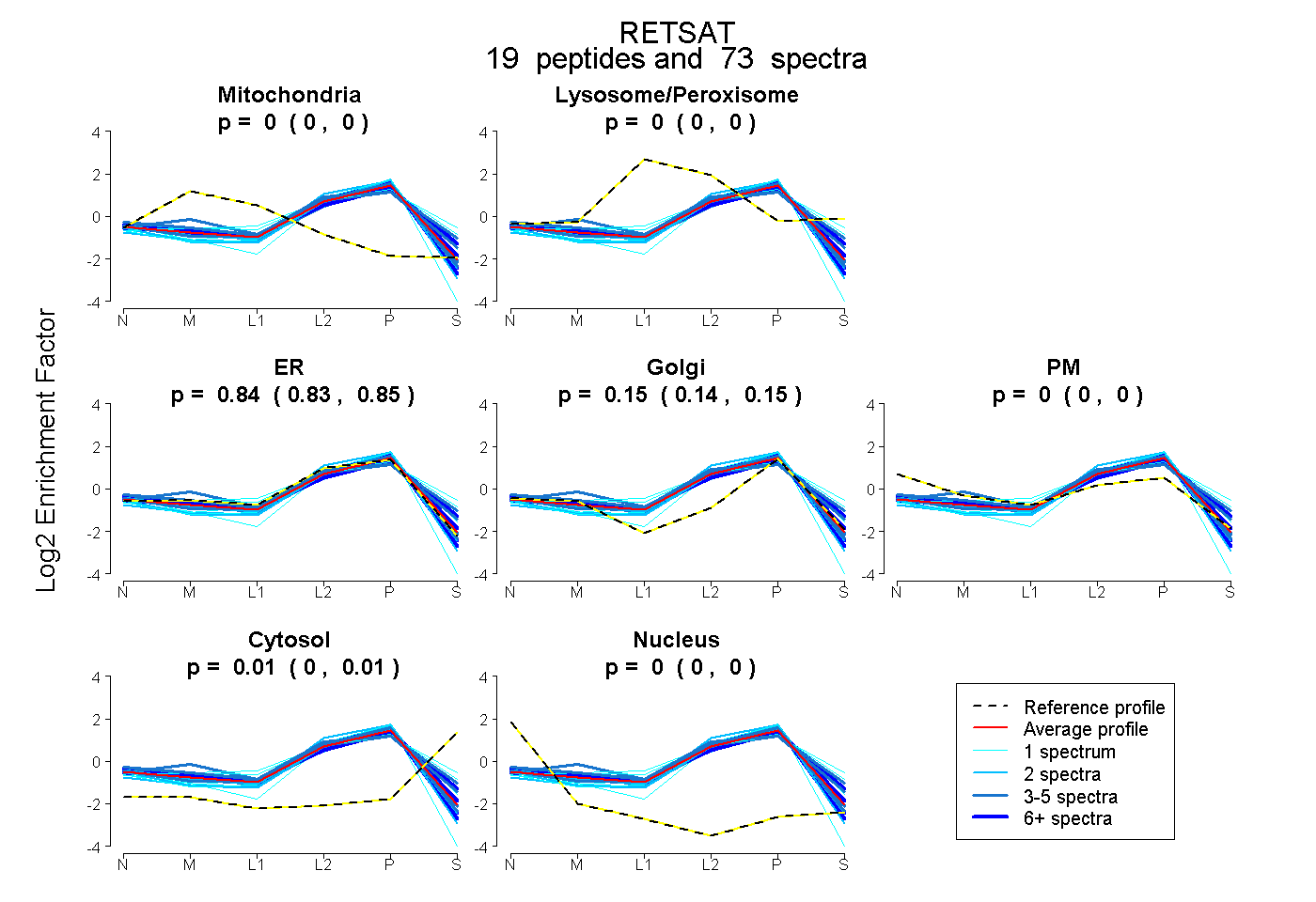 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.002 |
0.842 0.834 | 0.845 |
0.148 0.143 | 0.155 |
0.000 0.000 | 0.000 |
0.010 0.004 | 0.013 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
266 spectra |
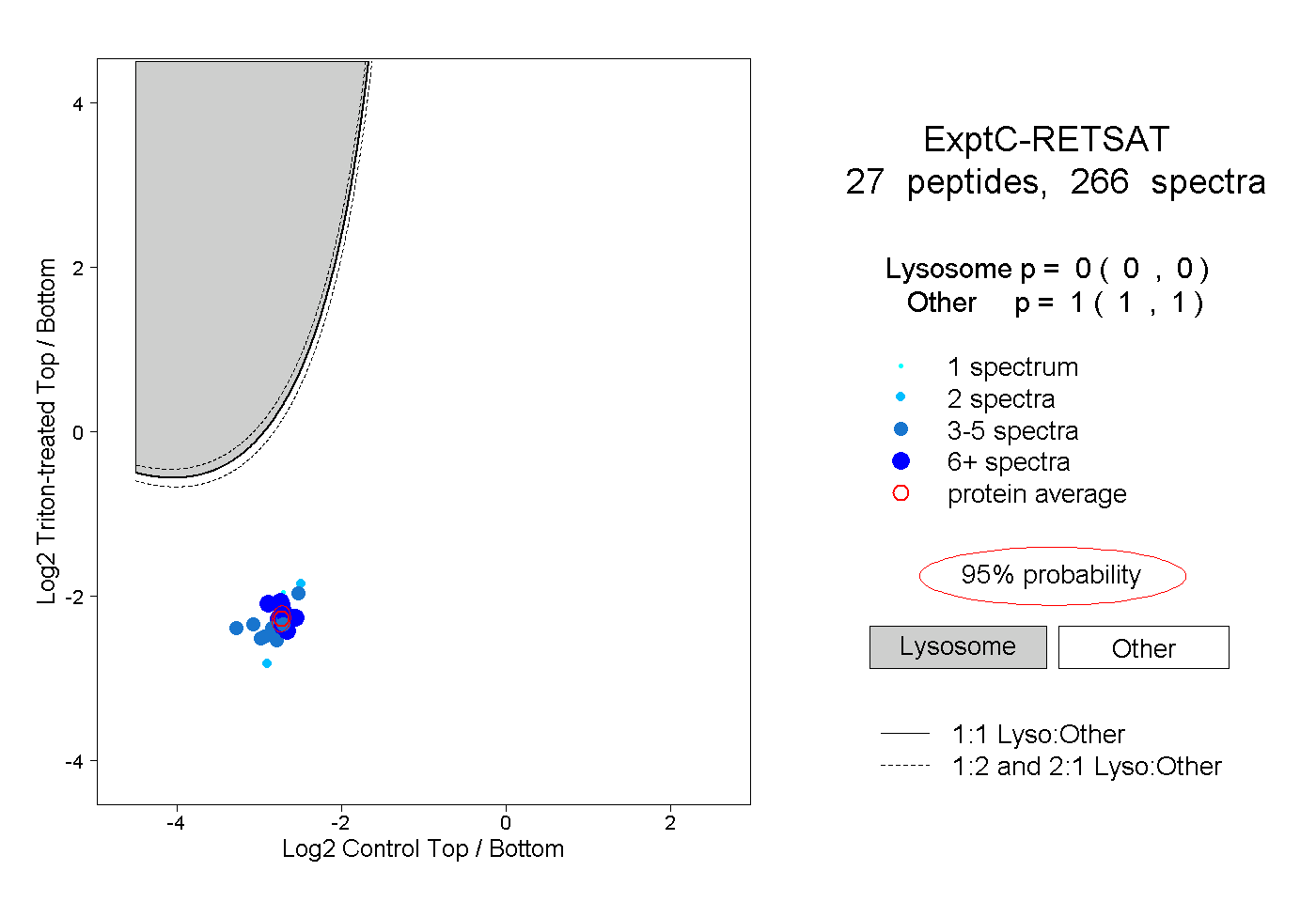 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
24 spectra |
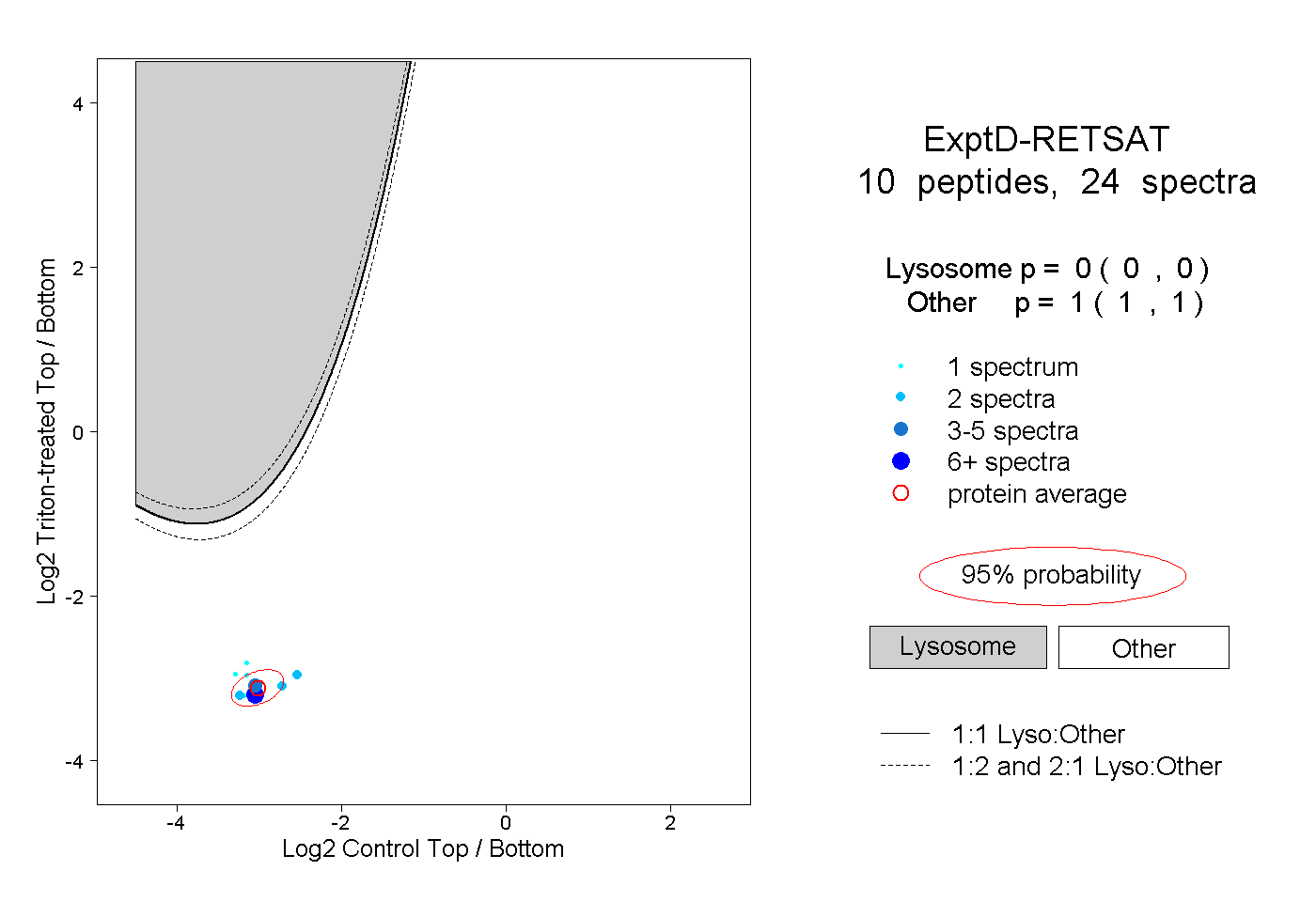 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |