peptides
spectra
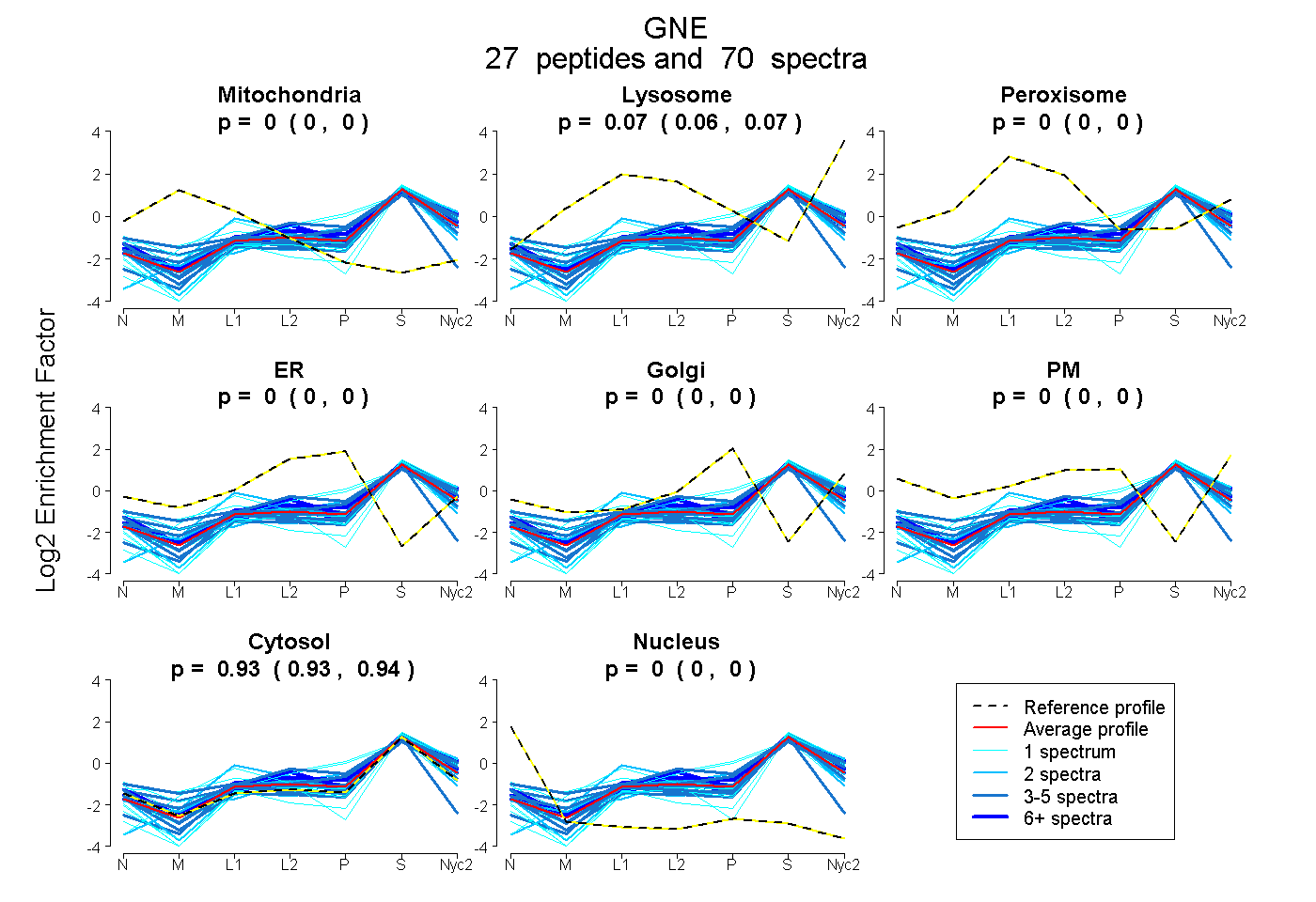
0.000 | 0.000
0.063 | 0.069
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.931 | 0.936
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
70 spectra |
 |
0.000 0.000 | 0.000 |
0.066 0.063 | 0.069 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.934 0.931 | 0.936 |
0.000 0.000 | 0.000 |
| 2 spectra, MWLGDDVK | 0.000 | 0.016 | 0.000 | 0.000 | 0.000 | 0.000 | 0.984 | 0.000 | ||
| 1 spectrum, FCFPPVK | 0.000 | 0.034 | 0.000 | 0.033 | 0.000 | 0.000 | 0.933 | 0.000 | ||
| 1 spectrum, ETGENVLHVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 6 spectra, LAPIMFGIK | 0.000 | 0.077 | 0.007 | 0.046 | 0.000 | 0.000 | 0.871 | 0.000 | ||
| 2 spectra, LIQEWNSVDLR | 0.000 | 0.140 | 0.000 | 0.000 | 0.000 | 0.000 | 0.860 | 0.000 | ||
| 3 spectra, GEDEAAMVESVGLALVK | 0.000 | 0.079 | 0.000 | 0.000 | 0.000 | 0.000 | 0.921 | 0.000 | ||
| 1 spectrum, TLVLFPNIDAGSK | 0.000 | 0.002 | 0.000 | 0.000 | 0.000 | 0.000 | 0.998 | 0.000 | ||
| 4 spectra, VNPQEGVVLHSTK | 0.083 | 0.089 | 0.008 | 0.000 | 0.000 | 0.022 | 0.797 | 0.000 | ||
| 4 spectra, VCVATCNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.895 | 0.105 | ||
| 8 spectra, LHTIVR | 0.000 | 0.147 | 0.000 | 0.000 | 0.000 | 0.000 | 0.853 | 0.000 | ||
| 2 spectra, GIEHHPNFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.998 | 0.002 | ||
| 4 spectra, LKPDIMIVHGDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, DYMSIIR | 0.099 | 0.000 | 0.123 | 0.000 | 0.000 | 0.000 | 0.778 | 0.000 | ||
| 1 spectrum, LPDVLNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, SIDLQEPLQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, DADTQDK | 0.000 | 0.041 | 0.000 | 0.000 | 0.000 | 0.000 | 0.959 | 0.000 | ||
| 1 spectrum, DEAVGALHLIQAAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, TPLSDTLHLPVWVDNDGNCAAMAER | 0.000 | 0.164 | 0.000 | 0.000 | 0.000 | 0.000 | 0.836 | 0.000 | ||
| 1 spectrum, SAEQHLISMCEDHDR | 0.000 | 0.025 | 0.007 | 0.125 | 0.107 | 0.000 | 0.736 | 0.000 | ||
| 6 spectra, ILGVGISTGGR | 0.000 | 0.062 | 0.000 | 0.000 | 0.000 | 0.000 | 0.938 | 0.000 | ||
| 2 spectra, ILHIEGGEVSGTIDDSIR | 0.000 | 0.178 | 0.000 | 0.000 | 0.000 | 0.000 | 0.822 | 0.000 | ||
| 3 spectra, YTQFNPK | 0.000 | 0.169 | 0.000 | 0.034 | 0.000 | 0.000 | 0.796 | 0.000 | ||
| 1 spectrum, EVGAFGTPVINLGTR | 0.000 | 0.003 | 0.000 | 0.101 | 0.145 | 0.000 | 0.751 | 0.000 | ||
| 5 spectra, QYPCSK | 0.000 | 0.004 | 0.000 | 0.000 | 0.000 | 0.000 | 0.996 | 0.000 | ||
| 2 spectra, LAHYHVCCTR | 0.000 | 0.000 | 0.000 | 0.027 | 0.079 | 0.000 | 0.894 | 0.000 | ||
| 3 spectra, VAIVSMK | 0.000 | 0.062 | 0.000 | 0.000 | 0.064 | 0.000 | 0.874 | 0.000 | ||
| 3 spectra, IYGDGNAVPR | 0.000 | 0.136 | 0.000 | 0.000 | 0.000 | 0.000 | 0.864 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
17 spectra |
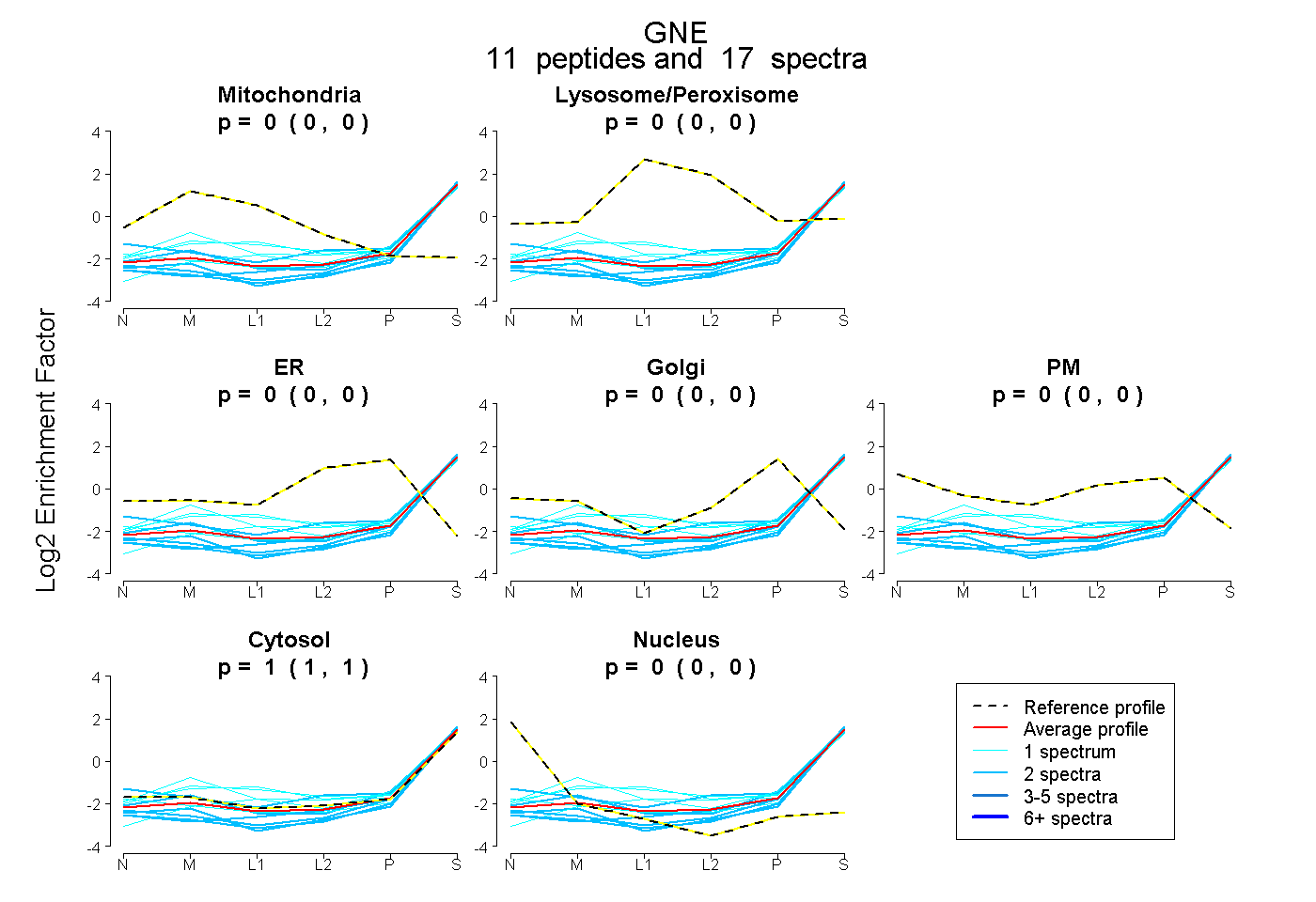 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
67 spectra |
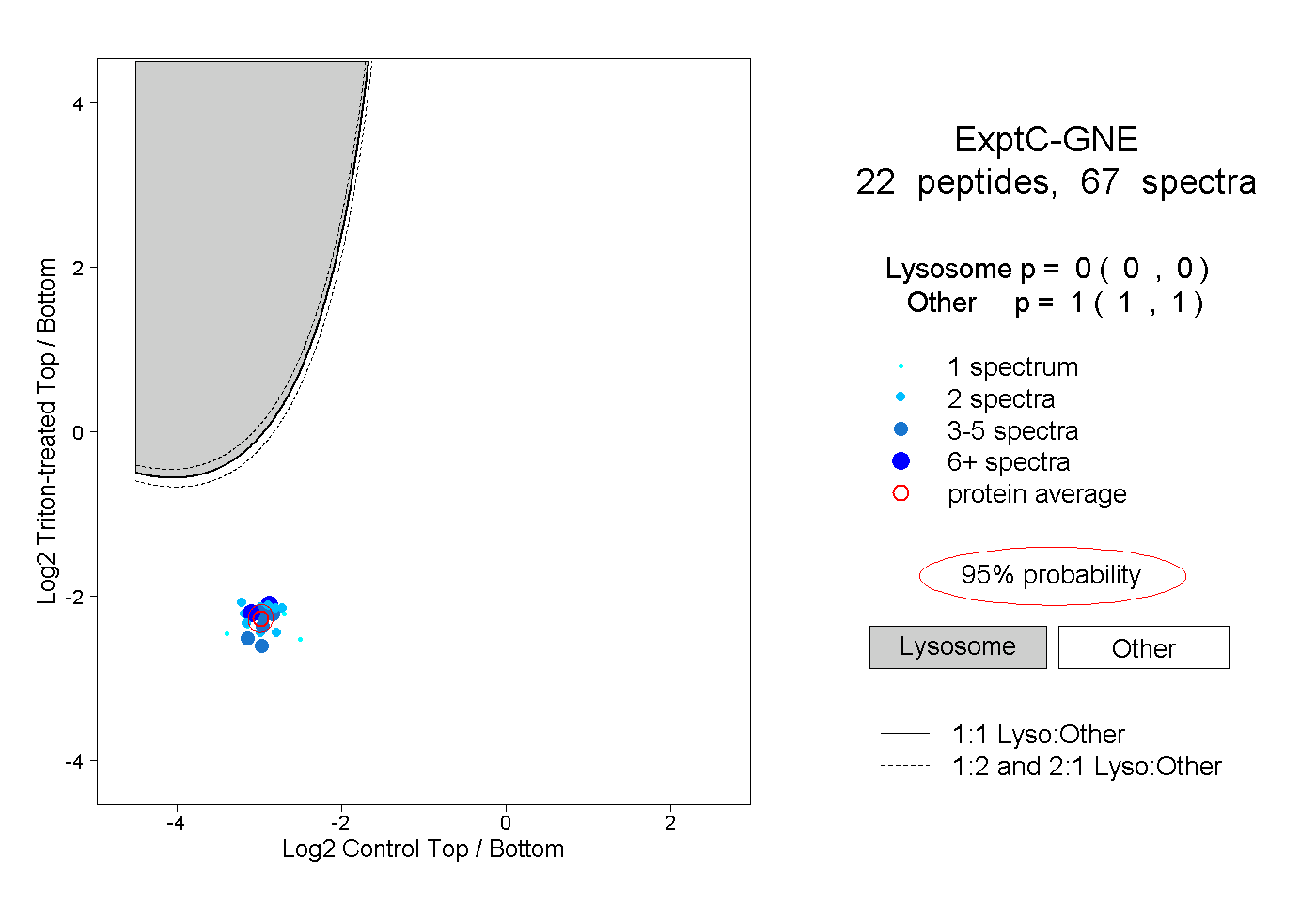 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
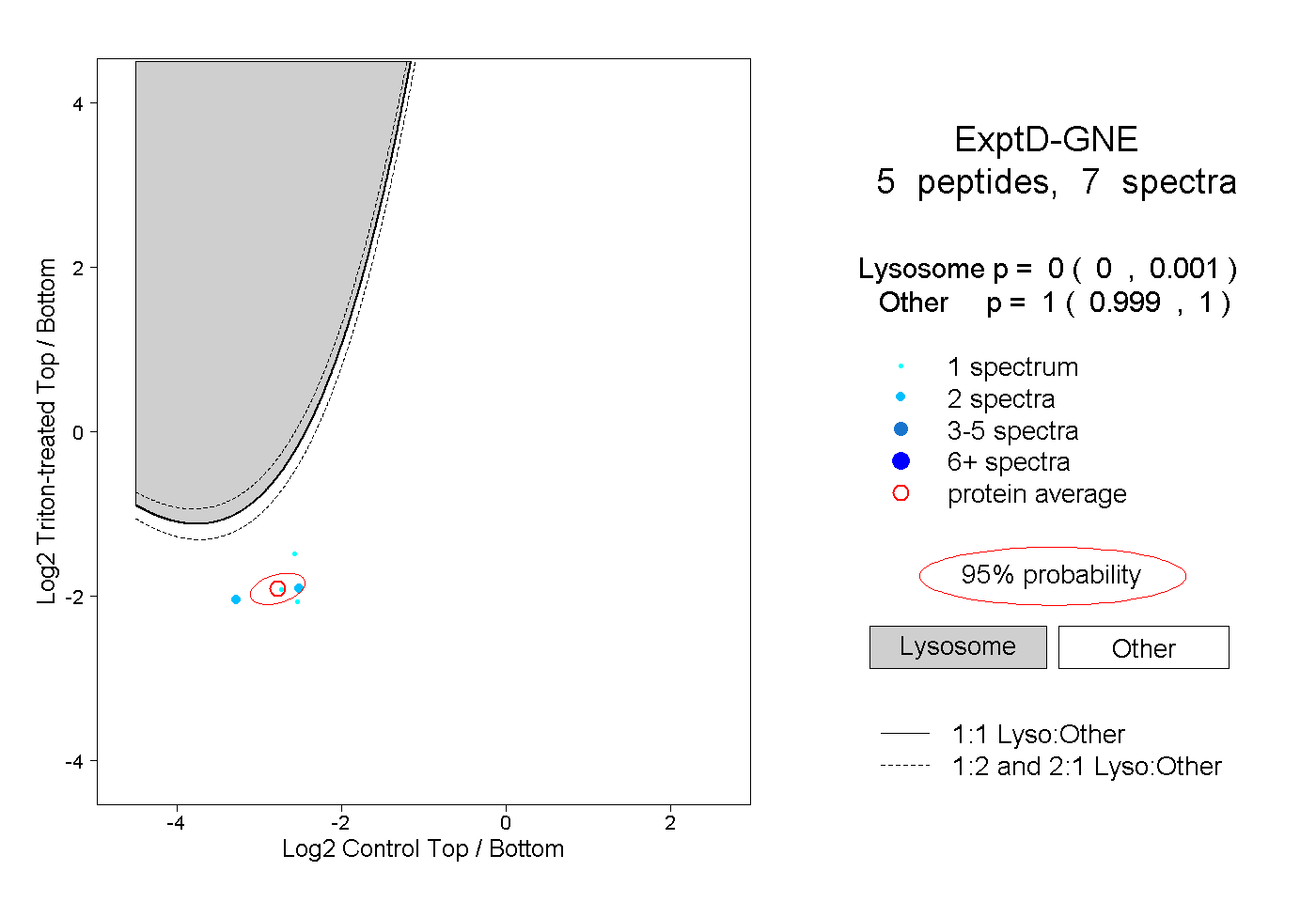 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |