peptides
spectra
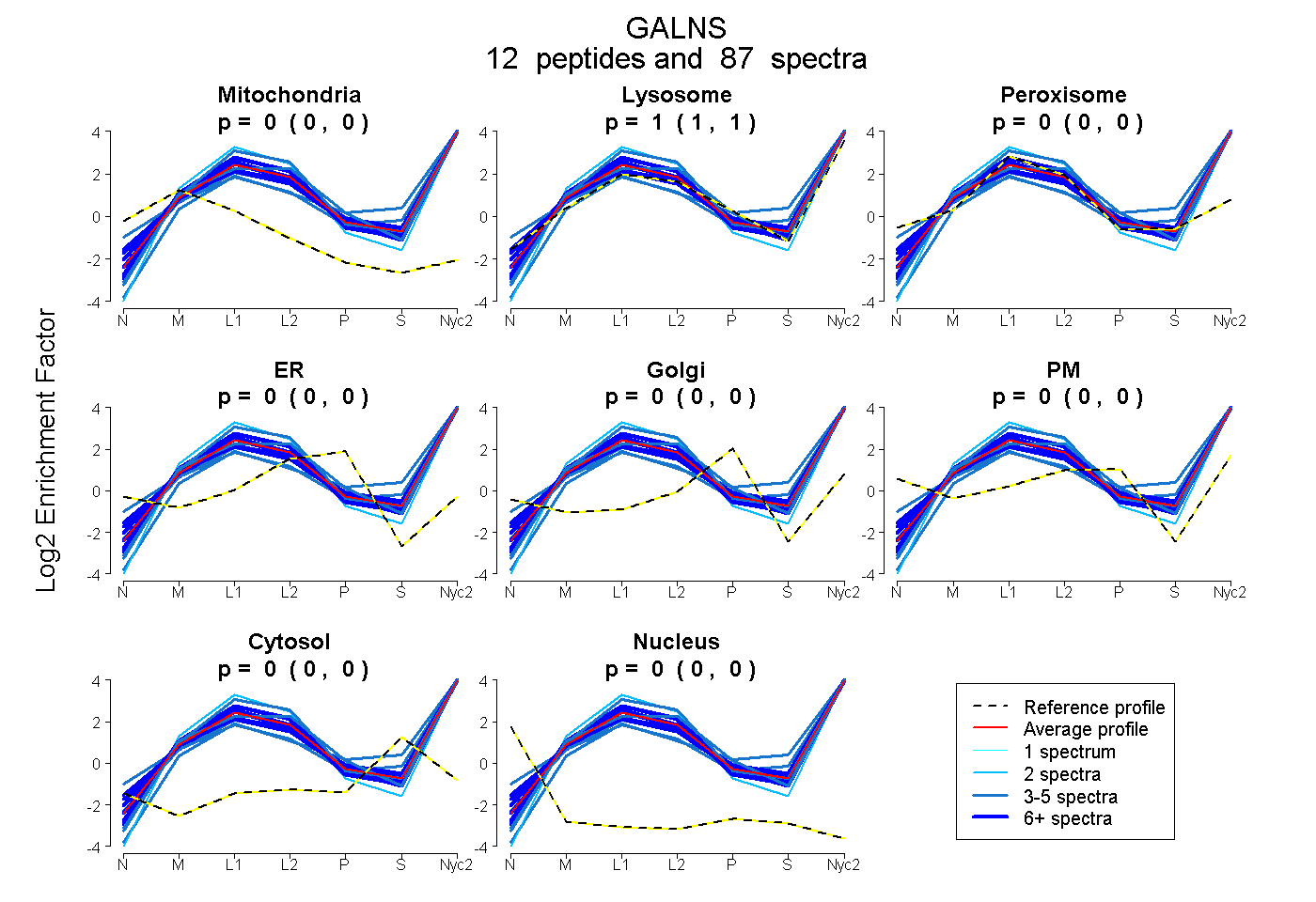
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
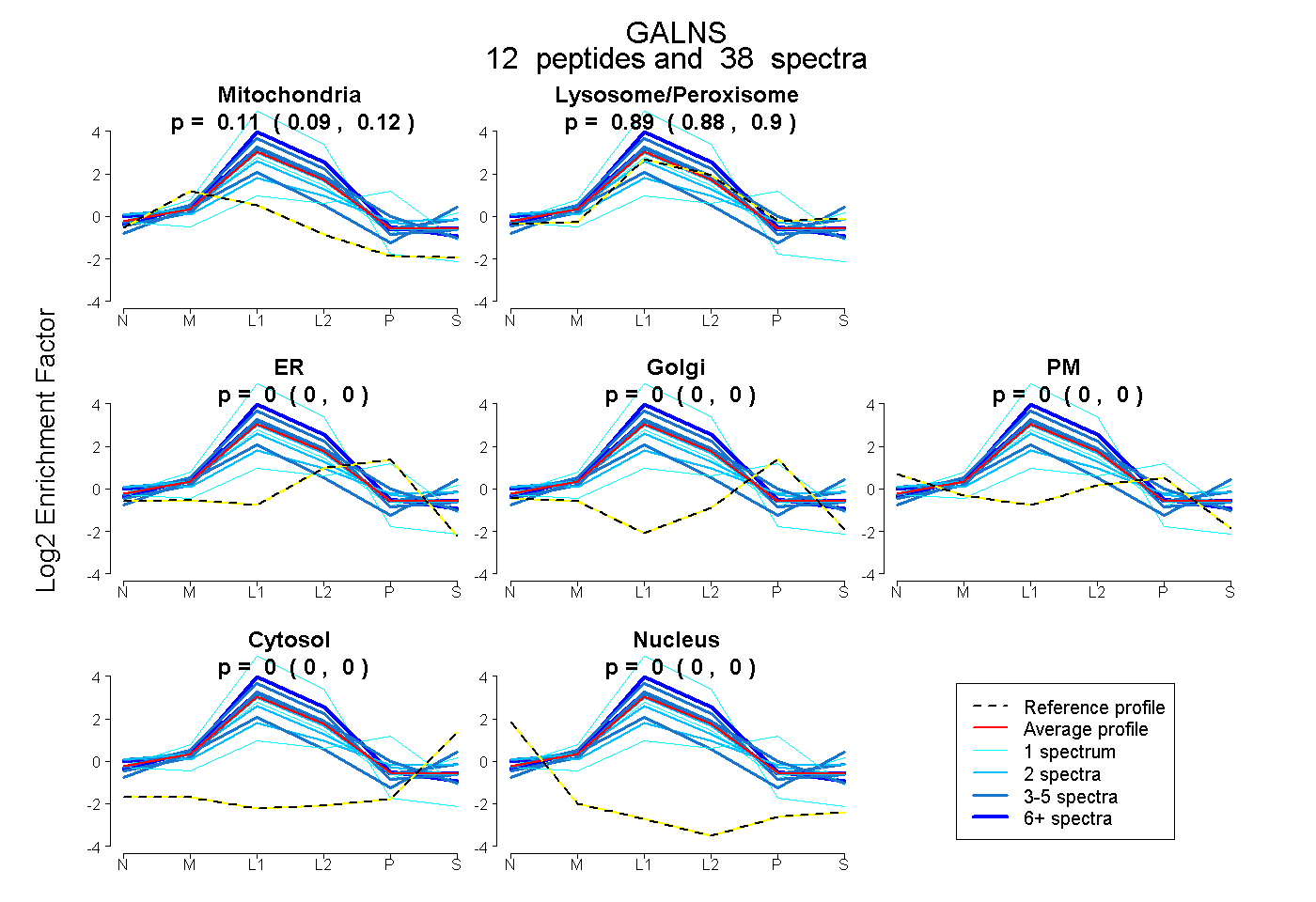
0.093 | 0.117
0.880 | 0.905
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
87 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
38 spectra |
 |
0.106 0.093 | 0.117 |
0.894 0.880 | 0.905 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, GNTLMAVTLGQYK | 0.096 | 0.704 | 0.000 | 0.000 | 0.148 | 0.048 | 0.004 | |||
| 2 spectra, EGGSNGPFLCGK | 0.198 | 0.800 | 0.000 | 0.000 | 0.002 | 0.000 | 0.000 | |||
| 1 spectrum, NGFYTTNAHAR | 0.000 | 0.507 | 0.175 | 0.318 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, QFLGTSLR | 0.010 | 0.990 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, AALLTGR | 0.088 | 0.912 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EIDDSVGK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, TTQVIQQHQK | 0.055 | 0.945 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, AALLASR | 0.124 | 0.876 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, ETPNLDR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, FYEEFPINLK | 0.032 | 0.968 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, VKPNIPVYR | 0.122 | 0.878 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, ILSLLQNLGISK | 0.207 | 0.653 | 0.000 | 0.000 | 0.000 | 0.139 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
262 spectra |
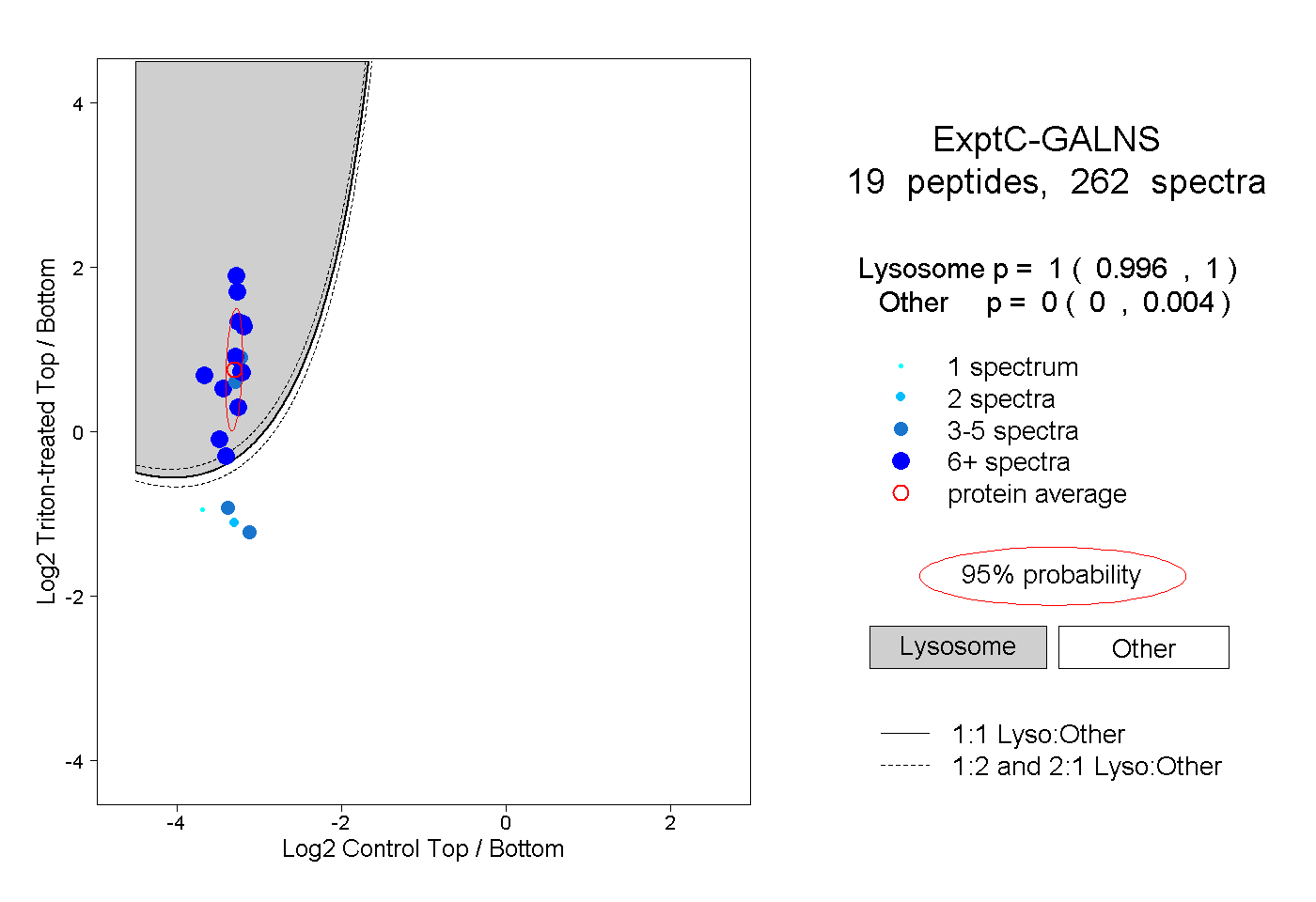 |
1.000 0.996 | 1.000 |
0.000 0.000 | 0.004 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
14 spectra |
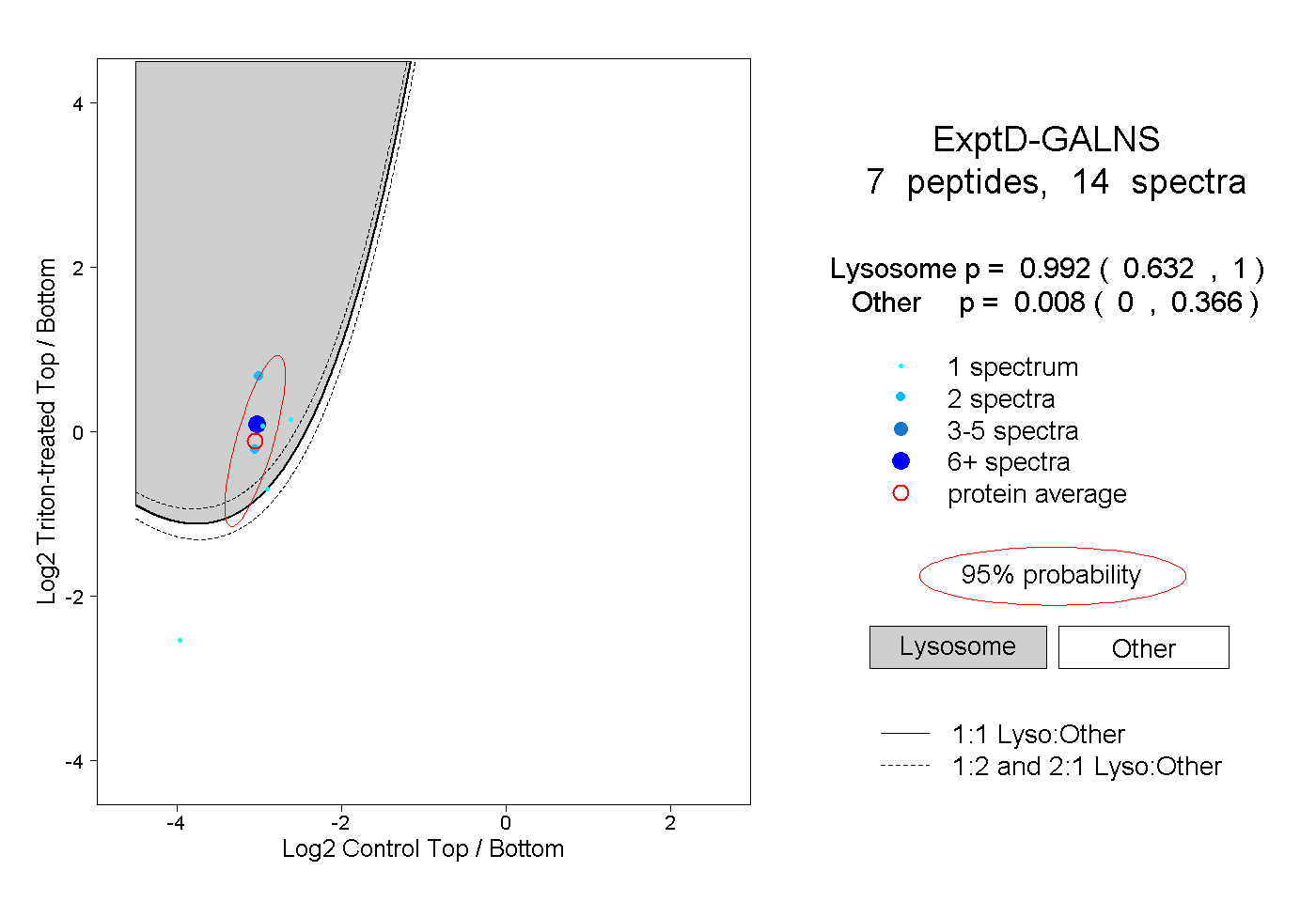 |
0.992 0.632 | 1.000 |
0.008 0.000 | 0.366 |