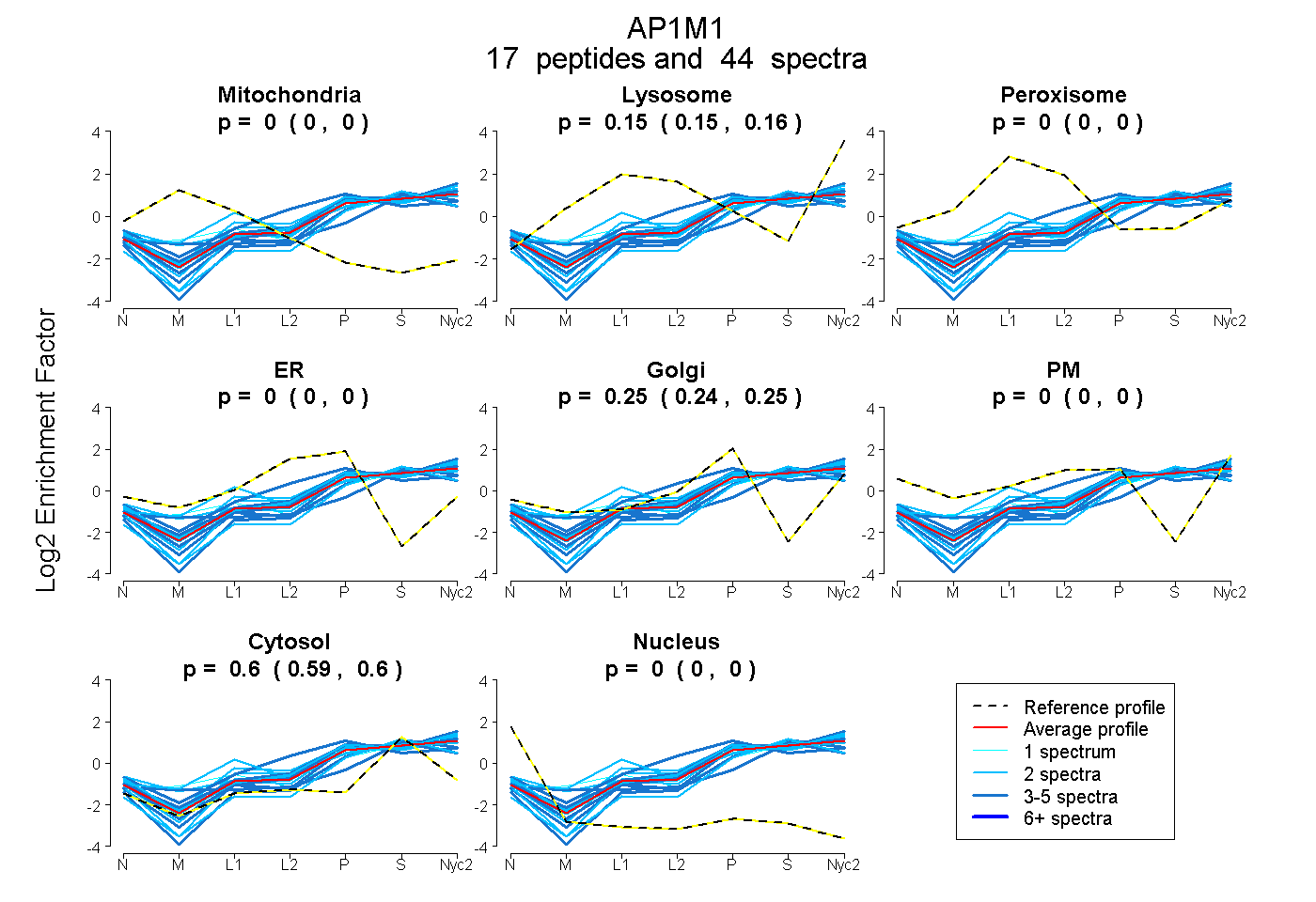
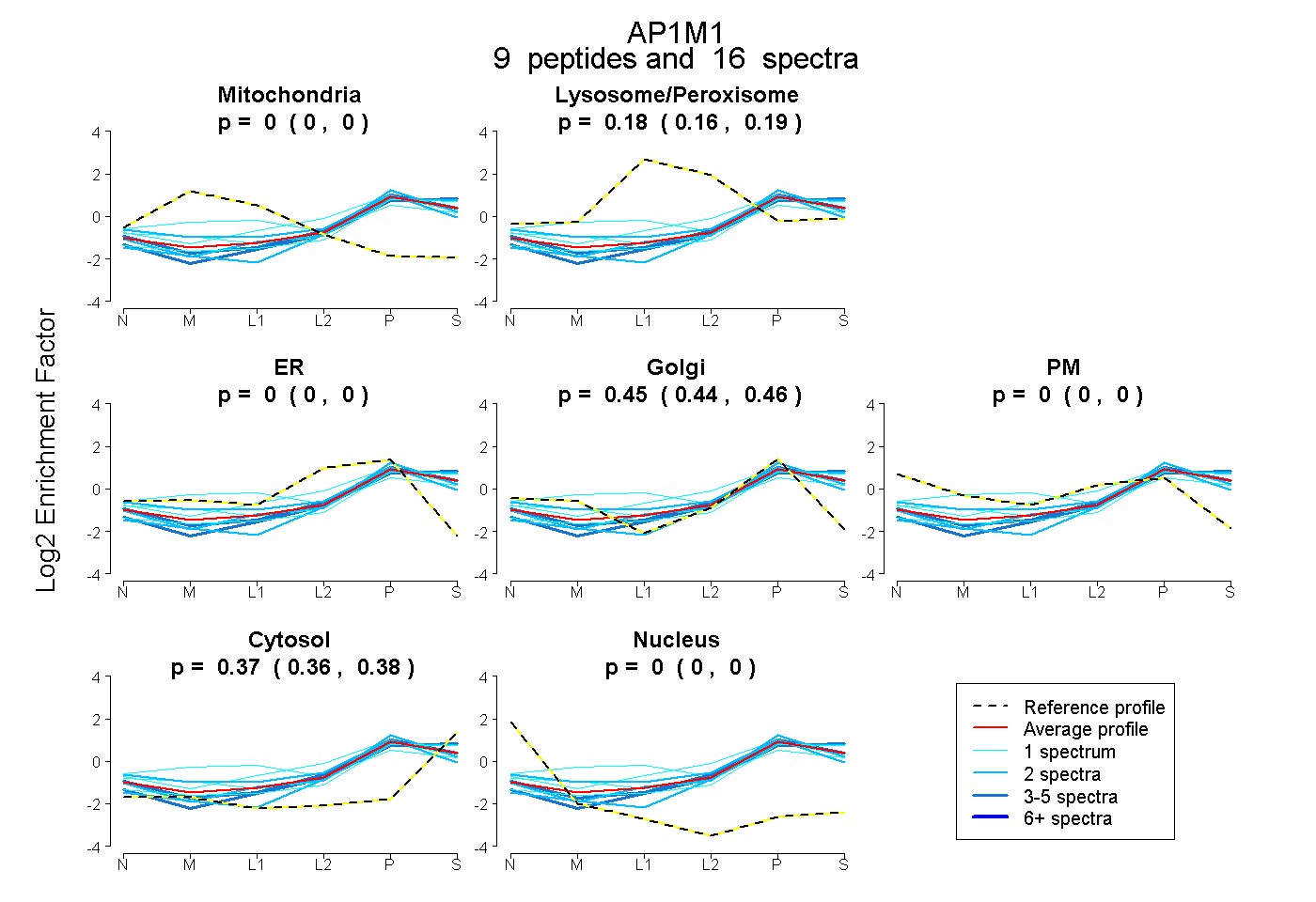
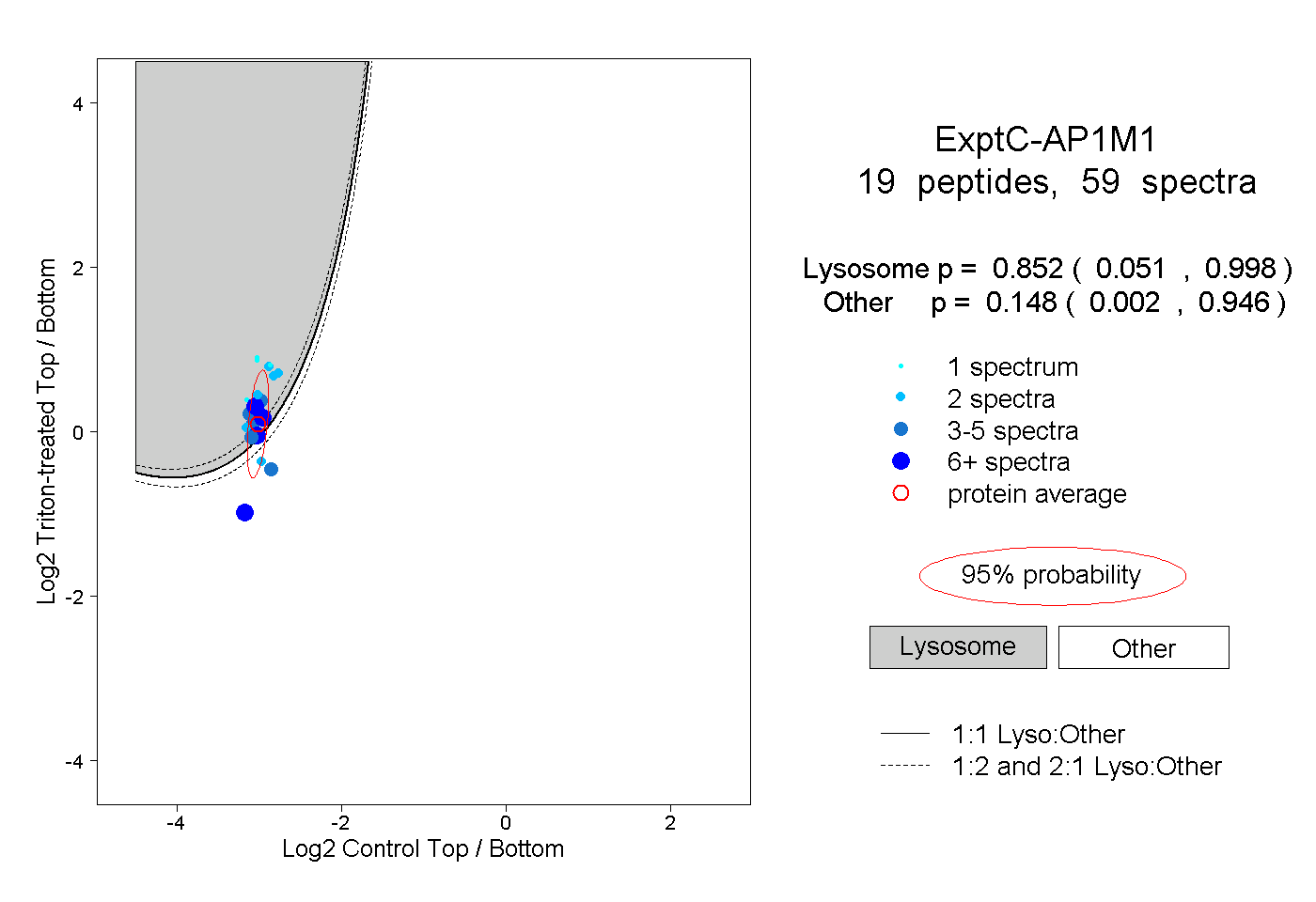
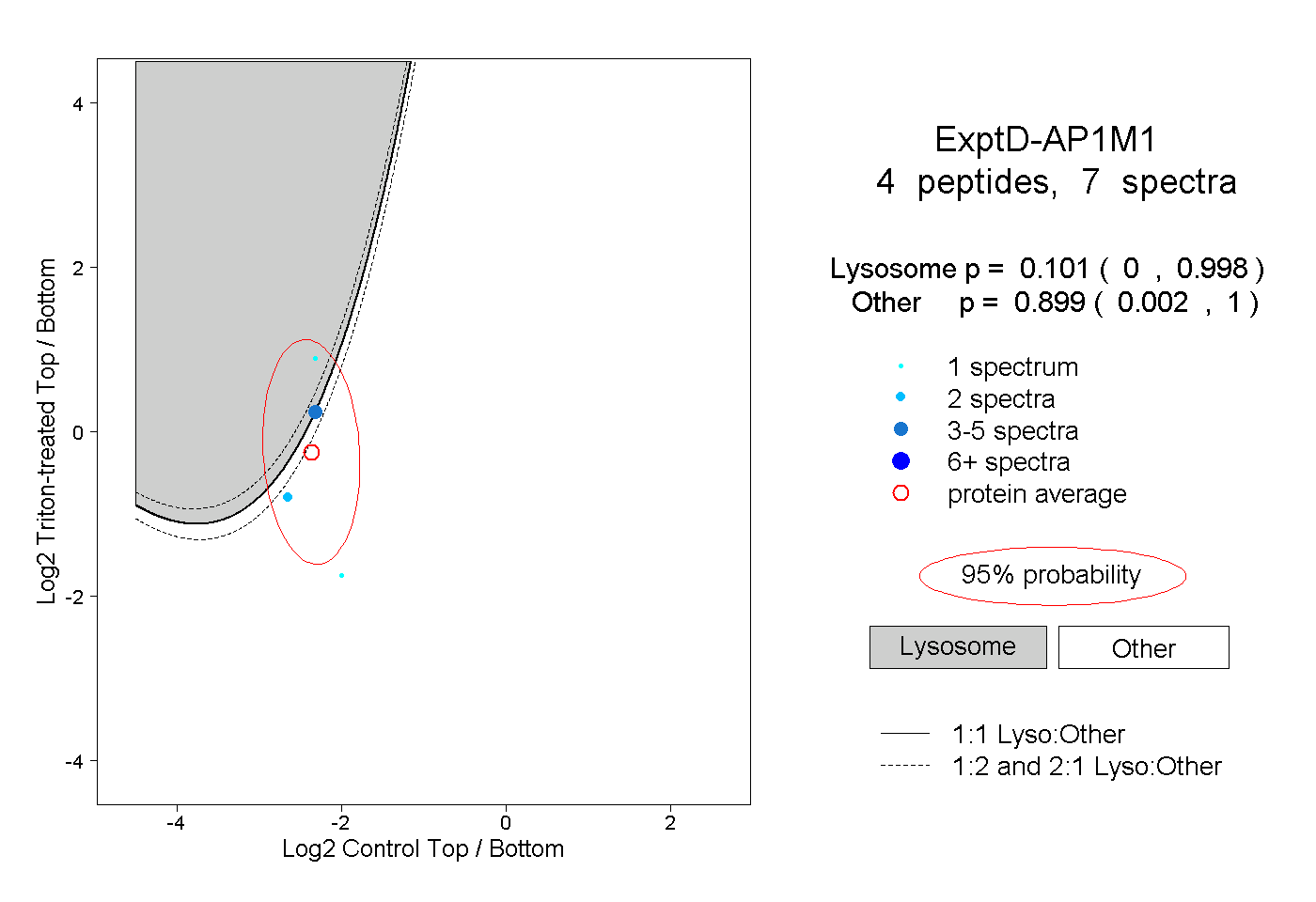
| 3 spectra, VLFDNTGR |
|
0.006 |
|
|
|
|
|
|
|
0.994 |
| 2 spectra, ELEEESIR |
|
0.982 |
|
|
|
|
|
|
|
0.018 |
| 1 spectrum, VVQVFSEYFK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 1 spectrum, TISFIPPDGEFELMSYR |
|
0.998 |
|
|
|
|
|
|
|
0.002 |
| 6 spectra, SFPGGK |
|
0.613 |
|
|
|
|
|
|
|
0.387 |
| 6 spectra, TTVGSVK |
|
0.984 |
|
|
|
|
|
|
|
0.016 |
| 6 spectra, FHQCVR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 3 spectra, SVELEDVK |
|
0.982 |
|
|
|
|
|
|
|
0.018 |
| 2 spectra, EGKPPISVK |
|
0.044 |
|
|
|
|
|
|
|
0.956 |
| 2 spectra, LGLNDK |
|
0.936 |
|
|
|
|
|
|
|
0.064 |
| 1 spectrum, STANNVEIHIPVPNDADSPK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 5 spectra, FEIPYFTTSGIQVR |
|
0.982 |
|
|
|
|
|
|
|
0.018 |
| 3 spectra, LETGAPRPPATVTNAVSWR |
|
0.913 |
|
|
|
|
|
|
|
0.087 |
| 1 spectrum, YITQNGDYQLR |
|
0.998 |
|
|
|
|
|
|
|
0.002 |
| 8 spectra, VFLSGMPELR |
|
0.860 |
|
|
|
|
|
|
|
0.140 |
| 3 spectra, SGYQALPWVR |
|
0.742 |
|
|
|
|
|
|
|
0.258 |
| 2 spectra, WVPENSEIVWSIK |
|
0.993 |
|
|
|
|
|
|
|
0.007 |
| 2 spectra, SEIVGSIK |
|
0.990 |
|
|
|
|
|
|
|
0.010 |
| 2 spectra, IEYMVK |
|
0.998 |
|
|
|
|
|
|
|
0.002 |