peptides
spectra
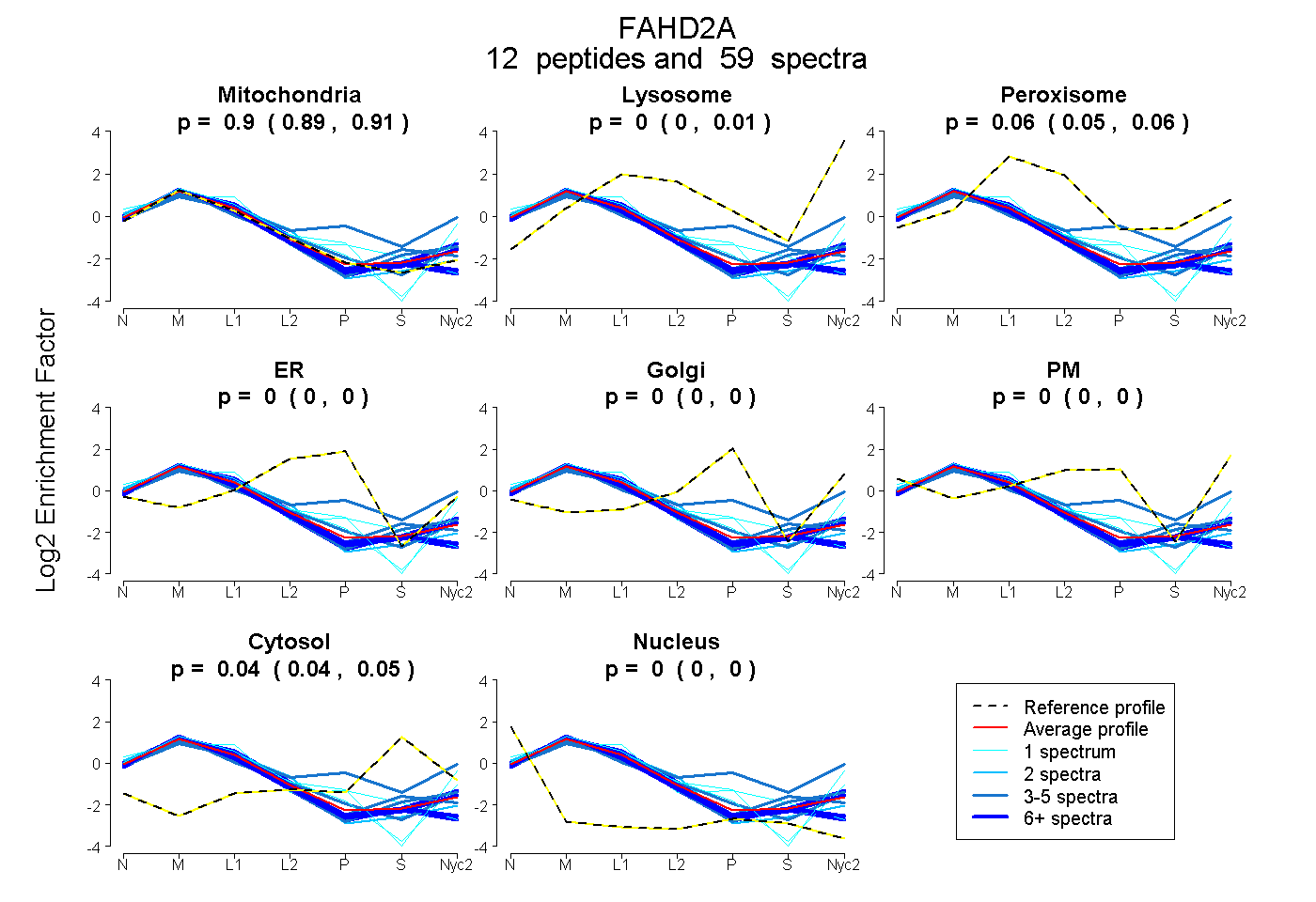
0.893 | 0.907
0.000 | 0.009
0.047 | 0.059
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.040 | 0.046
0.000 | 0.000
peptides
spectra
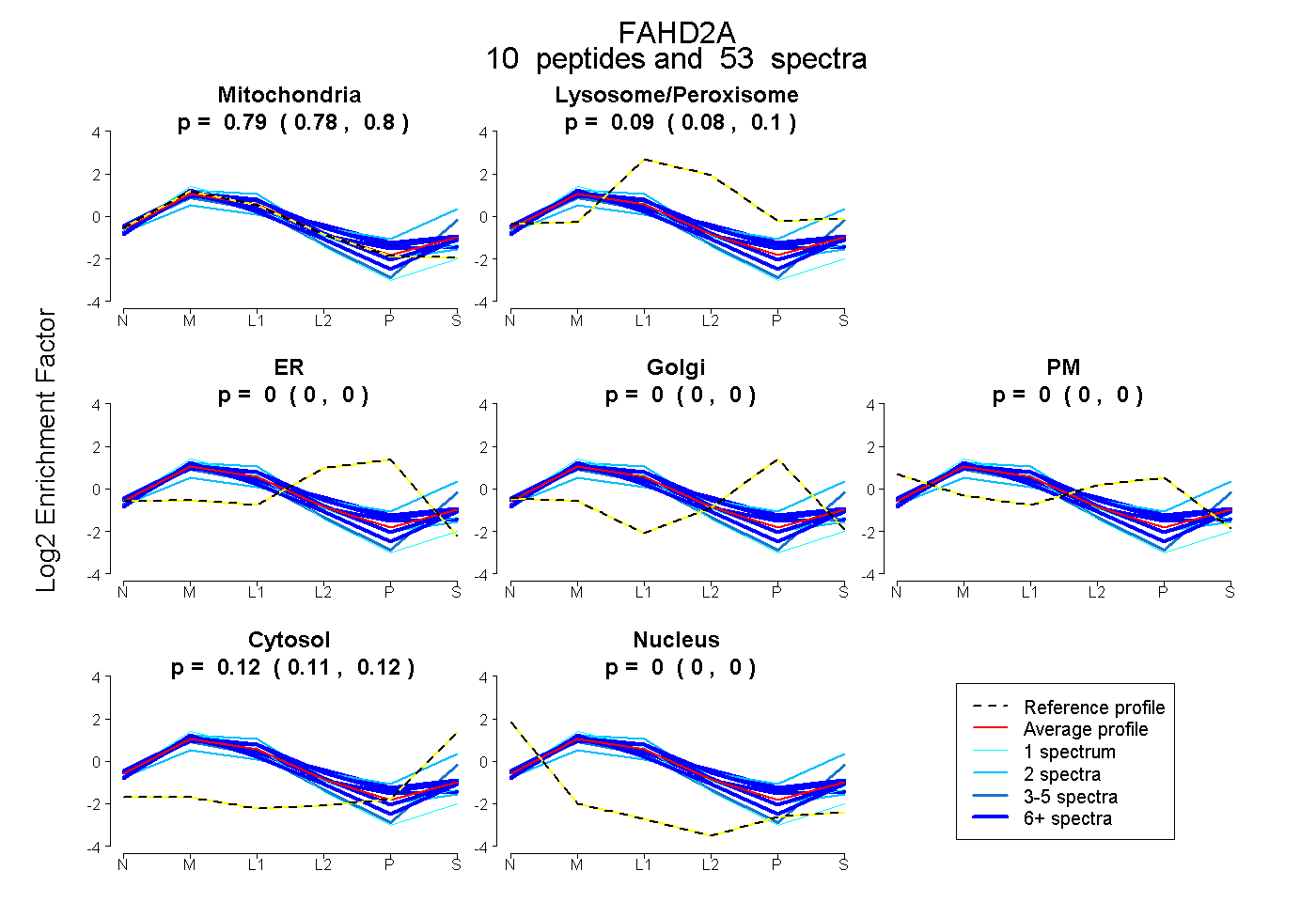
0.780 | 0.800
0.084 | 0.098
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.111 | 0.123
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
59 spectra |
 |
0.900 0.893 | 0.907 |
0.000 0.000 | 0.009 |
0.056 0.047 | 0.059 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.043 0.040 | 0.046 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
53 spectra |
 |
0.791 0.780 | 0.800 |
0.092 0.084 | 0.098 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.118 0.111 | 0.123 |
0.000 0.000 | 0.000 |
| 8 spectra, GETALSVAR | 0.850 | 0.063 | 0.000 | 0.028 | 0.000 | 0.059 | 0.000 | |||
| 3 spectra, ALAAQLPLIPR | 0.741 | 0.000 | 0.000 | 0.000 | 0.000 | 0.259 | 0.000 | |||
| 7 spectra, VICVGLNYADHCQEQNVR | 0.832 | 0.099 | 0.000 | 0.000 | 0.000 | 0.069 | 0.000 | |||
| 7 spectra, TMVQFLER | 0.860 | 0.000 | 0.000 | 0.000 | 0.000 | 0.140 | 0.000 | |||
| 1 spectrum, QWLLGK | 0.906 | 0.059 | 0.000 | 0.000 | 0.000 | 0.035 | 0.000 | |||
| 2 spectra, KPPVFLK | 0.933 | 0.067 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 16 spectra, ATDVMAYVAGFTVAHDVSAR | 0.665 | 0.181 | 0.000 | 0.038 | 0.000 | 0.116 | 0.000 | |||
| 2 spectra, DTIADPHNLK | 0.357 | 0.290 | 0.000 | 0.000 | 0.000 | 0.353 | 0.000 | |||
| 6 spectra, TFDTFCPLGPALVTK | 0.711 | 0.198 | 0.000 | 0.000 | 0.000 | 0.091 | 0.000 | |||
| 1 spectrum, NPIIFSK | 0.969 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.031 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
325 spectra |
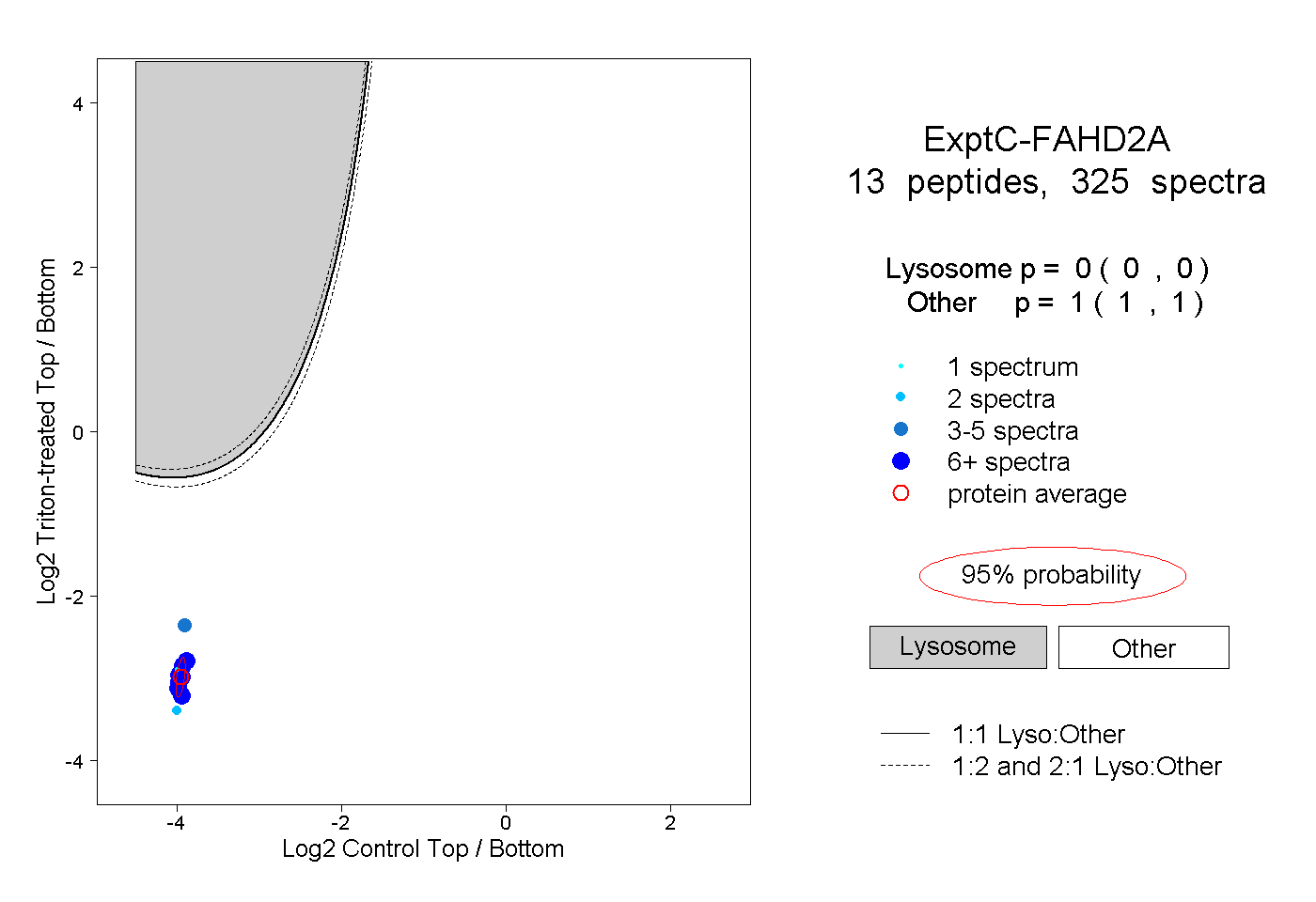 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
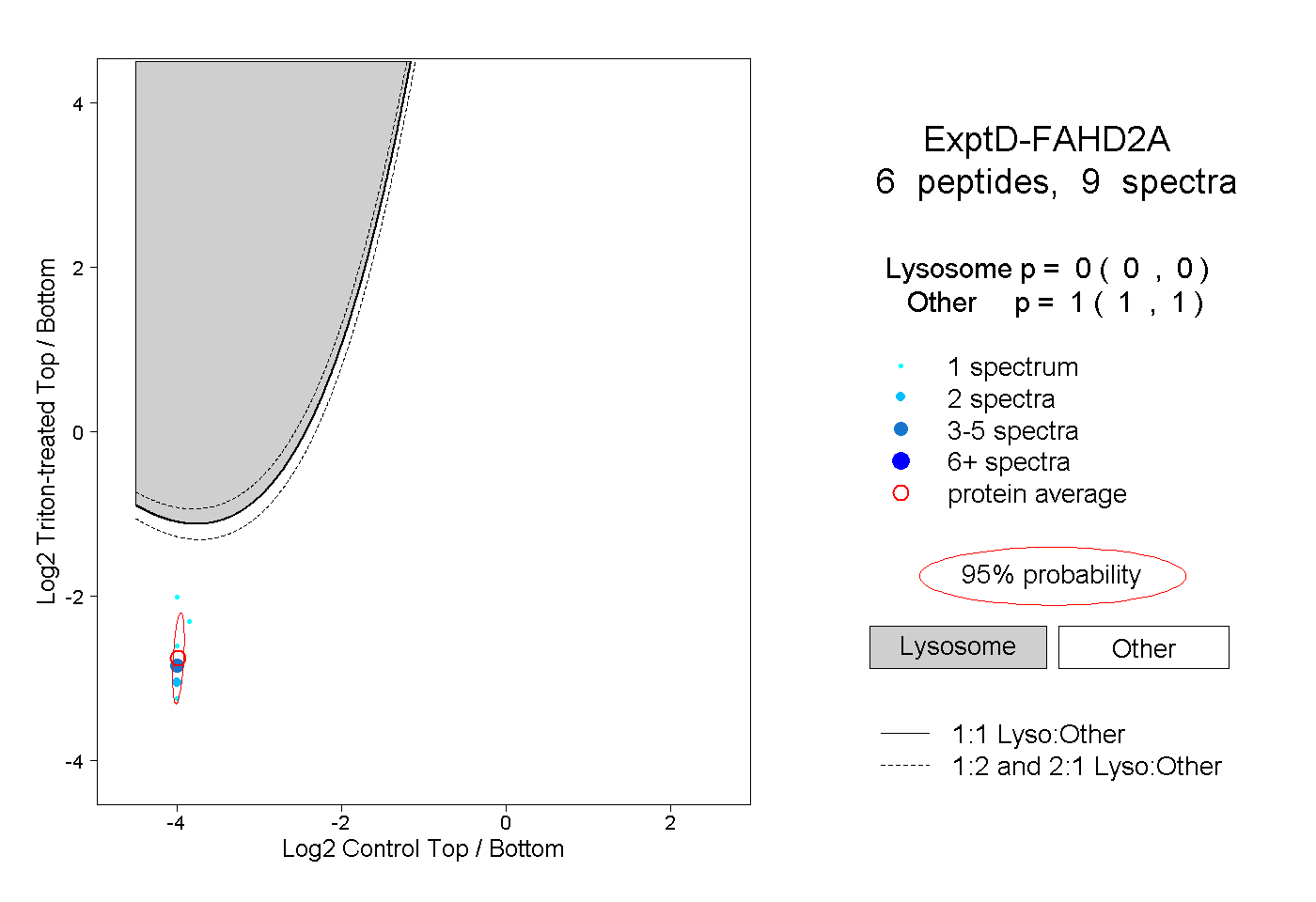 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |