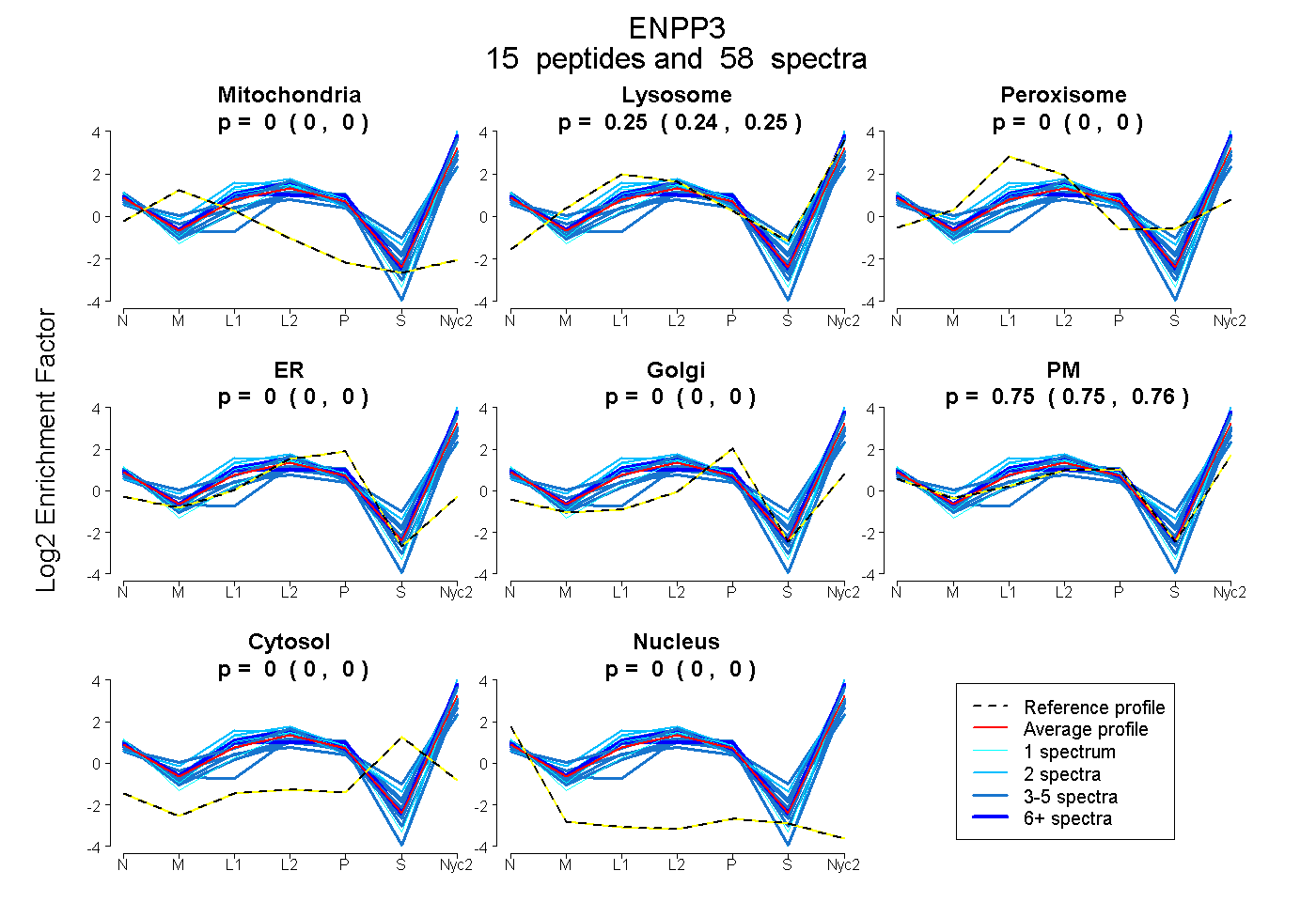
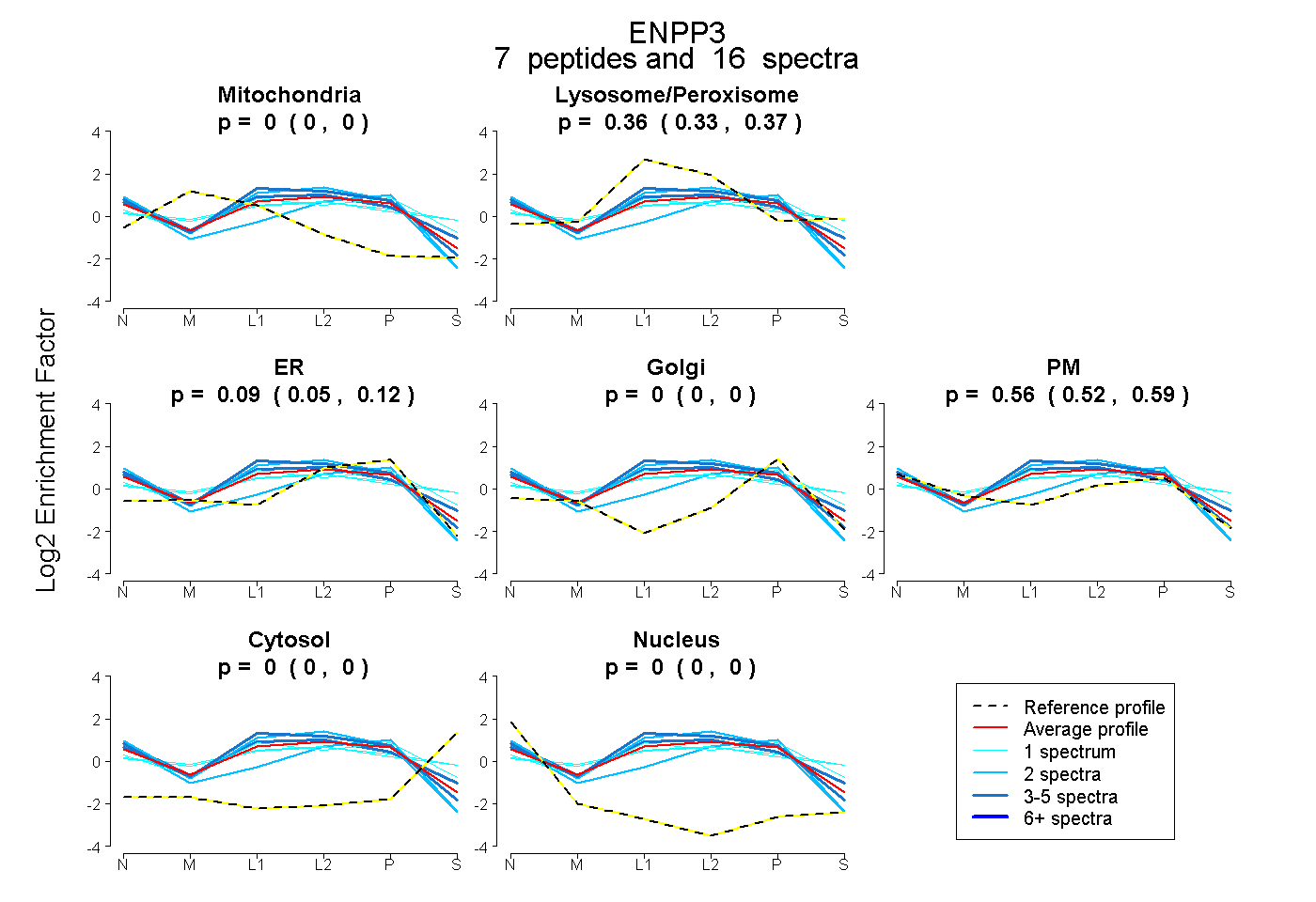
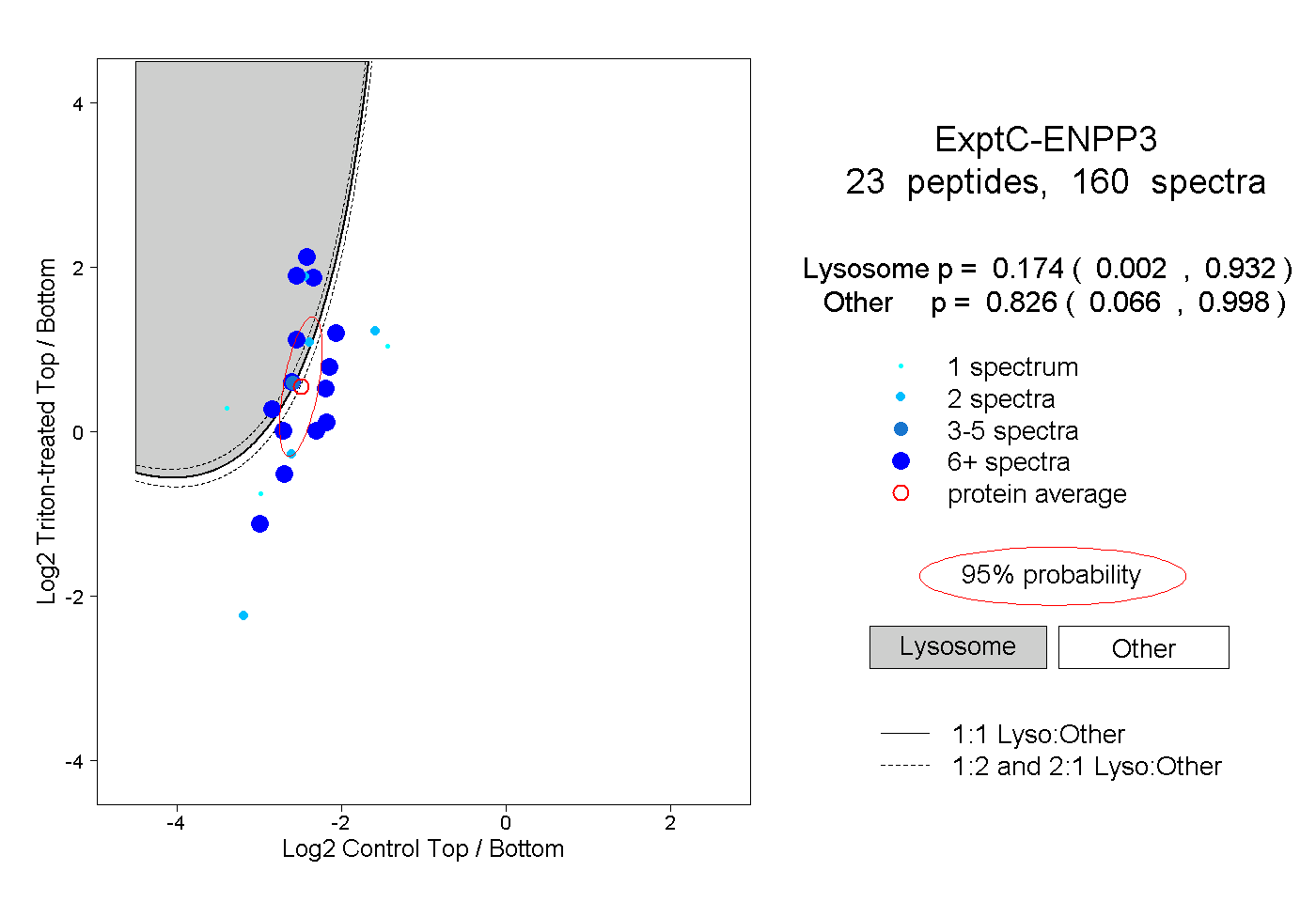
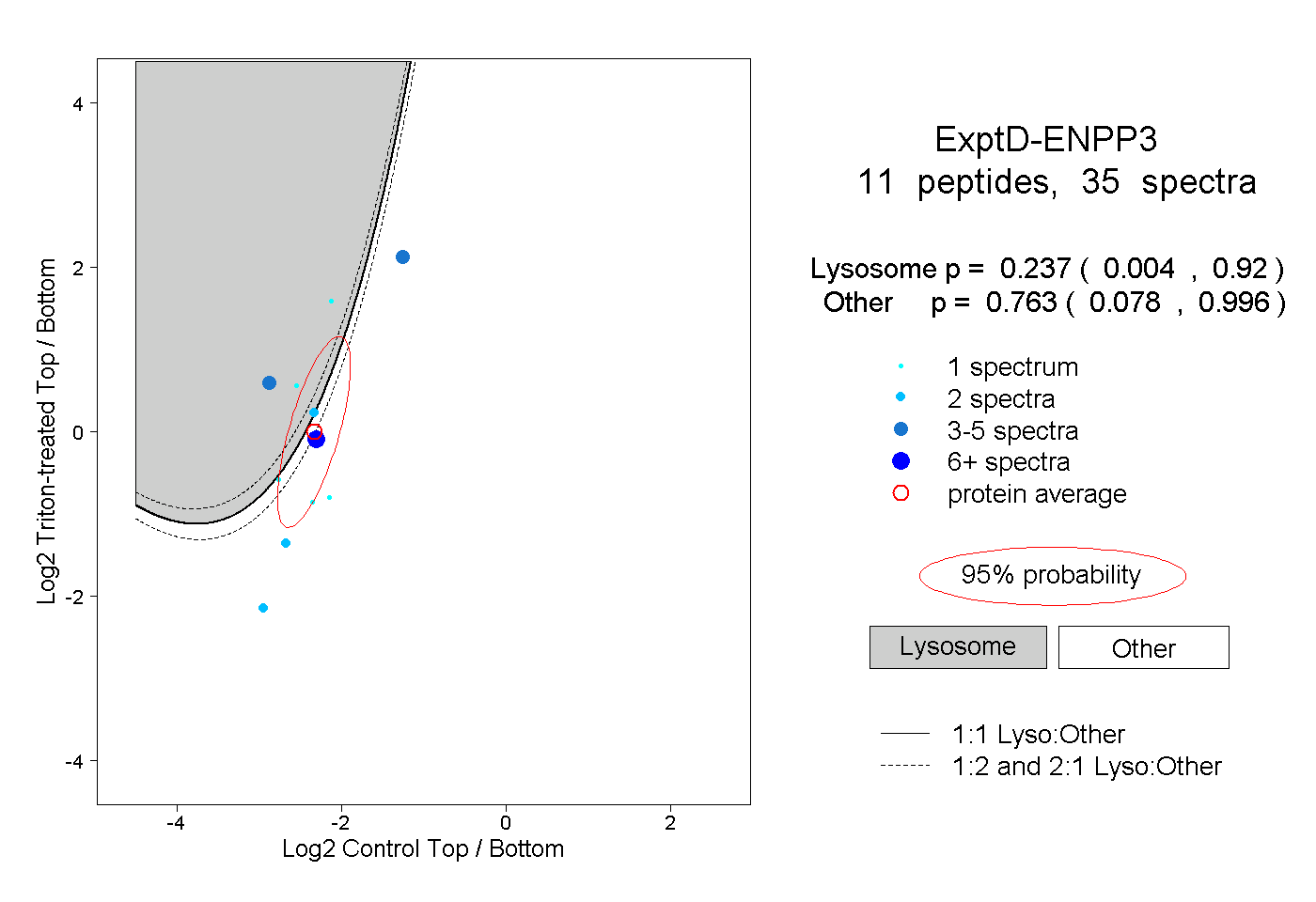
| 6 spectra, SMEAIFLAHGPSFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LEAALCSCADDCLQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, SGPVSAGVIK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 8 spectra, MWDYFHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GSSNCEGGTHGYNNEFK |
|
0.999 |
|
|
|
|
|
|
|
0.001 |
| 8 spectra, DCCTDYK |
|
0.005 |
|
|
|
|
|
|
|
0.995 |
| 19 spectra, APFYQPSHAEELSK |
|
0.063 |
|
|
|
|
|
|
|
0.937 |
| 14 spectra, AMYPTK |
|
0.647 |
|
|
|
|
|
|
|
0.353 |
| 1 spectrum, AEDLWVEER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TQPVSEILQLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TCGLHSK |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 2 spectra, LNLSGGEVSATEK |
|
0.647 |
|
|
|
|
|
|
|
0.353 |
| 9 spectra, DLSCR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 1 spectrum, DVELLTGLDFYQEK |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 13 spectra, VDPSESQK |
|
0.002 |
|
|
|
|
|
|
|
0.998 |
| 16 spectra, TNLPFGRPR |
|
0.798 |
|
|
|
|
|
|
|
0.202 |
| 7 spectra, QWLAYR |
|
0.976 |
|
|
|
|
|
|
|
0.024 |
| 2 spectra, NIPQDFFTFNSEEIVR |
|
0.999 |
|
|
|
|
|
|
|
0.001 |
| 9 spectra, VHLMVDR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 3 spectra, SAGCGFTTPLPK |
|
0.601 |
|
|
|
|
|
|
|
0.399 |
| 8 spectra, STQIWTCNSFR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 7 spectra, EYVSGFGK |
|
0.994 |
|
|
|
|
|
|
|
0.006 |
| 12 spectra, GLEGCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |