peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.003
0.000 | 0.000
0.936 | 0.940
0.058 | 0.063
peptides
spectra
0.000 | 0.000
0.000 | 0.020
0.097 | 0.151
0.219 | 0.272
0.000 | 0.000
0.609 | 0.626
0.000 | 0.000
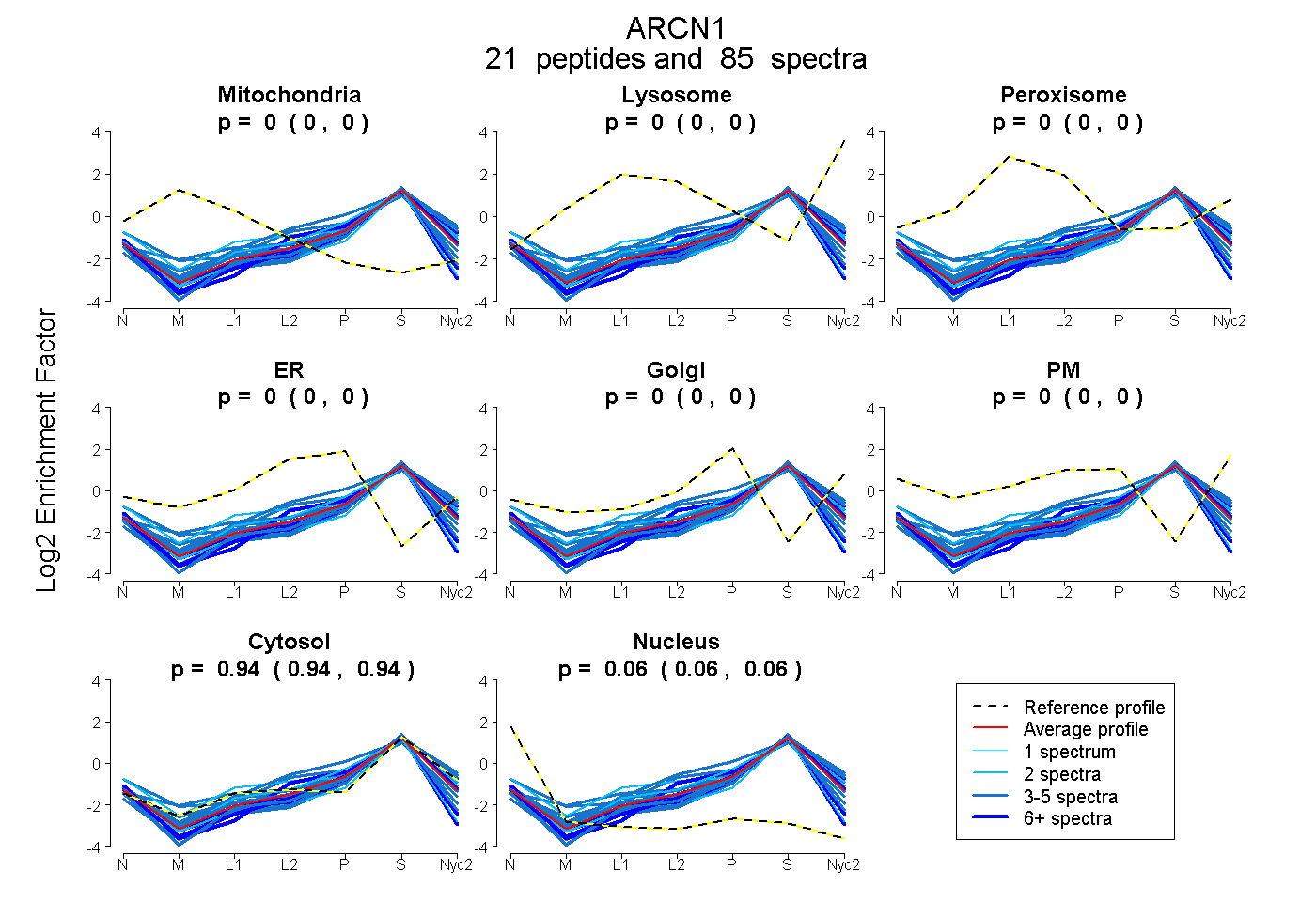
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
85 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.001 0.000 | 0.003 |
0.000 0.000 | 0.000 |
0.939 0.936 | 0.940 |
0.061 0.058 | 0.063 |
||
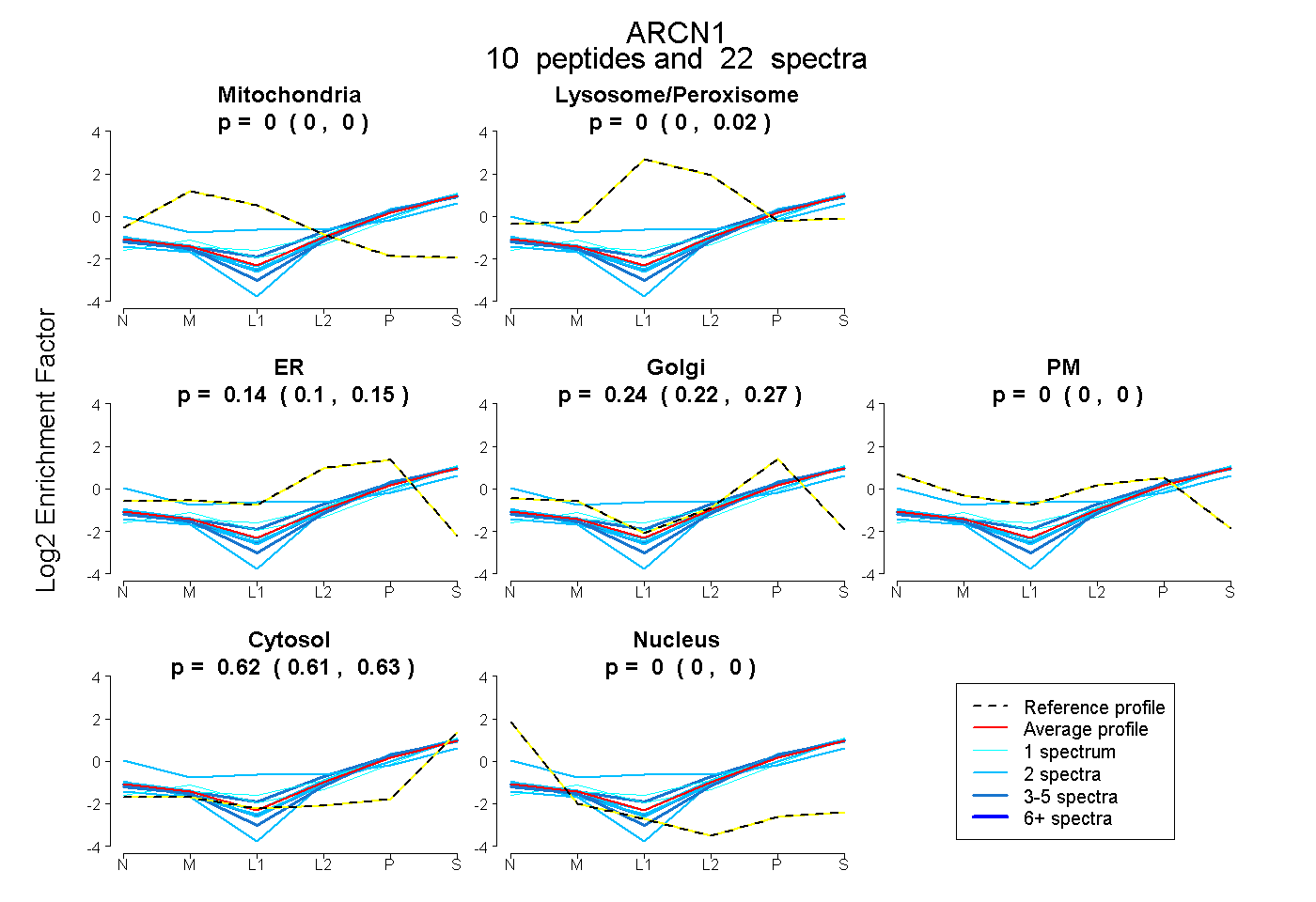
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.020 |
0.138 0.097 | 0.151 |
0.240 0.219 | 0.272 |
0.000 0.000 | 0.000 |
0.622 0.609 | 0.626 |
0.000 0.000 | 0.000 |
| 2 spectra, LFTAESLIGLK | 0.000 | 0.000 | 0.000 | 0.356 | 0.000 | 0.644 | 0.000 | |||
| 1 spectrum, SFPVNSDVGVLK | 0.000 | 0.148 | 0.000 | 0.305 | 0.000 | 0.547 | 0.000 | |||
| 2 spectra, QHTFVETESVR | 0.000 | 0.217 | 0.000 | 0.000 | 0.347 | 0.436 | 0.000 | |||
| 2 spectra, VLLAAAVCTK | 0.000 | 0.000 | 0.065 | 0.296 | 0.000 | 0.639 | 0.000 | |||
| 4 spectra, VTQVDGNSPVR | 0.000 | 0.000 | 0.000 | 0.386 | 0.000 | 0.614 | 0.000 | |||
| 2 spectra, ENVNLAQIR | 0.000 | 0.000 | 0.145 | 0.248 | 0.000 | 0.607 | 0.000 | |||
| 3 spectra, ITLTCGR | 0.000 | 0.000 | 0.030 | 0.349 | 0.000 | 0.621 | 0.000 | |||
| 2 spectra, VIPEYCR | 0.000 | 0.000 | 0.027 | 0.376 | 0.000 | 0.597 | 0.000 | |||
| 3 spectra, NSNILEDLETLR | 0.000 | 0.050 | 0.207 | 0.150 | 0.000 | 0.593 | 0.000 | |||
| 1 spectrum, QFVEMTR | 0.000 | 0.068 | 0.000 | 0.256 | 0.000 | 0.676 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
78 spectra |
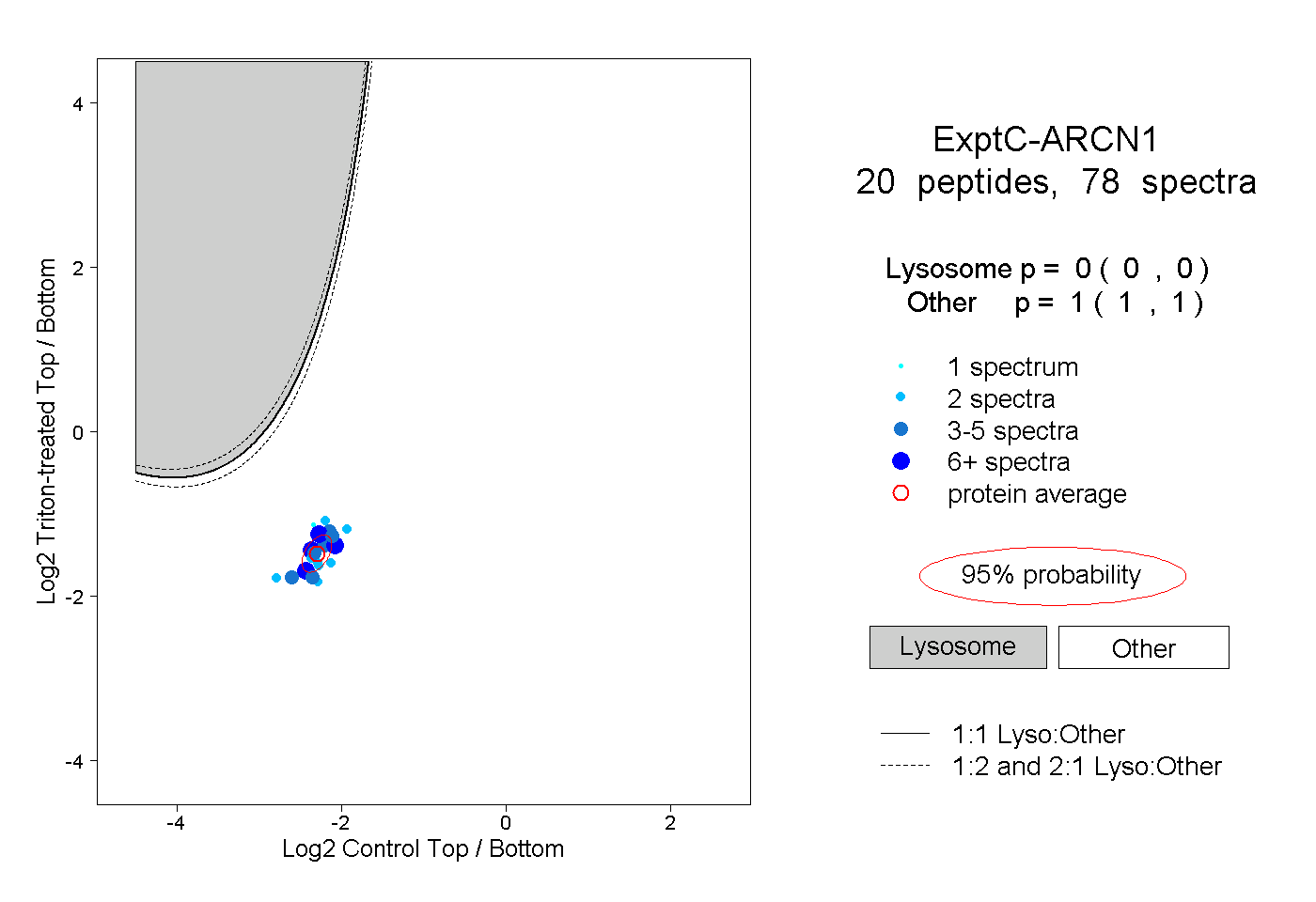 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
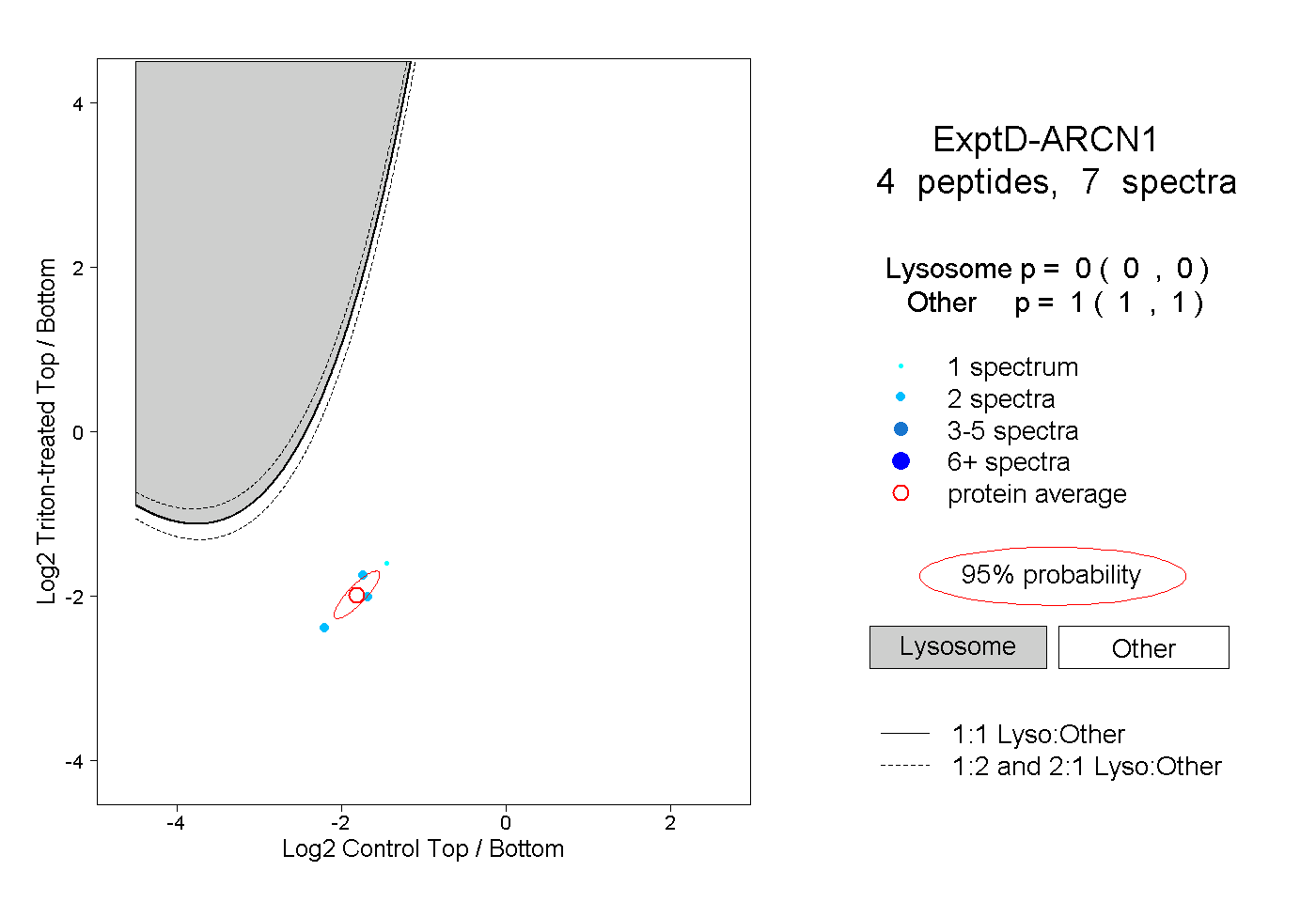 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |