C9
[ENSRNOP00000018545]
Main page
| | | Plot |
Mito |
Lyso |
|
Perox |
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt A |
 16
16
peptides |
74
spectra |
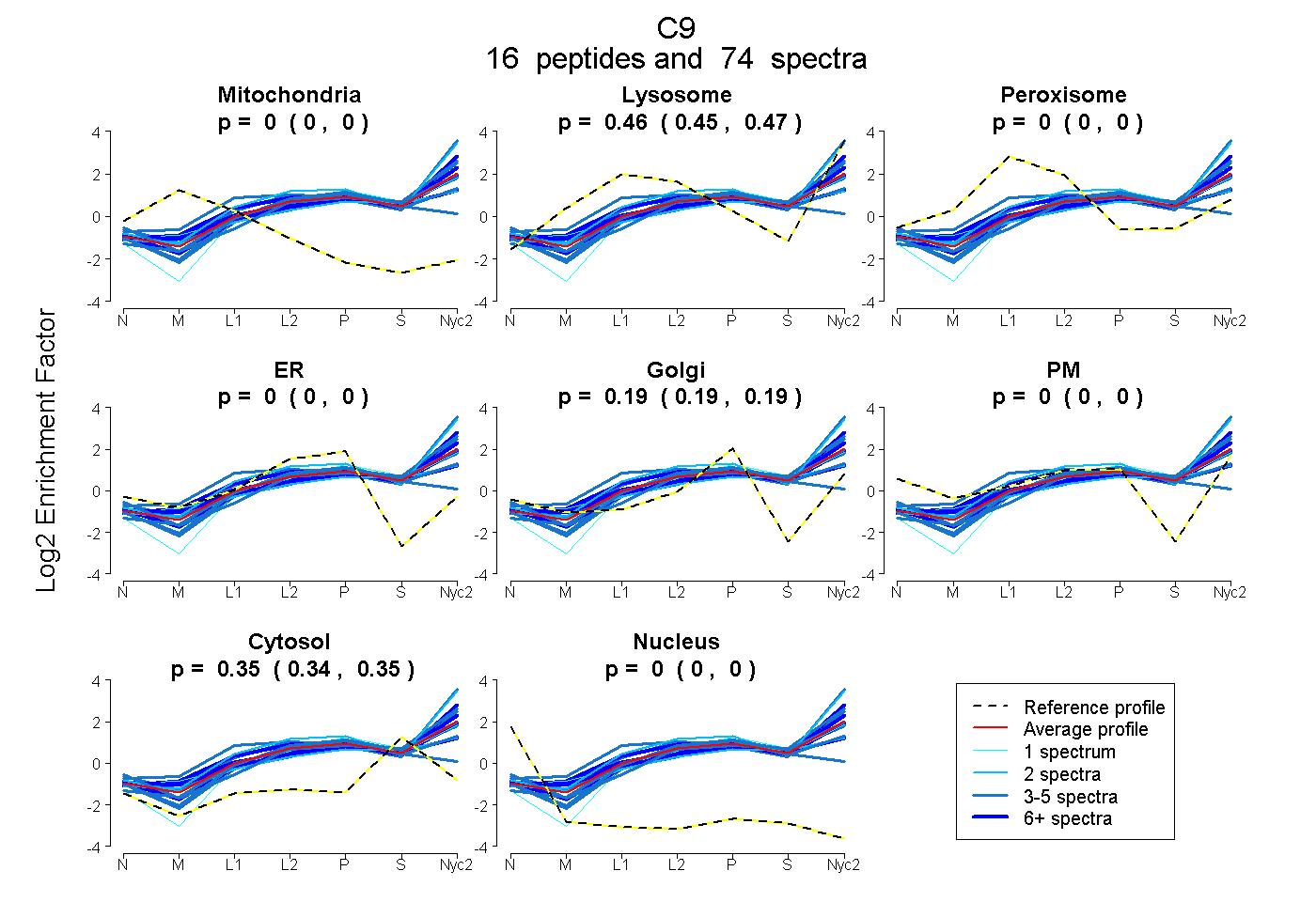 |
0.000
0.000 | 0.000 |
0.460
0.455 | 0.465 |
|
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.192
0.188 | 0.195 |
0.000
0.000 | 0.000 |
0.348
0.344 | 0.350 |
0.000
0.000 | 0.000 |
|
| | | Plot |
Mito |
|
Lyso or Perox |
|
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt B |
 10
10
peptides |
21
spectra |
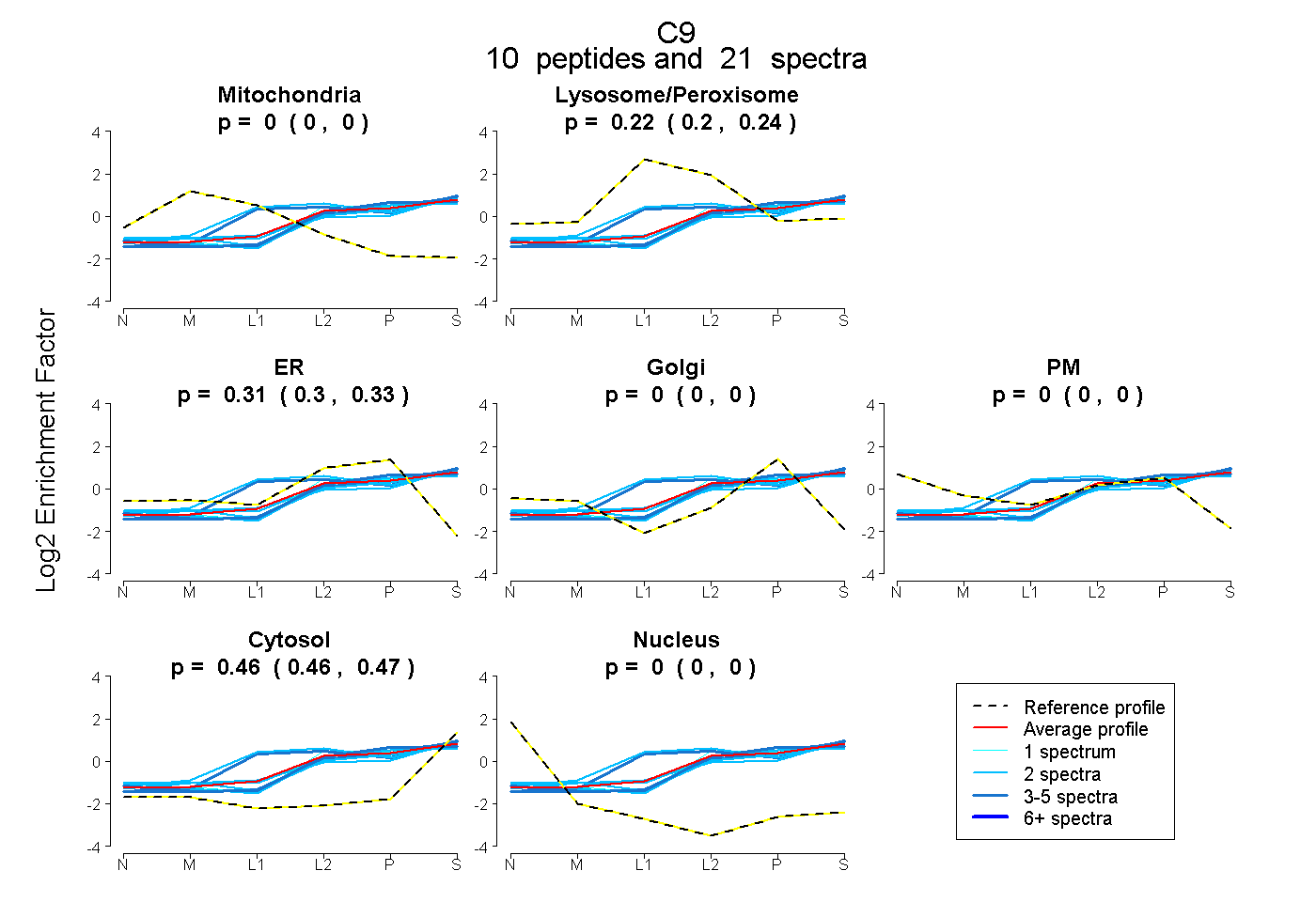 |
0.000
0.000 | 0.000 |
|
0.221
0.203 | 0.239 |
|
0.315
0.300 | 0.326 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.464
0.457 | 0.470 |
0.000
0.000 | 0.000 |
|
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
| Expt C |
 22
22
peptides |
143
spectra |
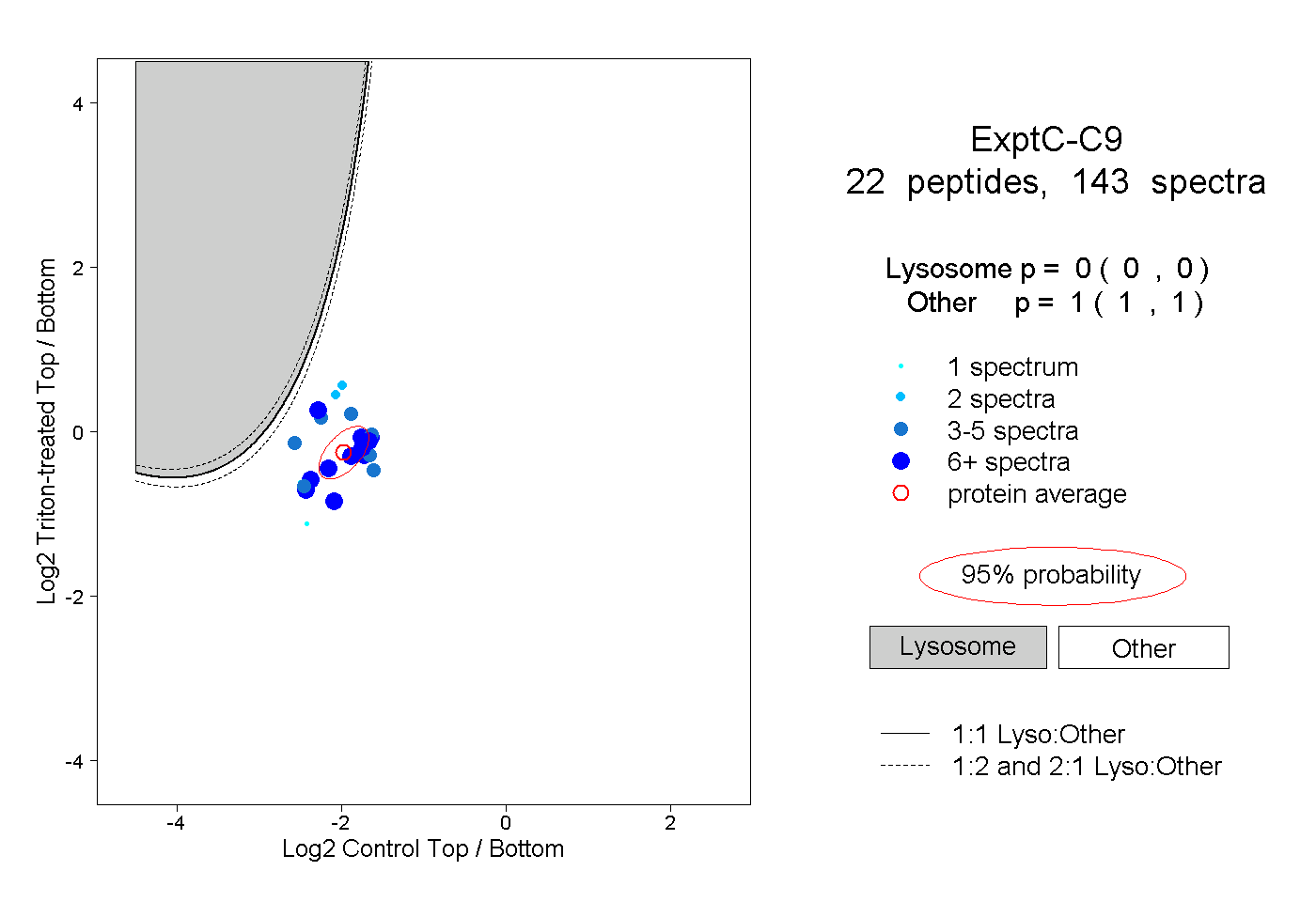 |
|
0.000
0.000 | 0.000 |
|
|
|
|
|
|
|
1.000
1.000 | 1.000 |
| 9 spectra, DGNTLTYYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, MFLHVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VGVDEVSPEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, TENYEEQFEMFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, VVNISR |
|
0.003 |
|
|
|
|
|
|
|
0.997 |
| 2 spectra, TTSFNANLALK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, DAYAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, DHIIDDVISFIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, QAVLLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, AIEDYVNEFSAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, LSSYLSQTK |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 9 spectra, ALPVSYEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GVELSDVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, SCADALGDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, GIACEISK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, KPWNVAFLAYETK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GVMLTTTFLDDVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SIEVFGQFQGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, DSSVDFQFSYFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, VVEESELGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, FTITEAPIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, GMIQLGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
| Expt D |
 10
10
peptides |
17
spectra |
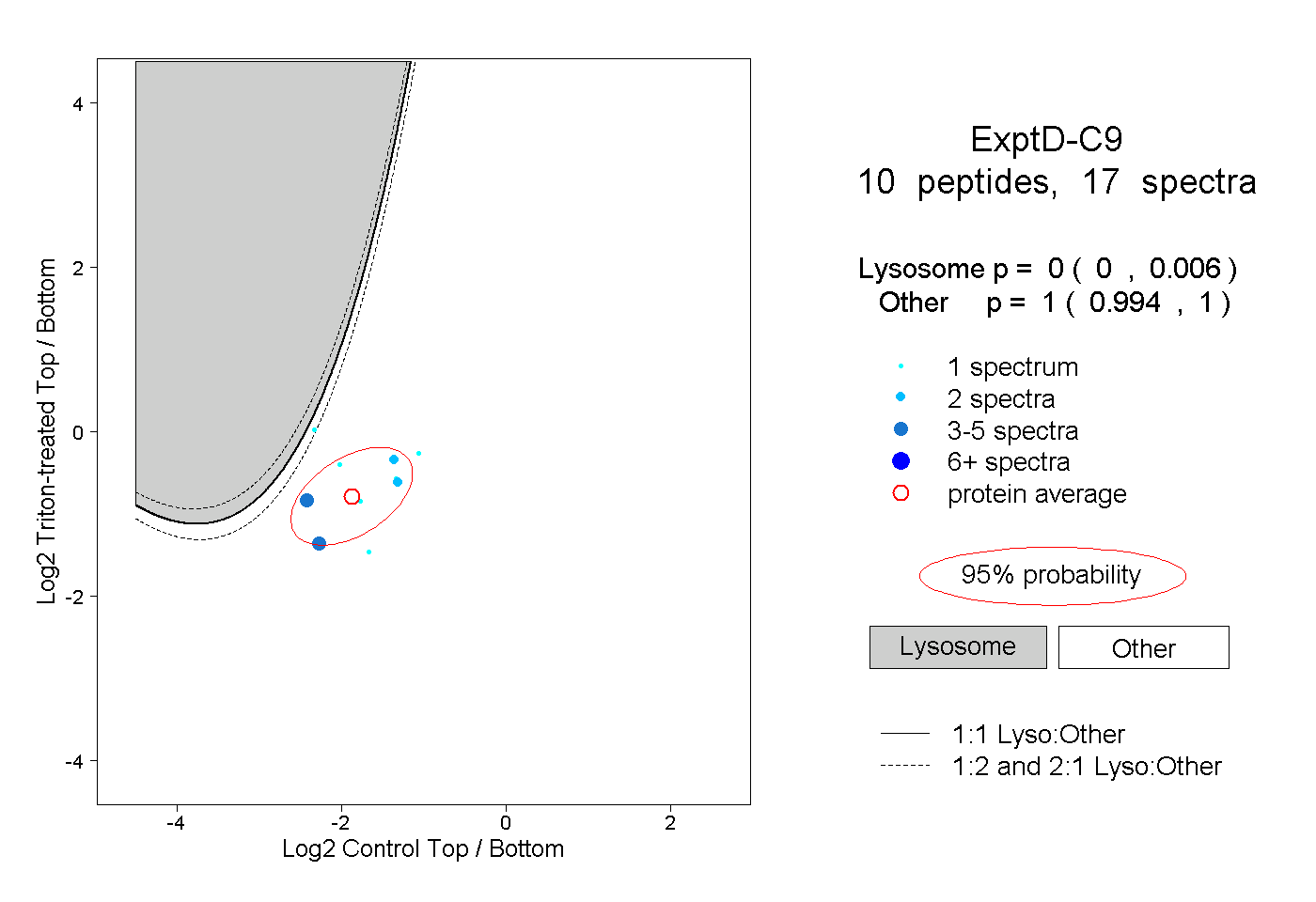 |
|
0.000
0.000 | 0.006 |
|
|
|
|
|
|
|
1.000
0.994 | 1.000 |



