peptides
spectra
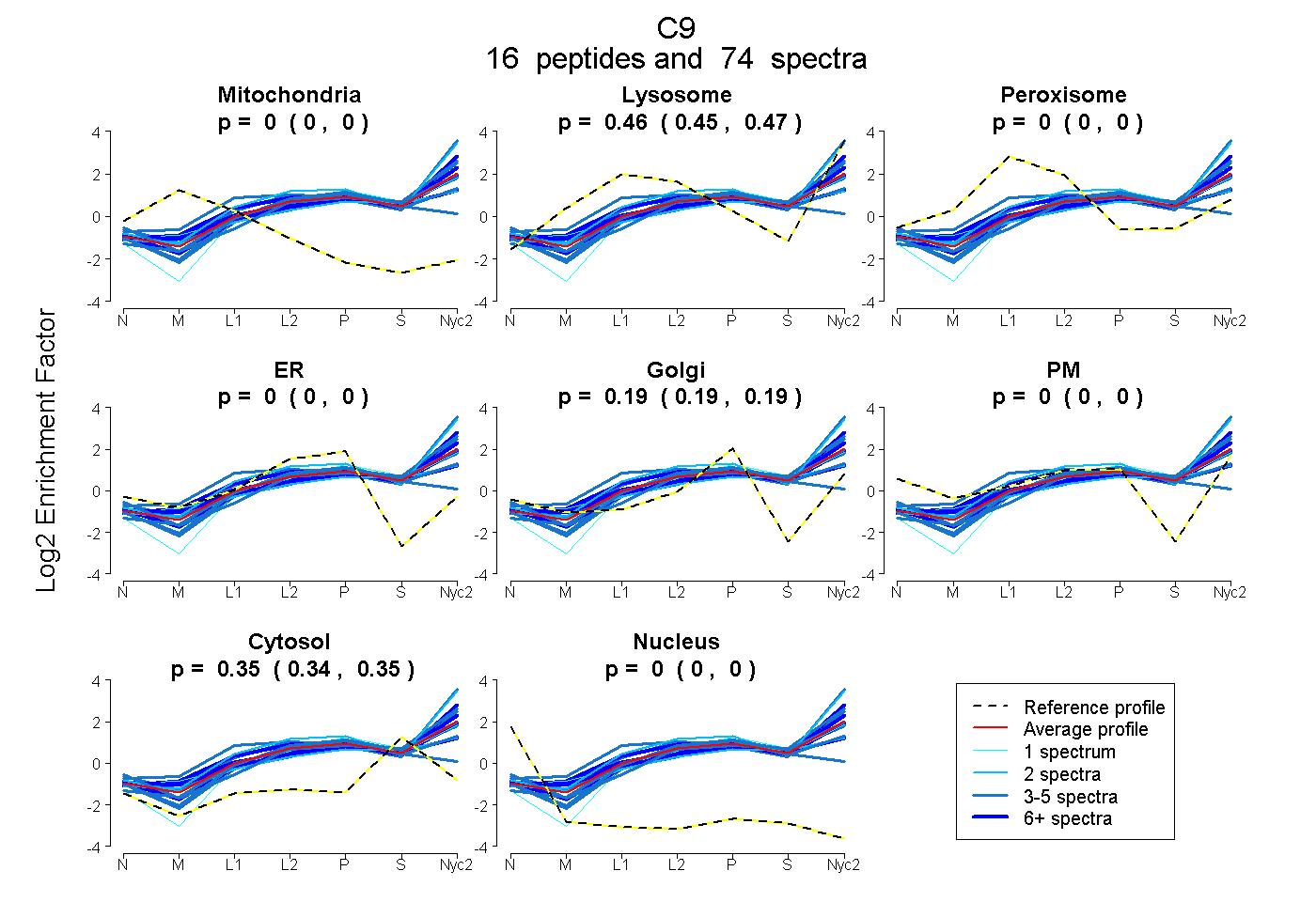
0.000 | 0.000
0.455 | 0.465
0.000 | 0.000
0.000 | 0.000
0.188 | 0.195
0.000 | 0.000
0.344 | 0.350
0.000 | 0.000
peptides
spectra
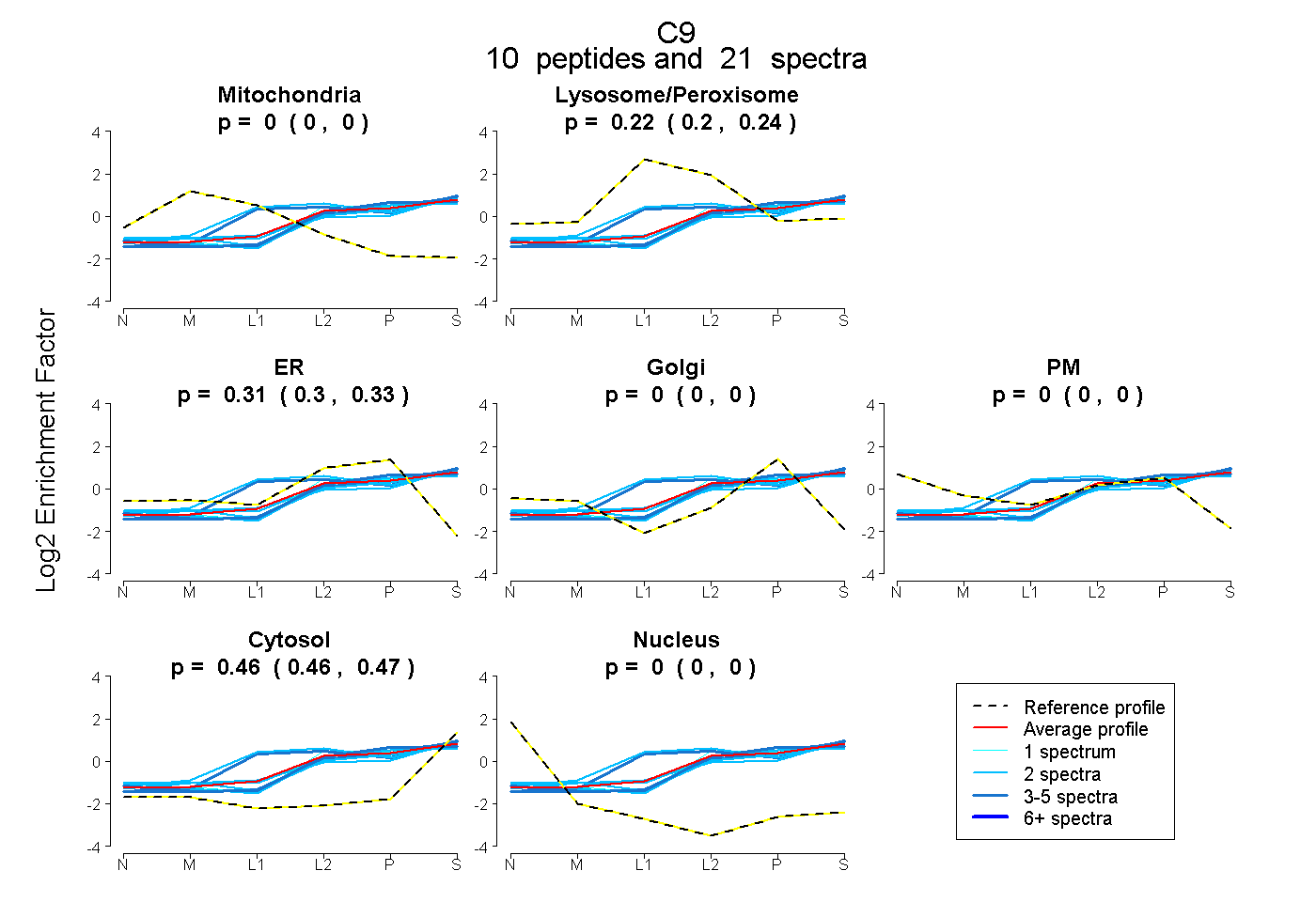
0.000 | 0.000
0.203 | 0.239
0.300 | 0.326
0.000 | 0.000
0.000 | 0.000
0.457 | 0.470
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
74 spectra |
 |
0.000 0.000 | 0.000 |
0.460 0.455 | 0.465 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.192 0.188 | 0.195 |
0.000 0.000 | 0.000 |
0.348 0.344 | 0.350 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
21 spectra |
 |
0.000 0.000 | 0.000 |
0.221 0.203 | 0.239 |
0.315 0.300 | 0.326 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.464 0.457 | 0.470 |
0.000 0.000 | 0.000 |
| 1 spectrum, LSPIYNLIPLTMK | 0.000 | 0.135 | 0.383 | 0.000 | 0.000 | 0.481 | 0.000 | |||
| 2 spectra, DGNTLTYYR | 0.000 | 0.174 | 0.390 | 0.020 | 0.000 | 0.416 | 0.000 | |||
| 2 spectra, SCADALGDR | 0.000 | 0.135 | 0.361 | 0.000 | 0.000 | 0.504 | 0.000 | |||
| 3 spectra, MFLHVR | 0.000 | 0.497 | 0.096 | 0.000 | 0.000 | 0.407 | 0.000 | |||
| 2 spectra, TTSFNANLALK | 0.000 | 0.523 | 0.120 | 0.000 | 0.000 | 0.357 | 0.000 | |||
| 3 spectra, GVMLTTTFLDDVK | 0.000 | 0.135 | 0.342 | 0.000 | 0.000 | 0.523 | 0.000 | |||
| 2 spectra, SIEVFGQFQGK | 0.000 | 0.104 | 0.418 | 0.000 | 0.000 | 0.478 | 0.000 | |||
| 1 spectrum, AIEDYVNEFSAR | 0.000 | 0.129 | 0.398 | 0.000 | 0.000 | 0.473 | 0.000 | |||
| 3 spectra, VVEESELGR | 0.000 | 0.113 | 0.418 | 0.000 | 0.000 | 0.469 | 0.000 | |||
| 2 spectra, GMIQLGR | 0.000 | 0.244 | 0.233 | 0.000 | 0.000 | 0.523 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
143 spectra |
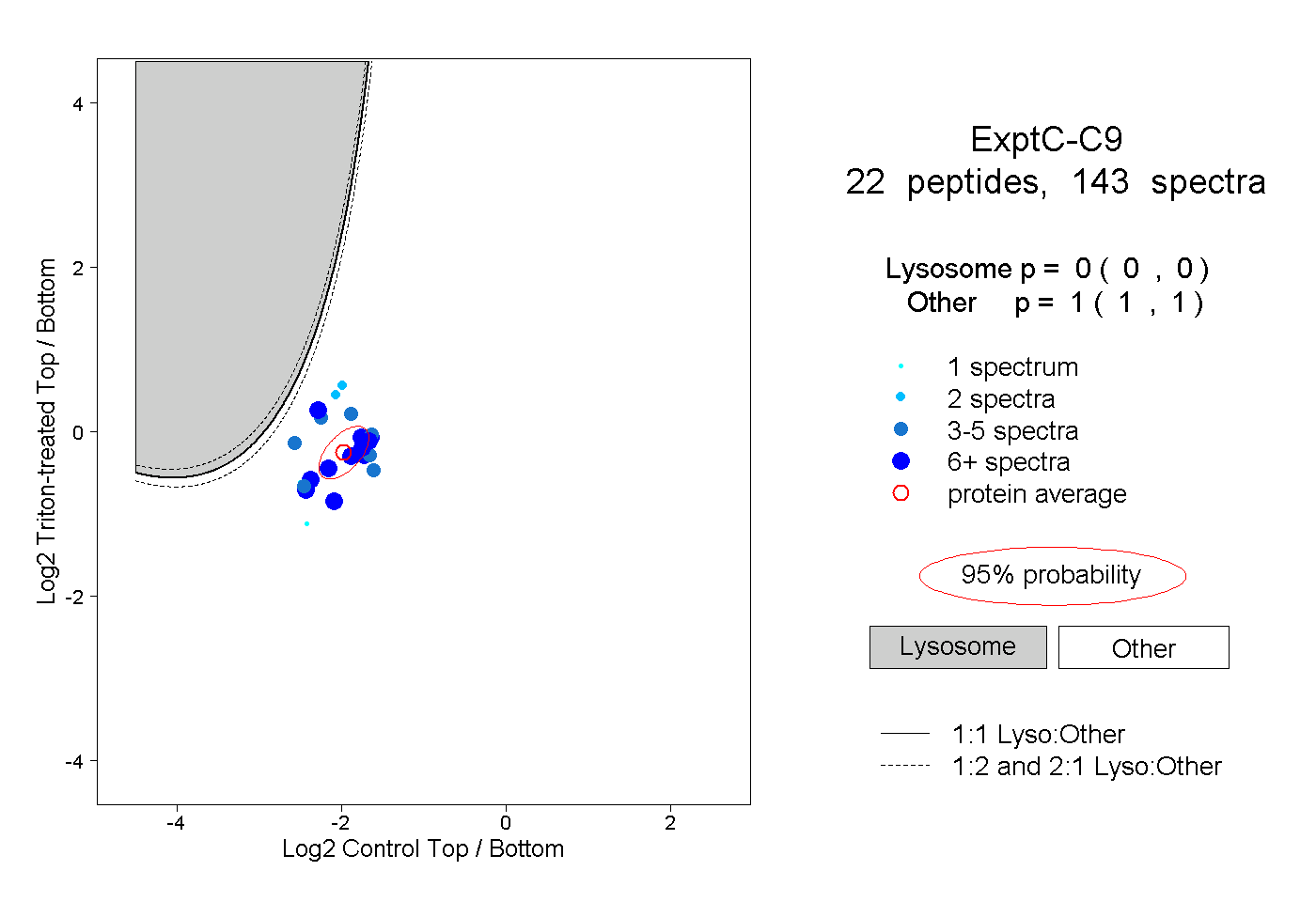 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
17 spectra |
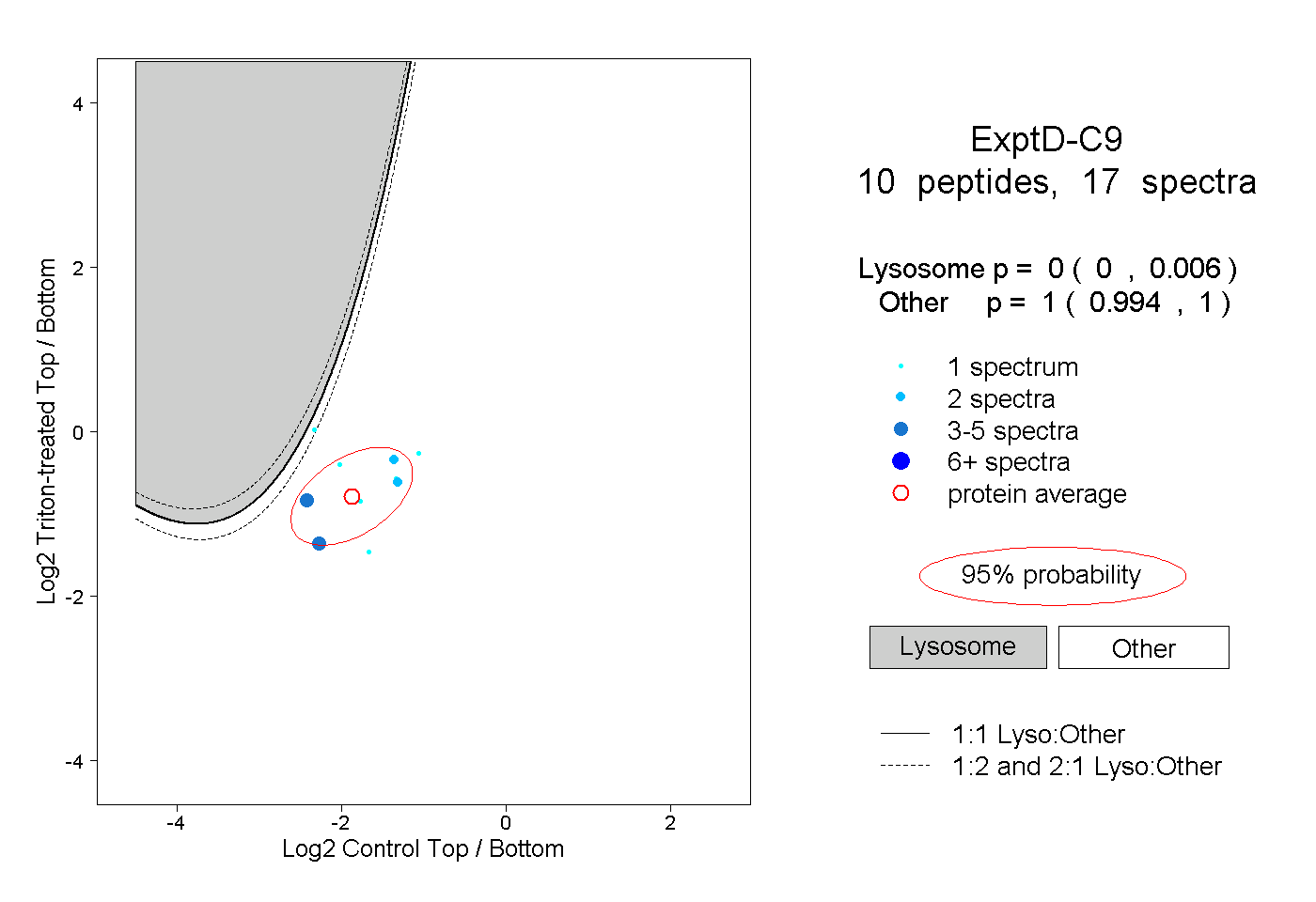 |
0.000 0.000 | 0.006 |
1.000 0.994 | 1.000 |