peptides
spectra
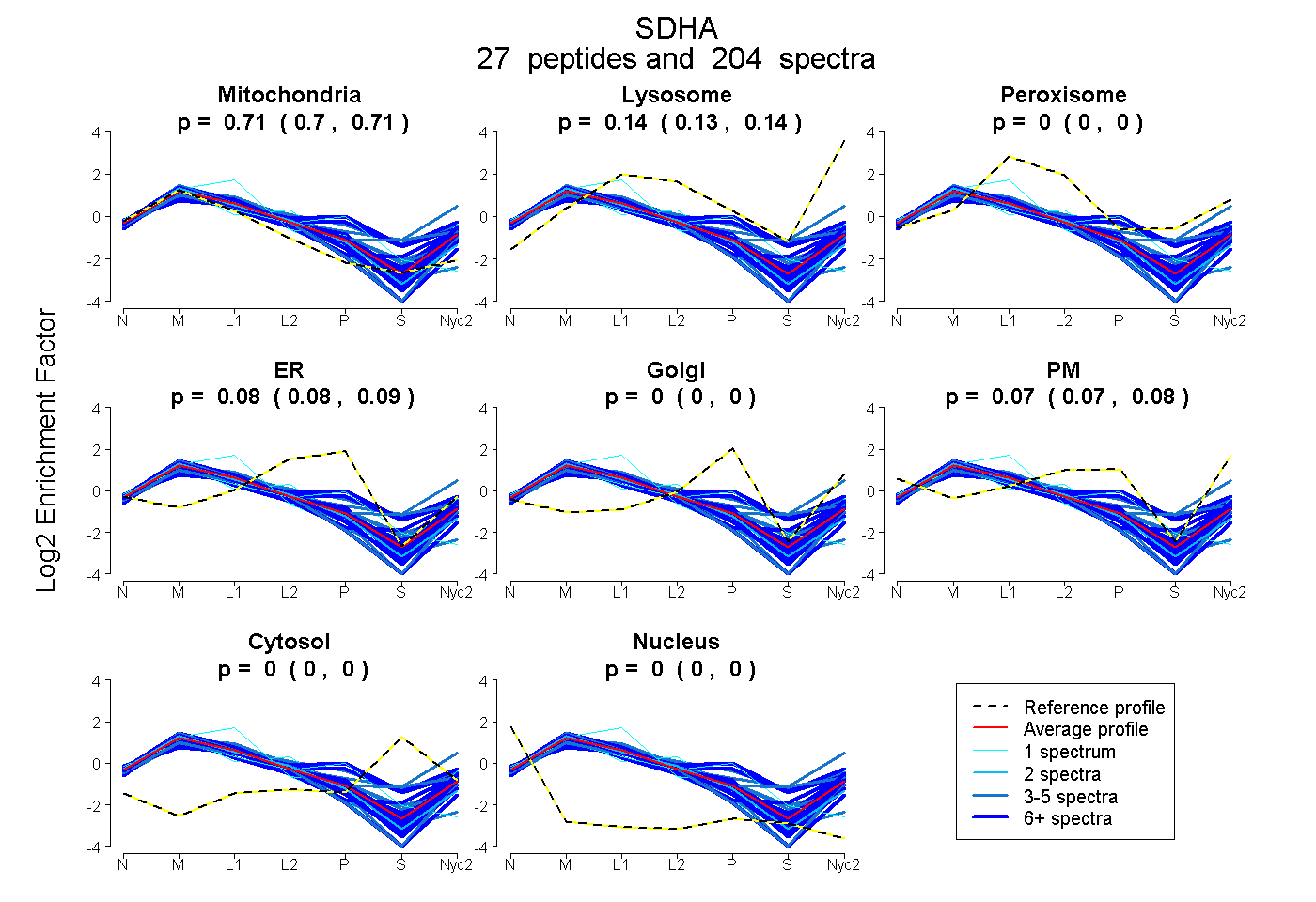
0.704 | 0.708
0.134 | 0.139
0.000 | 0.000
0.080 | 0.089
0.000 | 0.000
0.067 | 0.076
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
204 spectra |
 |
0.707 0.704 | 0.708 |
0.137 0.134 | 0.139 |
0.000 0.000 | 0.000 |
0.085 0.080 | 0.089 |
0.000 0.000 | 0.000 |
0.072 0.067 | 0.076 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 10 spectra, VSQLYGDLQHLK | 0.759 | 0.079 | 0.000 | 0.000 | 0.000 | 0.161 | 0.000 | 0.000 | ||
| 3 spectra, GGQAHR | 0.790 | 0.012 | 0.000 | 0.000 | 0.000 | 0.198 | 0.000 | 0.000 | ||
| 3 spectra, VGSVLQEGCEK | 0.536 | 0.099 | 0.200 | 0.000 | 0.037 | 0.000 | 0.127 | 0.000 | ||
| 1 spectrum, TYFSCTSAHTSTGDGTAMVTR | 0.678 | 0.227 | 0.000 | 0.000 | 0.000 | 0.095 | 0.000 | 0.000 | ||
| 18 spectra, SMQSHAAVFR | 0.443 | 0.000 | 0.299 | 0.000 | 0.238 | 0.000 | 0.020 | 0.000 | ||
| 12 spectra, WHFYDTVK | 0.669 | 0.112 | 0.000 | 0.017 | 0.000 | 0.202 | 0.000 | 0.000 | ||
| 3 spectra, HTLSYVDTK | 0.631 | 0.000 | 0.213 | 0.157 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 26 spectra, ANAGEESVMNLDK | 0.640 | 0.137 | 0.000 | 0.058 | 0.000 | 0.165 | 0.000 | 0.000 | ||
| 4 spectra, VSDAISTQYPVVDHEFDAVVVGAGGAGLR | 0.819 | 0.086 | 0.000 | 0.000 | 0.000 | 0.095 | 0.000 | 0.000 | ||
| 14 spectra, KPFAEHWR | 0.726 | 0.153 | 0.000 | 0.010 | 0.000 | 0.110 | 0.000 | 0.000 | ||
| 3 spectra, ACALSIAESCRPGDK | 0.920 | 0.000 | 0.001 | 0.079 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 14 spectra, NTIIATGGYGR | 0.734 | 0.214 | 0.000 | 0.000 | 0.000 | 0.000 | 0.053 | 0.000 | ||
| 2 spectra, YAPVAK | 0.758 | 0.063 | 0.000 | 0.169 | 0.000 | 0.010 | 0.000 | 0.000 | ||
| 17 spectra, FADGSVR | 0.669 | 0.162 | 0.088 | 0.006 | 0.000 | 0.075 | 0.000 | 0.000 | ||
| 1 spectrum, TLNEADCATVPPAIR | 0.670 | 0.000 | 0.000 | 0.330 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, IDEYDYSKPIEGQQK | 0.742 | 0.048 | 0.000 | 0.188 | 0.000 | 0.023 | 0.000 | 0.000 | ||
| 7 spectra, SMTLEIR | 0.713 | 0.030 | 0.000 | 0.211 | 0.000 | 0.047 | 0.000 | 0.000 | ||
| 5 spectra, AAFGLSEAGFNTACLTK | 0.675 | 0.000 | 0.172 | 0.008 | 0.145 | 0.000 | 0.000 | 0.000 | ||
| 11 spectra, GEGGILINSQGER | 0.768 | 0.042 | 0.000 | 0.031 | 0.000 | 0.159 | 0.000 | 0.000 | ||
| 4 spectra, LPGISETAMIFAGVDVTK | 0.705 | 0.141 | 0.000 | 0.000 | 0.056 | 0.098 | 0.000 | 0.000 | ||
| 7 spectra, VTLDYRPVIDK | 0.715 | 0.099 | 0.000 | 0.061 | 0.000 | 0.126 | 0.000 | 0.000 | ||
| 4 spectra, GVIALCIEDGSIHR | 0.411 | 0.044 | 0.311 | 0.000 | 0.192 | 0.000 | 0.042 | 0.000 | ||
| 9 spectra, TGHSLLHTLYGR | 0.364 | 0.000 | 0.294 | 0.000 | 0.320 | 0.000 | 0.022 | 0.000 | ||
| 1 spectrum, EPIPVLPTVHYNMGGIPTNYK | 0.818 | 0.141 | 0.000 | 0.000 | 0.000 | 0.042 | 0.000 | 0.000 | ||
| 7 spectra, LGANSLLDLVVFGR | 0.881 | 0.019 | 0.000 | 0.052 | 0.000 | 0.048 | 0.000 | 0.000 | ||
| 14 spectra, AFGGQSLK | 0.684 | 0.120 | 0.000 | 0.068 | 0.000 | 0.128 | 0.000 | 0.000 | ||
| 3 spectra, DHVYLQLHHLPPEQLATR | 0.448 | 0.342 | 0.000 | 0.000 | 0.000 | 0.096 | 0.114 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
126 spectra |
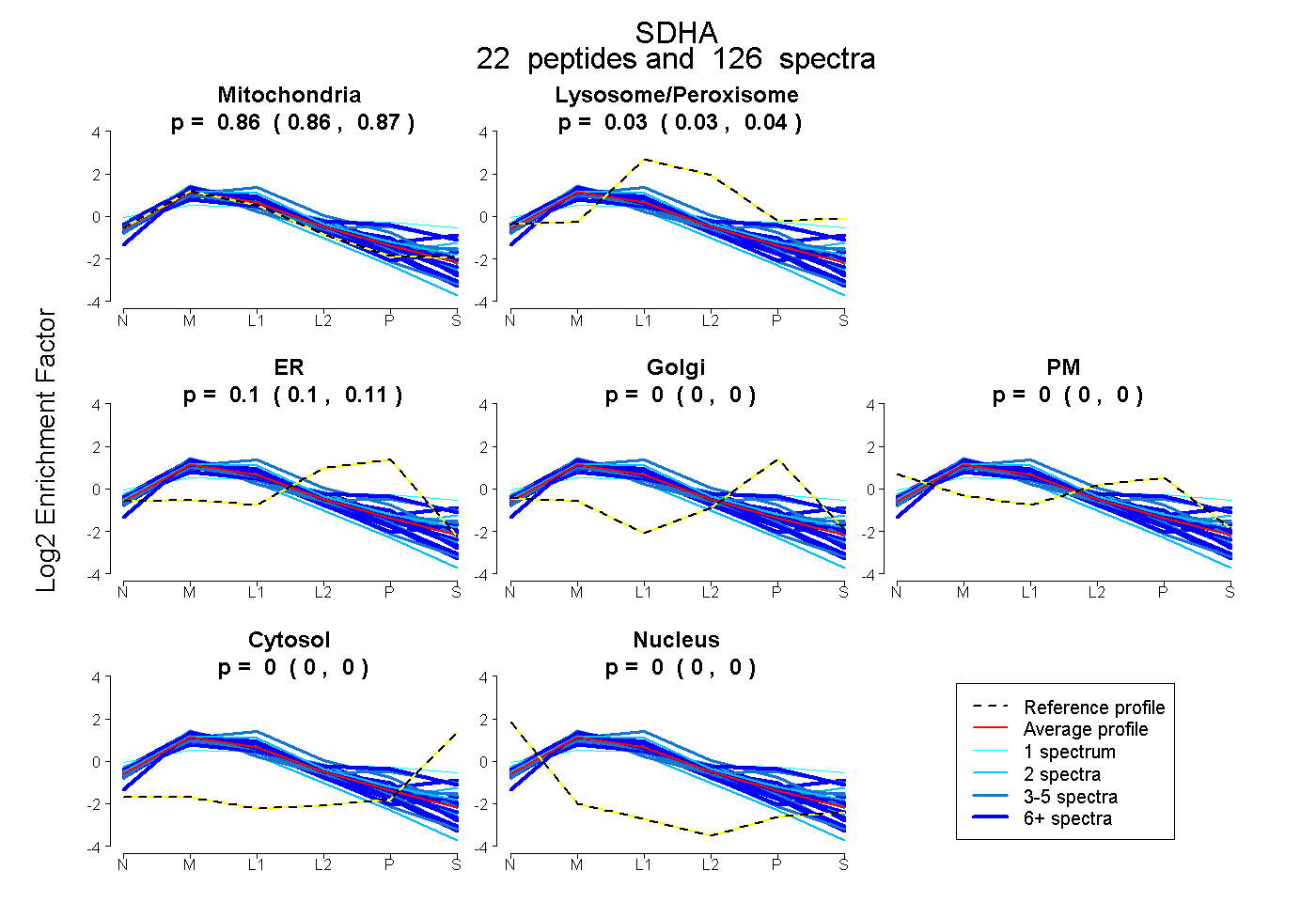 |
0.864 0.860 | 0.868 |
0.034 0.030 | 0.038 |
0.101 0.097 | 0.105 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
943 spectra |
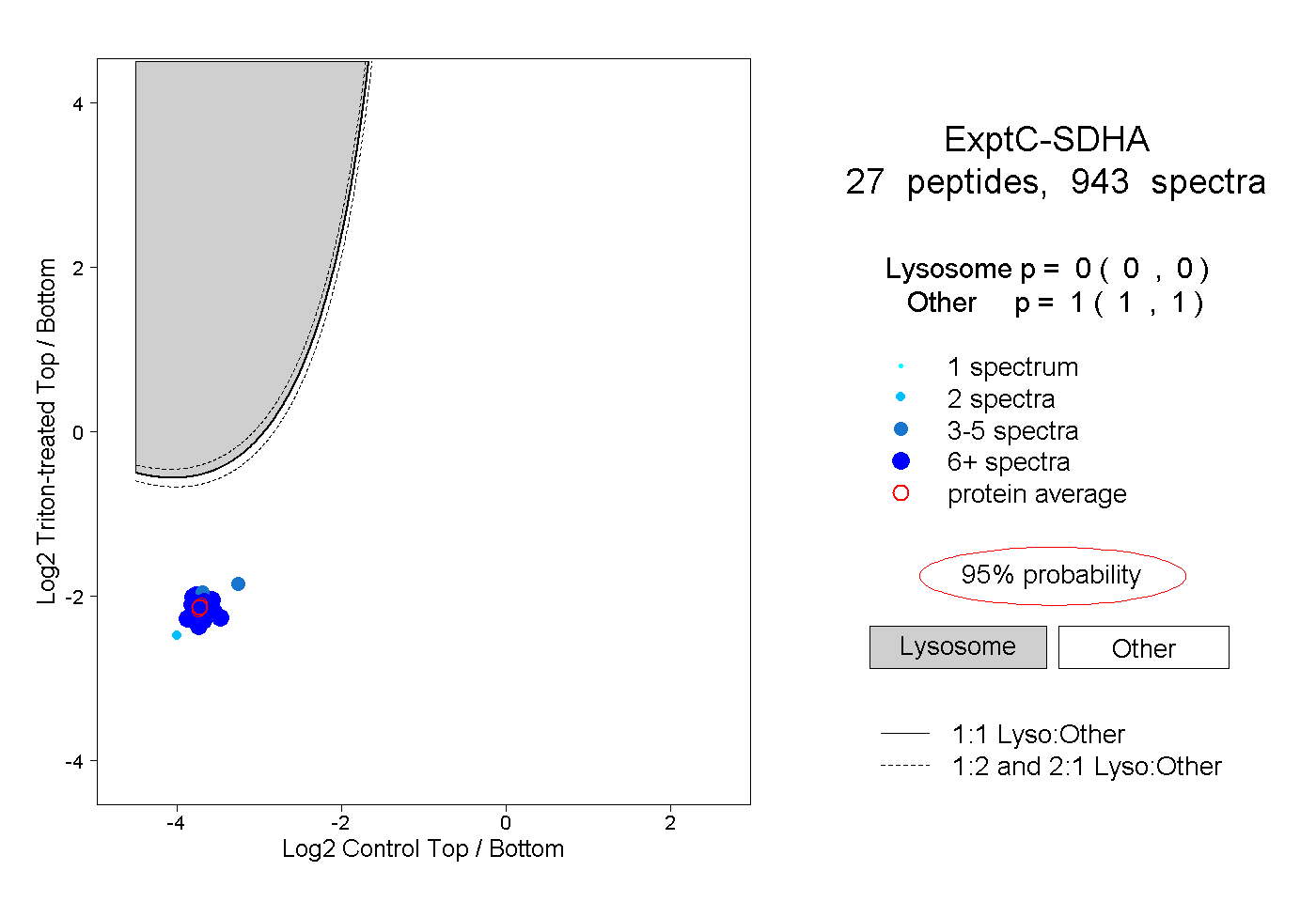 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
61 spectra |
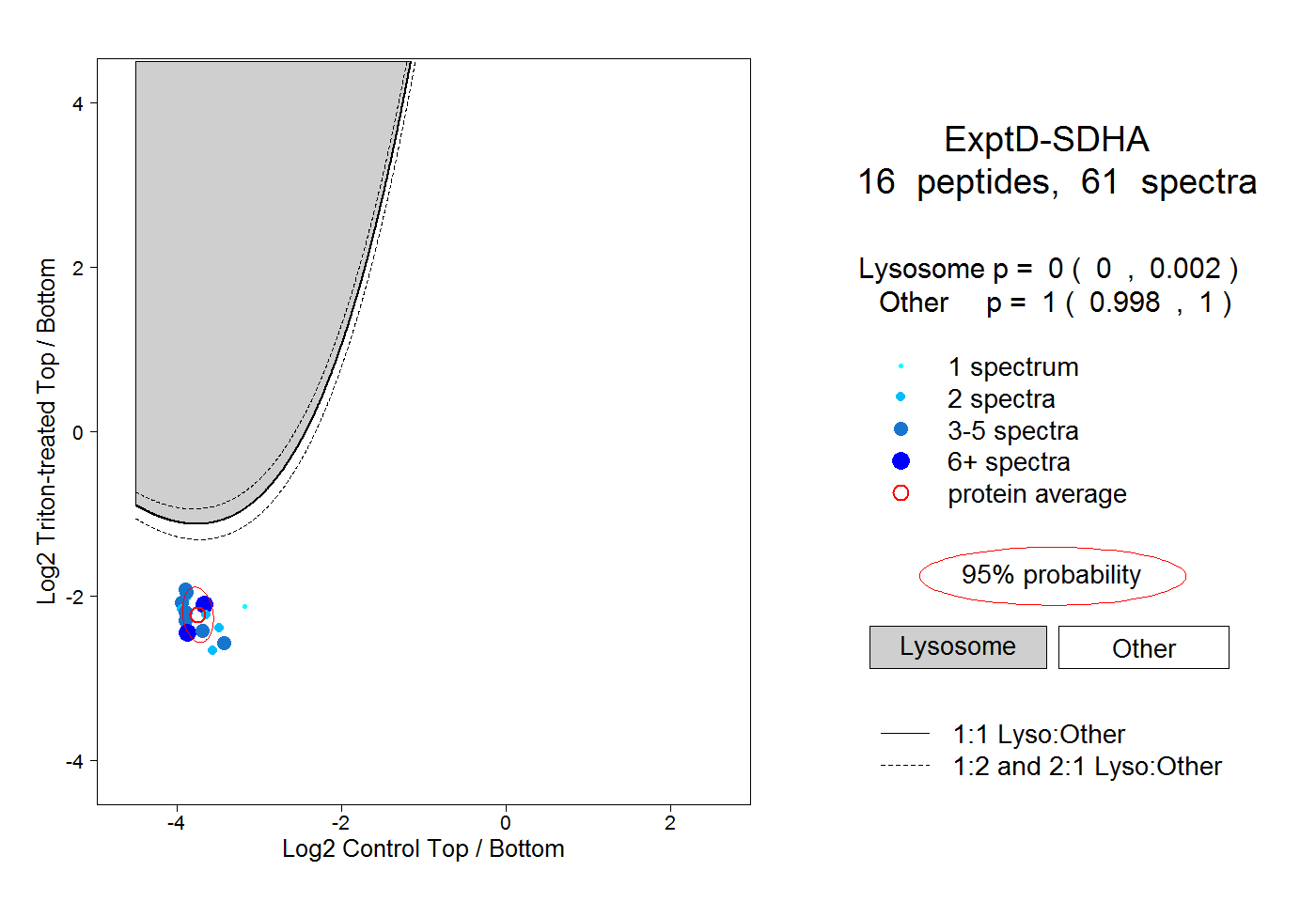 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |