peptides
spectra
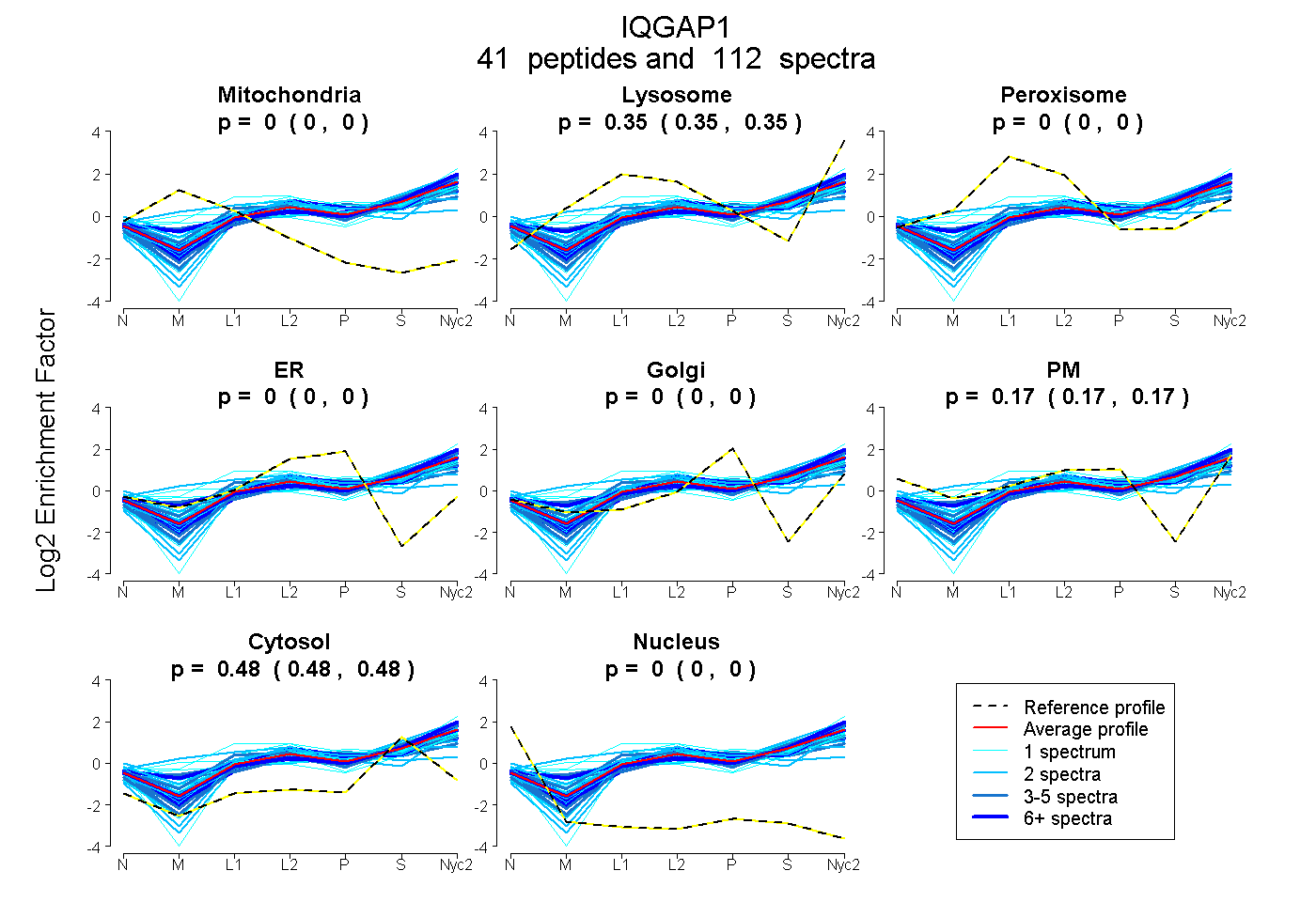
0.000 | 0.000
0.345 | 0.350
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.168 | 0.172
0.481 | 0.484
0.000 | 0.000
peptides
spectra
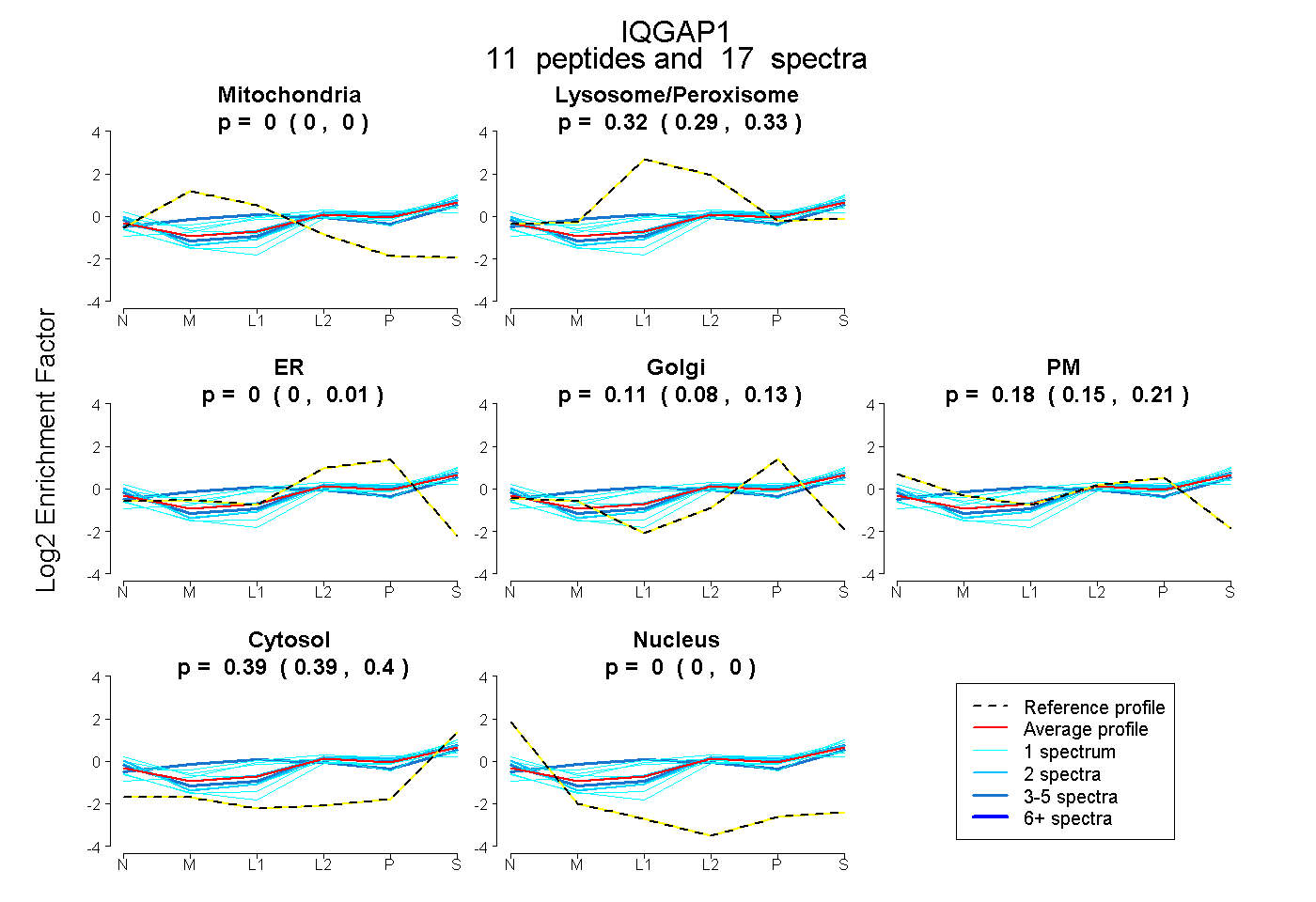
0.000 | 0.000
0.291 | 0.331
0.000 | 0.015
0.076 | 0.127
0.149 | 0.212
0.386 | 0.403
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
112 spectra |
 |
0.000 0.000 | 0.000 |
0.348 0.345 | 0.350 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.170 0.168 | 0.172 |
0.482 0.481 | 0.484 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
17 spectra |
 |
0.000 0.000 | 0.000 |
0.316 0.291 | 0.331 |
0.000 0.000 | 0.015 |
0.106 0.076 | 0.127 |
0.184 0.149 | 0.212 |
0.394 0.386 | 0.403 |
0.000 0.000 | 0.000 |
| 1 spectrum, IQAFIR | 0.000 | 0.195 | 0.065 | 0.000 | 0.301 | 0.438 | 0.000 | |||
| 1 spectrum, EQLWLANEGLITK | 0.000 | 0.343 | 0.000 | 0.000 | 0.314 | 0.343 | 0.000 | |||
| 2 spectra, IIGNLLYYR | 0.000 | 0.201 | 0.082 | 0.000 | 0.312 | 0.406 | 0.000 | |||
| 3 spectra, ALQSVALGLR | 0.000 | 0.243 | 0.066 | 0.000 | 0.265 | 0.426 | 0.000 | |||
| 1 spectrum, DHINDIIK | 0.000 | 0.481 | 0.000 | 0.242 | 0.022 | 0.256 | 0.000 | |||
| 1 spectrum, GVLLEIEDLQANQFK | 0.000 | 0.477 | 0.000 | 0.059 | 0.000 | 0.464 | 0.000 | |||
| 1 spectrum, FPDAAEDELLK | 0.000 | 0.156 | 0.327 | 0.000 | 0.000 | 0.516 | 0.000 | |||
| 2 spectra, LEGVLPEVAQHYQDTLIR | 0.000 | 0.344 | 0.000 | 0.111 | 0.148 | 0.397 | 0.000 | |||
| 1 spectrum, LQSIAR | 0.000 | 0.209 | 0.000 | 0.021 | 0.480 | 0.290 | 0.000 | |||
| 3 spectra, ATGLHFR | 0.031 | 0.435 | 0.000 | 0.068 | 0.110 | 0.356 | 0.000 | |||
| 1 spectrum, LTAEEMDER | 0.000 | 0.092 | 0.287 | 0.000 | 0.028 | 0.593 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
129 spectra |
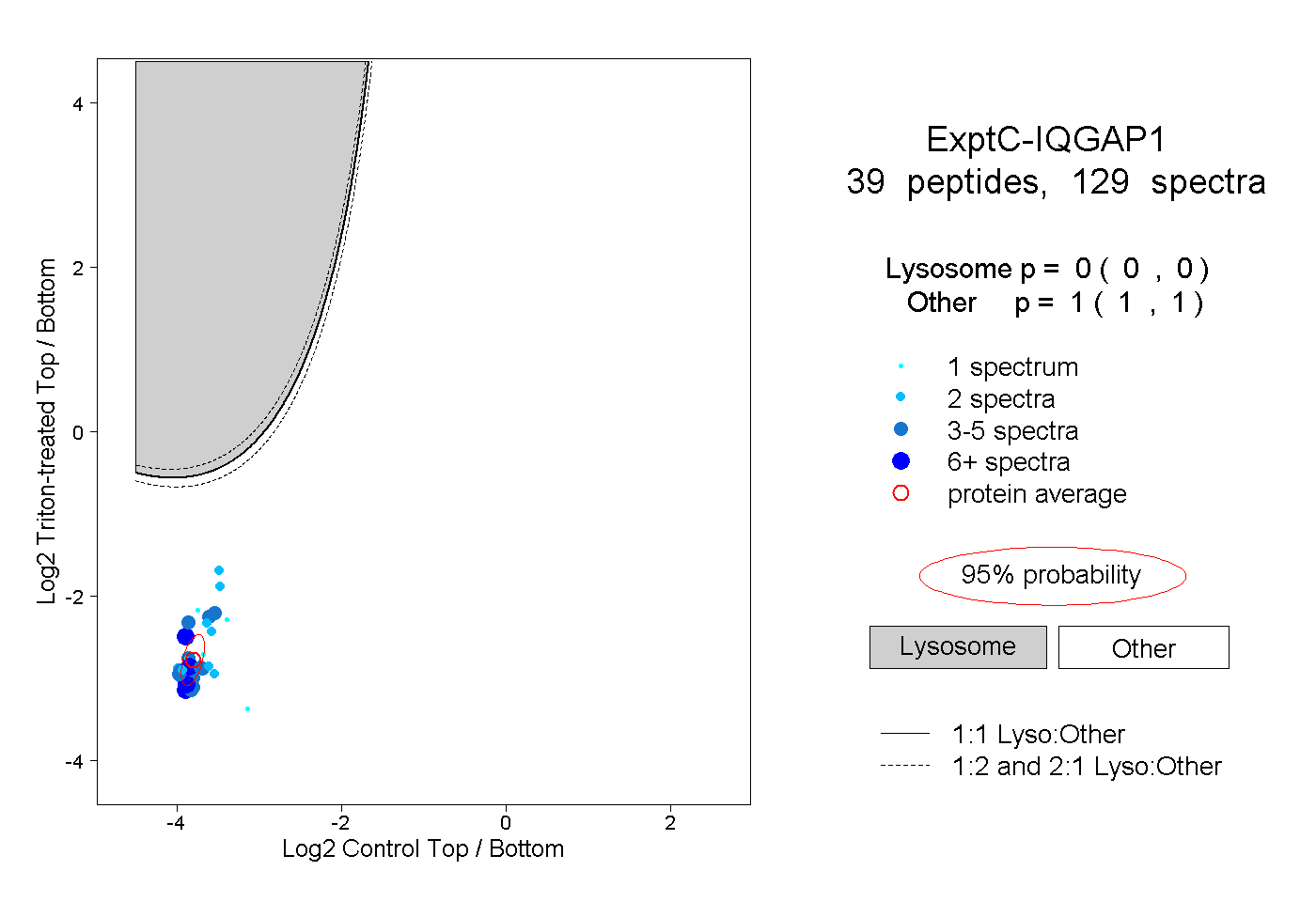 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
10 spectra |
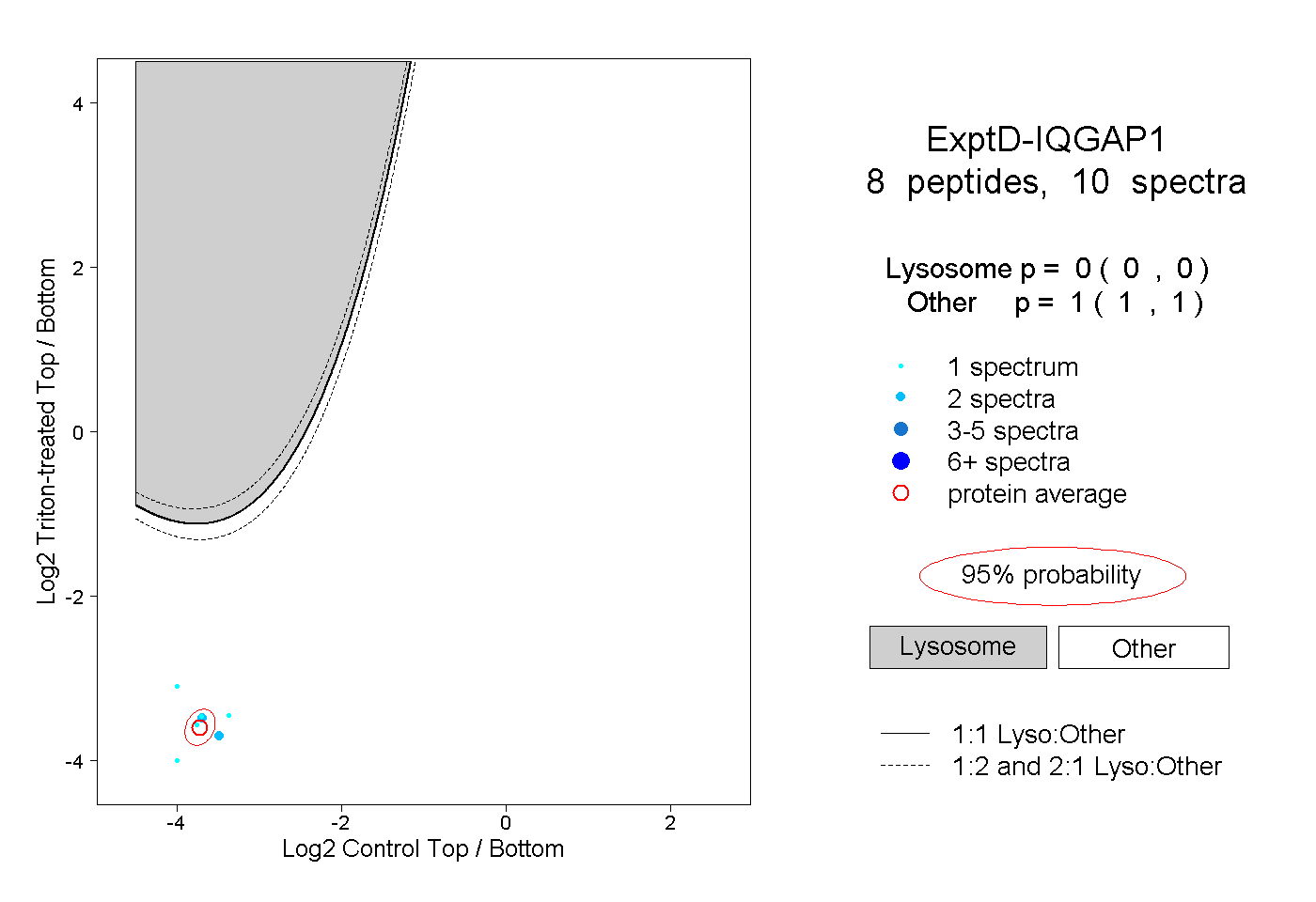 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |