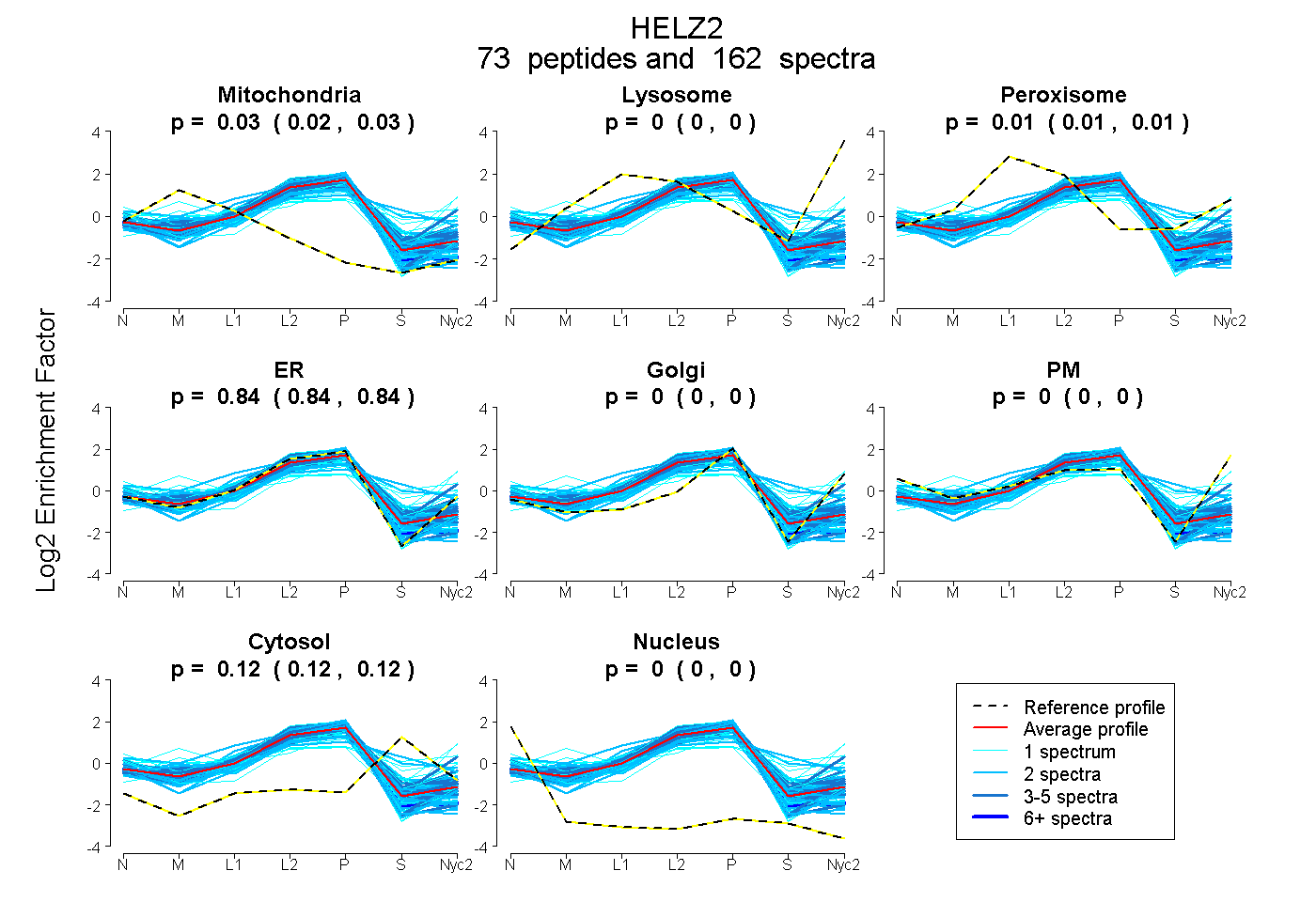
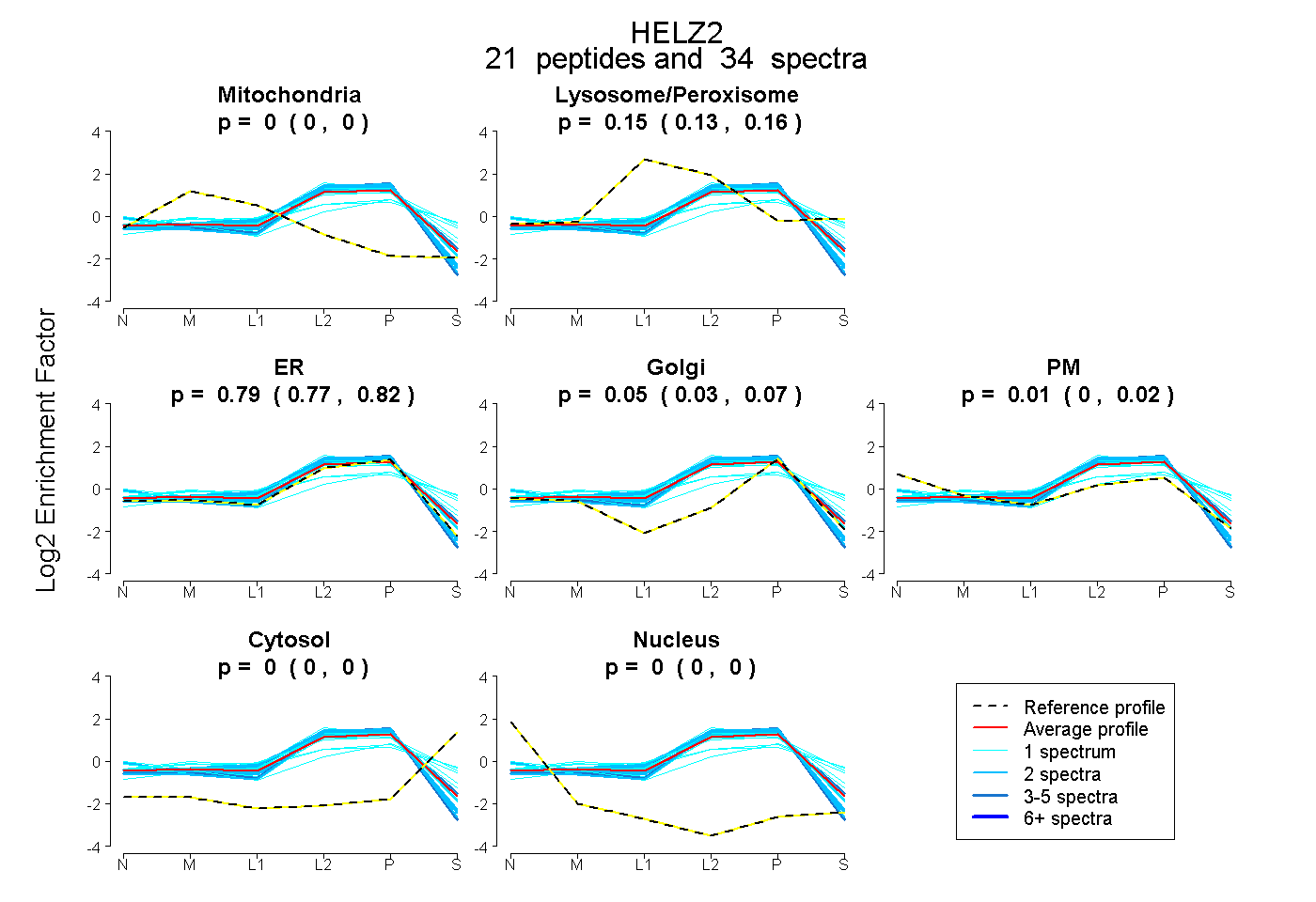
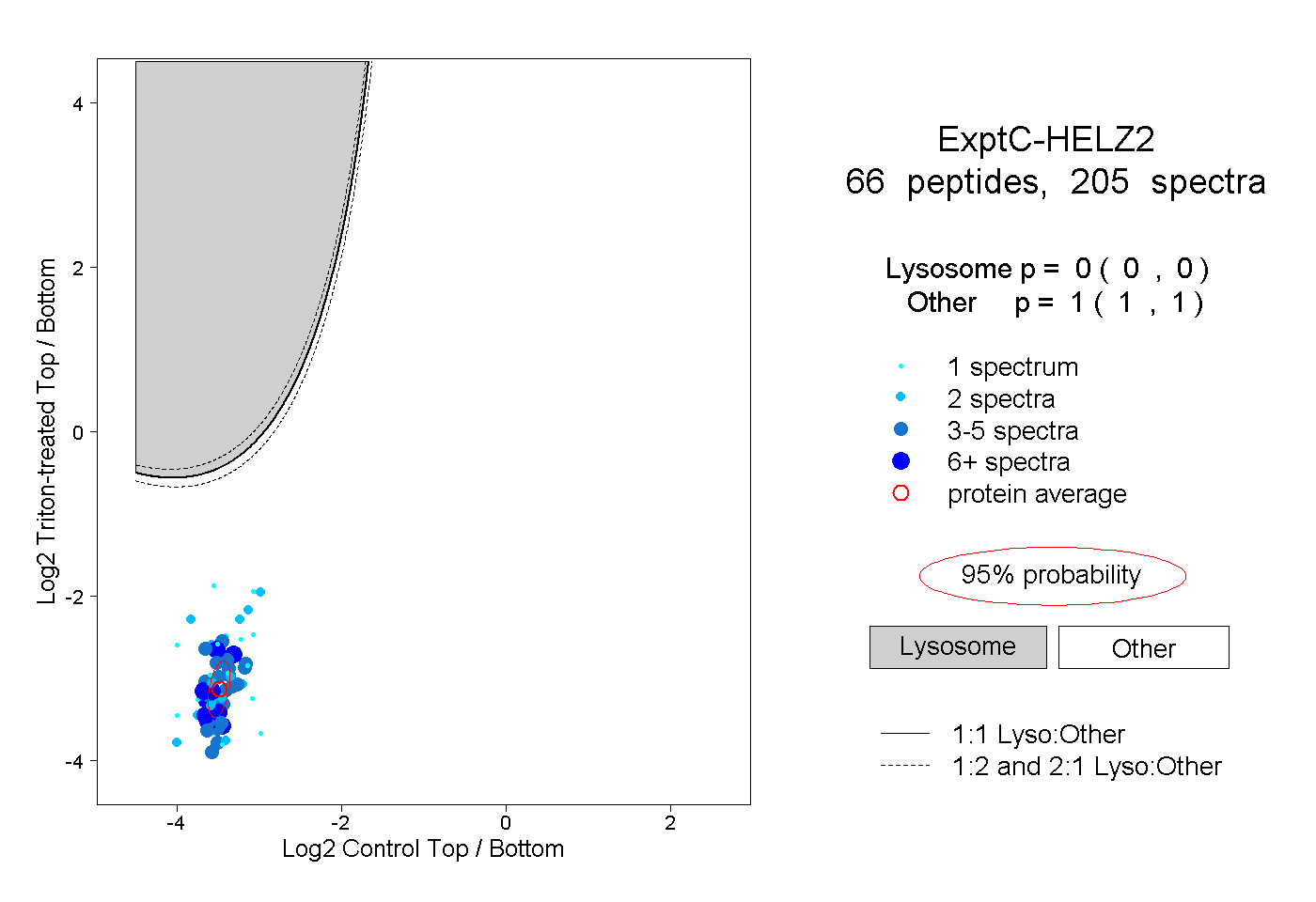
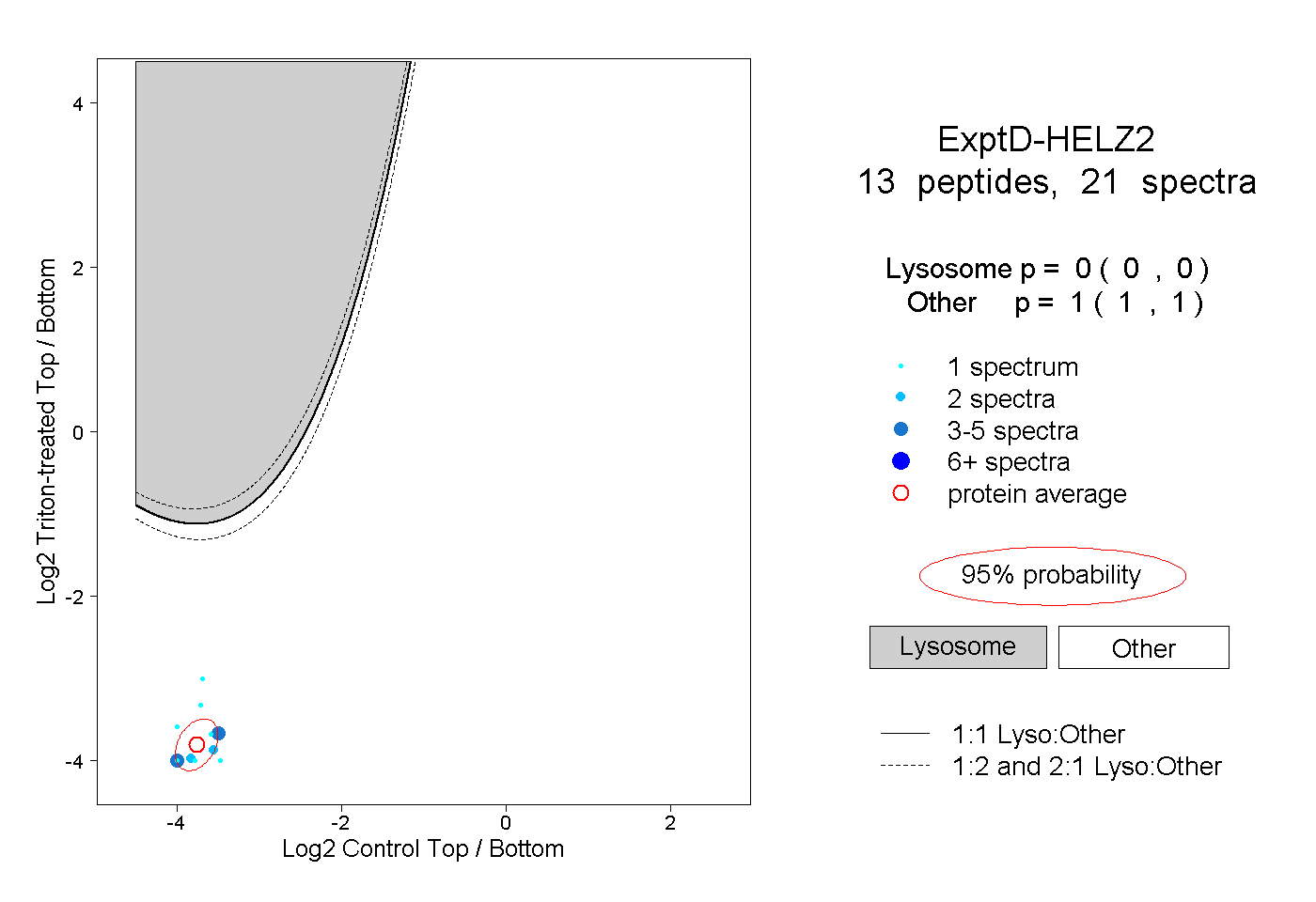
| 9 spectra, VLFPINR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, QAFRPPTFPELLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LLVSTEEGNENSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LFSVPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, APPMGLSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ISQEGRPNQSLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, QLTLDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VAEFLVGDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LILLALGHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LQTPADTIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LLVLLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, ANPEEVTEVVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, STAAIINFVSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GAMLTGPPGTGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FTVEVLSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YVIVSTVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, DDLLVYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, TYSVQASK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, HIPPLLIYGPFGTGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, SDMDQRPTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, QVQLAAGTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ALATPLDDMASSPIQVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, IFVAGLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GVTGVTVTSITK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QQLDSVFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LGFVVDVETGAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QYINLPSSALR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, IVFHENYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DAIMLDTQYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SIPGSLLGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QAPNPYAAEIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, FAPSIVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LFAVGIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, RPVLLQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, AAATAQTEAVAAGGTAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LFLYYQQEVHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, VMGVLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, WQPTPSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, AEQLDGLQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VLNTVMTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, VVLAGDHMQVTPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, TQPQNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, DIDGLCQDFSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GNPIQASGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, RPEGSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, QLPDLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LNQSQDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, QLRPVVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GQVSLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, VVLLGDHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, HPGAGLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SVDVLGGLLLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, HFYVAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VDLHLGCSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, EQAAWQDGLVPYQAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, AQDMELR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LVVTTTSQAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VQEIYNTWPHCWGPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, DGALDVEAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QFVEVRPLPQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, AHTPDPASVSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, ELAFVCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, VPEEVLRPSTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VMYADRPPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, ELLDESR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VGLRPSFPIPVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |