peptides
spectra
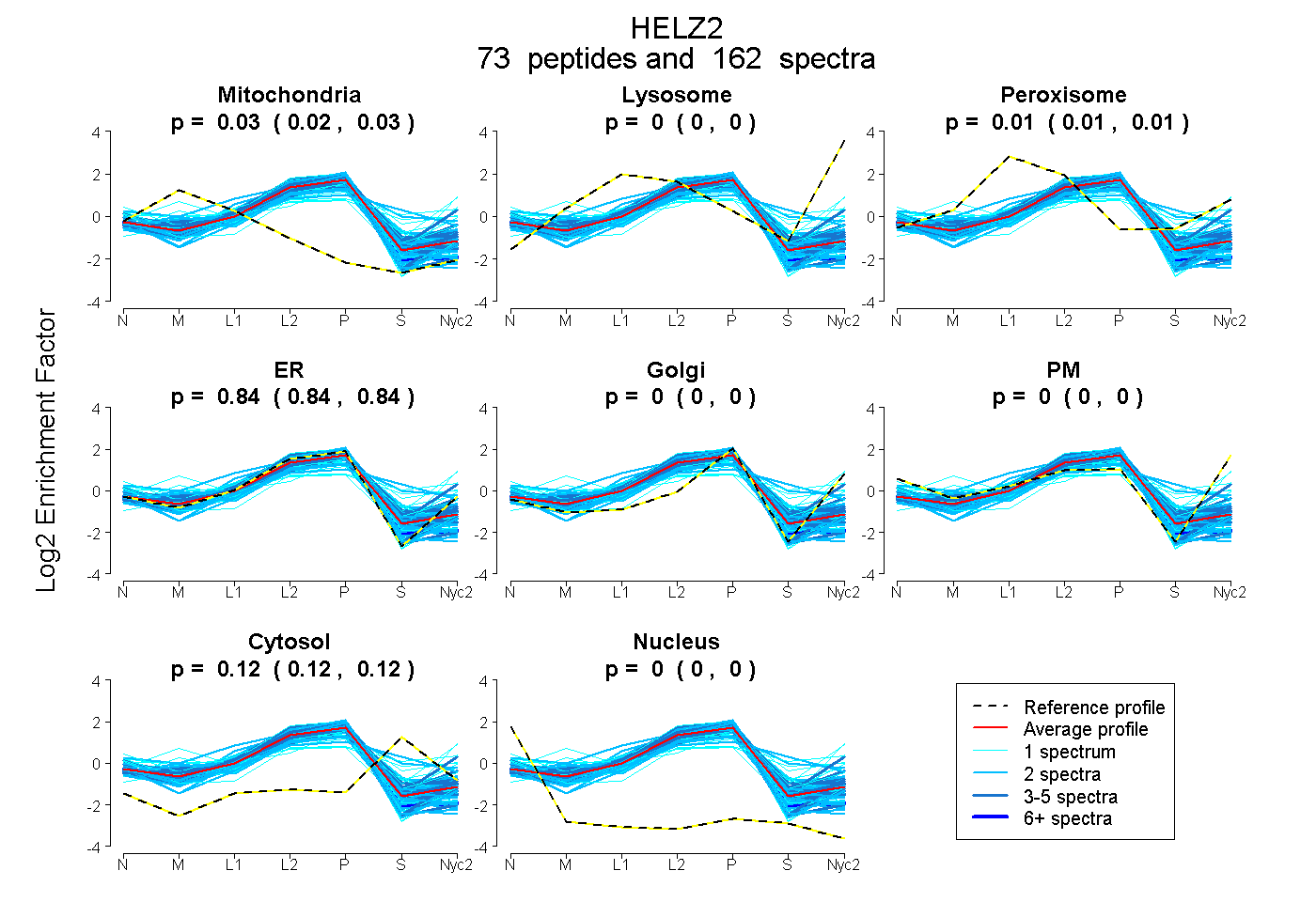
0.024 | 0.028
0.000 | 0.000
0.009 | 0.013
0.838 | 0.841
0.000 | 0.000
0.000 | 0.000
0.122 | 0.124
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
162 spectra |
 |
0.026 0.024 | 0.028 |
0.000 0.000 | 0.000 |
0.011 0.009 | 0.013 |
0.839 0.838 | 0.841 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.123 0.122 | 0.124 |
0.000 0.000 | 0.000 |
| 2 spectra, QQGTVFYAPSR | 0.031 | 0.000 | 0.000 | 0.942 | 0.000 | 0.000 | 0.000 | 0.027 | ||
| 2 spectra, QYACAQSYQR | 0.052 | 0.000 | 0.000 | 0.849 | 0.000 | 0.000 | 0.077 | 0.022 | ||
| 4 spectra, VLFPINR | 0.021 | 0.000 | 0.000 | 0.979 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, QAFRPPTFPELLR | 0.000 | 0.000 | 0.000 | 0.875 | 0.000 | 0.000 | 0.125 | 0.000 | ||
| 3 spectra, LLVSTEEGNENSR | 0.077 | 0.000 | 0.000 | 0.792 | 0.000 | 0.000 | 0.132 | 0.000 | ||
| 4 spectra, LFSVPR | 0.005 | 0.000 | 0.011 | 0.922 | 0.000 | 0.000 | 0.062 | 0.000 | ||
| 4 spectra, ISQEGRPNQSLR | 0.036 | 0.000 | 0.080 | 0.712 | 0.000 | 0.000 | 0.172 | 0.000 | ||
| 4 spectra, QLTLDR | 0.000 | 0.000 | 0.035 | 0.771 | 0.000 | 0.000 | 0.194 | 0.000 | ||
| 1 spectrum, ASSEHALWLLLPAR | 0.250 | 0.173 | 0.000 | 0.226 | 0.180 | 0.171 | 0.000 | 0.000 | ||
| 2 spectra, DVAVLTPYNAQAAAISR | 0.000 | 0.000 | 0.000 | 0.872 | 0.000 | 0.000 | 0.072 | 0.057 | ||
| 2 spectra, EILLAR | 0.000 | 0.000 | 0.000 | 0.920 | 0.000 | 0.000 | 0.066 | 0.013 | ||
| 1 spectrum, LGGPCVLYCGPSNK | 0.059 | 0.000 | 0.000 | 0.682 | 0.000 | 0.000 | 0.259 | 0.000 | ||
| 2 spectra, RPPSLLGHVGK | 0.181 | 0.000 | 0.000 | 0.746 | 0.000 | 0.000 | 0.013 | 0.060 | ||
| 2 spectra, CTEYLNESTYILR | 0.000 | 0.000 | 0.000 | 0.875 | 0.000 | 0.000 | 0.047 | 0.077 | ||
| 2 spectra, LQTPADTIR | 0.000 | 0.000 | 0.000 | 0.863 | 0.000 | 0.000 | 0.137 | 0.000 | ||
| 3 spectra, LLVLLK | 0.029 | 0.000 | 0.000 | 0.918 | 0.000 | 0.000 | 0.052 | 0.000 | ||
| 2 spectra, HQISWPR | 0.092 | 0.000 | 0.189 | 0.720 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, ANPEEVTEVVR | 0.000 | 0.000 | 0.027 | 0.808 | 0.000 | 0.000 | 0.165 | 0.000 | ||
| 2 spectra, STAAIINFVSR | 0.018 | 0.000 | 0.000 | 0.925 | 0.000 | 0.000 | 0.000 | 0.057 | ||
| 4 spectra, YVIVSTVR | 0.000 | 0.000 | 0.044 | 0.852 | 0.000 | 0.000 | 0.104 | 0.000 | ||
| 1 spectrum, HICAVSHGAQVSALR | 0.175 | 0.000 | 0.060 | 0.722 | 0.000 | 0.000 | 0.043 | 0.000 | ||
| 1 spectrum, TYSVQASK | 0.067 | 0.000 | 0.000 | 0.933 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, STSTSTTNGLSLAELCAK | 0.000 | 0.000 | 0.105 | 0.254 | 0.021 | 0.587 | 0.034 | 0.000 | ||
| 1 spectrum, SDMDQRPTK | 0.160 | 0.000 | 0.059 | 0.588 | 0.000 | 0.000 | 0.193 | 0.000 | ||
| 4 spectra, QVQLAAGTR | 0.148 | 0.000 | 0.000 | 0.852 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, ALATPLDDMASSPIQVR | 0.000 | 0.000 | 0.000 | 0.942 | 0.000 | 0.000 | 0.058 | 0.000 | ||
| 2 spectra, CSFLQETFER | 0.000 | 0.000 | 0.076 | 0.817 | 0.000 | 0.000 | 0.107 | 0.000 | ||
| 2 spectra, LAVGLIAGR | 0.000 | 0.000 | 0.000 | 0.855 | 0.000 | 0.000 | 0.107 | 0.038 | ||
| 2 spectra, EVEHTCSR | 0.000 | 0.000 | 0.003 | 0.709 | 0.000 | 0.000 | 0.288 | 0.000 | ||
| 2 spectra, LGFVVDVETGAR | 0.000 | 0.000 | 0.001 | 0.840 | 0.000 | 0.000 | 0.159 | 0.000 | ||
| 4 spectra, QYINLPSSALR | 0.084 | 0.000 | 0.046 | 0.773 | 0.000 | 0.000 | 0.096 | 0.000 | ||
| 1 spectrum, IVFHENYR | 0.000 | 0.000 | 0.179 | 0.601 | 0.000 | 0.031 | 0.189 | 0.000 | ||
| 2 spectra, DAIMLDTQYR | 0.000 | 0.000 | 0.028 | 0.803 | 0.000 | 0.000 | 0.169 | 0.000 | ||
| 1 spectrum, YHSEIDMAASHR | 0.000 | 0.000 | 0.022 | 0.195 | 0.000 | 0.386 | 0.396 | 0.000 | ||
| 3 spectra, SIPGSLLGR | 0.042 | 0.000 | 0.000 | 0.951 | 0.000 | 0.000 | 0.000 | 0.007 | ||
| 1 spectrum, TSWLNSAEVTQVVEK | 0.021 | 0.000 | 0.000 | 0.886 | 0.000 | 0.000 | 0.044 | 0.049 | ||
| 4 spectra, QAPNPYAAEIR | 0.000 | 0.000 | 0.000 | 0.880 | 0.000 | 0.000 | 0.118 | 0.001 | ||
| 2 spectra, FAPSIVR | 0.001 | 0.000 | 0.000 | 0.860 | 0.000 | 0.000 | 0.109 | 0.030 | ||
| 2 spectra, RPVLLQK | 0.085 | 0.000 | 0.000 | 0.842 | 0.000 | 0.000 | 0.000 | 0.073 | ||
| 1 spectrum, HSVILCTCSCAASGSLK | 0.000 | 0.030 | 0.205 | 0.219 | 0.327 | 0.000 | 0.219 | 0.000 | ||
| 2 spectra, VMGVLK | 0.000 | 0.000 | 0.090 | 0.556 | 0.000 | 0.000 | 0.354 | 0.000 | ||
| 2 spectra, WQPTPSR | 0.000 | 0.000 | 0.064 | 0.803 | 0.000 | 0.000 | 0.132 | 0.000 | ||
| 3 spectra, VVLAGDHMQVTPR | 0.000 | 0.061 | 0.114 | 0.530 | 0.229 | 0.000 | 0.067 | 0.000 | ||
| 1 spectrum, VLNTVMTR | 0.033 | 0.000 | 0.000 | 0.967 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, AEQLDGLQR | 0.177 | 0.000 | 0.000 | 0.804 | 0.000 | 0.000 | 0.000 | 0.019 | ||
| 2 spectra, DIDGLCQDFSR | 0.039 | 0.000 | 0.000 | 0.924 | 0.000 | 0.000 | 0.037 | 0.000 | ||
| 1 spectrum, GNPIQASGK | 0.070 | 0.000 | 0.000 | 0.930 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, QELQEWVQR | 0.000 | 0.000 | 0.000 | 0.916 | 0.000 | 0.000 | 0.016 | 0.068 | ||
| 1 spectrum, WPEVAALIQEQDK | 0.000 | 0.000 | 0.082 | 0.789 | 0.000 | 0.000 | 0.129 | 0.000 | ||
| 3 spectra, HPLNYCMFVGR | 0.000 | 0.000 | 0.012 | 0.717 | 0.000 | 0.086 | 0.184 | 0.000 | ||
| 2 spectra, RPEGSK | 0.050 | 0.000 | 0.026 | 0.849 | 0.000 | 0.000 | 0.075 | 0.000 | ||
| 3 spectra, QLRPVVK | 0.000 | 0.000 | 0.000 | 0.820 | 0.000 | 0.000 | 0.180 | 0.000 | ||
| 2 spectra, VVLLGDHK | 0.123 | 0.000 | 0.000 | 0.877 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, DICSFPSMEFYGGK | 0.025 | 0.000 | 0.122 | 0.717 | 0.043 | 0.019 | 0.056 | 0.017 | ||
| 1 spectrum, QFTVIQGPPGTGK | 0.000 | 0.000 | 0.000 | 0.879 | 0.000 | 0.000 | 0.121 | 0.000 | ||
| 2 spectra, HPGAGLK | 0.000 | 0.000 | 0.085 | 0.718 | 0.000 | 0.000 | 0.197 | 0.000 | ||
| 1 spectrum, SVDVLGGLLLR | 0.000 | 0.235 | 0.000 | 0.478 | 0.174 | 0.000 | 0.113 | 0.000 | ||
| 2 spectra, VDLHLGCSR | 0.000 | 0.000 | 0.169 | 0.433 | 0.000 | 0.000 | 0.398 | 0.000 | ||
| 2 spectra, YYSPGLGCK | 0.026 | 0.000 | 0.000 | 0.850 | 0.000 | 0.000 | 0.091 | 0.034 | ||
| 2 spectra, ASHGQPPAVK | 0.053 | 0.000 | 0.031 | 0.812 | 0.000 | 0.000 | 0.090 | 0.014 | ||
| 2 spectra, EQAAWQDGLVPYQAR | 0.169 | 0.000 | 0.000 | 0.741 | 0.000 | 0.000 | 0.074 | 0.015 | ||
| 3 spectra, AQDMELR | 0.000 | 0.000 | 0.056 | 0.764 | 0.000 | 0.000 | 0.179 | 0.000 | ||
| 7 spectra, LVVTTTSQAR | 0.024 | 0.000 | 0.000 | 0.914 | 0.000 | 0.000 | 0.013 | 0.048 | ||
| 2 spectra, YLDVVLQR | 0.100 | 0.000 | 0.017 | 0.793 | 0.000 | 0.000 | 0.090 | 0.000 | ||
| 1 spectrum, CCPLWHR | 0.000 | 0.000 | 0.365 | 0.154 | 0.241 | 0.000 | 0.240 | 0.000 | ||
| 3 spectra, QMTVTVR | 0.039 | 0.000 | 0.000 | 0.855 | 0.000 | 0.000 | 0.104 | 0.001 | ||
| 2 spectra, QFVEVRPLPQK | 0.034 | 0.000 | 0.051 | 0.753 | 0.000 | 0.000 | 0.163 | 0.000 | ||
| 2 spectra, AHTPDPASVSK | 0.000 | 0.000 | 0.053 | 0.716 | 0.000 | 0.000 | 0.231 | 0.000 | ||
| 2 spectra, VPEEVLRPSTR | 0.000 | 0.000 | 0.000 | 0.912 | 0.000 | 0.000 | 0.000 | 0.088 | ||
| 1 spectrum, SQGSEWR | 0.000 | 0.000 | 0.000 | 0.605 | 0.000 | 0.230 | 0.166 | 0.000 | ||
| 2 spectra, ELLDESR | 0.000 | 0.000 | 0.051 | 0.925 | 0.000 | 0.000 | 0.024 | 0.000 | ||
| 4 spectra, EAVQGTR | 0.000 | 0.000 | 0.009 | 0.804 | 0.000 | 0.000 | 0.186 | 0.000 | ||
| 2 spectra, LLGFCEAQNSLVPAER | 0.073 | 0.000 | 0.000 | 0.855 | 0.000 | 0.000 | 0.049 | 0.024 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
34 spectra |
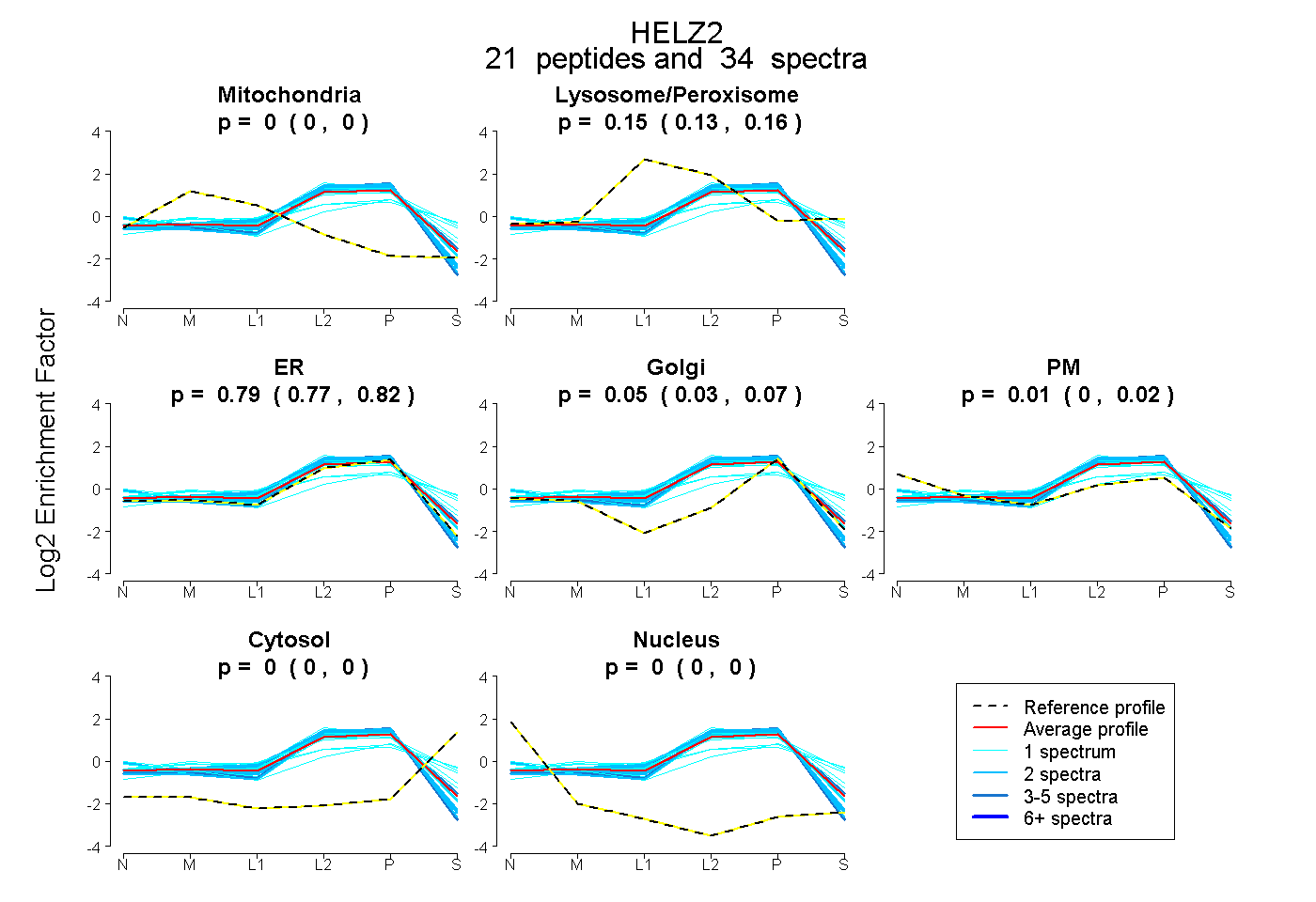 |
0.000 0.000 | 0.000 |
0.147 0.132 | 0.156 |
0.793 0.769 | 0.815 |
0.051 0.026 | 0.067 |
0.009 0.000 | 0.024 |
0.000 0.000 | 0.003 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
205 spectra |
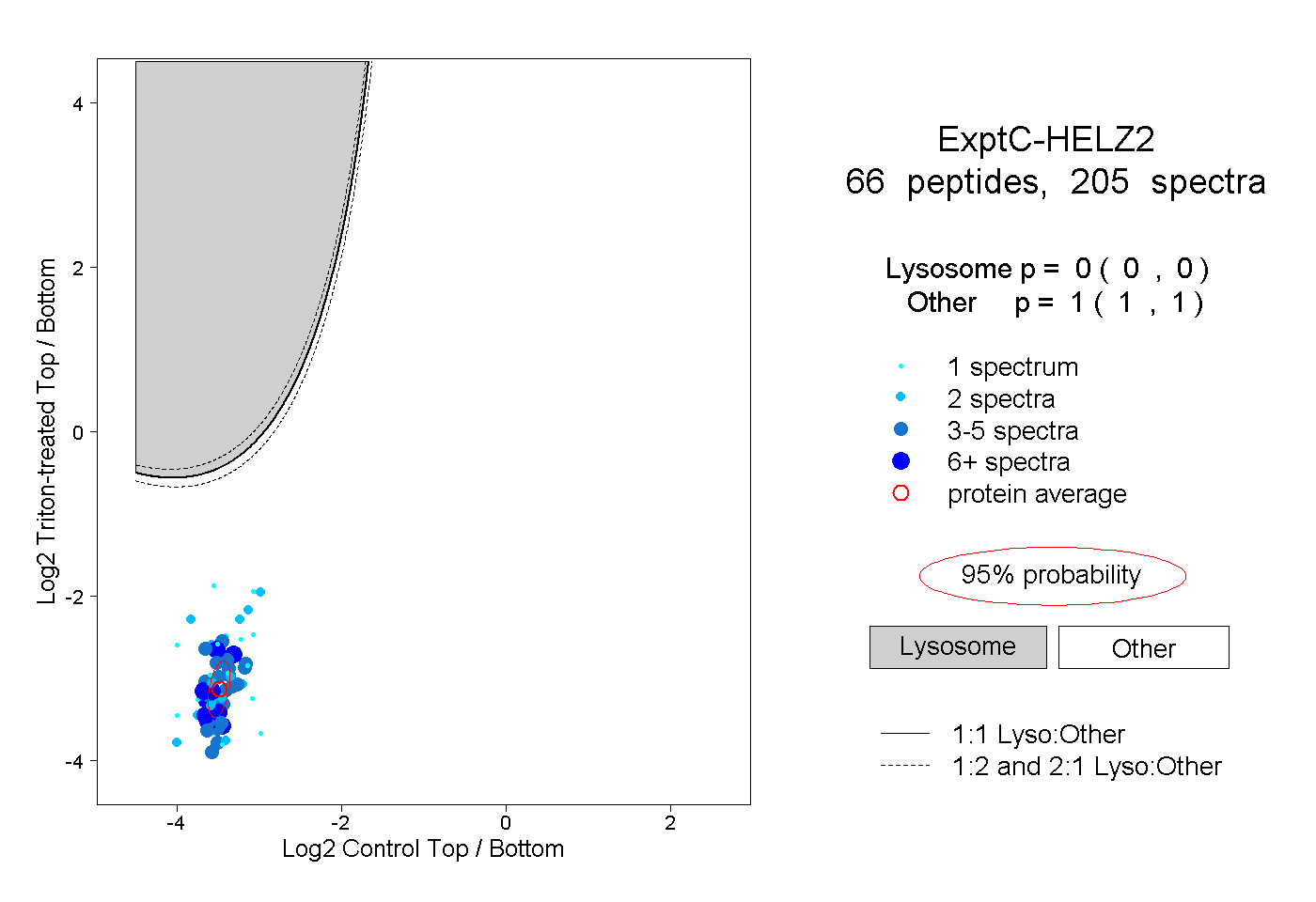 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
21 spectra |
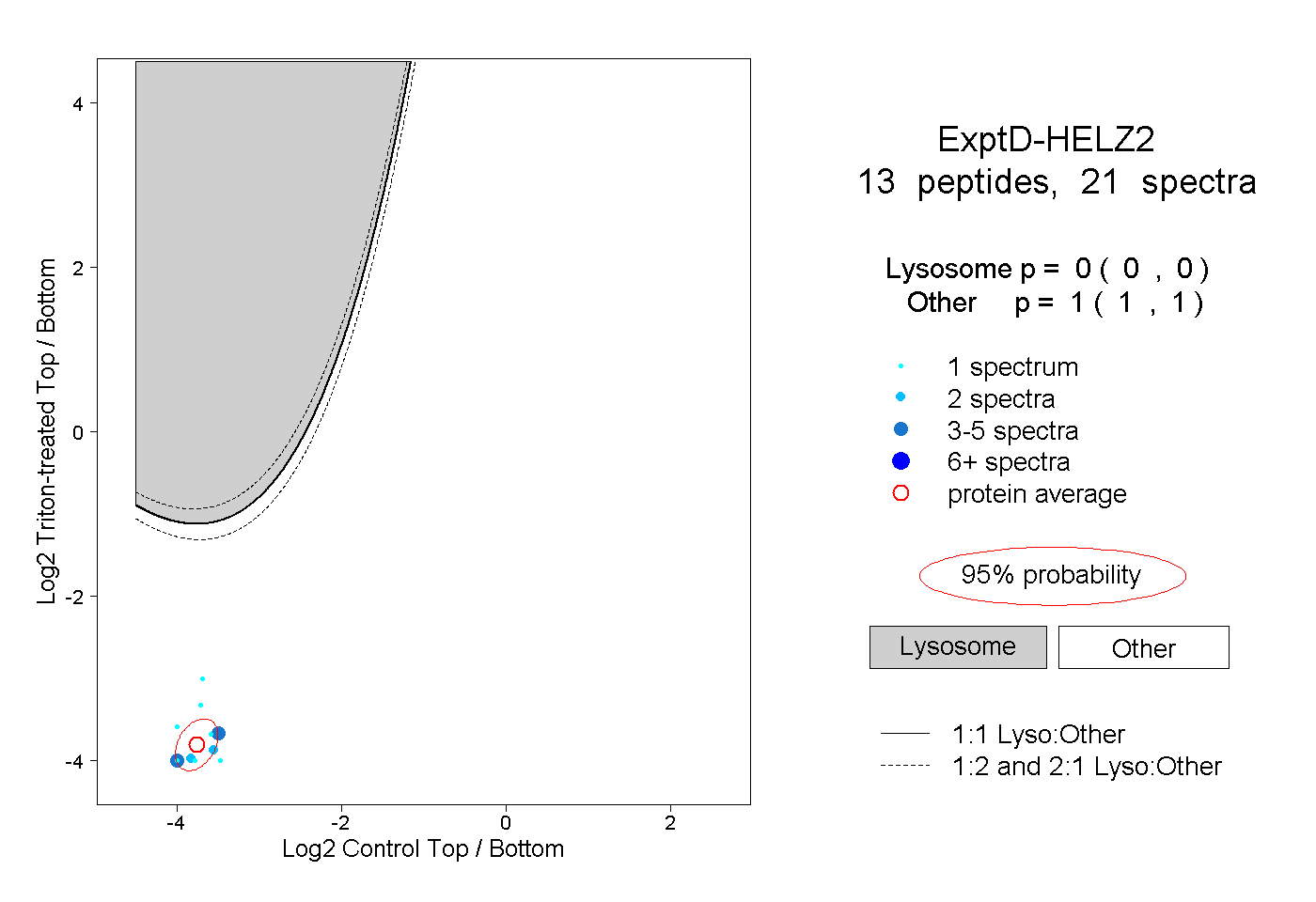 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |