peptides
spectra
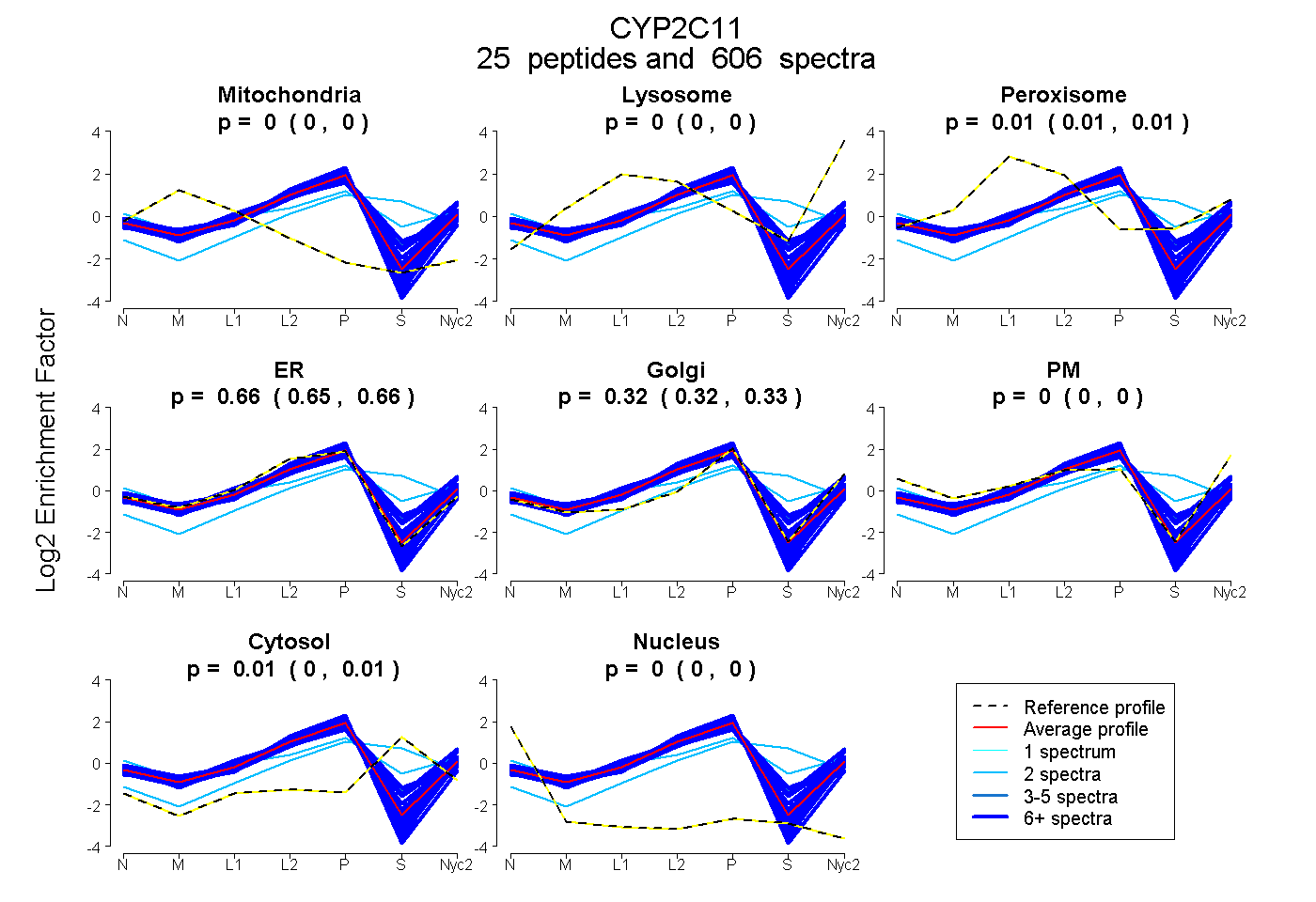
0.000 | 0.000
0.000 | 0.000
0.011 | 0.013
0.654 | 0.659
0.322 | 0.326
0.000 | 0.000
0.004 | 0.007
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
606 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.013 0.011 | 0.013 |
0.657 0.654 | 0.659 |
0.325 0.322 | 0.326 |
0.000 0.000 | 0.000 |
0.006 0.004 | 0.007 |
0.000 0.000 | 0.000 |
| 44 spectra, FSLMTLR | 0.002 | 0.000 | 0.000 | 0.787 | 0.211 | 0.000 | 0.000 | 0.000 | ||
| 37 spectra, VQEEIER | 0.000 | 0.000 | 0.000 | 0.780 | 0.220 | 0.000 | 0.000 | 0.000 | ||
| 26 spectra, HVDVTAK | 0.000 | 0.000 | 0.018 | 0.747 | 0.235 | 0.000 | 0.000 | 0.000 | ||
| 10 spectra, SDYFMPFSAGK | 0.000 | 0.000 | 0.000 | 0.660 | 0.320 | 0.000 | 0.000 | 0.020 | ||
| 11 spectra, NYFIPK | 0.000 | 0.000 | 0.000 | 0.656 | 0.344 | 0.000 | 0.000 | 0.000 | ||
| 62 spectra, GSFPVSER | 0.000 | 0.000 | 0.000 | 0.726 | 0.274 | 0.000 | 0.000 | 0.000 | ||
| 19 spectra, YIDLVPTNLPHLVTR | 0.000 | 0.000 | 0.034 | 0.492 | 0.238 | 0.162 | 0.074 | 0.000 | ||
| 28 spectra, EALVDLGEEFSGR | 0.000 | 0.000 | 0.000 | 0.754 | 0.244 | 0.000 | 0.000 | 0.002 | ||
| 20 spectra, NFFYIK | 0.000 | 0.000 | 0.000 | 0.734 | 0.265 | 0.000 | 0.000 | 0.001 | ||
| 16 spectra, YGLLLLLK | 0.000 | 0.000 | 0.000 | 0.719 | 0.239 | 0.042 | 0.000 | 0.000 | ||
| 29 spectra, DFIDCFLNK | 0.000 | 0.000 | 0.000 | 0.757 | 0.220 | 0.000 | 0.000 | 0.023 | ||
| 3 spectra, DYFIPK | 0.000 | 0.000 | 0.064 | 0.531 | 0.288 | 0.000 | 0.117 | 0.000 | ||
| 42 spectra, ICAGEALAR | 0.000 | 0.000 | 0.030 | 0.594 | 0.185 | 0.000 | 0.191 | 0.000 | ||
| 40 spectra, SQMPYTDAVVHEIQR | 0.000 | 0.000 | 0.118 | 0.468 | 0.272 | 0.057 | 0.086 | 0.000 | ||
| 2 spectra, ADSLSSHL | 0.000 | 0.000 | 0.187 | 0.129 | 0.302 | 0.152 | 0.230 | 0.000 | ||
| 76 spectra, FDPGHFLDER | 0.000 | 0.000 | 0.000 | 0.728 | 0.246 | 0.000 | 0.020 | 0.006 | ||
| 12 spectra, IQEEAQCLVEELR | 0.000 | 0.000 | 0.000 | 0.891 | 0.097 | 0.000 | 0.000 | 0.013 | ||
| 28 spectra, TFGMGK | 0.000 | 0.008 | 0.000 | 0.554 | 0.348 | 0.090 | 0.000 | 0.000 | ||
| 2 spectra, DIGQSIK | 0.000 | 0.016 | 0.000 | 0.294 | 0.101 | 0.000 | 0.589 | 0.000 | ||
| 19 spectra, FNENFR | 0.000 | 0.137 | 0.000 | 0.470 | 0.283 | 0.024 | 0.086 | 0.000 | ||
| 3 spectra, EHQESLDK | 0.000 | 0.000 | 0.000 | 0.536 | 0.309 | 0.154 | 0.000 | 0.000 | ||
| 22 spectra, GLGVIFSNGMQWK | 0.012 | 0.000 | 0.068 | 0.558 | 0.349 | 0.000 | 0.013 | 0.000 | ||
| 24 spectra, DPTFLNLMHR | 0.000 | 0.056 | 0.055 | 0.444 | 0.283 | 0.028 | 0.134 | 0.000 | ||
| 17 spectra, VQEEELR | 0.000 | 0.000 | 0.000 | 0.802 | 0.192 | 0.000 | 0.000 | 0.006 | ||
| 14 spectra, SLVDVK | 0.000 | 0.008 | 0.000 | 0.703 | 0.249 | 0.040 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
319 spectra |
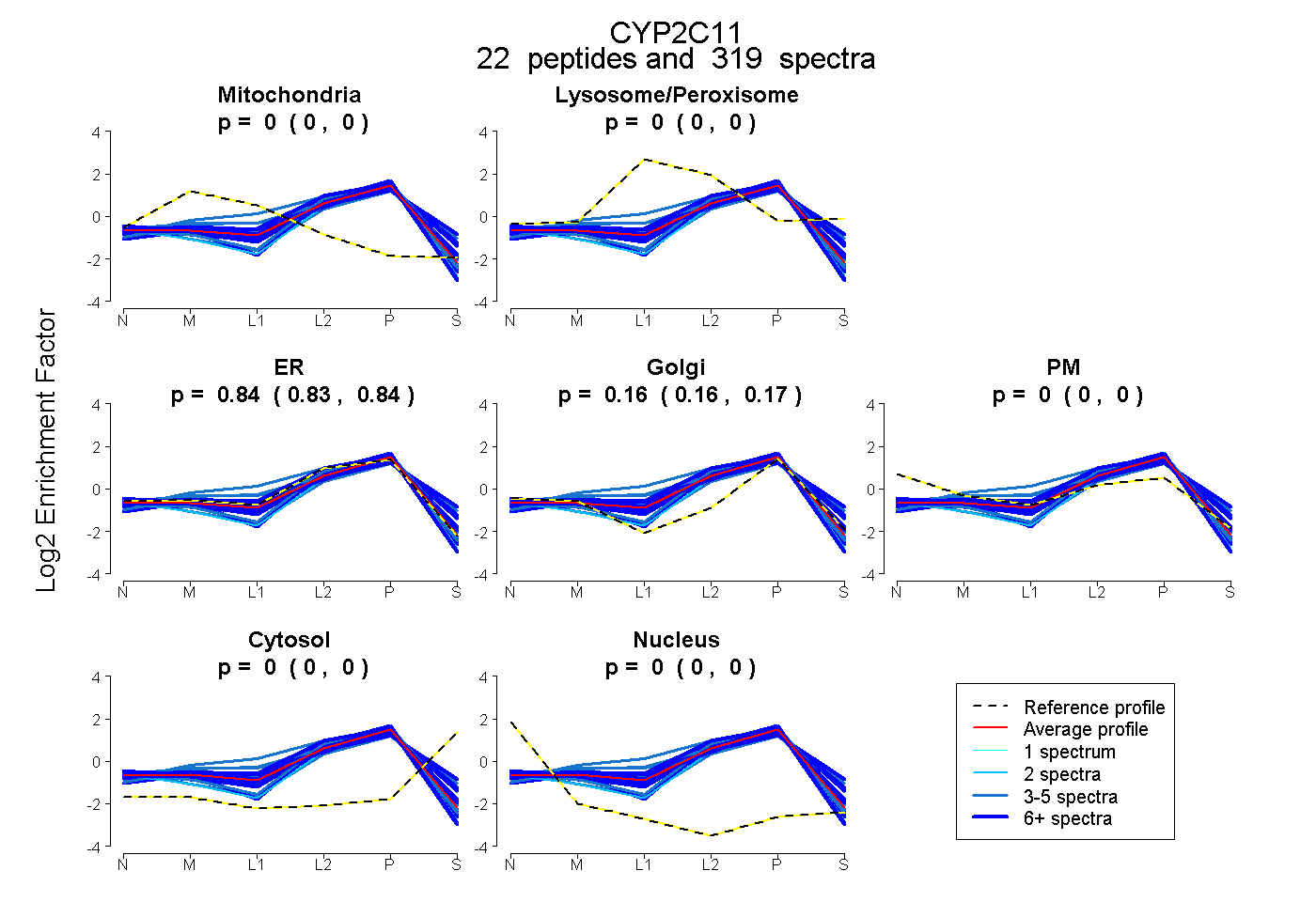 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.002 |
0.836 0.830 | 0.838 |
0.164 0.161 | 0.167 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
715 spectra |
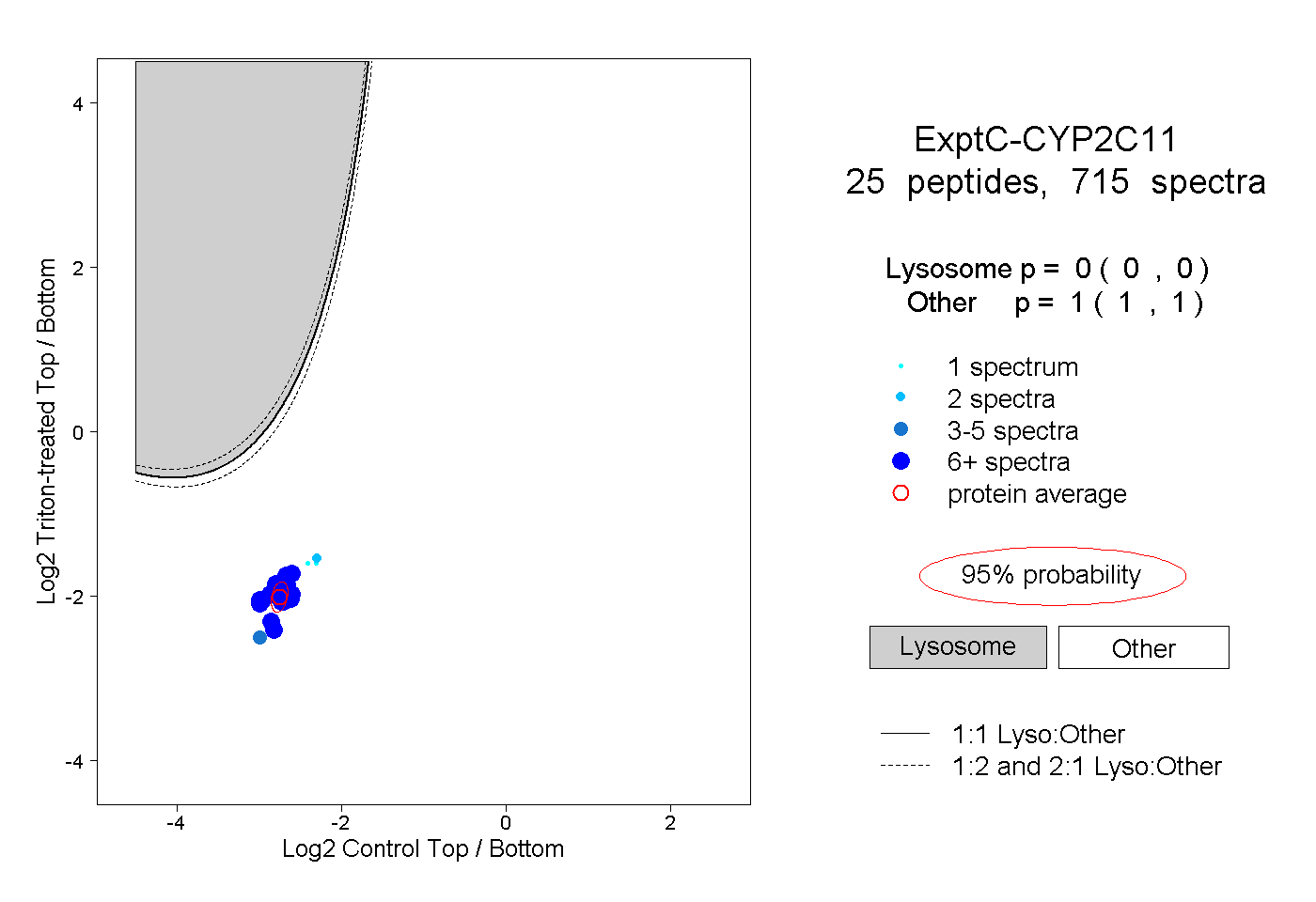 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
70 spectra |
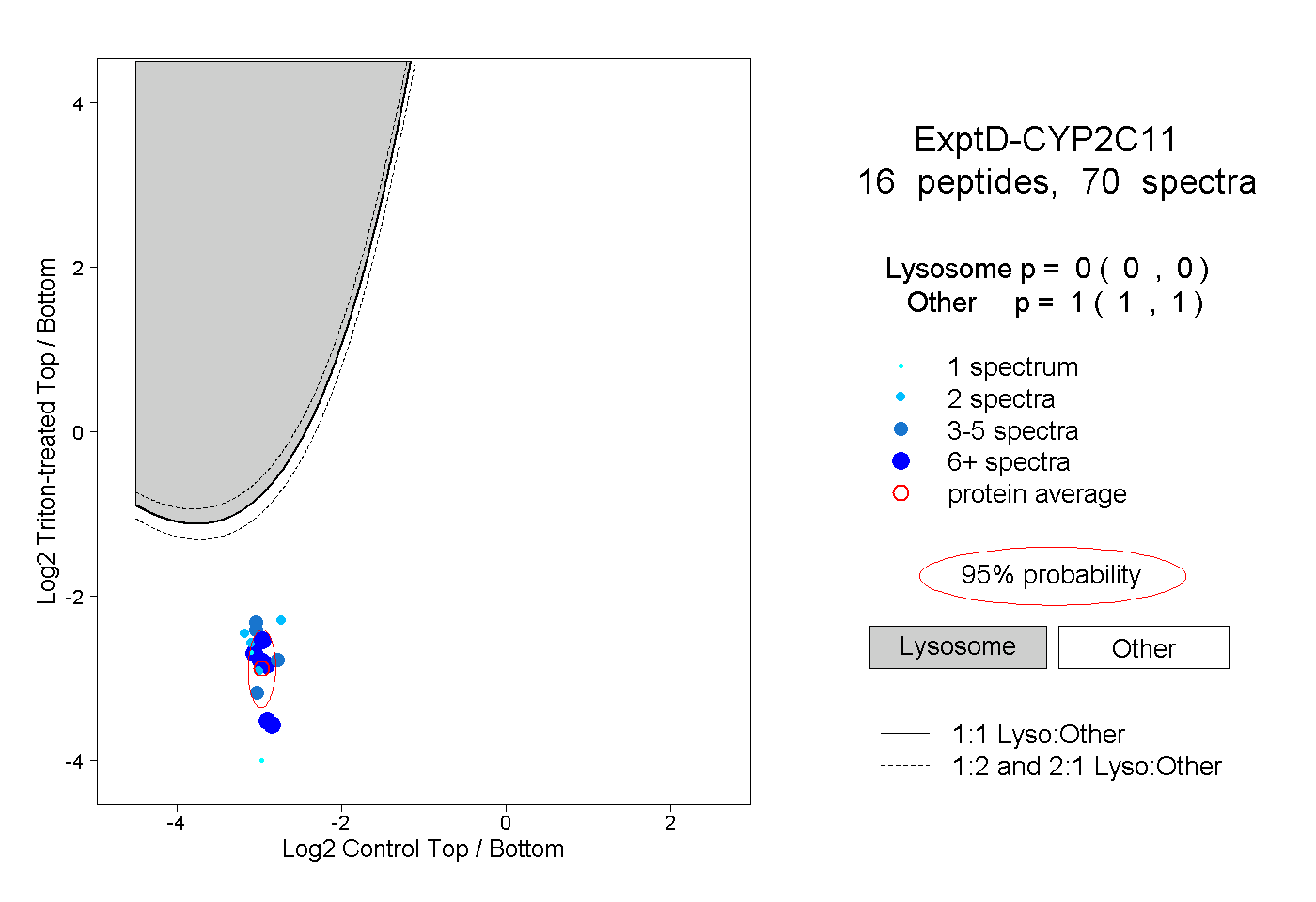 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |