peptides
spectra

0.028 | 0.034
0.000 | 0.000
0.000 | 0.000
0.966 | 0.971
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
89 spectra |
 |
0.031 0.028 | 0.034 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.969 0.966 | 0.971 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 9 spectra, NILDDFR | 0.020 | 0.000 | 0.000 | 0.980 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, HLEEAFTSEHWLVR | 0.021 | 0.000 | 0.082 | 0.782 | 0.000 | 0.000 | 0.115 | 0.000 | ||
| 6 spectra, EAYFWLR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, AGSPTLLNCLMYK | 0.113 | 0.000 | 0.000 | 0.869 | 0.000 | 0.000 | 0.000 | 0.018 | ||
| 12 spectra, EGDYFTQQGEFR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 10 spectra, VTNIFPK | 0.004 | 0.000 | 0.000 | 0.996 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, QNTDEHAR | 0.000 | 0.000 | 0.000 | 0.842 | 0.000 | 0.000 | 0.158 | 0.000 | ||
| 3 spectra, FYSLWDTGYAK | 0.000 | 0.172 | 0.001 | 0.644 | 0.000 | 0.130 | 0.052 | 0.000 | ||
| 7 spectra, ETLGHKPR | 0.046 | 0.000 | 0.000 | 0.926 | 0.000 | 0.000 | 0.000 | 0.028 | ||
| 6 spectra, TPPGFDR | 0.011 | 0.000 | 0.024 | 0.965 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, SPGNLYDK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 9 spectra, FGEMQLDFR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, IAEGEHPK | 0.047 | 0.000 | 0.000 | 0.953 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
45 spectra |
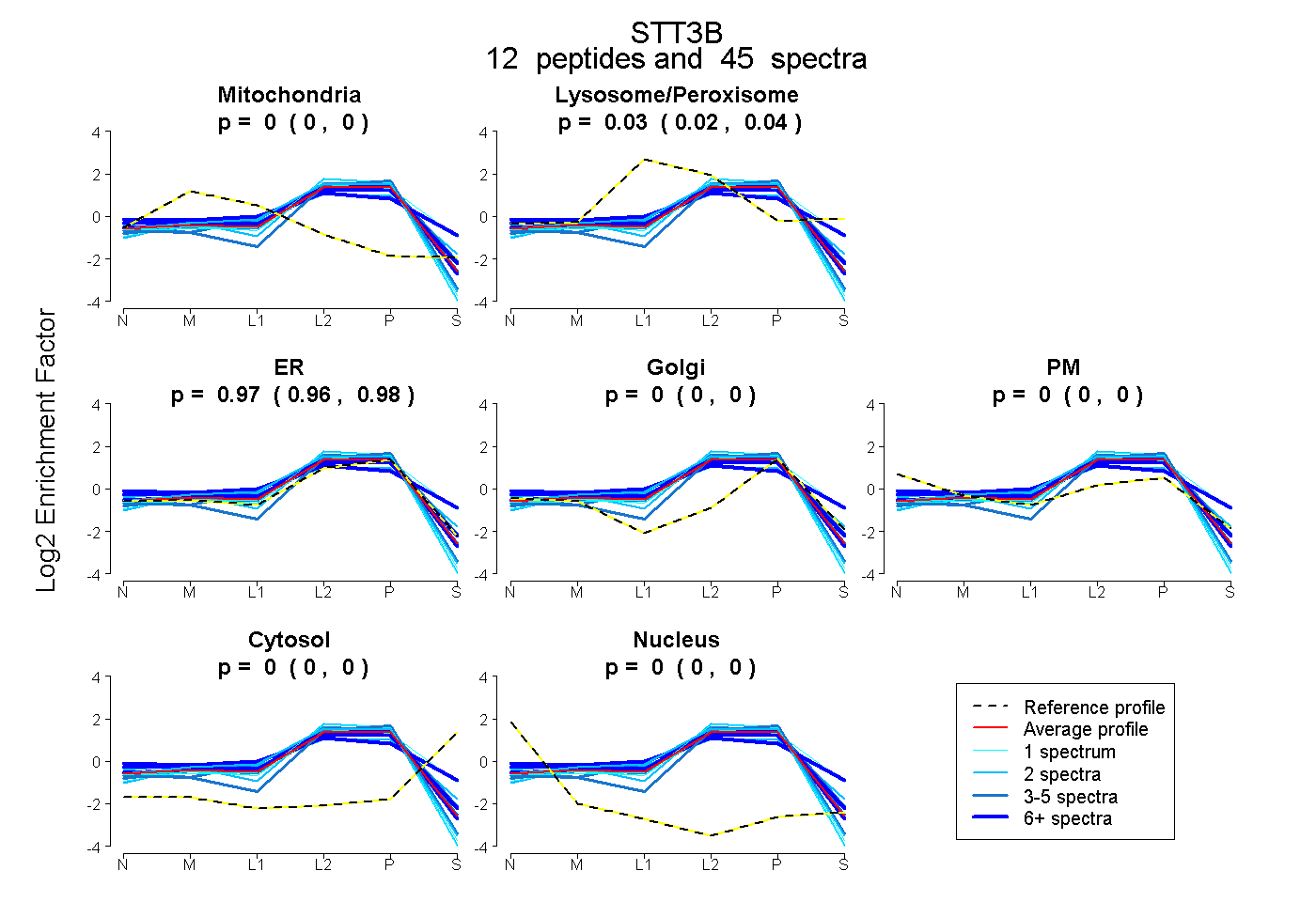 |
0.000 0.000 | 0.000 |
0.031 0.019 | 0.040 |
0.969 0.958 | 0.979 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
133 spectra |
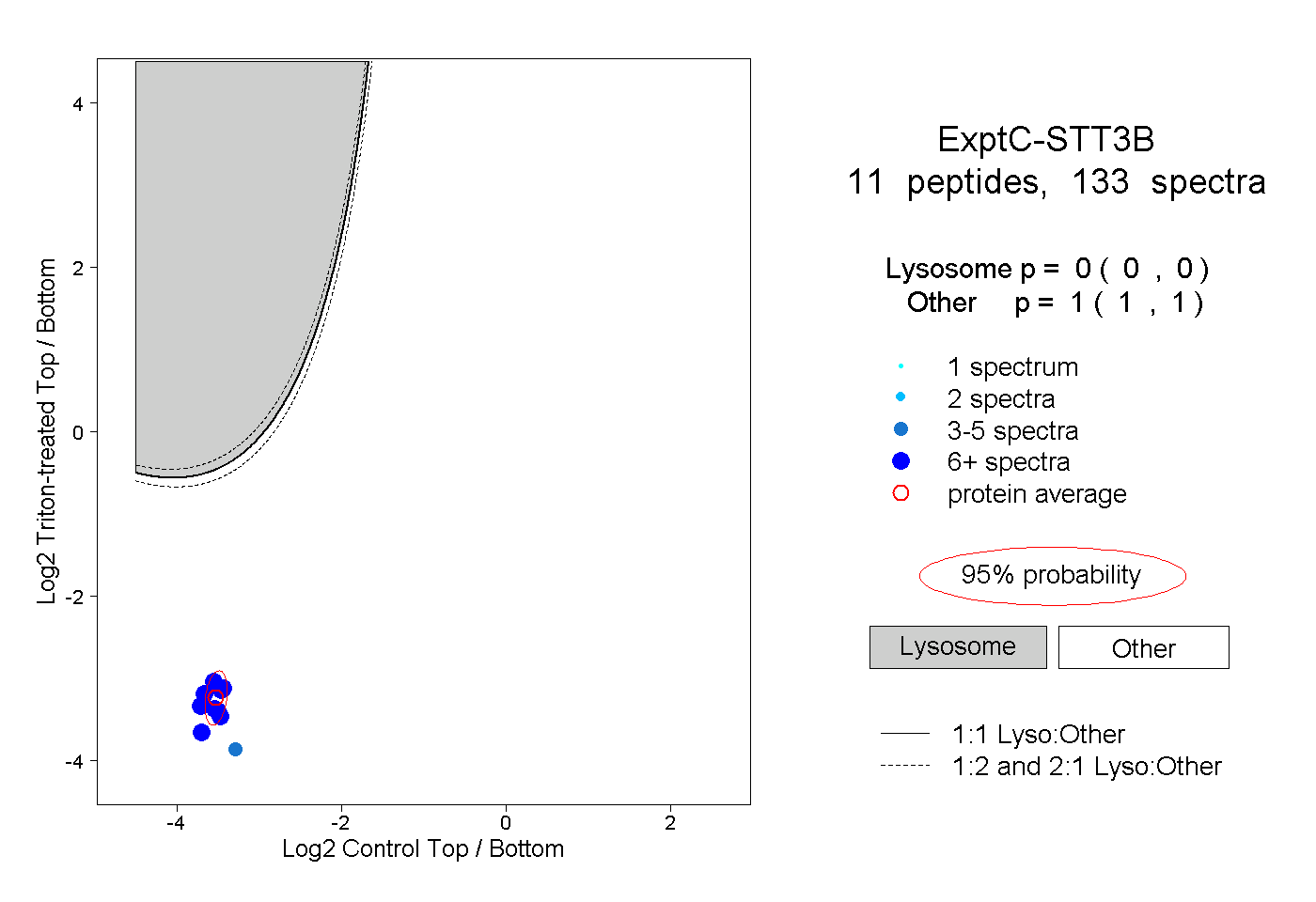 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
12 spectra |
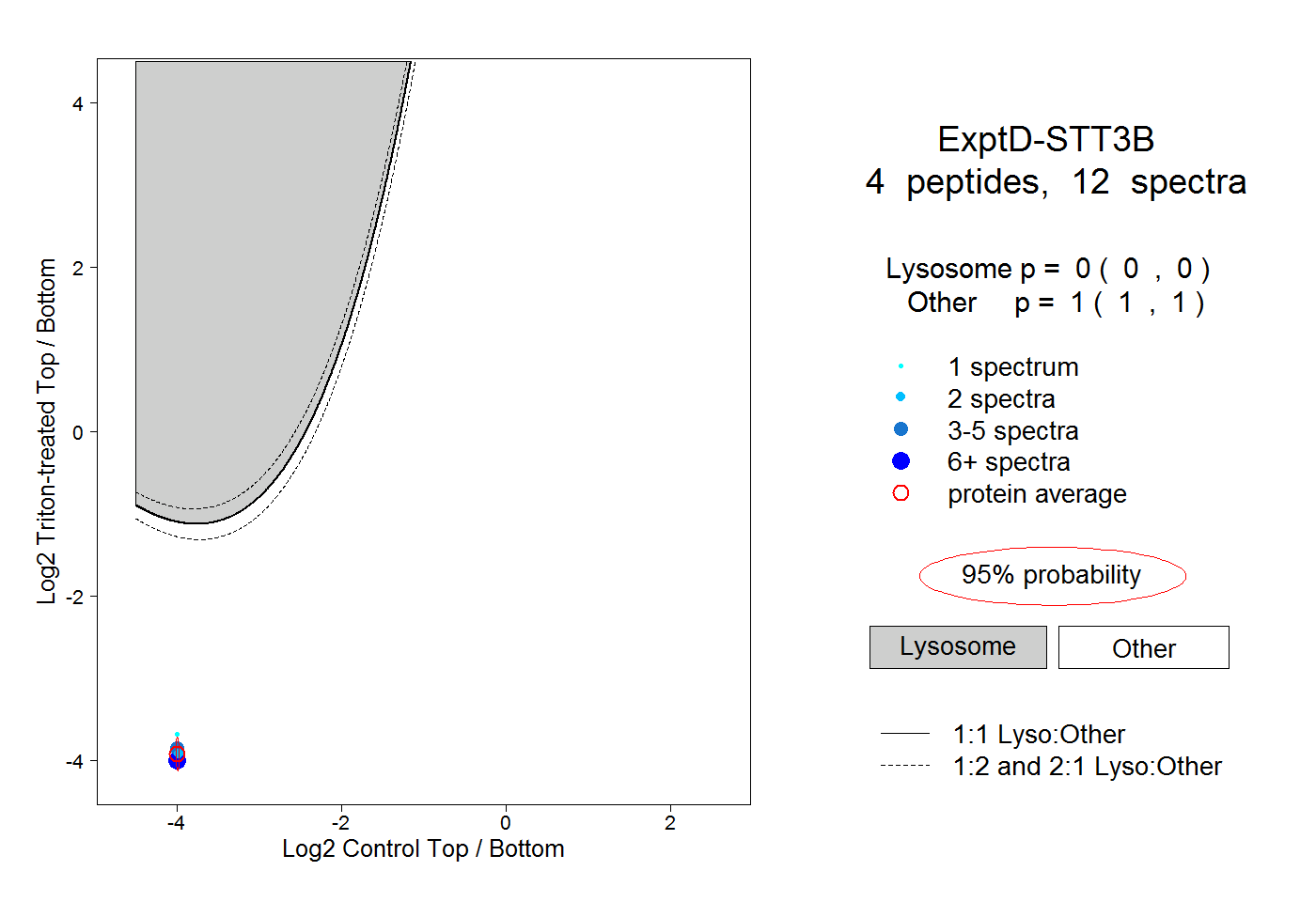 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |