peptides
spectra
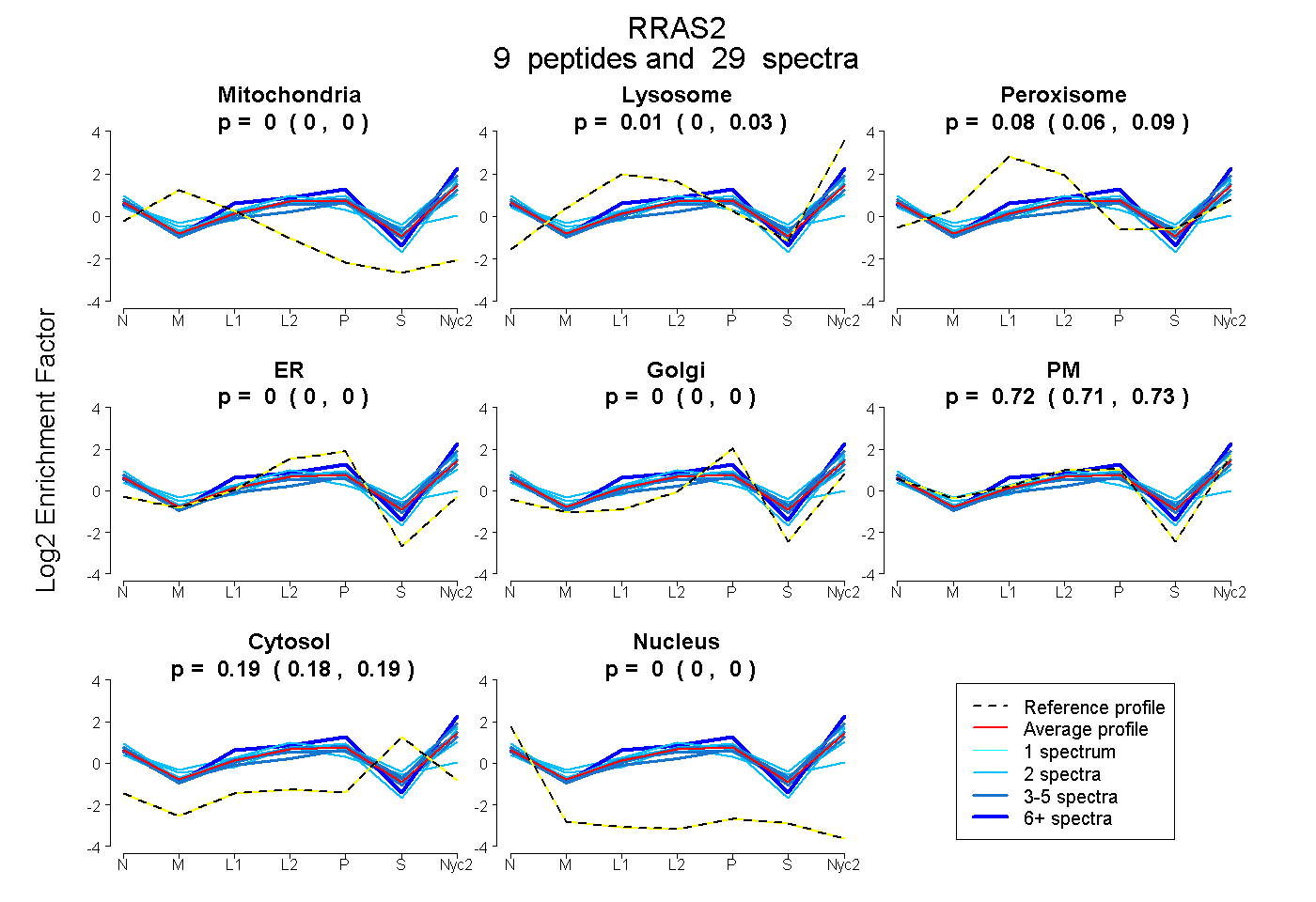
0.000 | 0.000
0.000 | 0.029
0.058 | 0.089
0.000 | 0.000
0.000 | 0.000
0.714 | 0.733
0.181 | 0.192
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
29 spectra |
 |
0.000 0.000 | 0.000 |
0.010 0.000 | 0.029 |
0.078 0.058 | 0.089 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.725 0.714 | 0.733 |
0.187 0.181 | 0.192 |
0.000 0.000 | 0.000 |
| 2 spectra, QVTQEEGQQLAR | 0.000 | 0.000 | 0.059 | 0.000 | 0.000 | 0.863 | 0.078 | 0.000 | ||
| 4 spectra, MNVDQAFHELVR | 0.000 | 0.051 | 0.035 | 0.000 | 0.000 | 0.690 | 0.224 | 0.000 | ||
| 5 spectra, GSFEEIYK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.763 | 0.237 | 0.000 | ||
| 6 spectra, LDILDTAGQEEFGAMR | 0.000 | 0.175 | 0.000 | 0.000 | 0.000 | 0.762 | 0.062 | 0.000 | ||
| 2 spectra, ADLDHQR | 0.000 | 0.000 | 0.178 | 0.000 | 0.000 | 0.634 | 0.188 | 0.000 | ||
| 2 spectra, DGSGQEK | 0.000 | 0.035 | 0.023 | 0.000 | 0.000 | 0.766 | 0.175 | 0.000 | ||
| 2 spectra, FQEQECPPSPEPTR | 0.000 | 0.000 | 0.206 | 0.142 | 0.000 | 0.353 | 0.241 | 0.058 | ||
| 4 spectra, VTYMEASAK | 0.000 | 0.131 | 0.000 | 0.000 | 0.000 | 0.659 | 0.210 | 0.000 | ||
| 2 spectra, LVVVGGGGVGK | 0.000 | 0.185 | 0.006 | 0.000 | 0.000 | 0.579 | 0.230 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
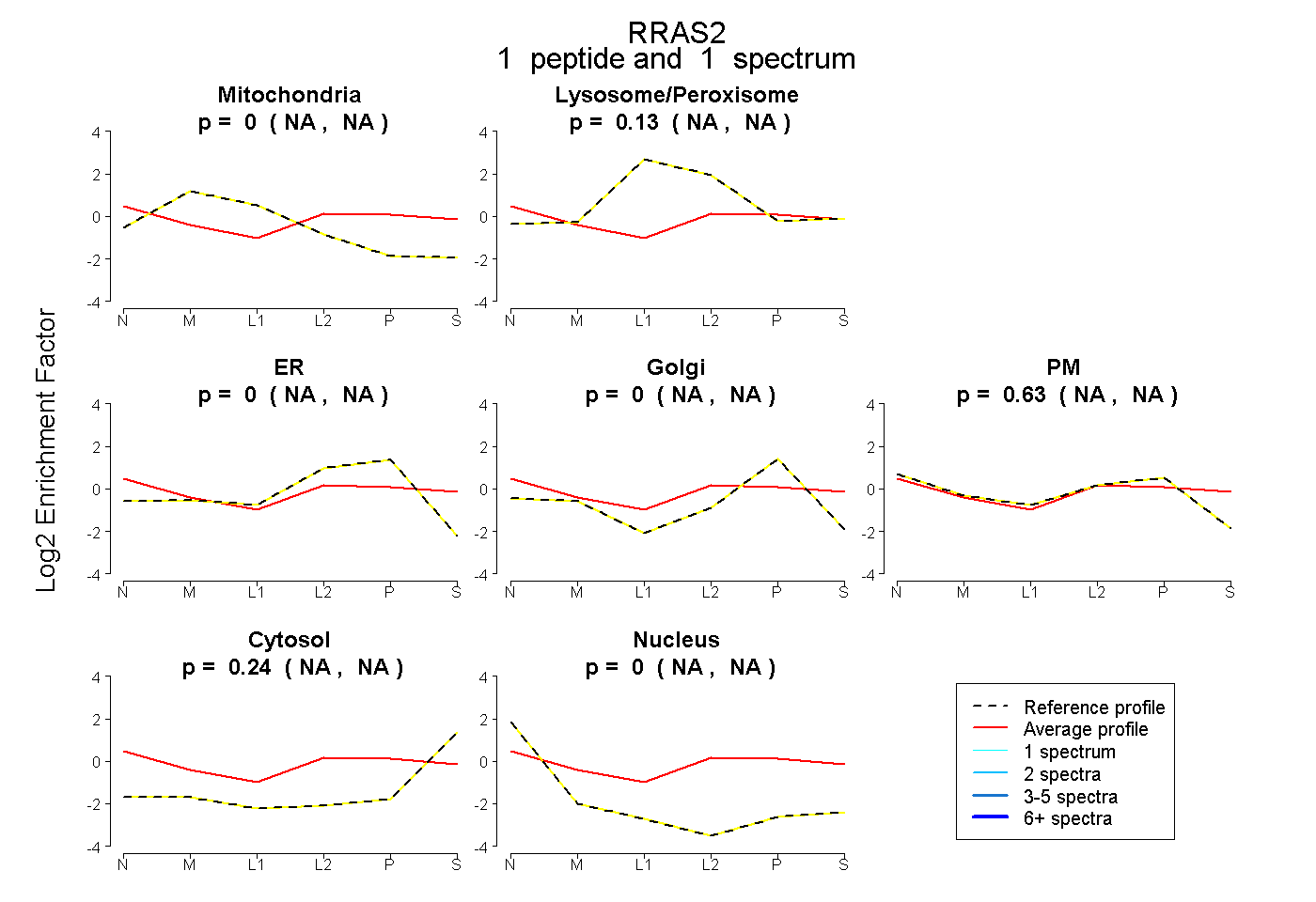 |
0.000 NA | NA |
0.129 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.626 NA | NA |
0.244 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
40 spectra |
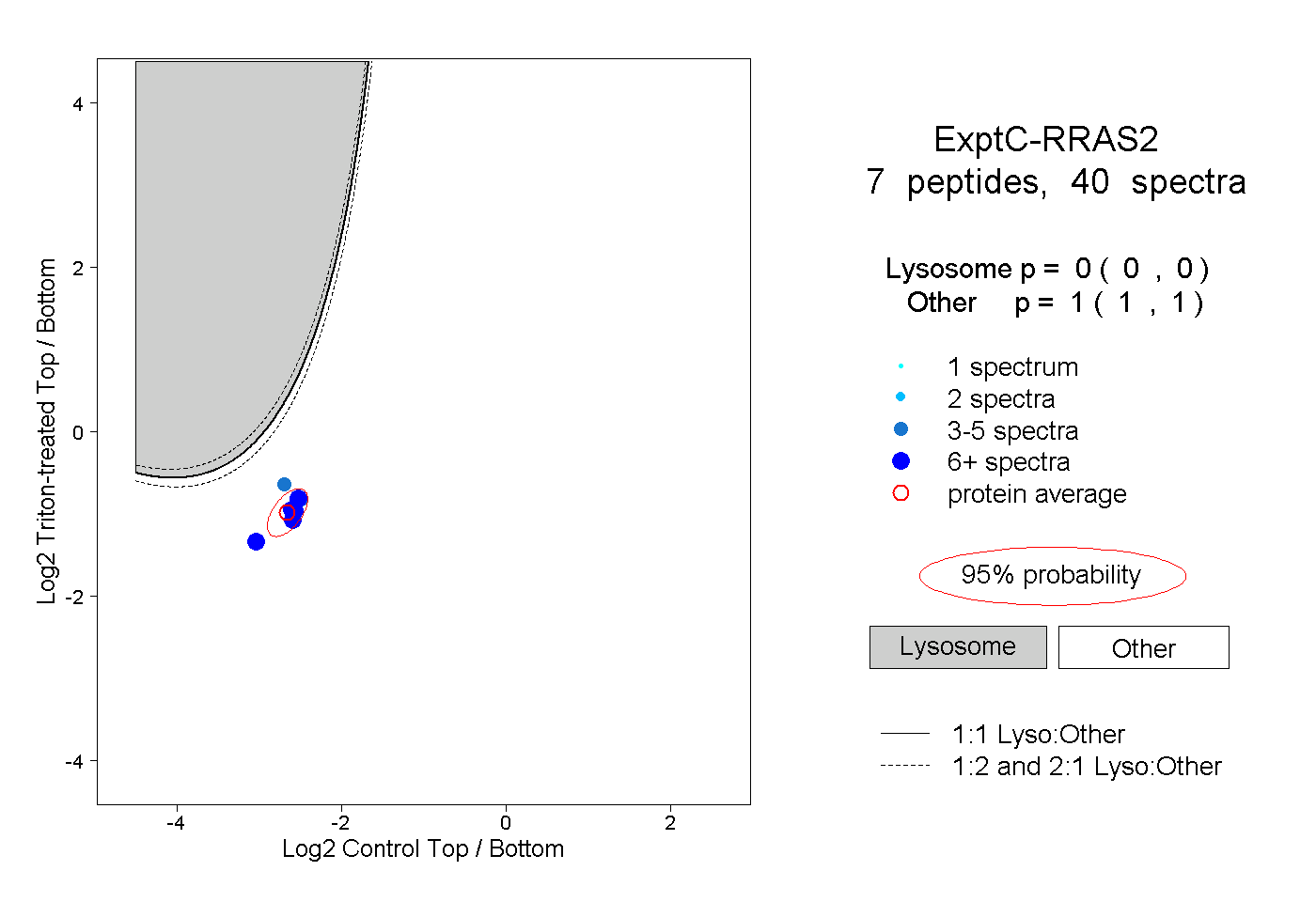 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
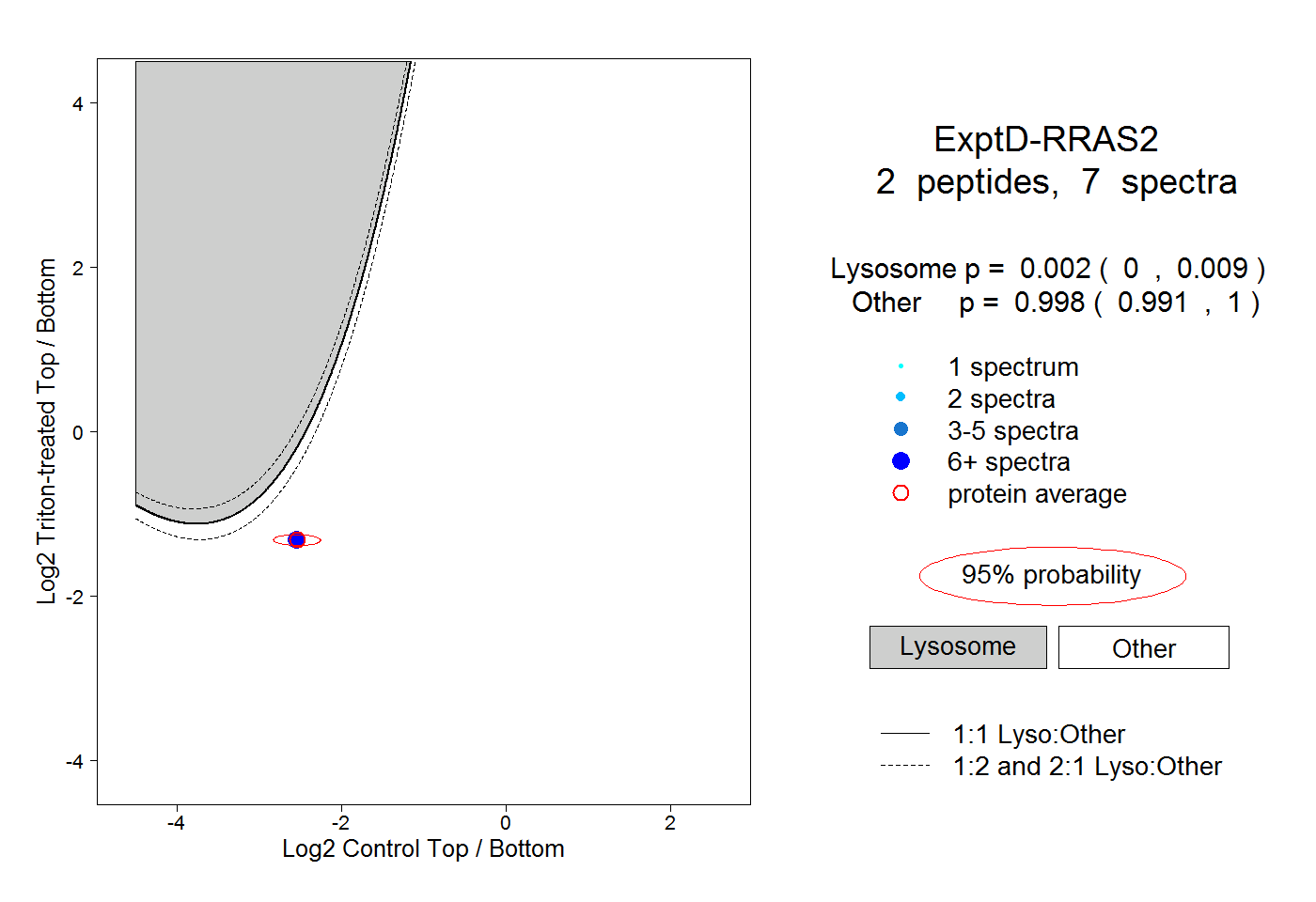 |
0.002 0.000 | 0.009 |
0.998 0.991 | 1.000 |