peptides
spectra
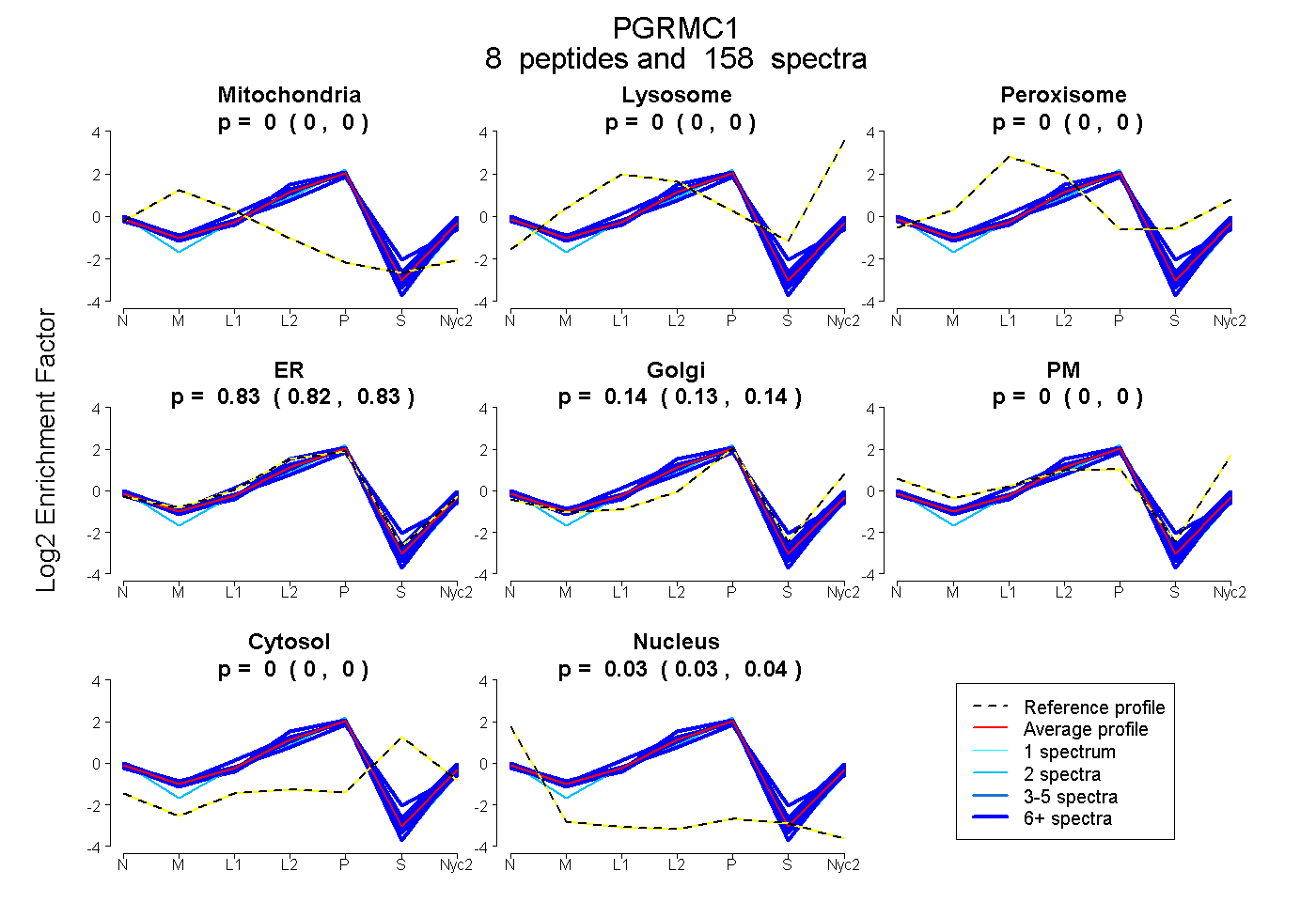
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.820 | 0.830
0.135 | 0.145
0.000 | 0.000
0.000 | 0.000
0.034 | 0.036
peptides
spectra
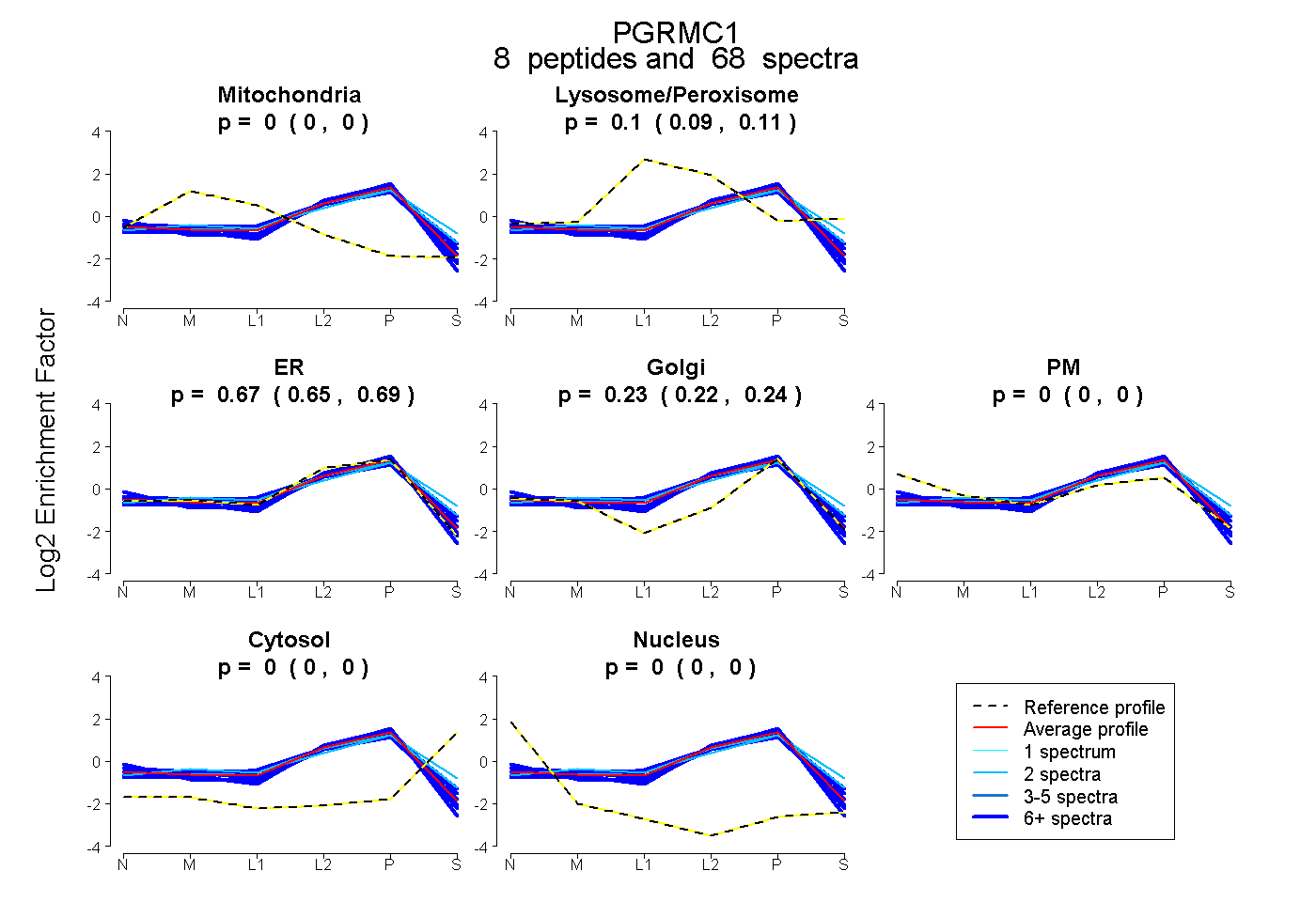
0.000 | 0.000
0.090 | 0.106
0.648 | 0.686
0.219 | 0.242
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
158 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.825 0.820 | 0.830 |
0.140 0.135 | 0.145 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.035 0.034 | 0.036 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
68 spectra |
 |
0.000 0.000 | 0.000 |
0.099 0.090 | 0.106 |
0.670 0.648 | 0.686 |
0.231 0.219 | 0.242 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 7 spectra, FYGPEGPYGVFAGR | 0.000 | 0.197 | 0.483 | 0.320 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, YDGVQDPR | 0.007 | 0.050 | 0.823 | 0.108 | 0.012 | 0.000 | 0.000 | |||
| 16 spectra, DFTPAELR | 0.000 | 0.000 | 0.980 | 0.011 | 0.000 | 0.000 | 0.008 | |||
| 7 spectra, GLATFCLDK | 0.000 | 0.108 | 0.485 | 0.204 | 0.136 | 0.066 | 0.000 | |||
| 19 spectra, ILMAINGK | 0.000 | 0.000 | 0.849 | 0.141 | 0.000 | 0.011 | 0.000 | |||
| 7 spectra, GDQPGASGDNDDDEPPPLPR | 0.000 | 0.085 | 0.549 | 0.213 | 0.137 | 0.016 | 0.000 | |||
| 2 spectra, VFDVTK | 0.000 | 0.318 | 0.136 | 0.513 | 0.000 | 0.033 | 0.000 | |||
| 2 spectra, YHHVGK | 0.000 | 0.212 | 0.444 | 0.313 | 0.000 | 0.030 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
155 spectra |
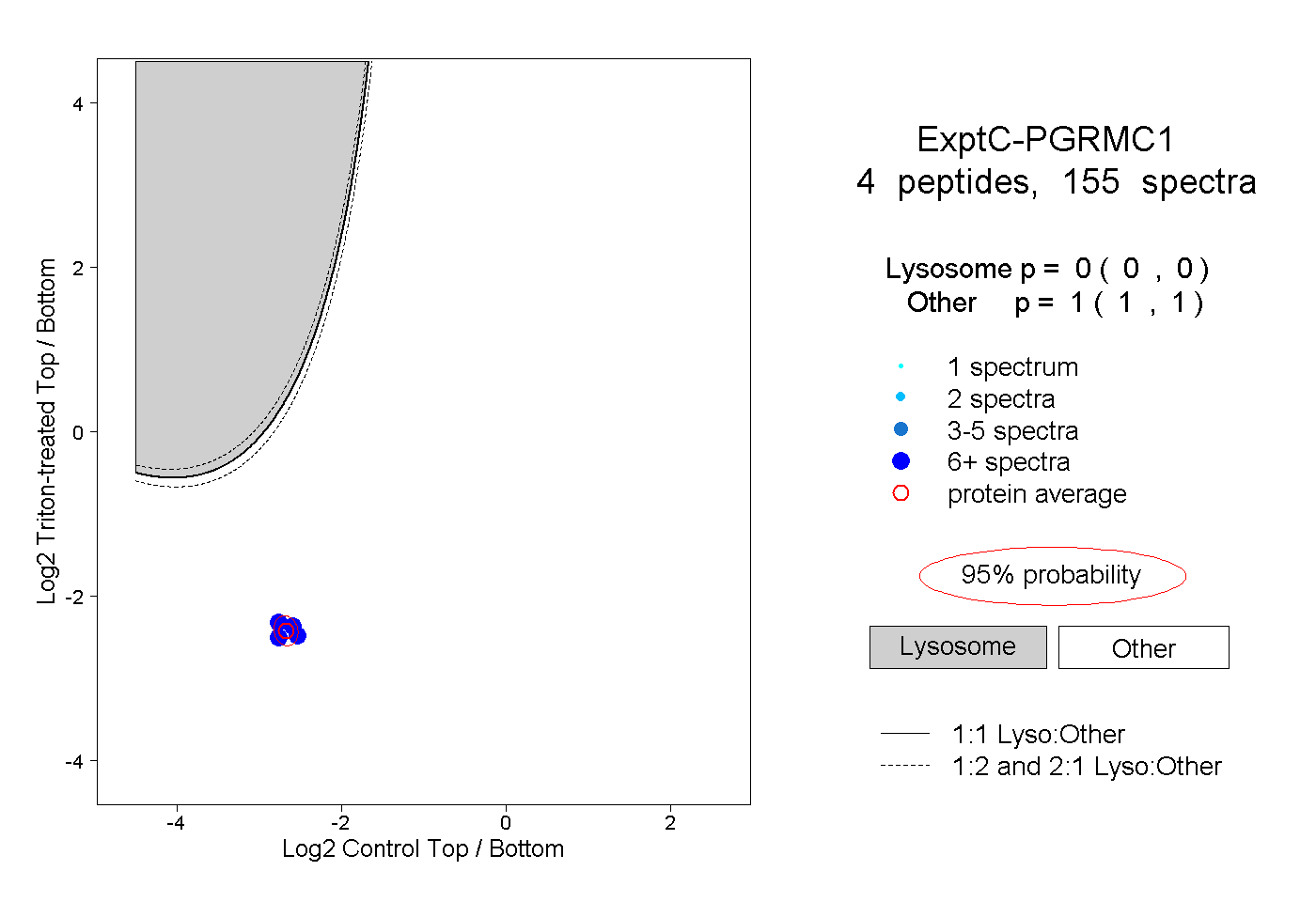 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
20 spectra |
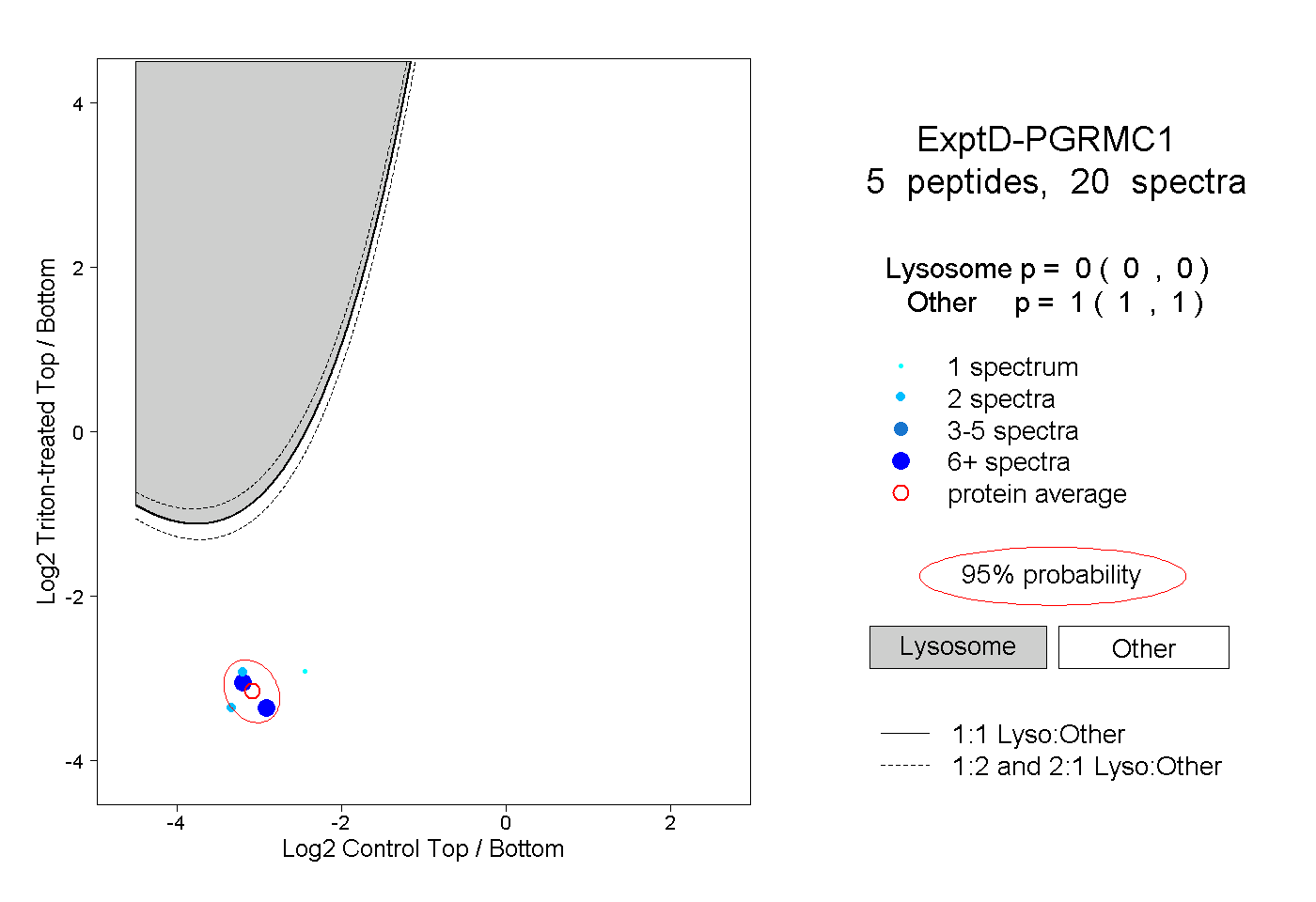 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |