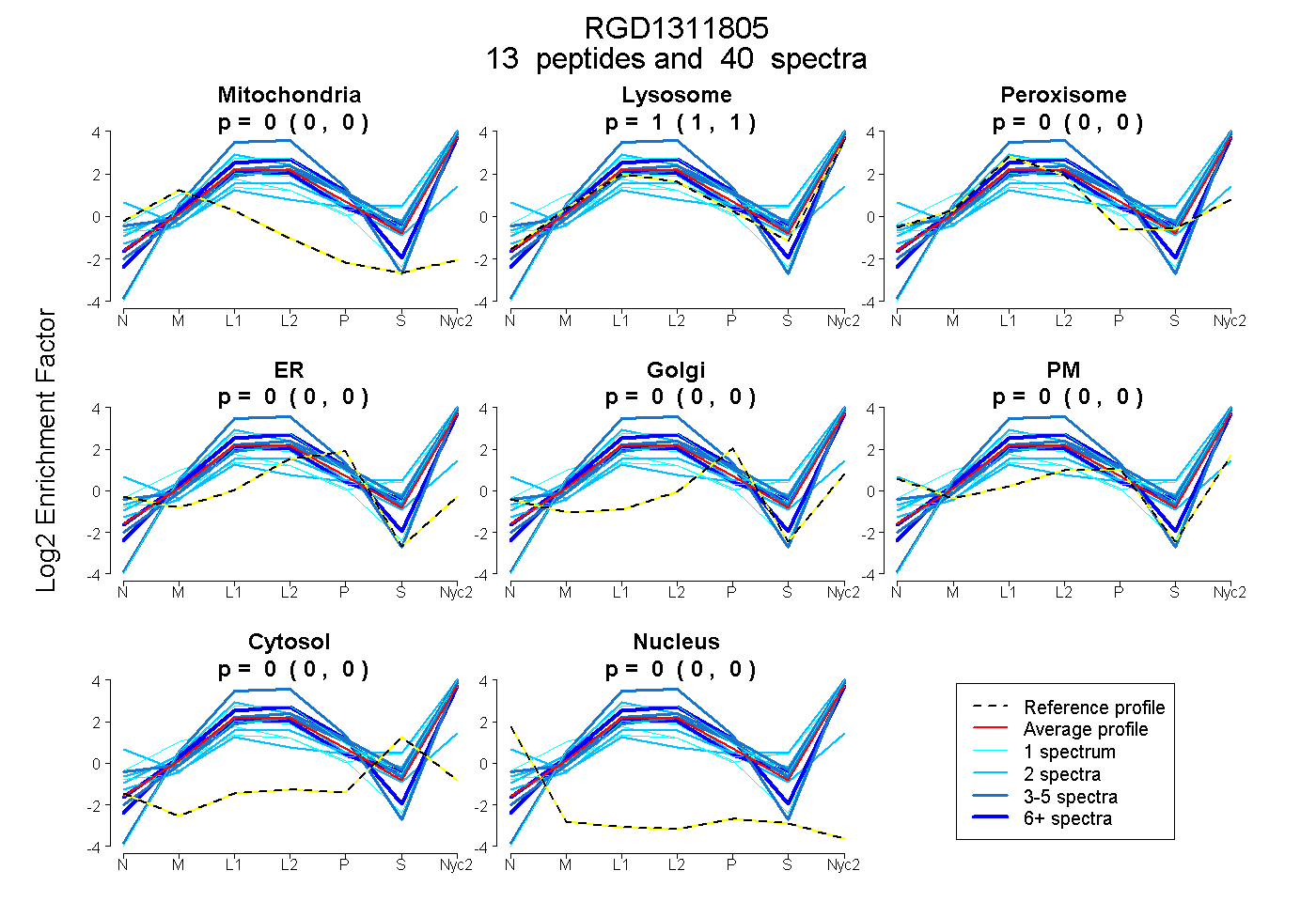
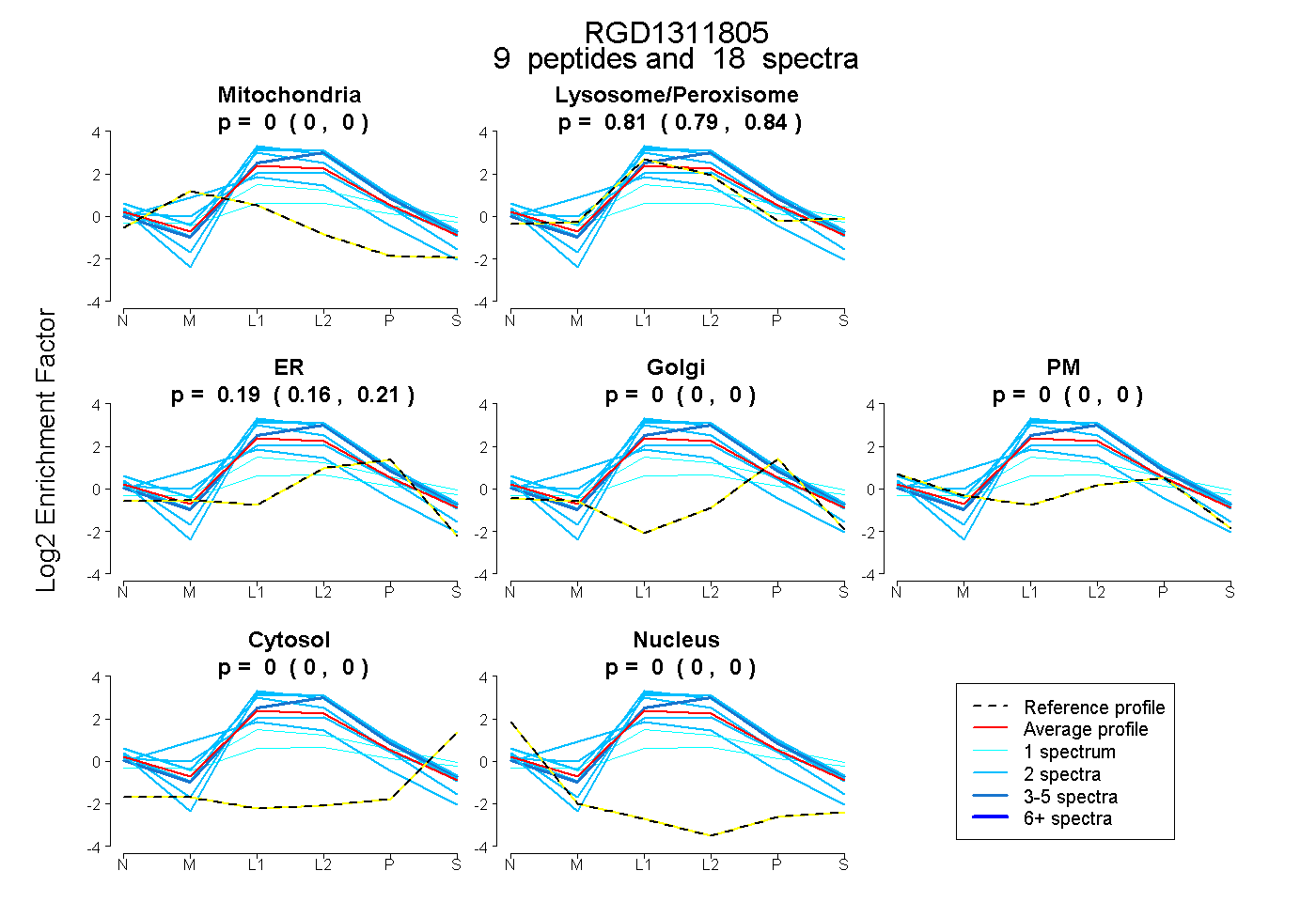
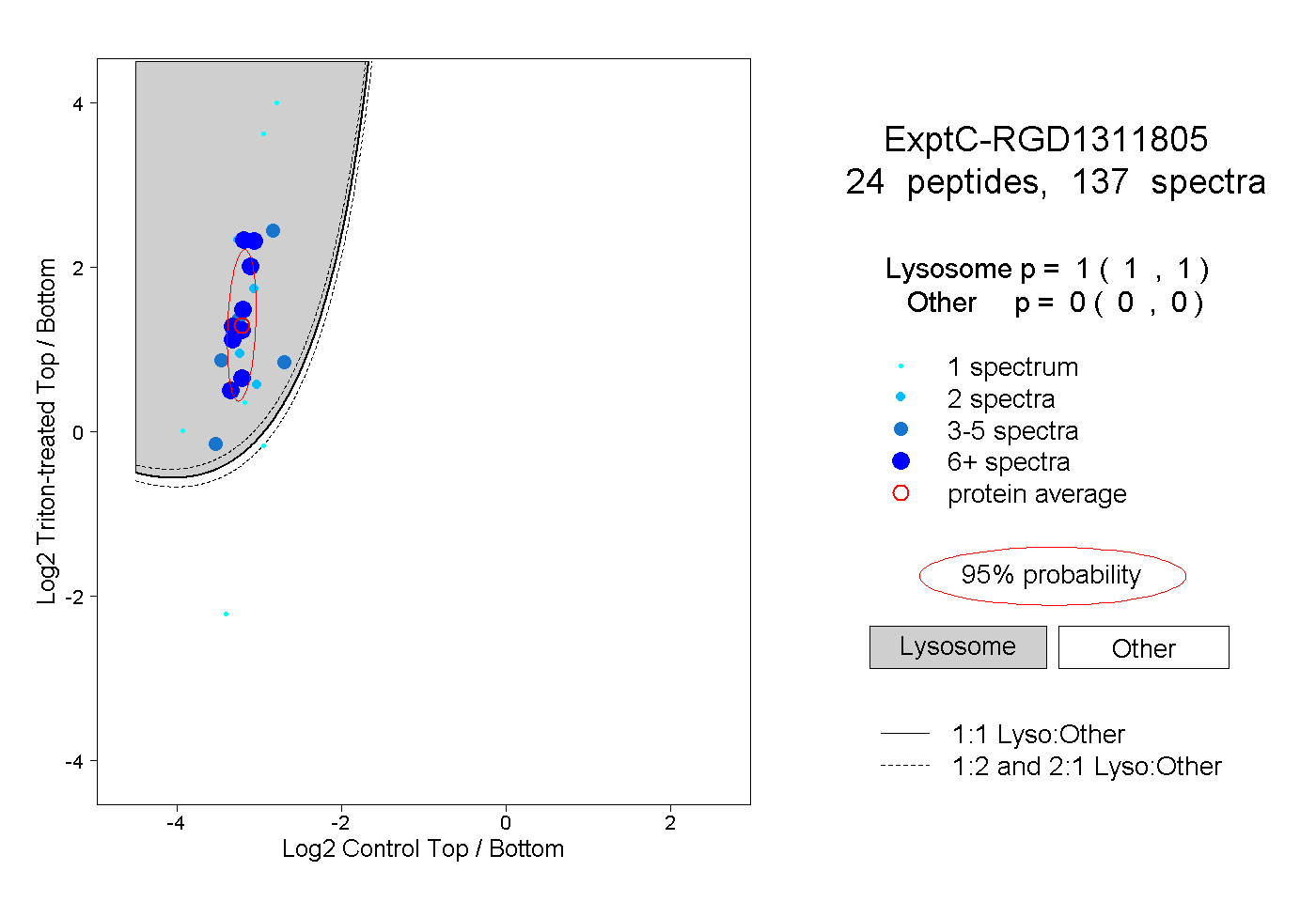
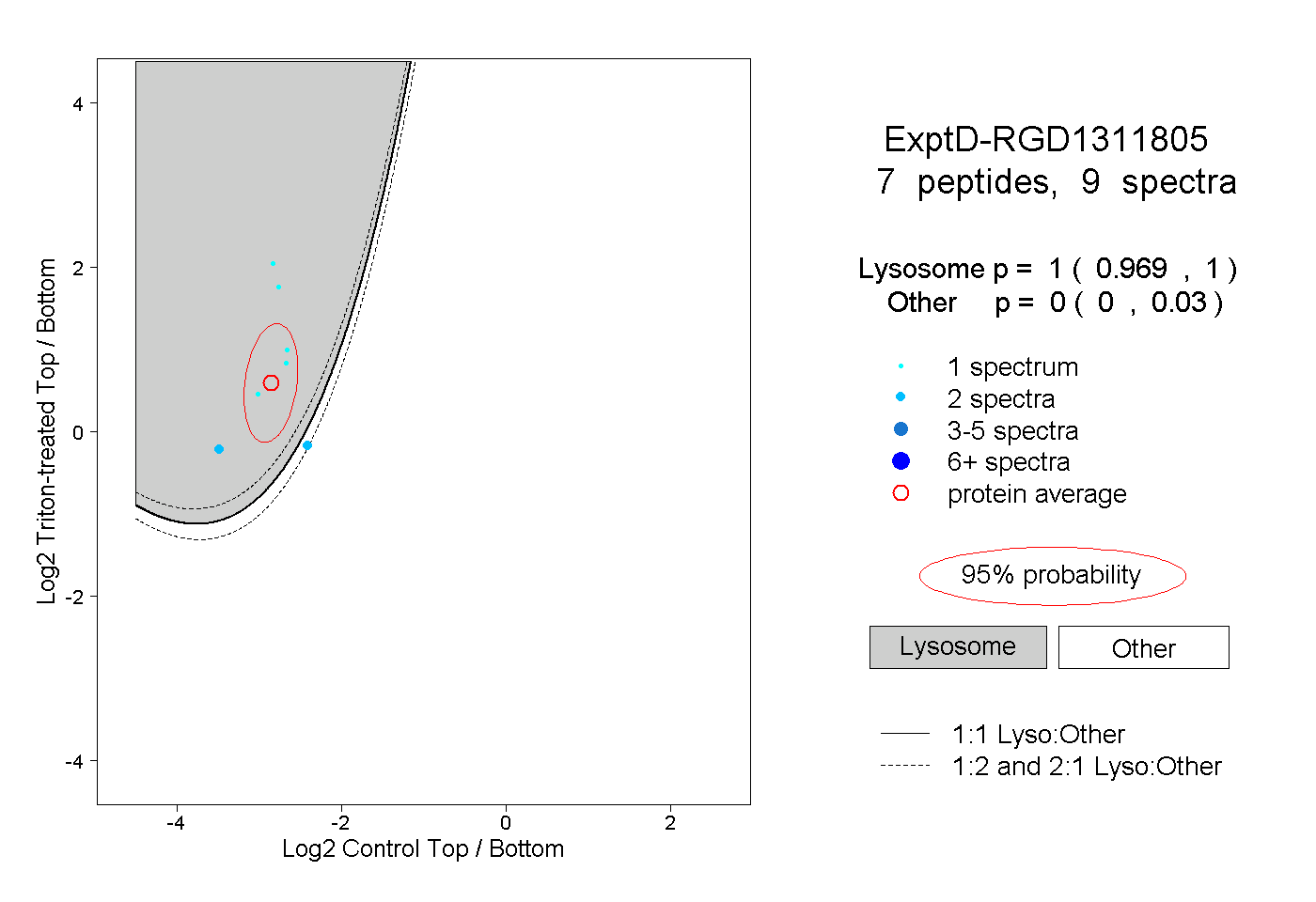
| 8 spectra, HQVLAALR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, EGACK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 1 spectrum, ATLPVIATVFDK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 1 spectrum, TQAVVDQSDVYTHVLSPFVENK |
|
0.998 |
|
|
|
|
|
|
|
0.002 |
| 2 spectra, NPISFR |
|
0.998 |
|
|
|
|
|
|
|
0.002 |
| 3 spectra, ISISER |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 6 spectra, QVFAVR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 7 spectra, QTDDVMLFYTIFR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 26 spectra, LMDFLLQR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 13 spectra, SNPPLK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 3 spectra, GEFDGTVTFHHPVLPAR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 1 spectrum, YLDAEQSYTMAVEAGQSR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 5 spectra, LNHEYK |
|
0.984 |
|
|
|
|
|
|
|
0.016 |
| 1 spectrum, ANPVNCVFFDEANK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, GIGGHDNISAR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, FEIELPAAPK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 9 spectra, SGGATGVVVK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 4 spectra, TSNSTGAEVVLYHLPR |
|
0.970 |
|
|
|
|
|
|
|
0.030 |
| 1 spectrum, FLDAAK |
|
0.999 |
|
|
|
|
|
|
|
0.001 |
| 4 spectra, GNPNFTPGEHCEEHVAFFK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 1 spectrum, QAFGEQALMRPTTF |
|
0.174 |
|
|
|
|
|
|
|
0.826 |
| 13 spectra, ILAVQR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, LQPIVNLLPDK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 13 spectra, AGTMSK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |