peptides
spectra
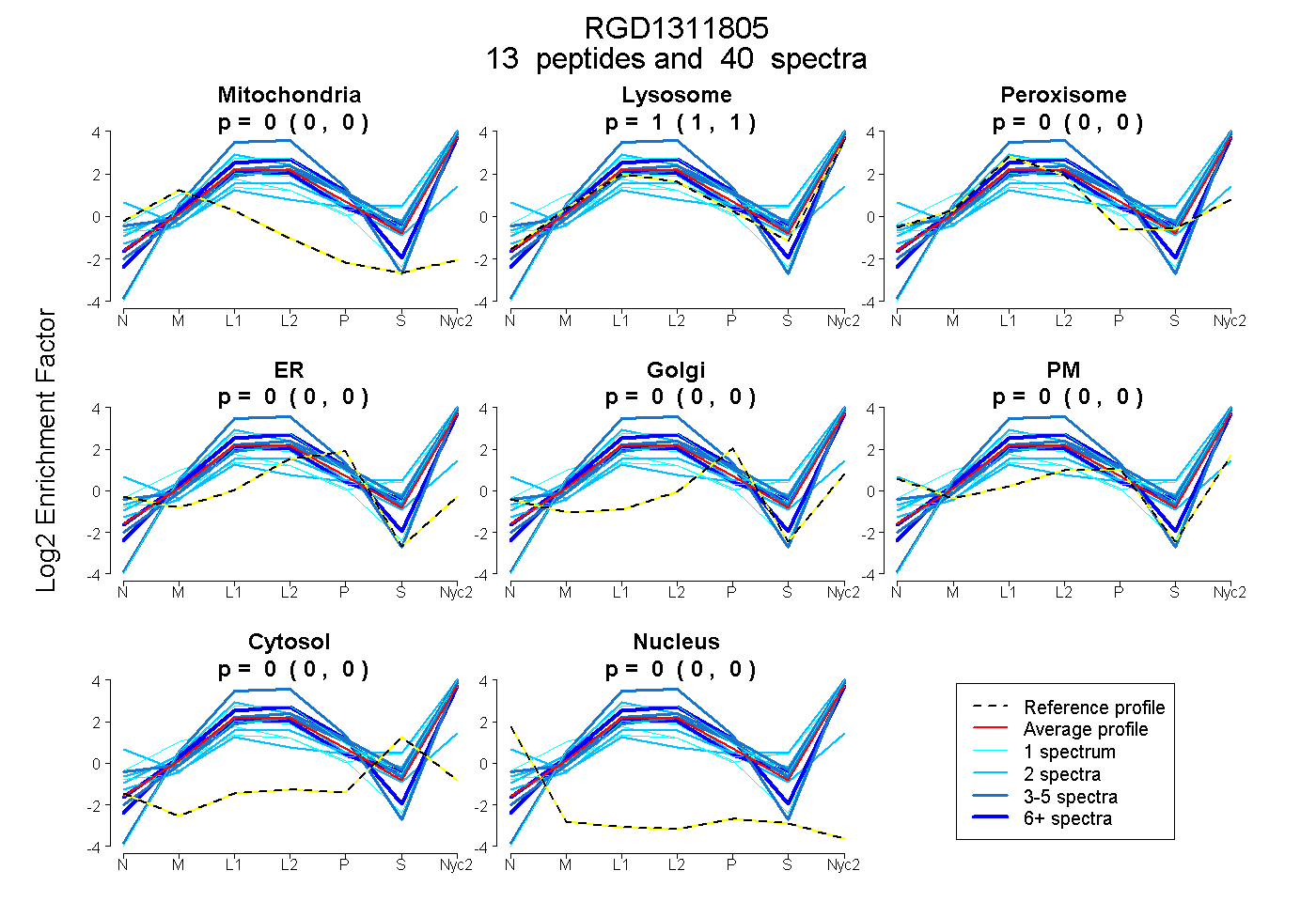
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
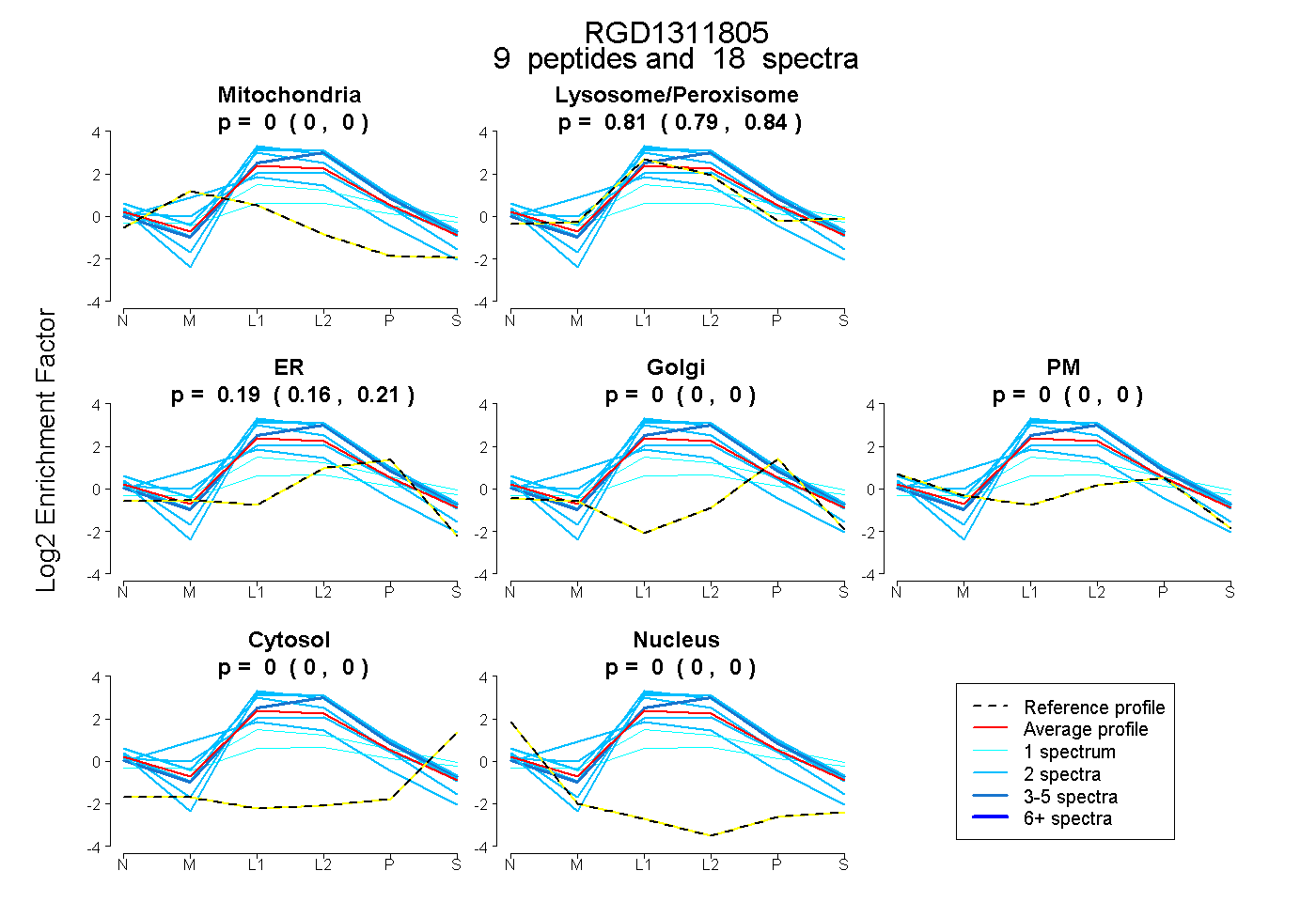
0.000 | 0.000
0.786 | 0.837
0.160 | 0.209
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
40 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
18 spectra |
 |
0.000 0.000 | 0.000 |
0.815 0.786 | 0.837 |
0.185 0.160 | 0.209 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, HQVLAALR | 0.000 | 0.977 | 0.023 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GIGGHDNISAR | 0.000 | 0.452 | 0.000 | 0.000 | 0.435 | 0.101 | 0.012 | |||
| 2 spectra, ANPVNCVFFDEANK | 0.351 | 0.507 | 0.142 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, ATLPVIATVFDK | 0.000 | 0.938 | 0.062 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LLAVQR | 0.000 | 0.880 | 0.120 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, SGGATGVVVK | 0.000 | 0.766 | 0.186 | 0.000 | 0.048 | 0.000 | 0.000 | |||
| 2 spectra, QVFAVR | 0.000 | 0.969 | 0.031 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, LMDFLLQR | 0.000 | 0.870 | 0.130 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GNPNFTPGEHCEEHVAFFK | 0.000 | 0.755 | 0.000 | 0.229 | 0.000 | 0.016 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
137 spectra |
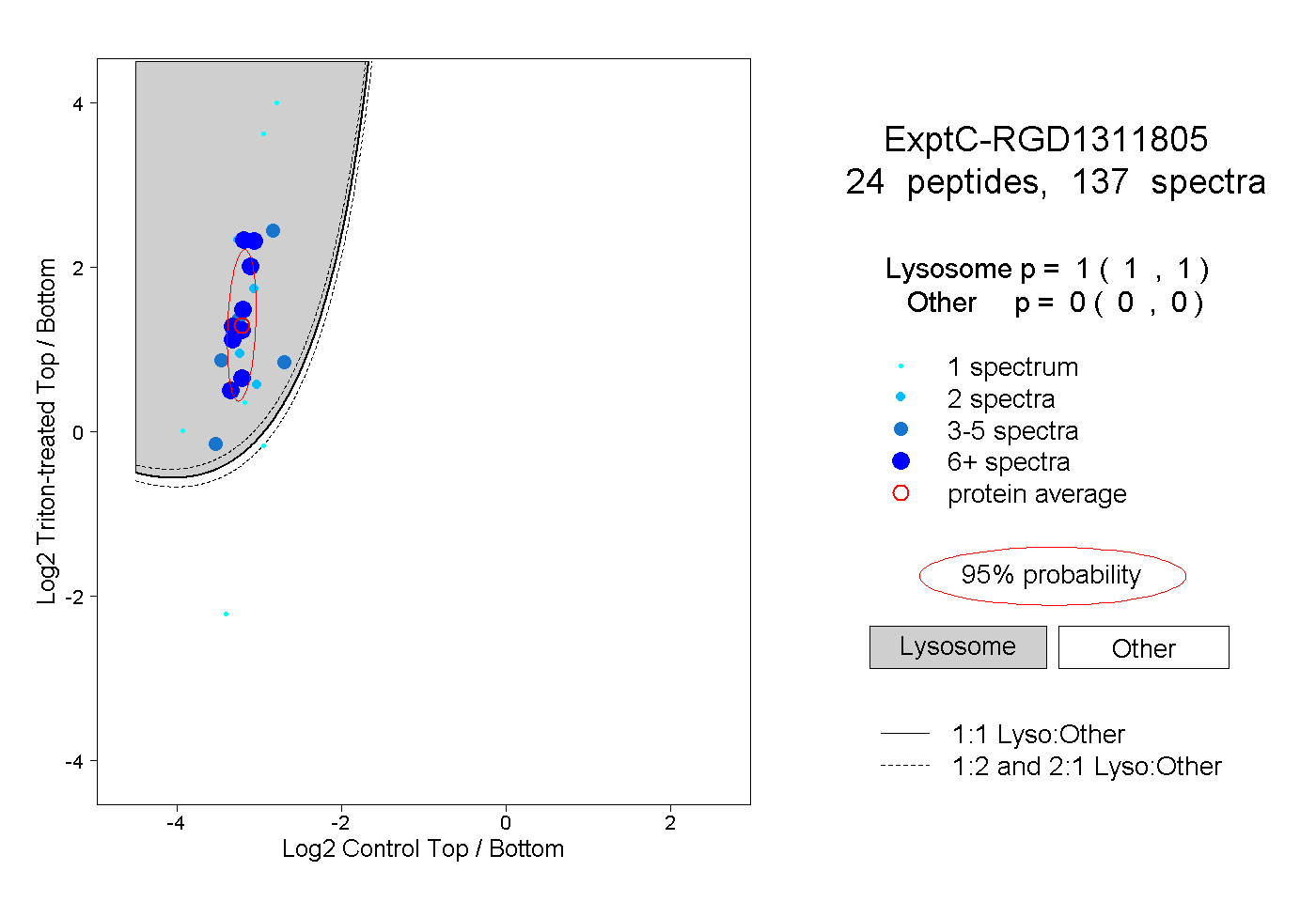 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
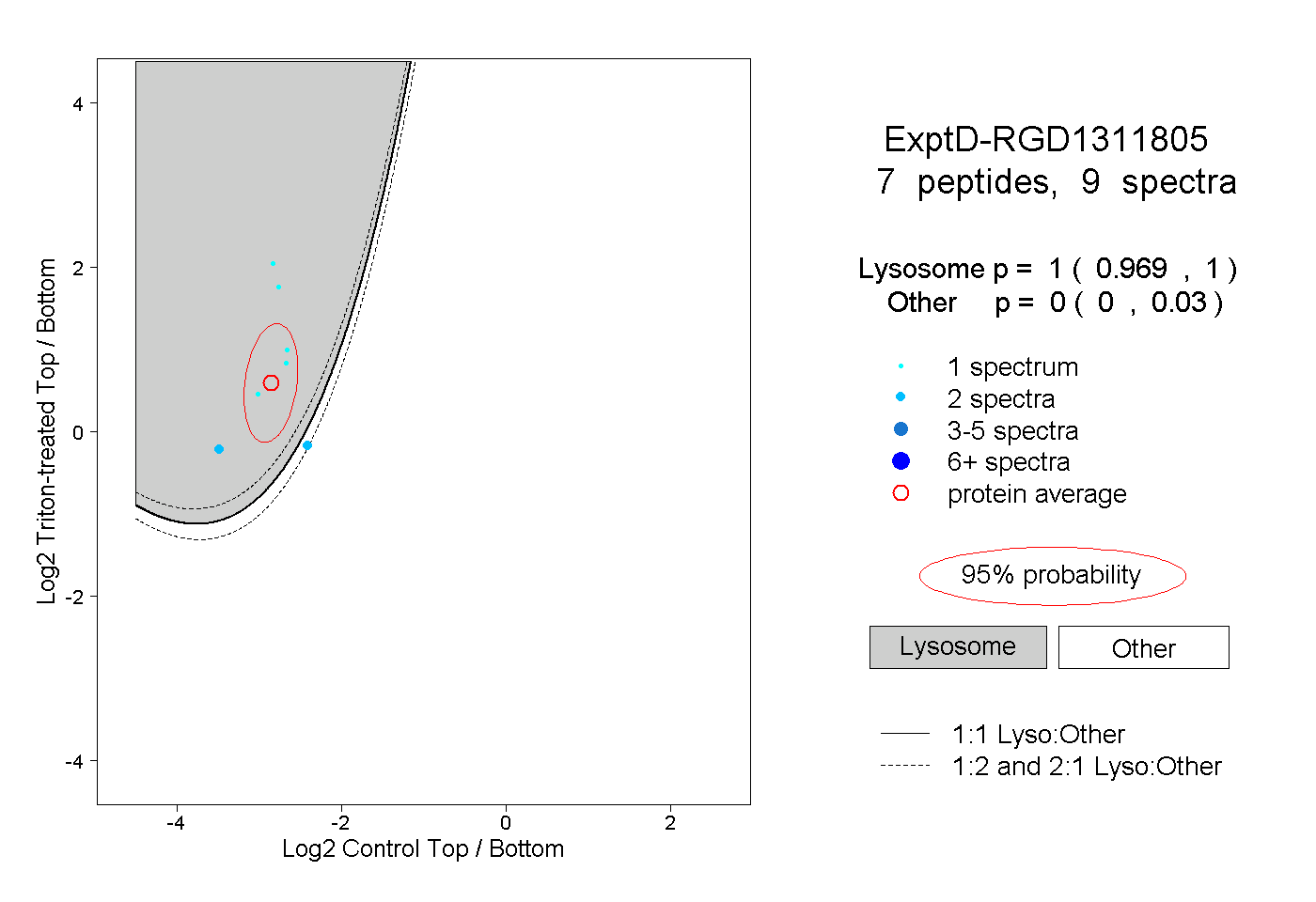 |
1.000 0.969 | 1.000 |
0.000 0.000 | 0.030 |