peptides
spectra
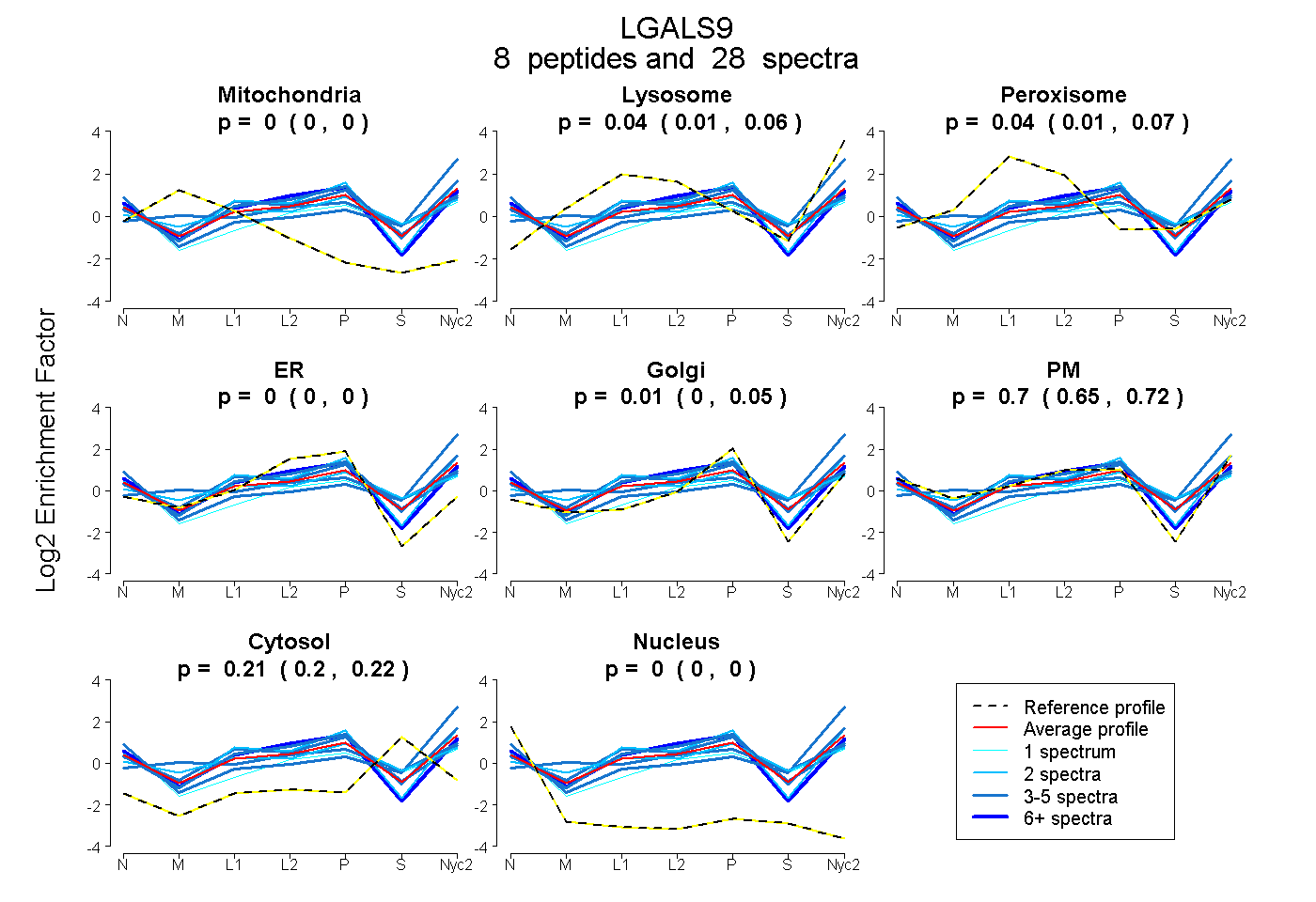
0.000 | 0.000
0.009 | 0.060
0.013 | 0.069
0.000 | 0.000
0.000 | 0.047
0.651 | 0.718
0.197 | 0.223
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
28 spectra |
 |
0.000 0.000 | 0.000 |
0.037 0.009 | 0.060 |
0.041 0.013 | 0.069 |
0.000 0.000 | 0.000 |
0.013 0.000 | 0.047 |
0.696 0.651 | 0.718 |
0.212 0.197 | 0.223 |
0.000 0.000 | 0.000 |
| 4 spectra, NTQINNSWGPEER | 0.000 | 0.137 | 0.000 | 0.000 | 0.000 | 0.595 | 0.268 | 0.000 | ||
| 9 spectra, FHINLR | 0.000 | 0.000 | 0.022 | 0.187 | 0.000 | 0.710 | 0.081 | 0.000 | ||
| 4 spectra, NFFVQYSHR | 0.001 | 0.114 | 0.177 | 0.000 | 0.188 | 0.281 | 0.238 | 0.000 | ||
| 2 spectra, MQMPFQK | 0.000 | 0.060 | 0.091 | 0.000 | 0.258 | 0.568 | 0.023 | 0.000 | ||
| 2 spectra, VAVDGQHICEYYHR | 0.000 | 0.000 | 0.255 | 0.000 | 0.248 | 0.276 | 0.221 | 0.000 | ||
| 1 spectrum, CGGDIAFHLNPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.606 | 0.365 | 0.029 | ||
| 3 spectra, GMPFELCFLVQR | 0.000 | 0.000 | 0.290 | 0.000 | 0.336 | 0.266 | 0.108 | 0.000 | ||
| 3 spectra, WGPEER | 0.000 | 0.124 | 0.035 | 0.000 | 0.117 | 0.593 | 0.131 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
8 spectra |
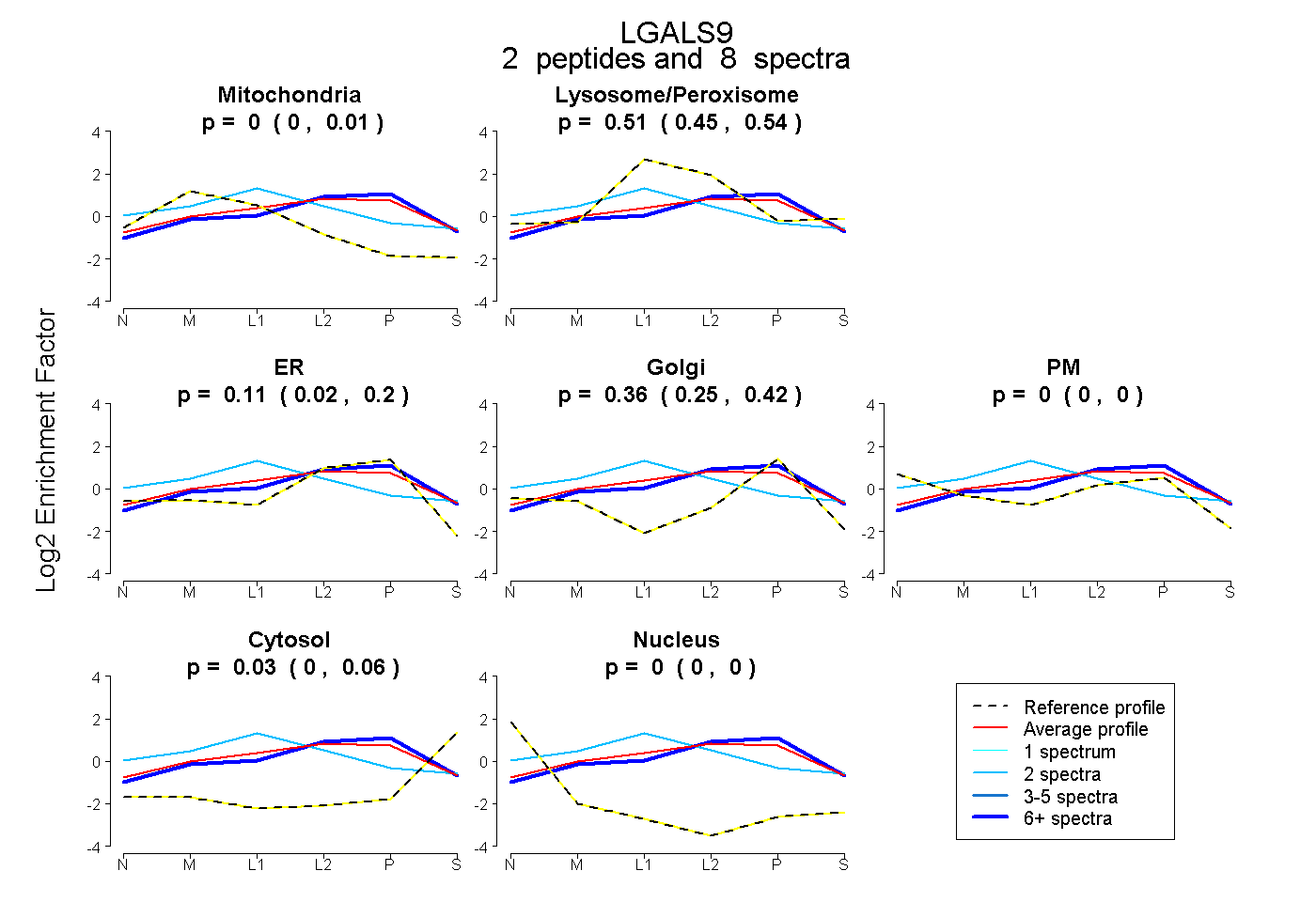 |
0.000 0.000 | 0.015 |
0.506 0.451 | 0.544 |
0.113 0.024 | 0.203 |
0.355 0.251 | 0.423 |
0.000 0.000 | 0.000 |
0.025 0.000 | 0.059 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
58 spectra |
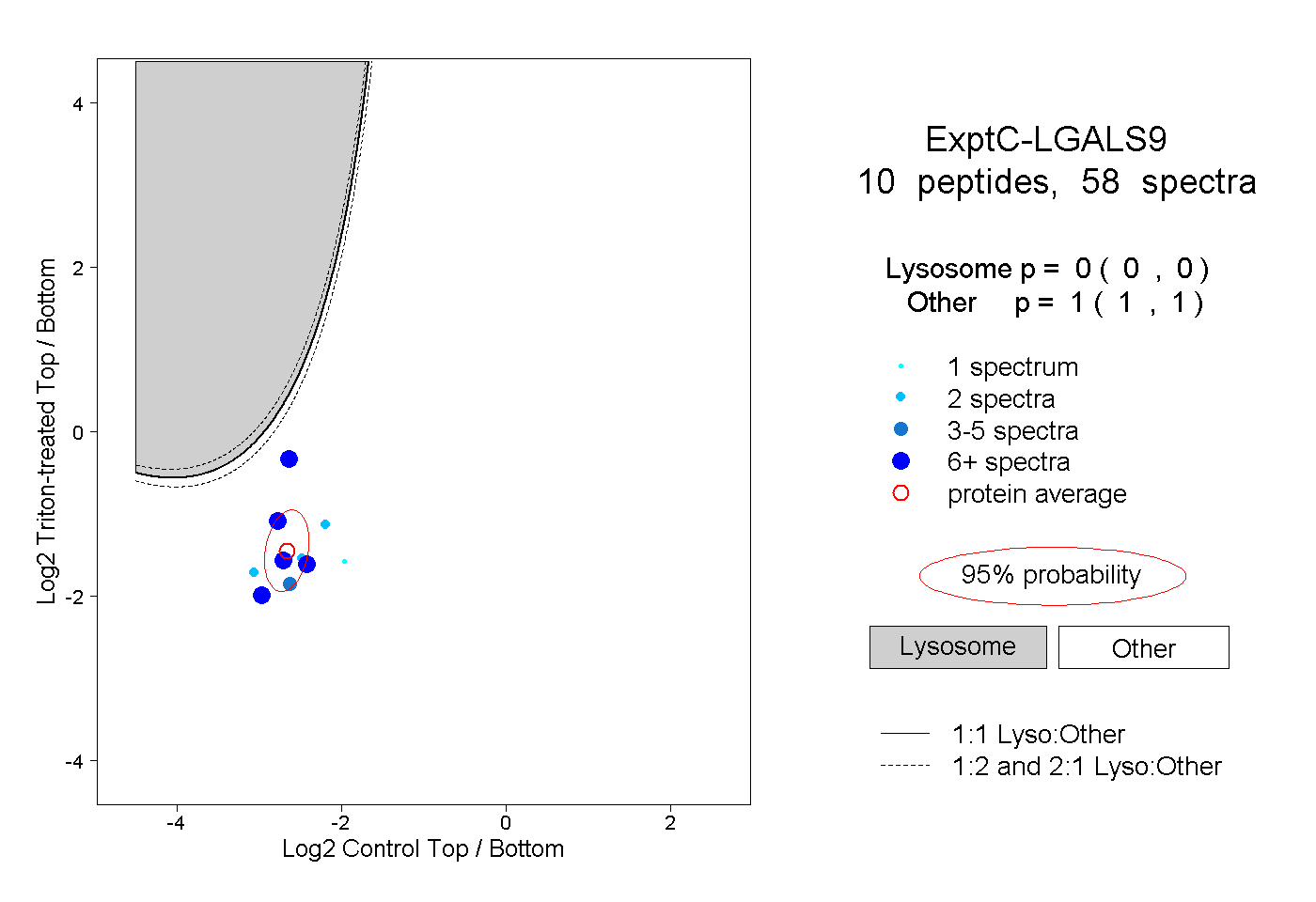 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
8 spectra |
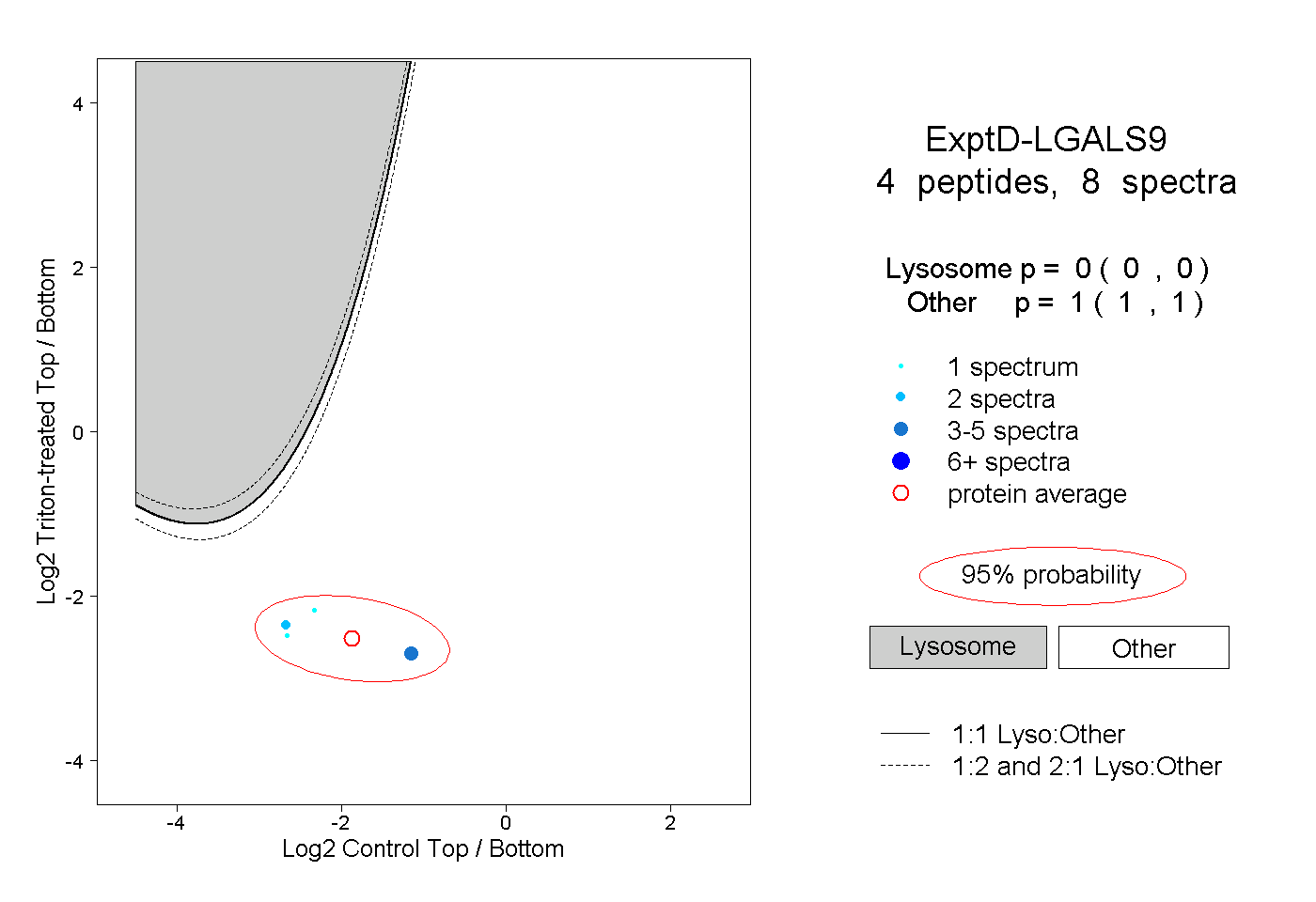 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |