peptides
spectra
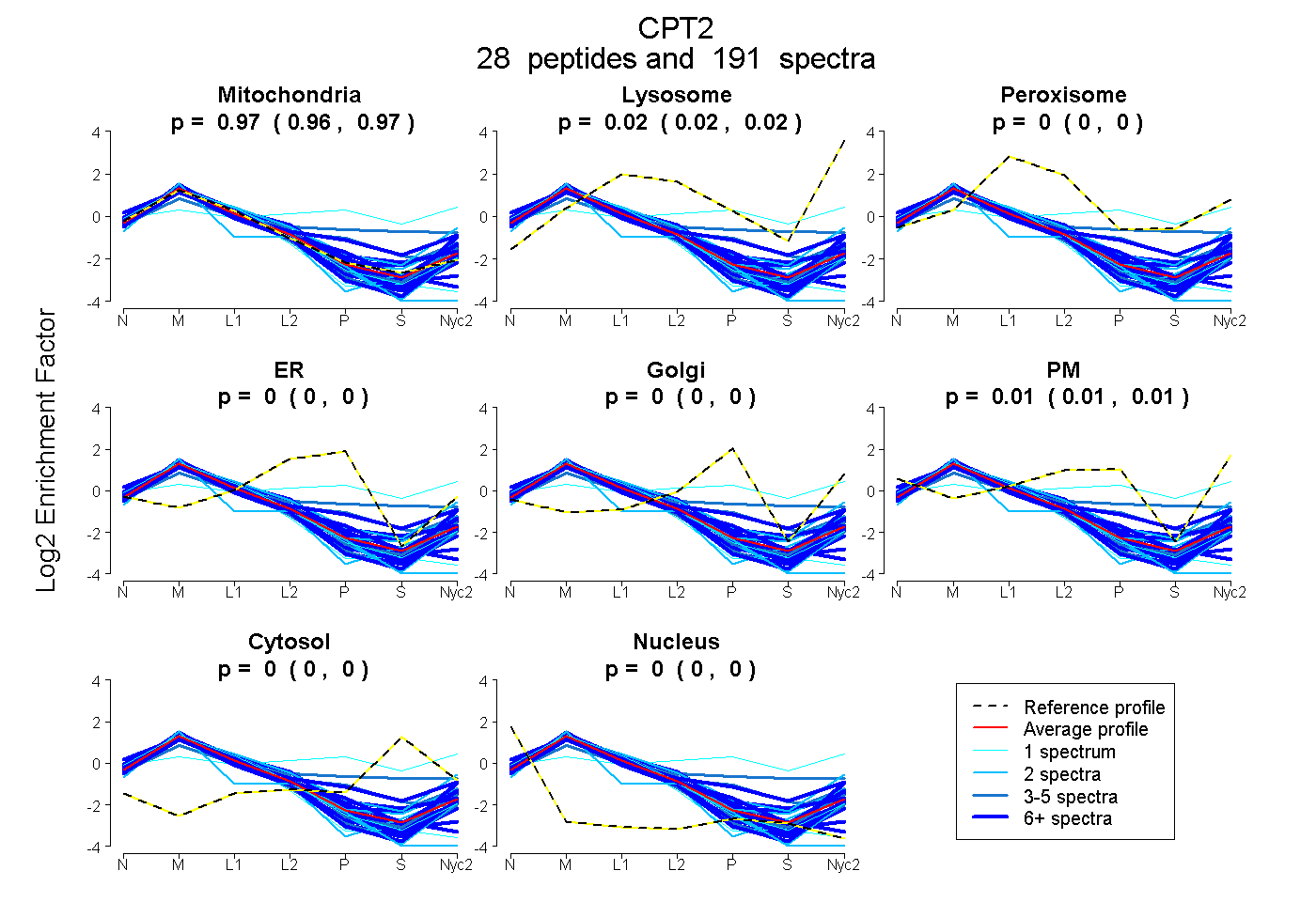
0.965 | 0.970
0.017 | 0.024
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.007 | 0.015
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
191 spectra |
 |
0.968 0.965 | 0.970 |
0.021 0.017 | 0.024 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.011 0.007 | 0.015 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, LIFDGNEETLK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, ELHAHLLAQDK | 0.886 | 0.039 | 0.000 | 0.000 | 0.000 | 0.074 | 0.000 | 0.000 | ||
| 4 spectra, DELFTDTK | 0.776 | 0.000 | 0.000 | 0.147 | 0.000 | 0.000 | 0.077 | 0.000 | ||
| 2 spectra, FDTTVK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, IPRPNR | 0.932 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.068 | ||
| 2 spectra, LEDTMK | 0.892 | 0.108 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, LFNSTR | 0.868 | 0.042 | 0.000 | 0.000 | 0.000 | 0.045 | 0.000 | 0.045 | ||
| 28 spectra, HLLILR | 0.983 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.017 | ||
| 8 spectra, TLSIDSIQFQR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, HLYALR | 0.995 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.005 | ||
| 7 spectra, CLEDIFDALEGK | 0.958 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.042 | ||
| 1 spectrum, DLIHLSHTMLHGDGTNR | 0.117 | 0.052 | 0.197 | 0.000 | 0.133 | 0.263 | 0.239 | 0.000 | ||
| 14 spectra, SEYNDQLTR | 0.875 | 0.012 | 0.007 | 0.000 | 0.000 | 0.049 | 0.057 | 0.000 | ||
| 2 spectra, VDSAVFCLCLDDFPMK | 0.858 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.142 | ||
| 1 spectrum, YLNAQKPLLDDSQFR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, TEALCK | 0.764 | 0.197 | 0.000 | 0.000 | 0.000 | 0.039 | 0.000 | 0.000 | ||
| 7 spectra, HSVGELQHMMAECSK | 0.995 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.005 | ||
| 2 spectra, NFETGVGK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 7 spectra, FFNEVFR | 0.956 | 0.044 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 18 spectra, YLATAR | 0.696 | 0.132 | 0.000 | 0.000 | 0.109 | 0.000 | 0.063 | 0.000 | ||
| 7 spectra, TETIRPASIFTK | 0.999 | 0.000 | 0.000 | 0.000 | 0.000 | 0.001 | 0.000 | 0.000 | ||
| 5 spectra, CSEAFVR | 0.888 | 0.072 | 0.000 | 0.000 | 0.000 | 0.000 | 0.040 | 0.000 | ||
| 5 spectra, QYGQTVATYESCSTAAFK | 0.963 | 0.037 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 14 spectra, DVWAELR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 15 spectra, EAAMGQGFDR | 0.906 | 0.071 | 0.000 | 0.000 | 0.000 | 0.000 | 0.023 | 0.000 | ||
| 10 spectra, ATNLTVSAVR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, EFLHCVQK | 0.456 | 0.048 | 0.155 | 0.000 | 0.136 | 0.000 | 0.205 | 0.000 | ||
| 8 spectra, YHGQLTK | 0.860 | 0.036 | 0.000 | 0.000 | 0.023 | 0.081 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
121 spectra |
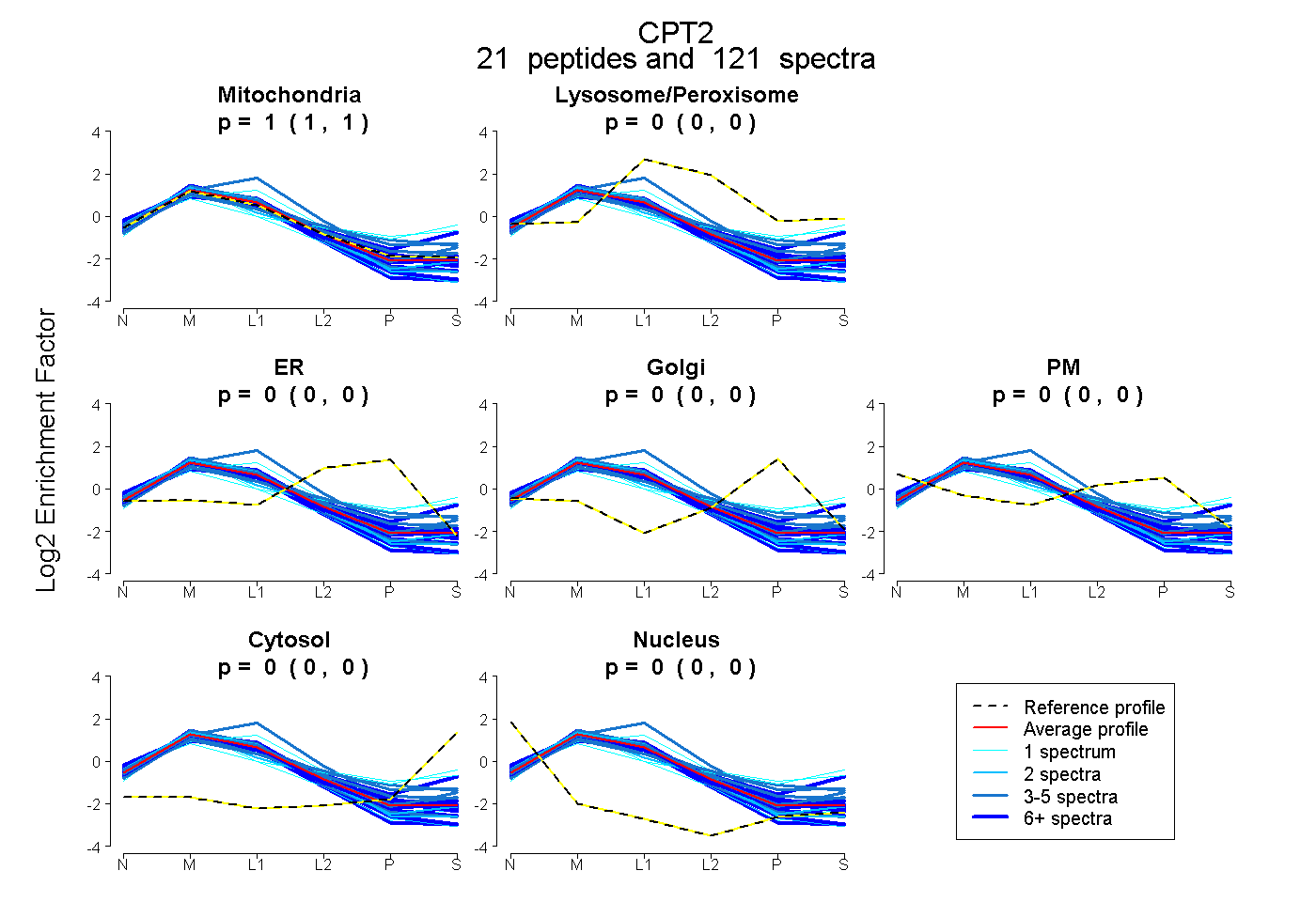 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
761 spectra |
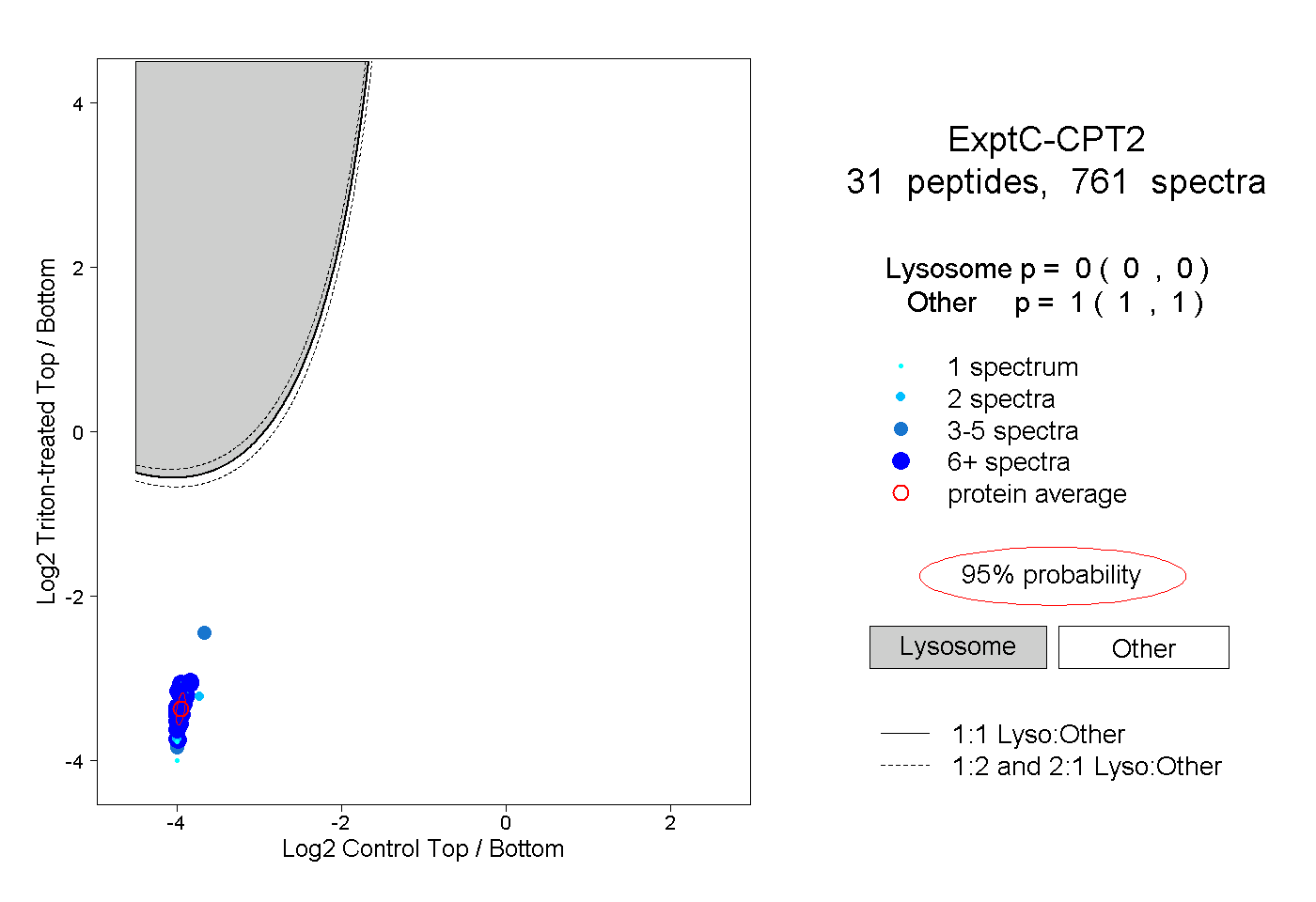 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
65 spectra |
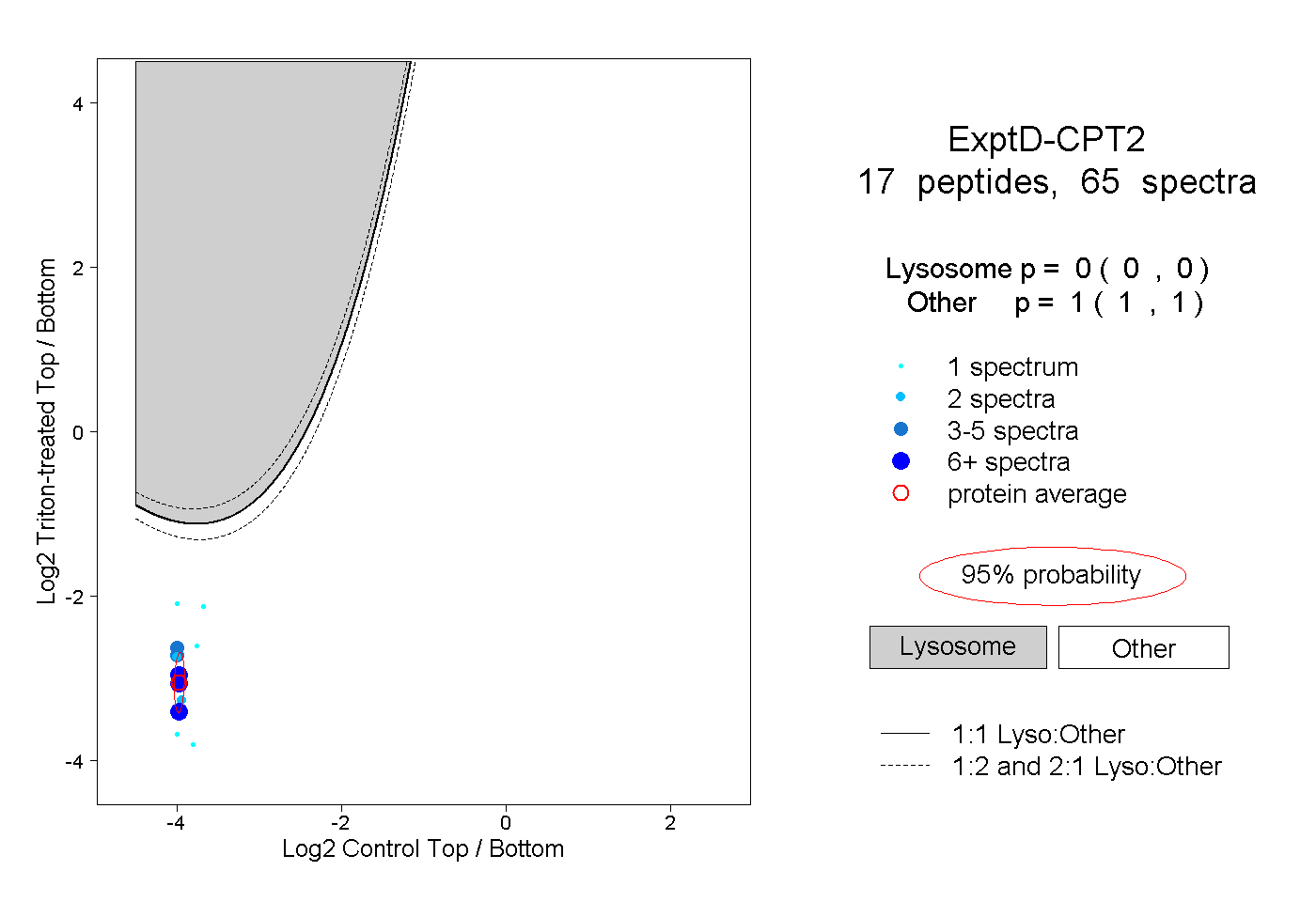 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |