peptides
spectra
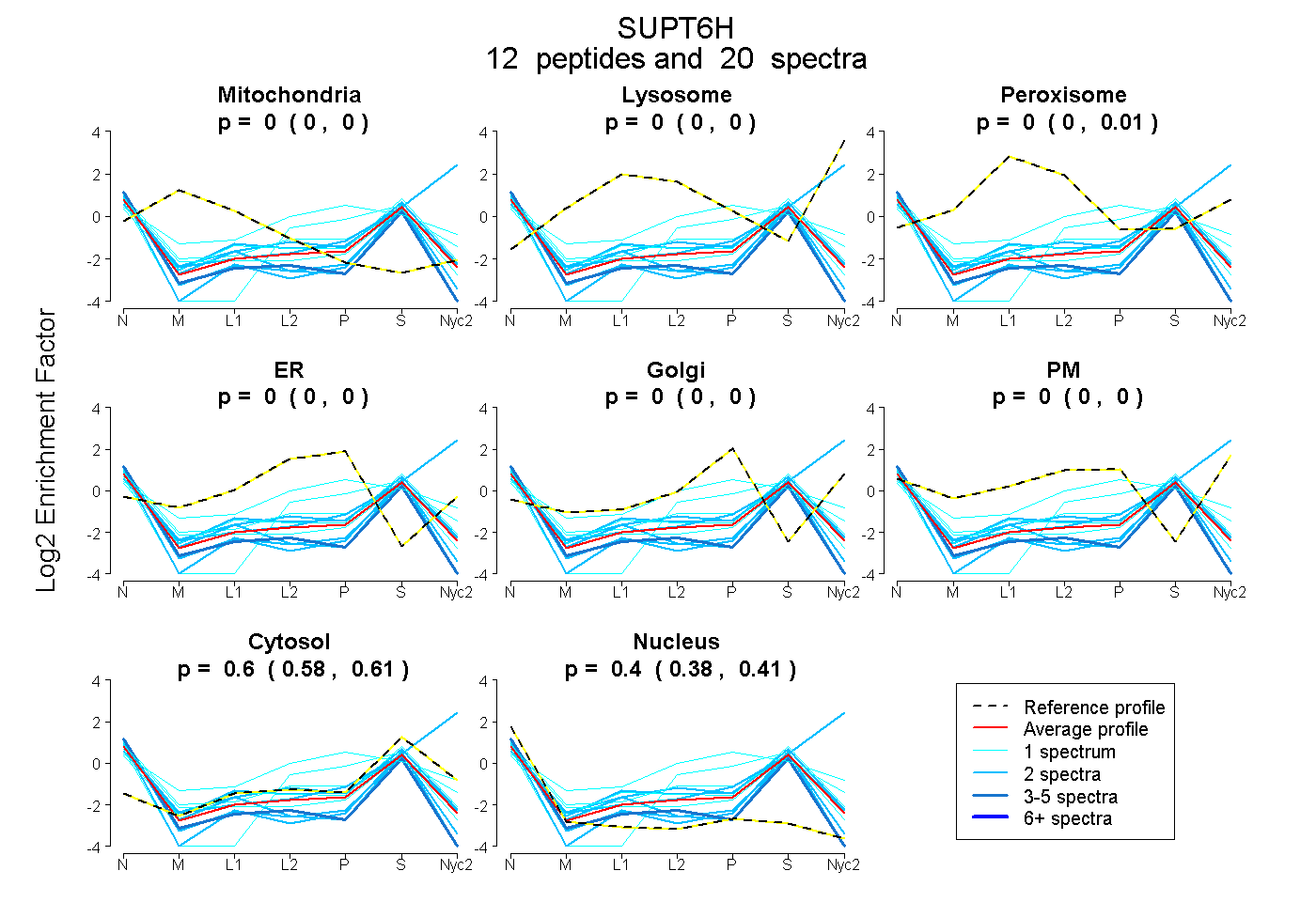
0.000 | 0.000
0.000 | 0.000
0.000 | 0.007
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.584 | 0.613
0.383 | 0.413
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
20 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.007 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.602 0.584 | 0.613 |
0.398 0.383 | 0.413 |
| 2 spectra, LIICNVTGIAHR | 0.000 | 0.227 | 0.000 | 0.000 | 0.000 | 0.000 | 0.545 | 0.229 | ||
| 2 spectra, VNEVGVDVNR | 0.000 | 0.000 | 0.000 | 0.043 | 0.000 | 0.000 | 0.587 | 0.370 | ||
| 2 spectra, FLLGYQPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.402 | 0.598 | ||
| 1 spectrum, YMVALQIAR | 0.000 | 0.000 | 0.003 | 0.000 | 0.000 | 0.000 | 0.548 | 0.449 | ||
| 3 spectra, VLGIAFSSAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.380 | 0.620 | ||
| 2 spectra, DEFSHQVQEWNR | 0.000 | 0.000 | 0.074 | 0.000 | 0.000 | 0.000 | 0.611 | 0.315 | ||
| 2 spectra, GQPTSSFSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.407 | 0.593 | ||
| 1 spectrum, SPNTEEIFNMLTK | 0.000 | 0.000 | 0.051 | 0.000 | 0.000 | 0.000 | 0.672 | 0.277 | ||
| 2 spectra, ALDTTDMER | 0.000 | 0.000 | 0.069 | 0.000 | 0.000 | 0.000 | 0.504 | 0.427 | ||
| 1 spectrum, VSDGIYQHVDVR | 0.000 | 0.000 | 0.000 | 0.346 | 0.000 | 0.121 | 0.473 | 0.060 | ||
| 1 spectrum, IEYVTVTPEGFR | 0.000 | 0.000 | 0.007 | 0.000 | 0.000 | 0.182 | 0.508 | 0.304 | ||
| 1 spectrum, FHPLQEHVVK | 0.000 | 0.000 | 0.000 | 0.016 | 0.000 | 0.000 | 0.515 | 0.469 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
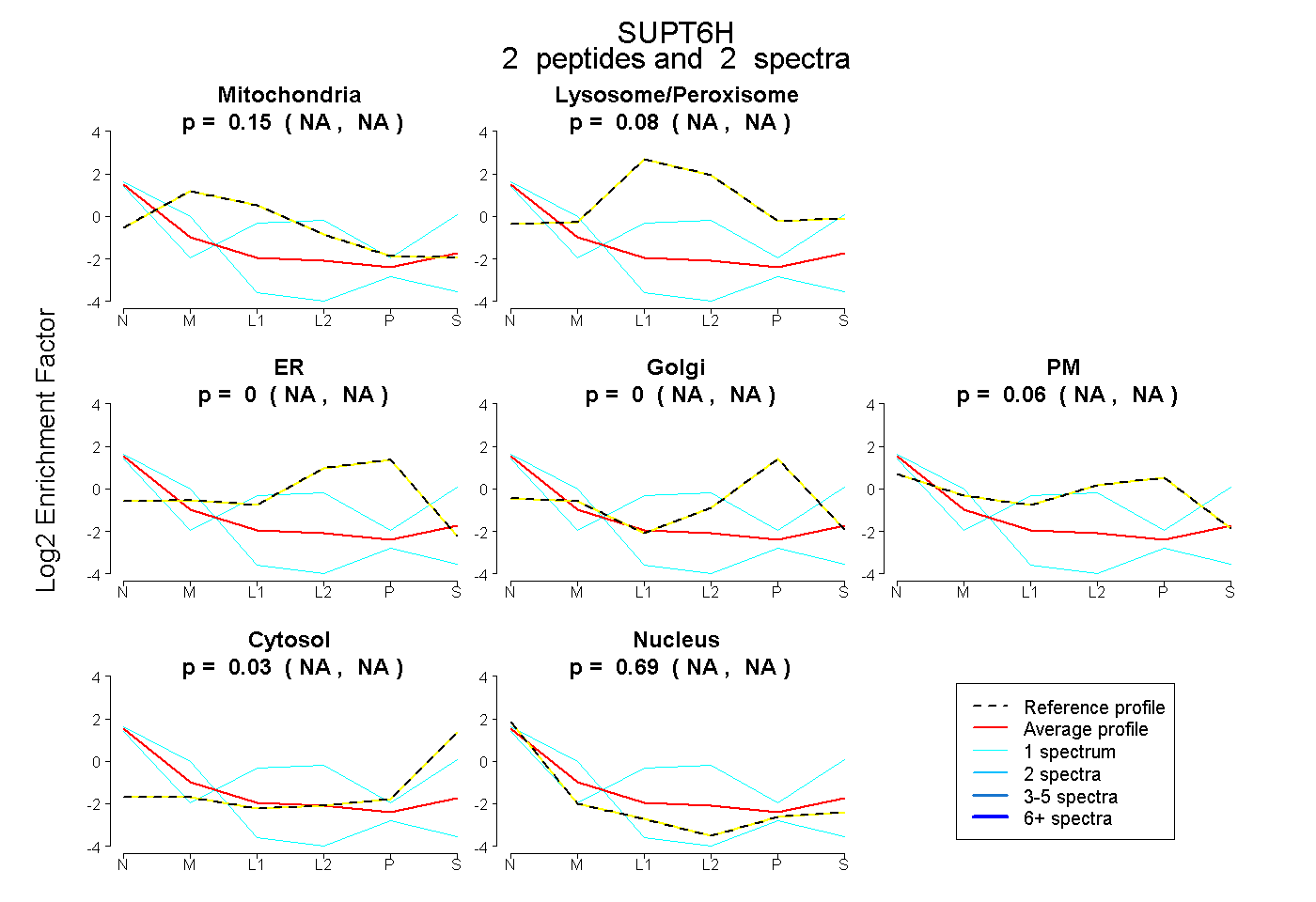 |
0.148 NA | NA |
0.075 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.063 NA | NA |
0.025 NA | NA |
0.688 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
8 spectra |
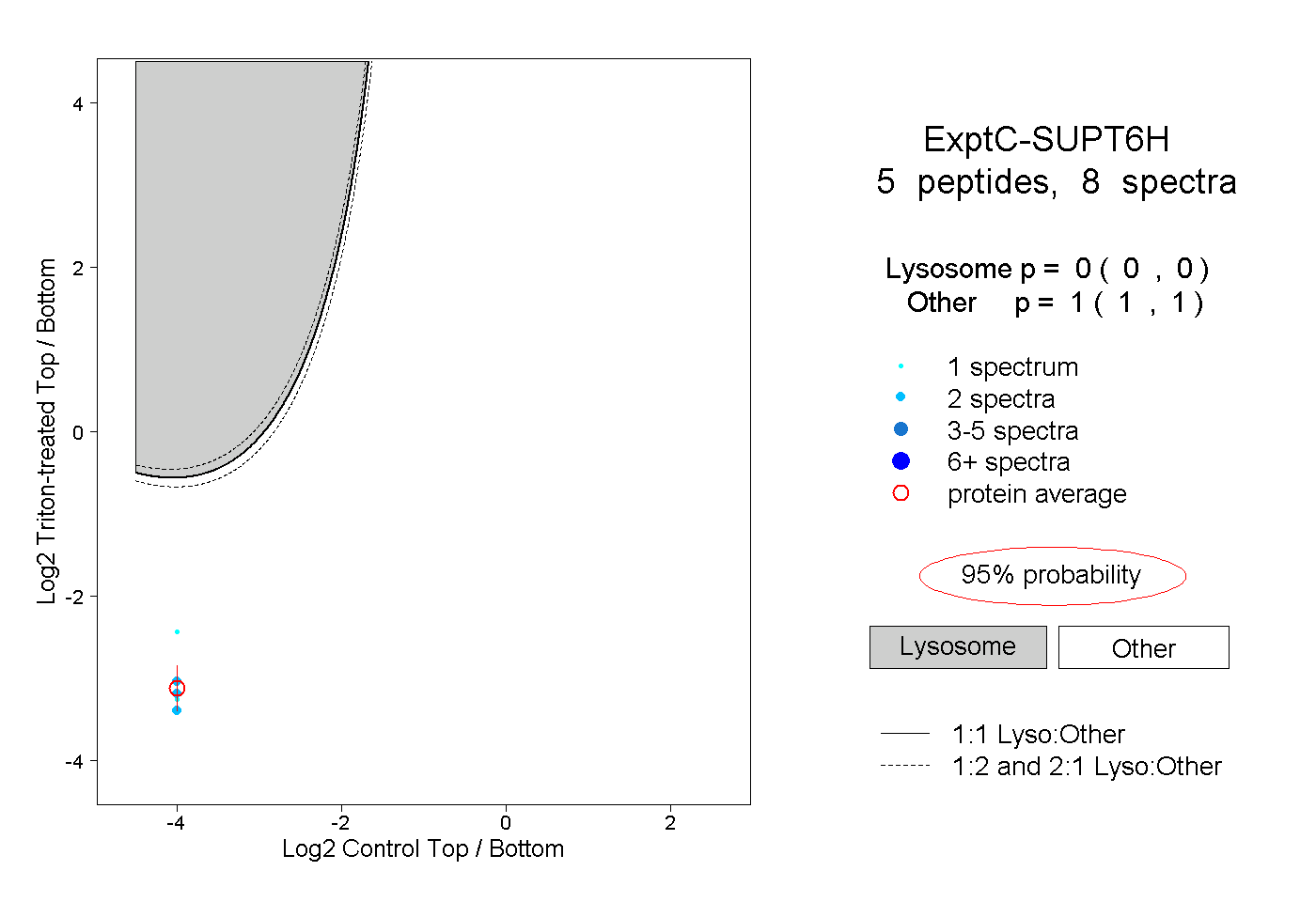 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |