peptides
spectra
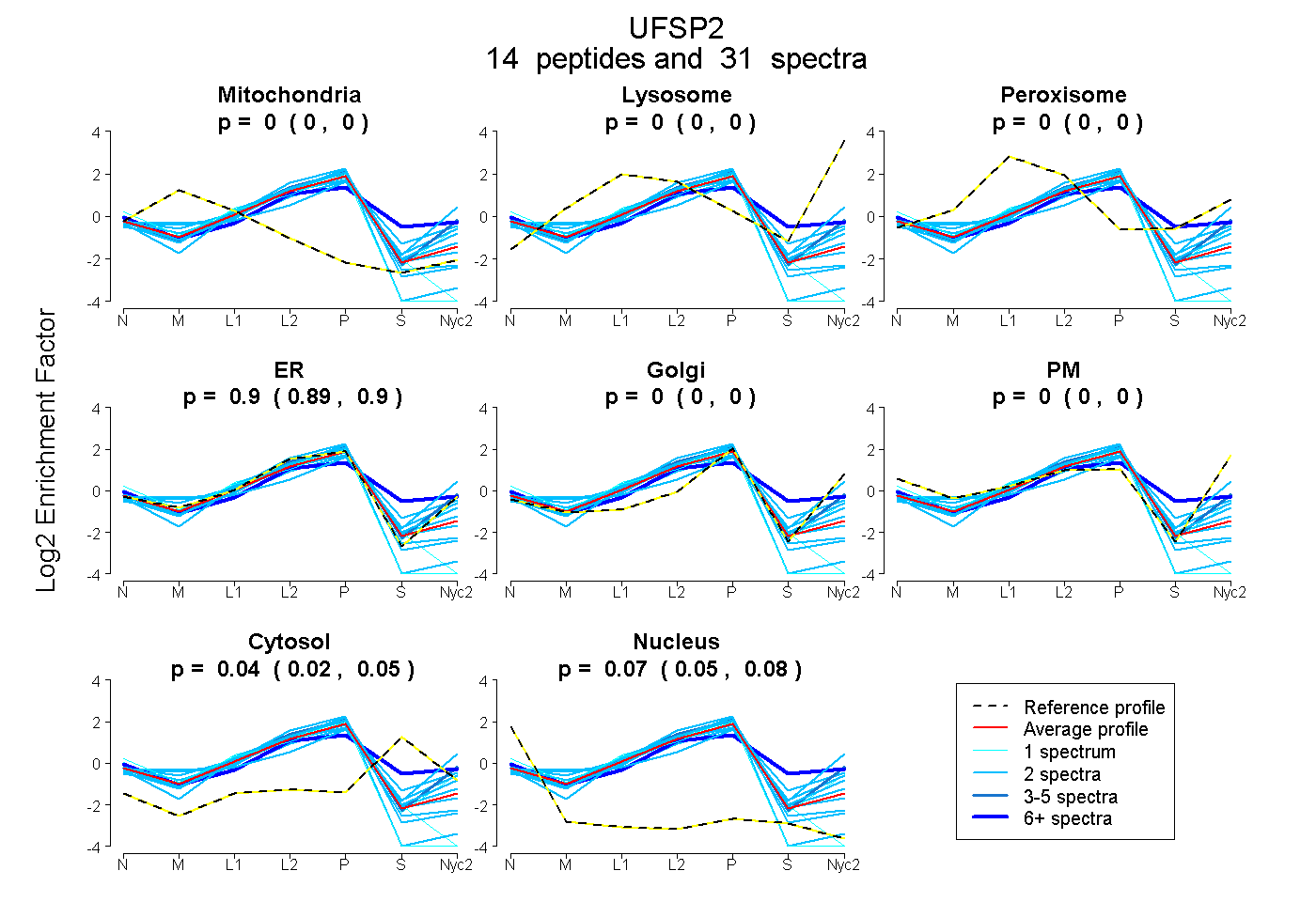
0.000 | 0.001
0.000 | 0.000
0.000 | 0.000
0.888 | 0.905
0.000 | 0.000
0.000 | 0.000
0.020 | 0.050
0.054 | 0.076
peptides
spectra
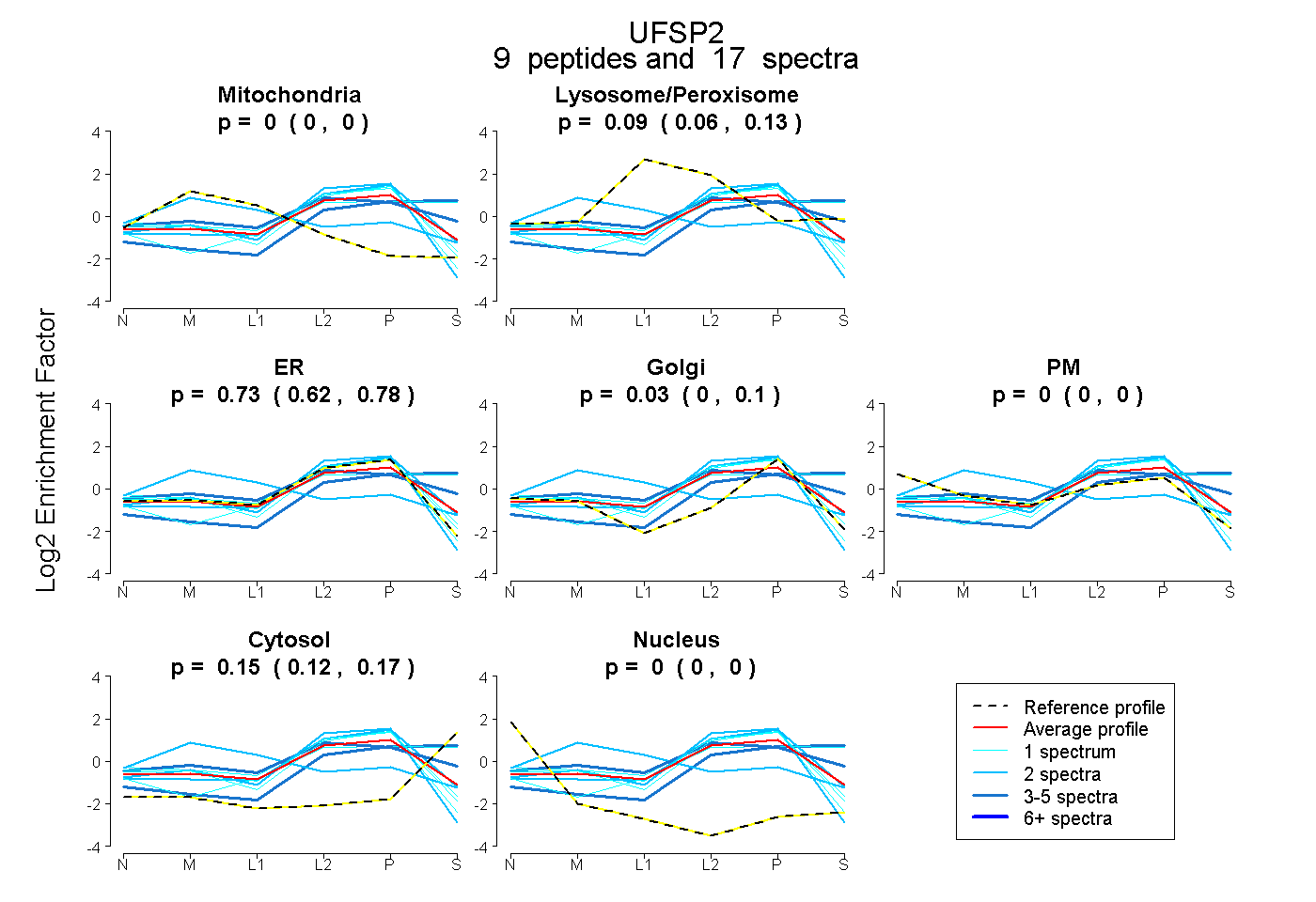
0.000 | 0.000
0.062 | 0.132
0.620 | 0.782
0.000 | 0.100
0.000 | 0.000
0.119 | 0.170
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
31 spectra |
 |
0.000 0.000 | 0.001 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.898 0.888 | 0.905 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.036 0.020 | 0.050 |
0.067 0.054 | 0.076 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
17 spectra |
 |
0.000 0.000 | 0.000 |
0.095 0.062 | 0.132 |
0.727 0.620 | 0.782 |
0.030 0.000 | 0.100 |
0.000 0.000 | 0.000 |
0.149 0.119 | 0.170 |
0.000 0.000 | 0.000 |
| 1 spectrum, SVVDLIQFDQEEDTK | 0.000 | 0.000 | 0.850 | 0.132 | 0.000 | 0.017 | 0.000 | |||
| 3 spectra, INAYHFPDELYK | 0.000 | 0.311 | 0.368 | 0.141 | 0.006 | 0.175 | 0.000 | |||
| 1 spectrum, FLILDPHYTGAEDLQVILEK | 0.000 | 0.241 | 0.376 | 0.000 | 0.000 | 0.383 | 0.000 | |||
| 1 spectrum, EIQQALVDAGDKPATFVGSR | 0.000 | 0.000 | 0.910 | 0.000 | 0.090 | 0.000 | 0.000 | |||
| 1 spectrum, SLQTVCSWFR | 0.000 | 0.030 | 0.879 | 0.000 | 0.051 | 0.040 | 0.000 | |||
| 2 spectra, ELHDLFK | 0.000 | 0.047 | 0.853 | 0.000 | 0.000 | 0.100 | 0.000 | |||
| 2 spectra, LPHDRPYLK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, ILFVNQGSEMASQGR | 0.510 | 0.204 | 0.000 | 0.286 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, DILFR | 0.000 | 0.033 | 0.476 | 0.000 | 0.000 | 0.492 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
39 spectra |
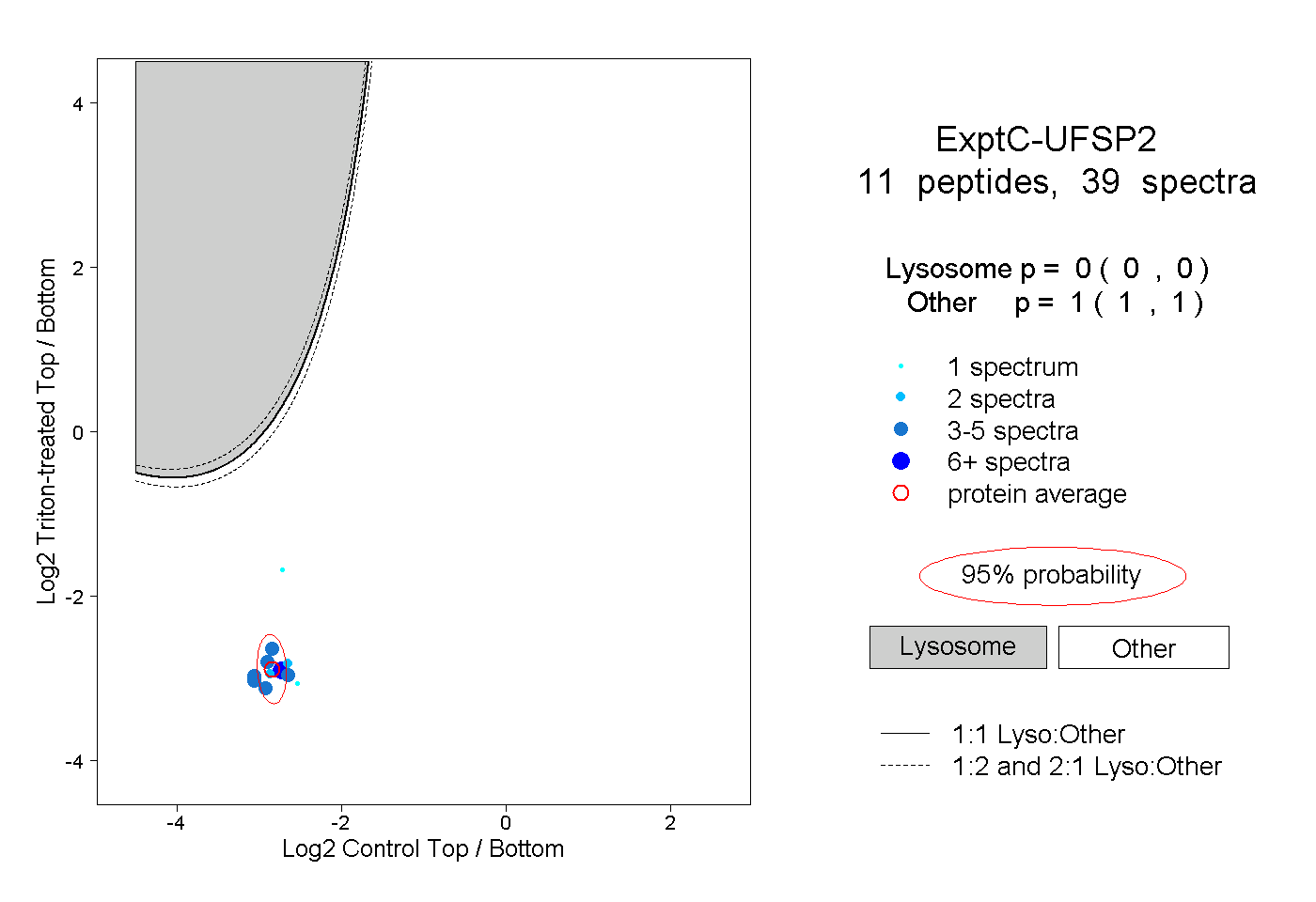 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
3 spectra |
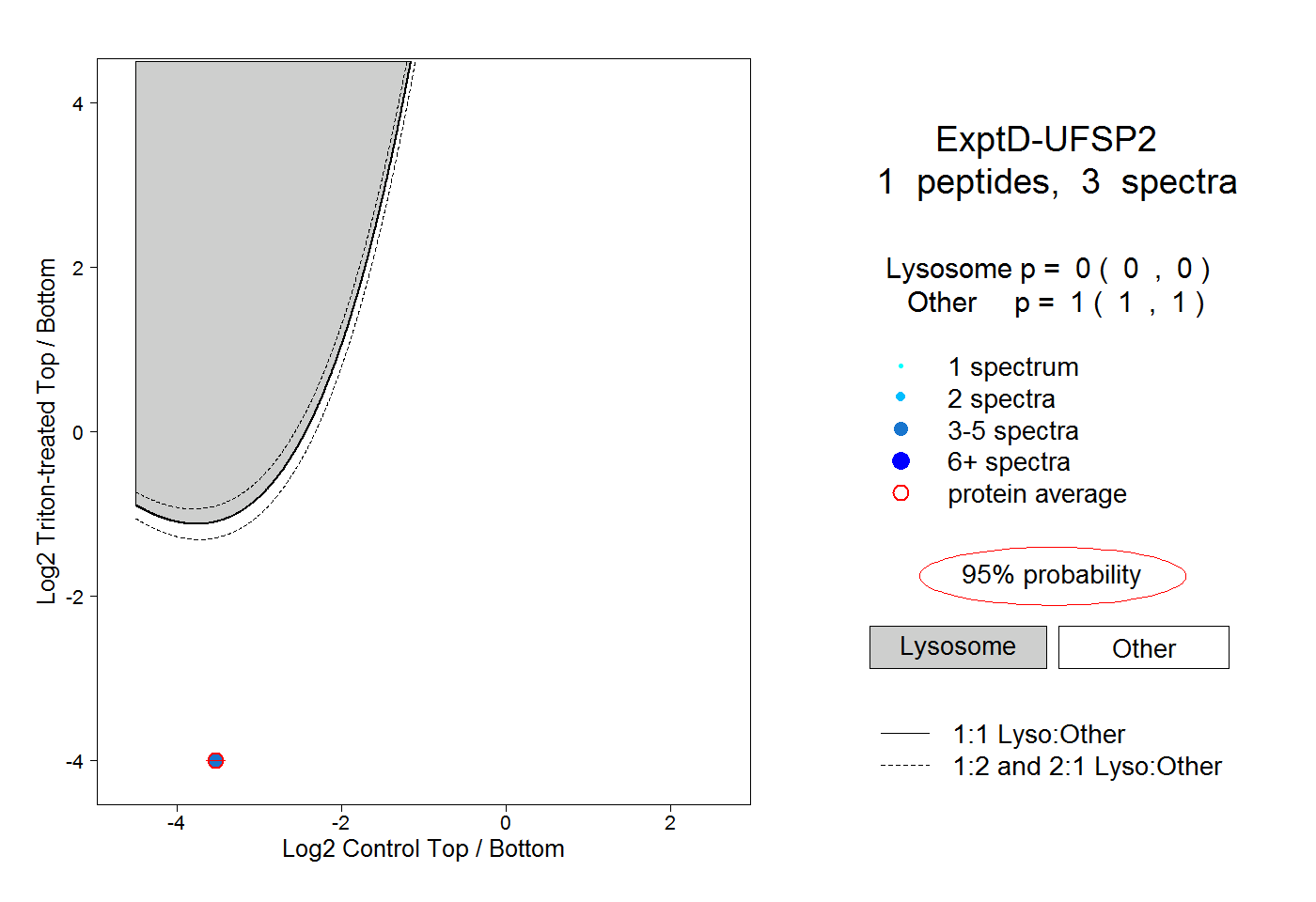 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |