peptides
spectra
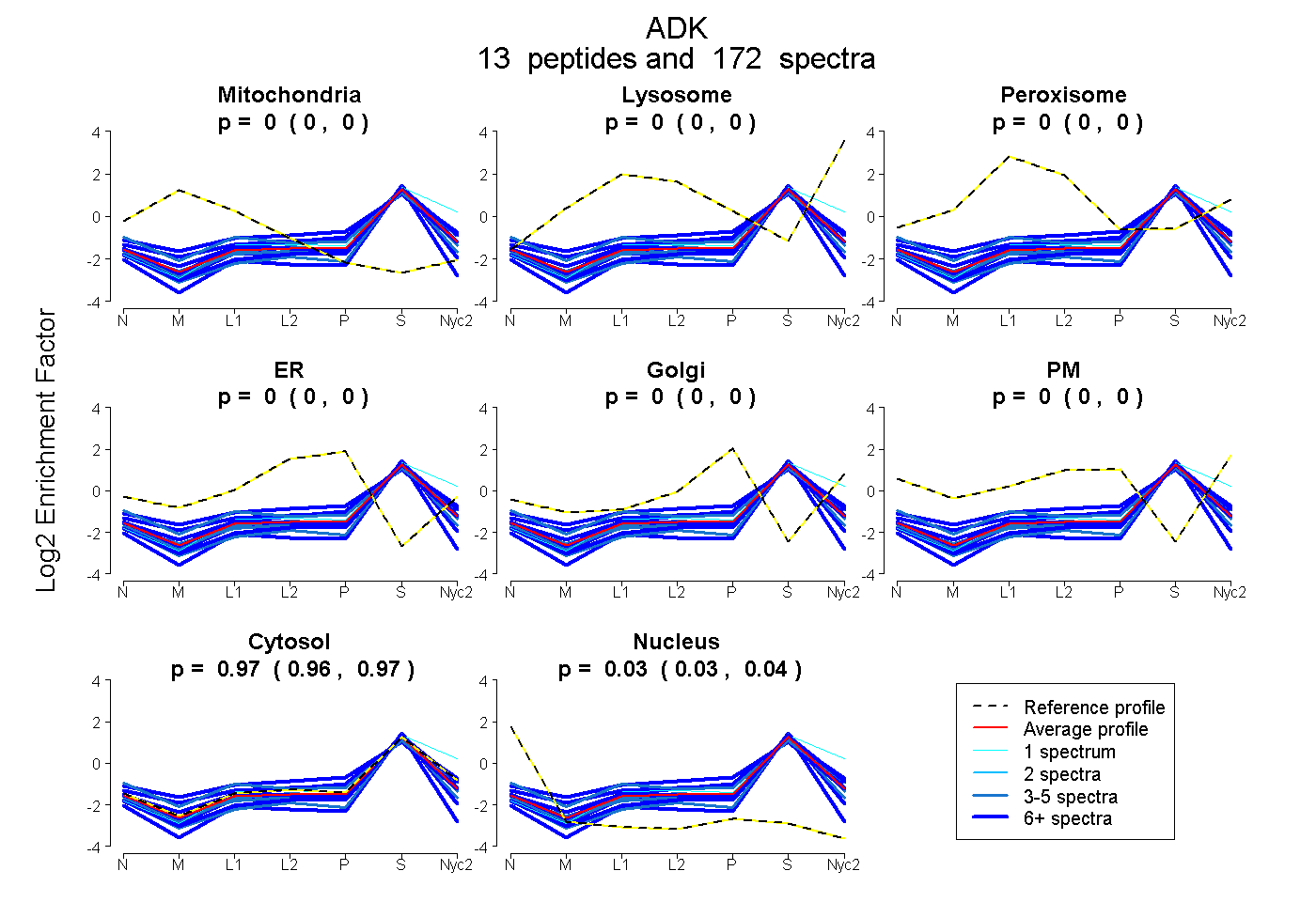
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.964 | 0.968
0.031 | 0.036
peptides
spectra
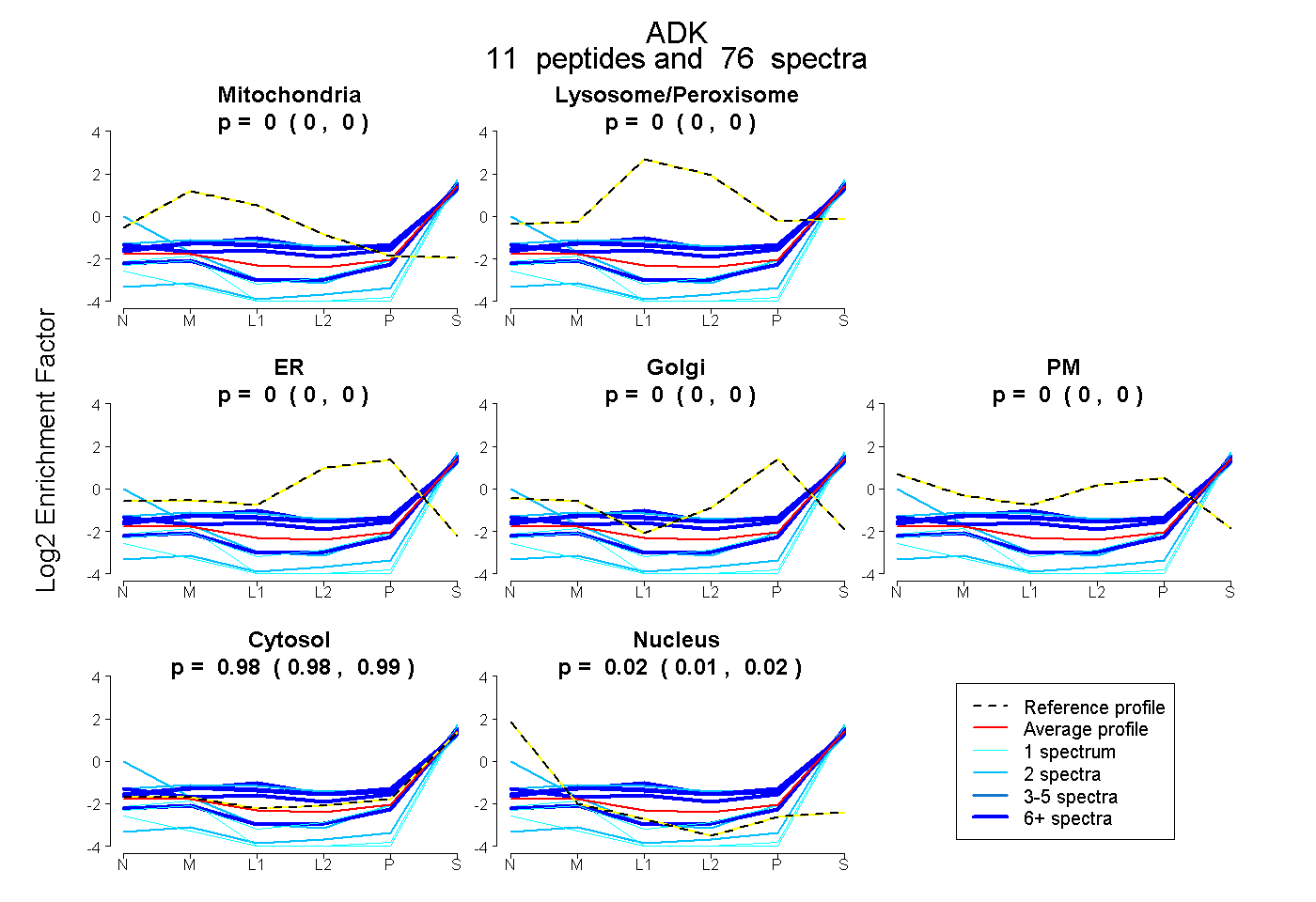
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.978 | 0.991
0.008 | 0.021
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
172 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.966 0.964 | 0.968 |
0.034 0.031 | 0.036 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
76 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.984 0.978 | 0.991 |
0.016 0.008 | 0.021 |
| 10 spectra, AATFFGCIGIDK | 0.006 | 0.155 | 0.000 | 0.000 | 0.000 | 0.839 | 0.000 | |||
| 12 spectra, AGHYAASVIIR | 0.000 | 0.192 | 0.000 | 0.000 | 0.000 | 0.808 | 0.000 | |||
| 1 spectrum, HLDLENNWMLVEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.902 | 0.098 | |||
| 2 spectra, TGCTFPEKPNFH | 0.030 | 0.192 | 0.000 | 0.001 | 0.000 | 0.777 | 0.000 | |||
| 2 spectra, SLVANLAAANCYK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.707 | 0.293 | |||
| 27 spectra, TVIFTQGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 7 spectra, VAQWMIQEPHR | 0.000 | 0.160 | 0.000 | 0.005 | 0.000 | 0.835 | 0.000 | |||
| 2 spectra, ELFDELVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, FGEILK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.952 | 0.048 | |||
| 11 spectra, YAAENNR | 0.000 | 0.096 | 0.000 | 0.000 | 0.000 | 0.885 | 0.018 | |||
| 1 spectrum, TVLFTNAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
117 spectra |
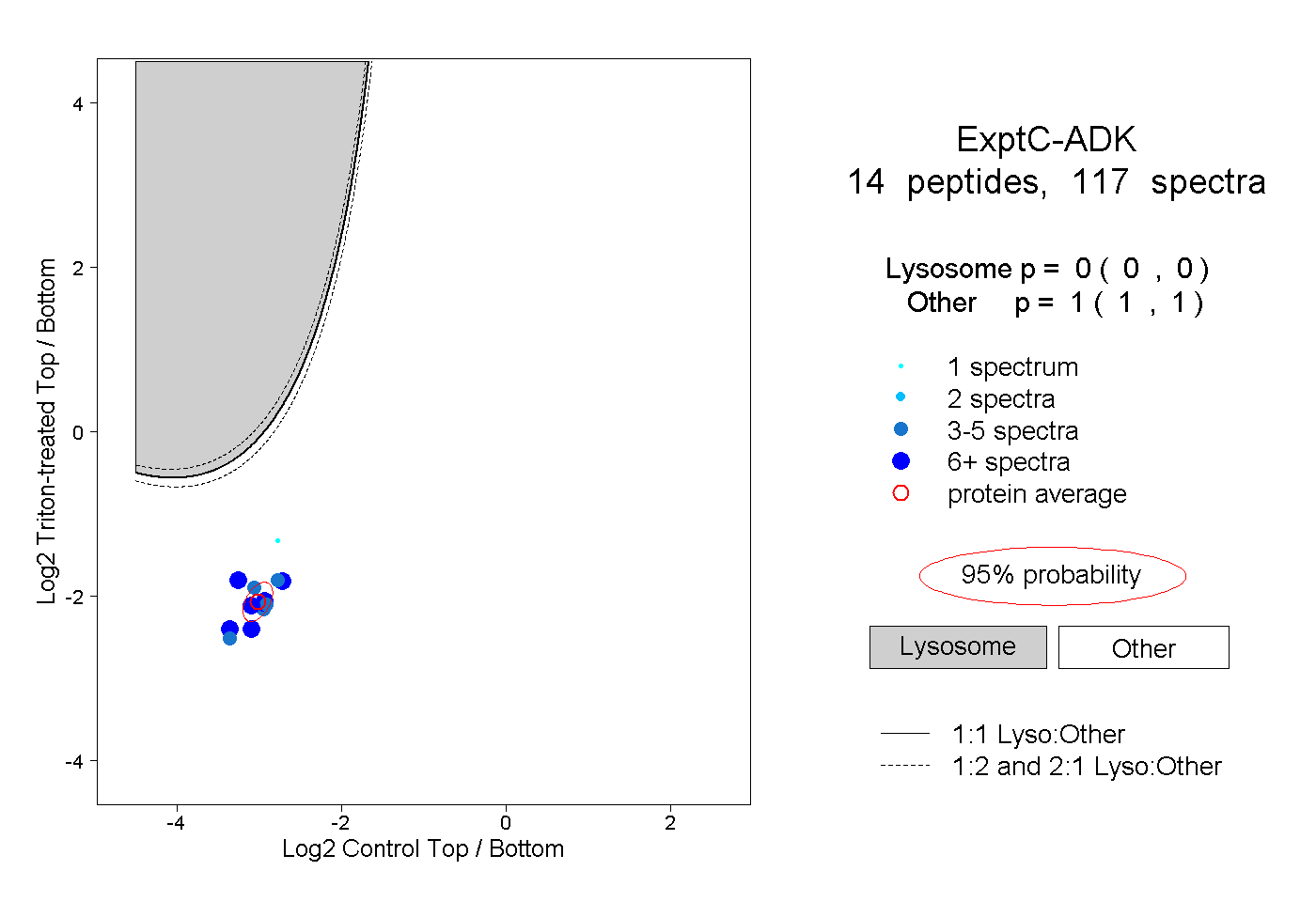 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
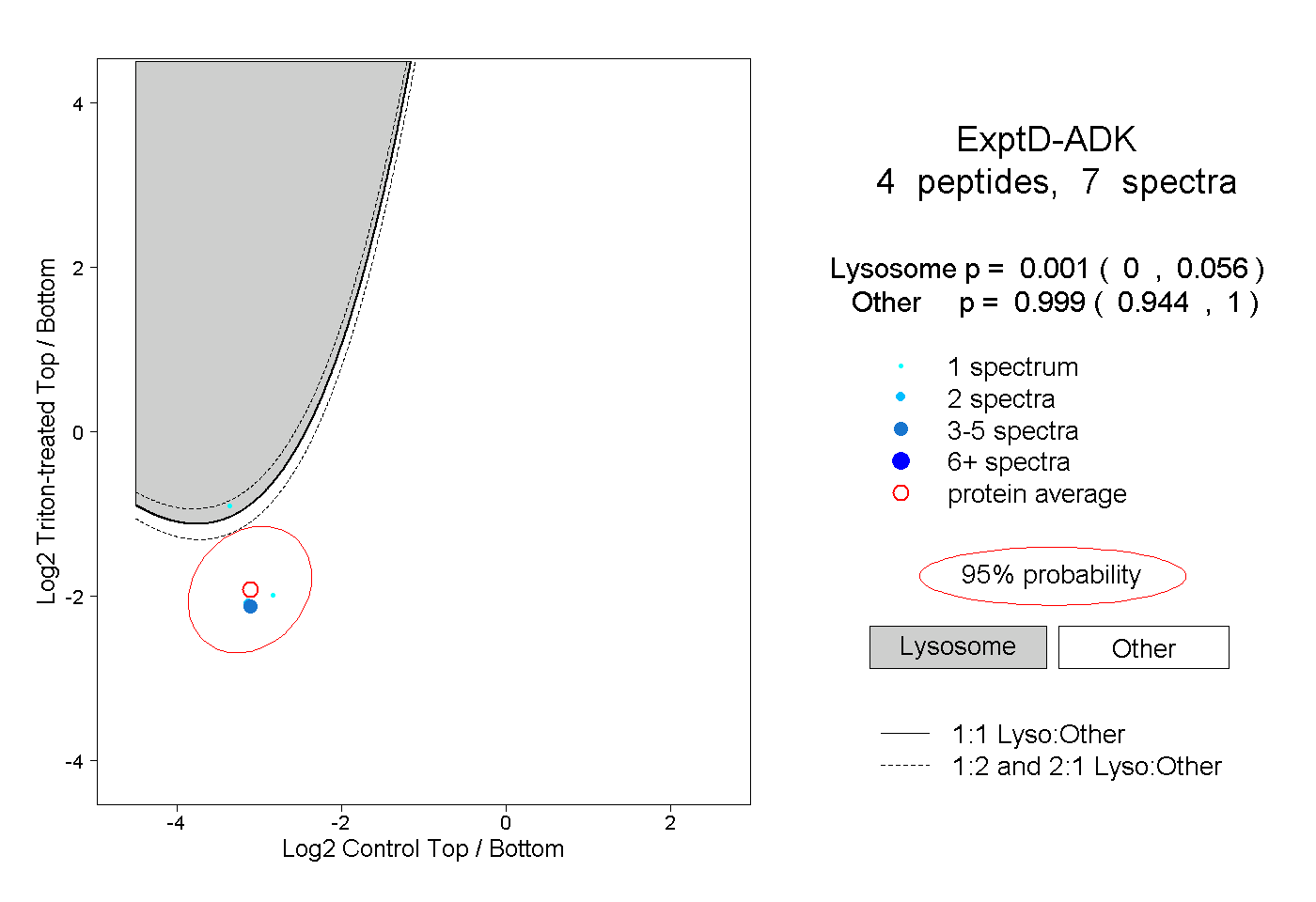 |
0.001 0.000 | 0.056 |
0.999 0.944 | 1.000 |