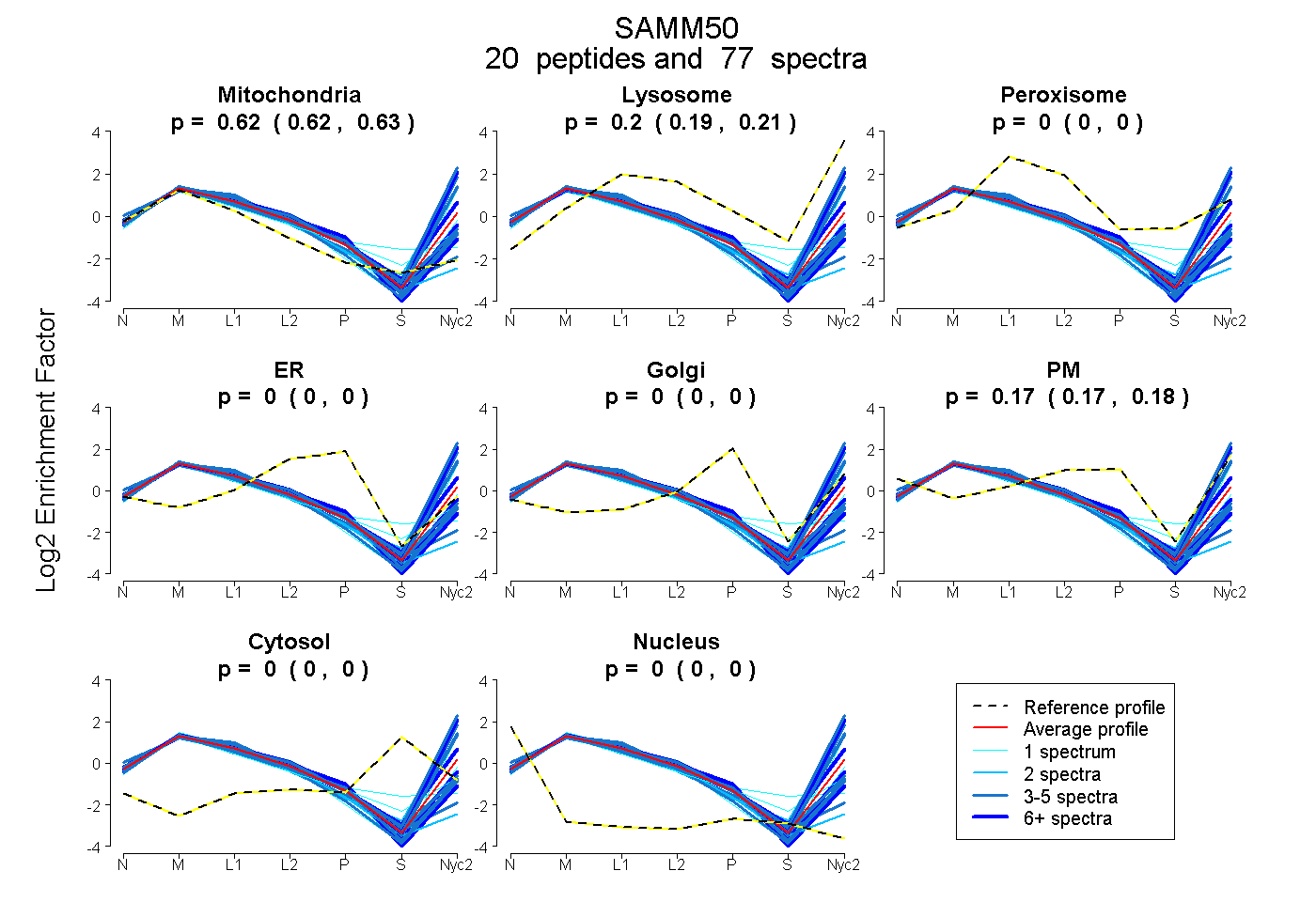
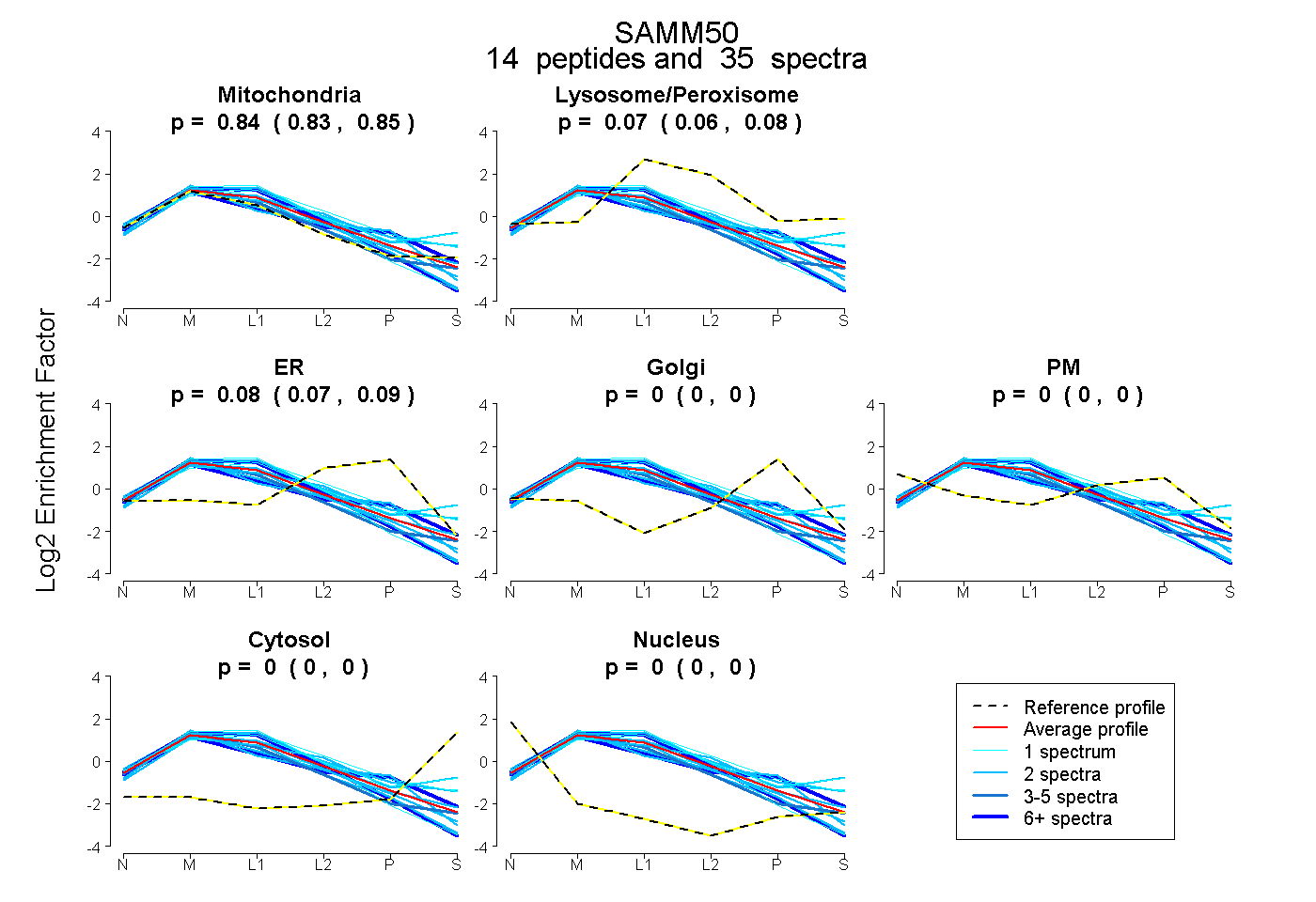
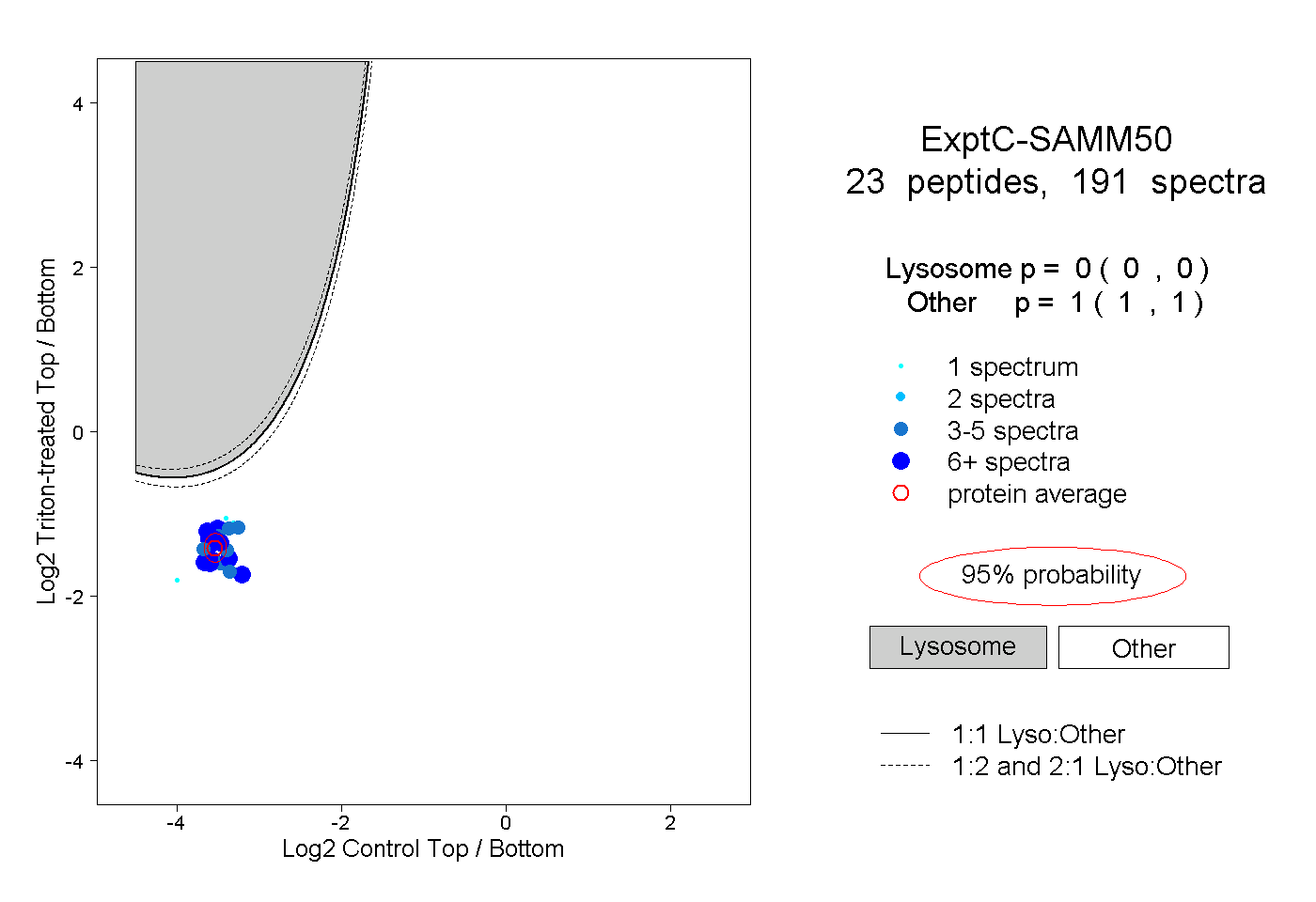
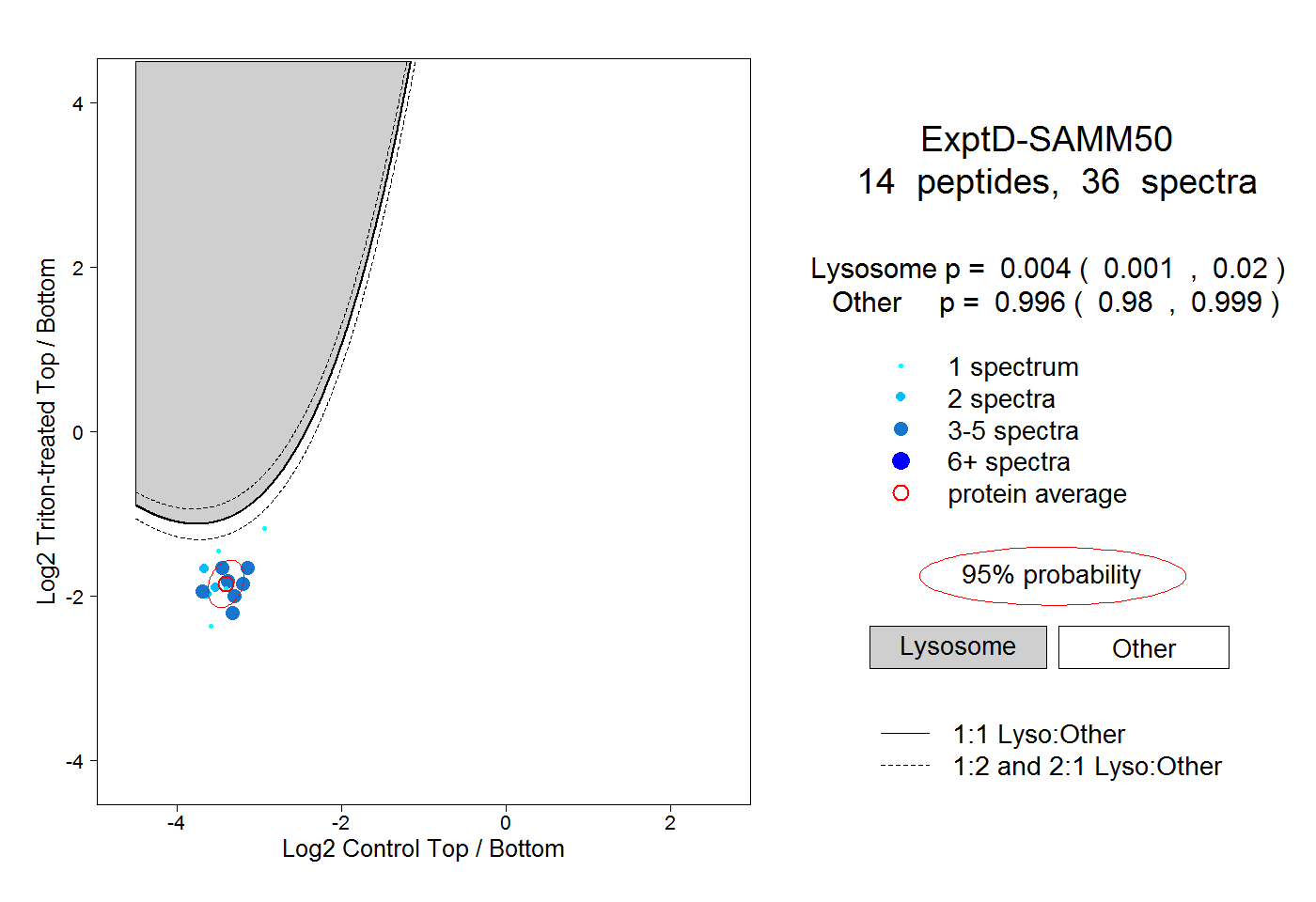
| 1 spectrum, VNQELAGYTGGDVSFIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, QEILENK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, SSLSHAMVIDSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, NLIEVMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LELNYCIPMGVQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, NFSVNLYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, LSSIADR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, NSSILPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, ICDGVQFGAGIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, ETSYGLSFFKPQPGNFEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, VTFQFSYGTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, TASFAVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, ELGCLAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, THFFLNAGNLCNLNYGEGPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, WSYGAGIVLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, DVVVQHVHFDGLER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 26 spectra, FYLGGPTSVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, IAECLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, WEGVWR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, VTGQFPWSSLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LGNIAR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 26 spectra, LPNLLGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, ESGHSLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |