peptides
spectra
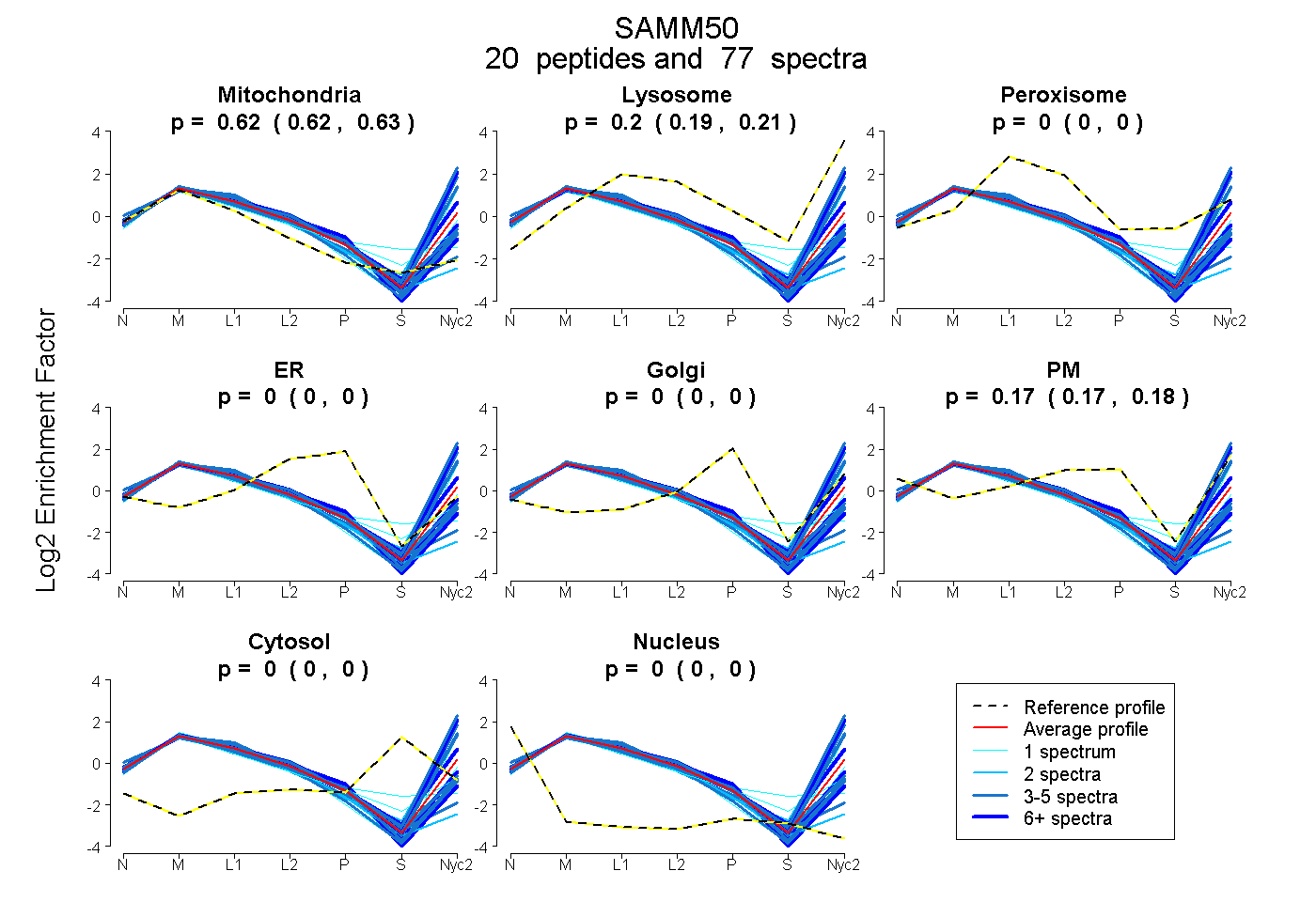
0.615 | 0.631
0.193 | 0.209
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.171 | 0.177
0.000 | 0.000
0.000 | 0.000
peptides
spectra
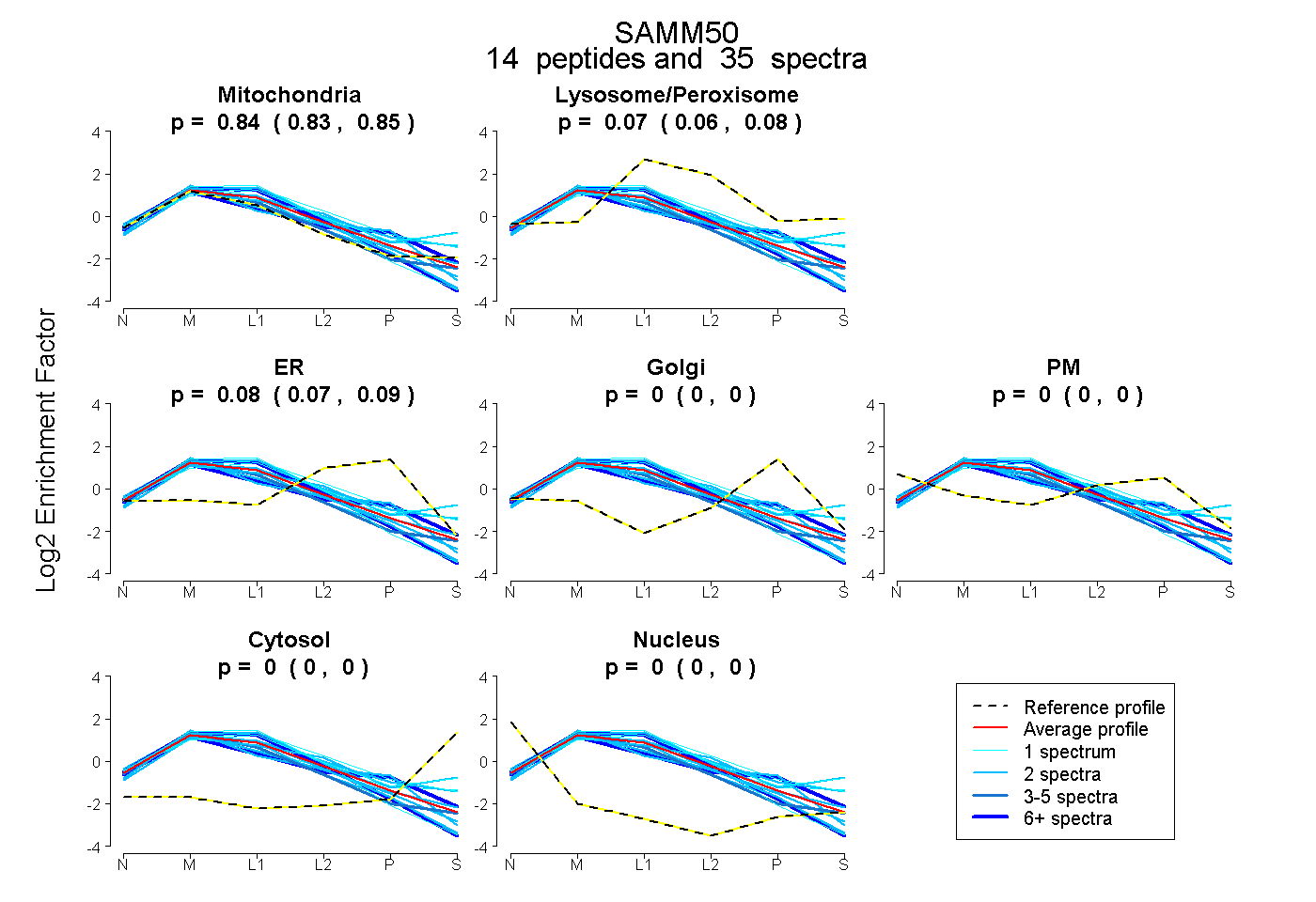
0.835 | 0.853
0.059 | 0.082
0.073 | 0.094
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
77 spectra |
 |
0.624 0.615 | 0.631 |
0.202 0.193 | 0.209 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.175 0.171 | 0.177 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
35 spectra |
 |
0.845 0.835 | 0.853 |
0.071 0.059 | 0.082 |
0.084 0.073 | 0.094 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, DVVVQHVHFDGLER | 0.735 | 0.165 | 0.000 | 0.071 | 0.015 | 0.014 | 0.000 | |||
| 7 spectra, FYLGGPTSVR | 0.750 | 0.000 | 0.250 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, NLIEVMR | 0.904 | 0.000 | 0.096 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LSSIADR | 0.890 | 0.000 | 0.110 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, NFSVNLYK | 0.607 | 0.337 | 0.056 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, WEGVWR | 0.609 | 0.348 | 0.000 | 0.000 | 0.000 | 0.043 | 0.000 | |||
| 1 spectrum, VTGQFPWSSLR | 0.964 | 0.036 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, NSSILPR | 0.757 | 0.000 | 0.243 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, VTFQFSYGTK | 0.810 | 0.190 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, GVSAEYSFPLCK | 0.676 | 0.239 | 0.081 | 0.004 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, TASFAVR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, LPNLLGR | 0.971 | 0.000 | 0.029 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, ELGCLAR | 0.973 | 0.000 | 0.027 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, THFFLNAGNLCNLNYGEGPR | 0.602 | 0.309 | 0.000 | 0.000 | 0.000 | 0.089 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
191 spectra |
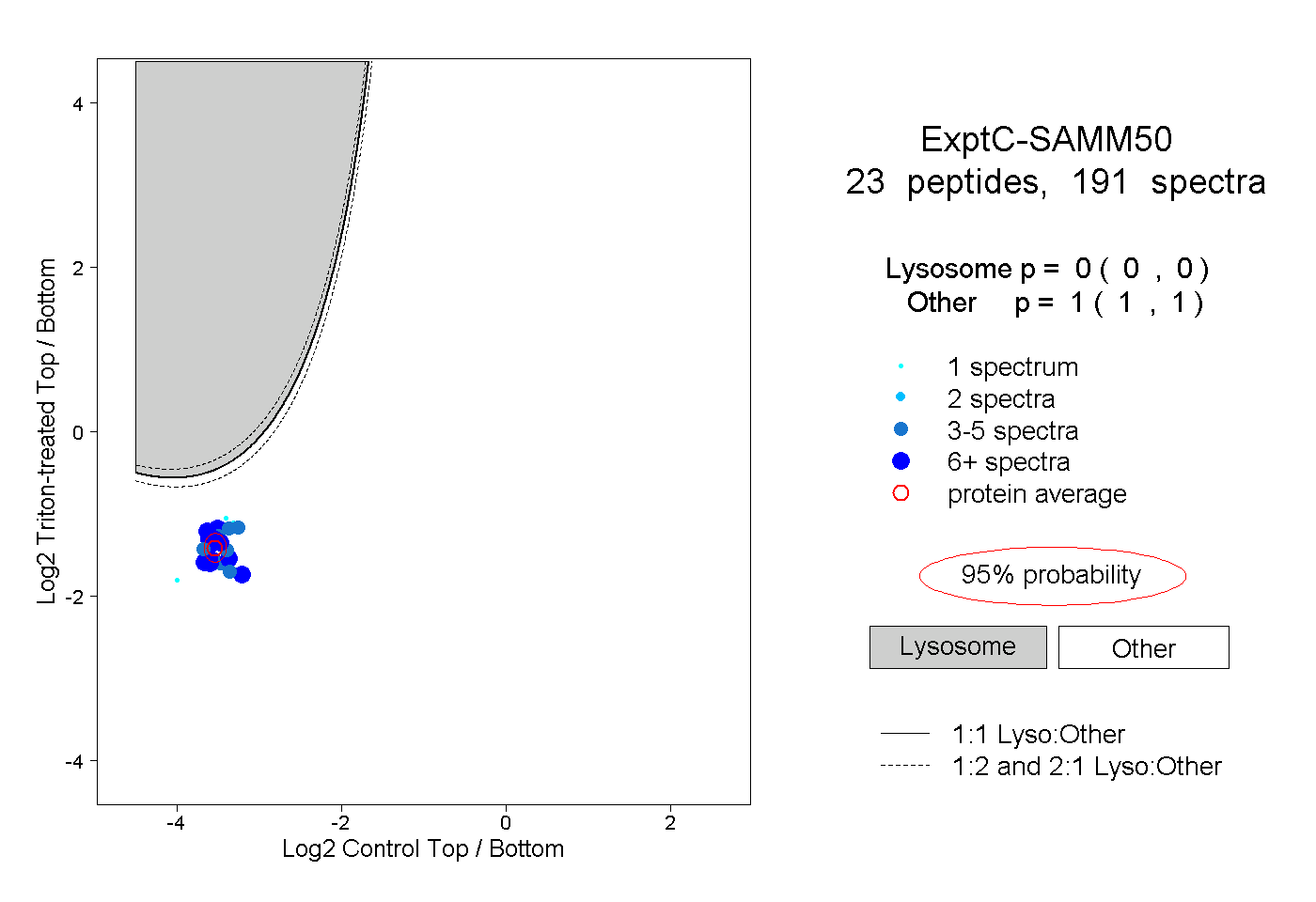 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
36 spectra |
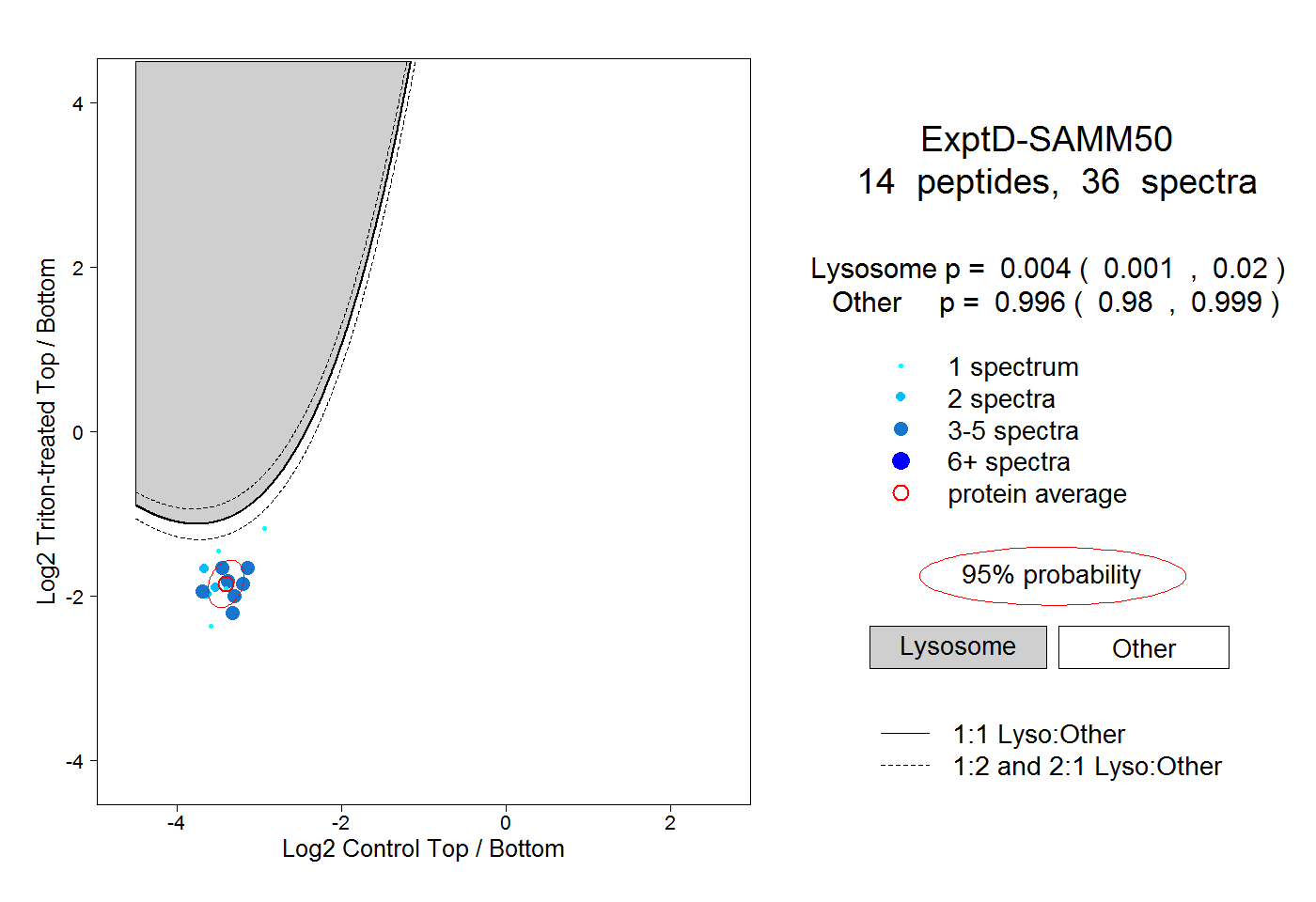 |
0.004 0.001 | 0.020 |
0.996 0.980 | 0.999 |