peptides
spectra
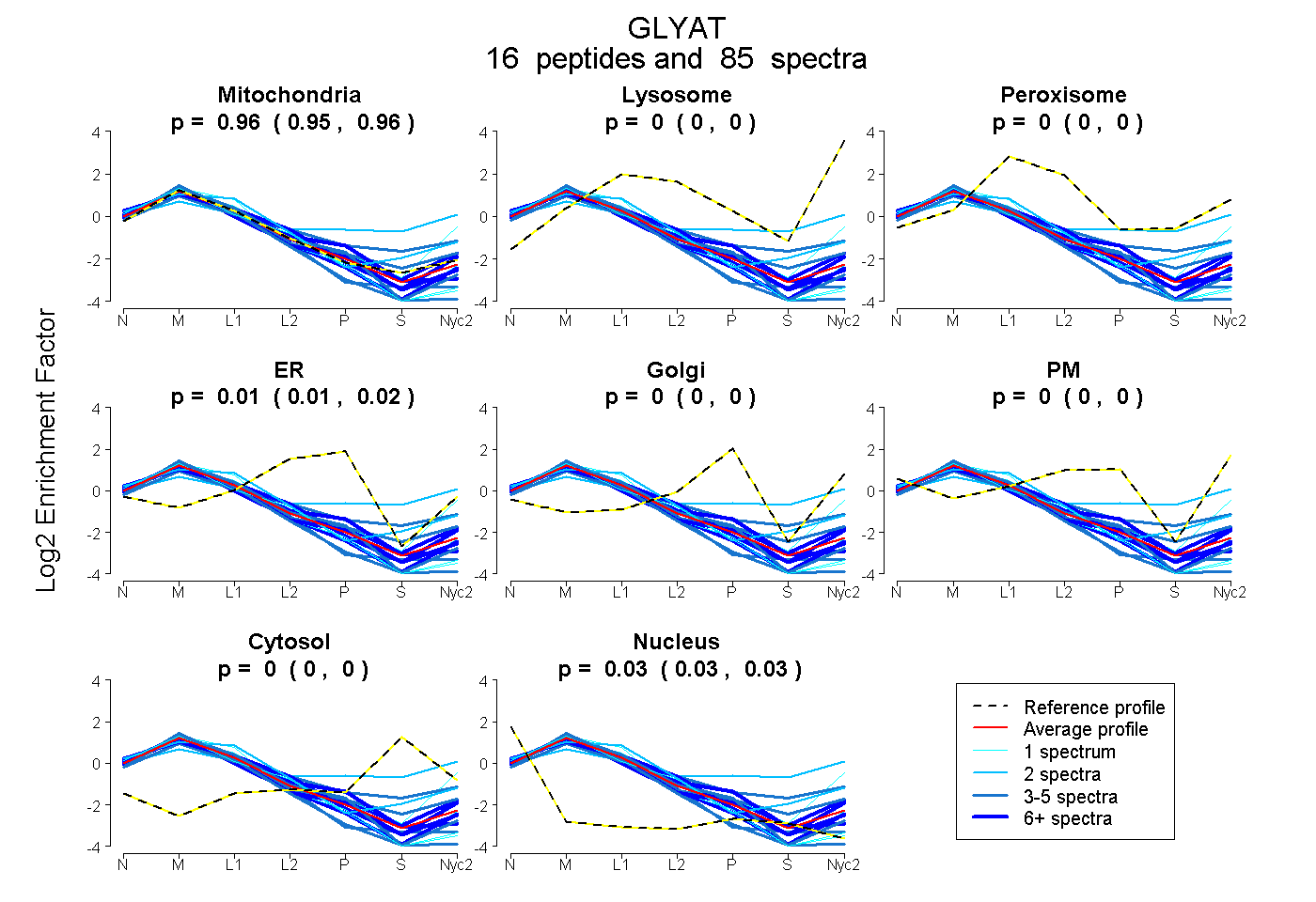
0.951 | 0.959
0.000 | 0.000
0.000 | 0.000
0.010 | 0.019
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.027 | 0.031
peptides
spectra
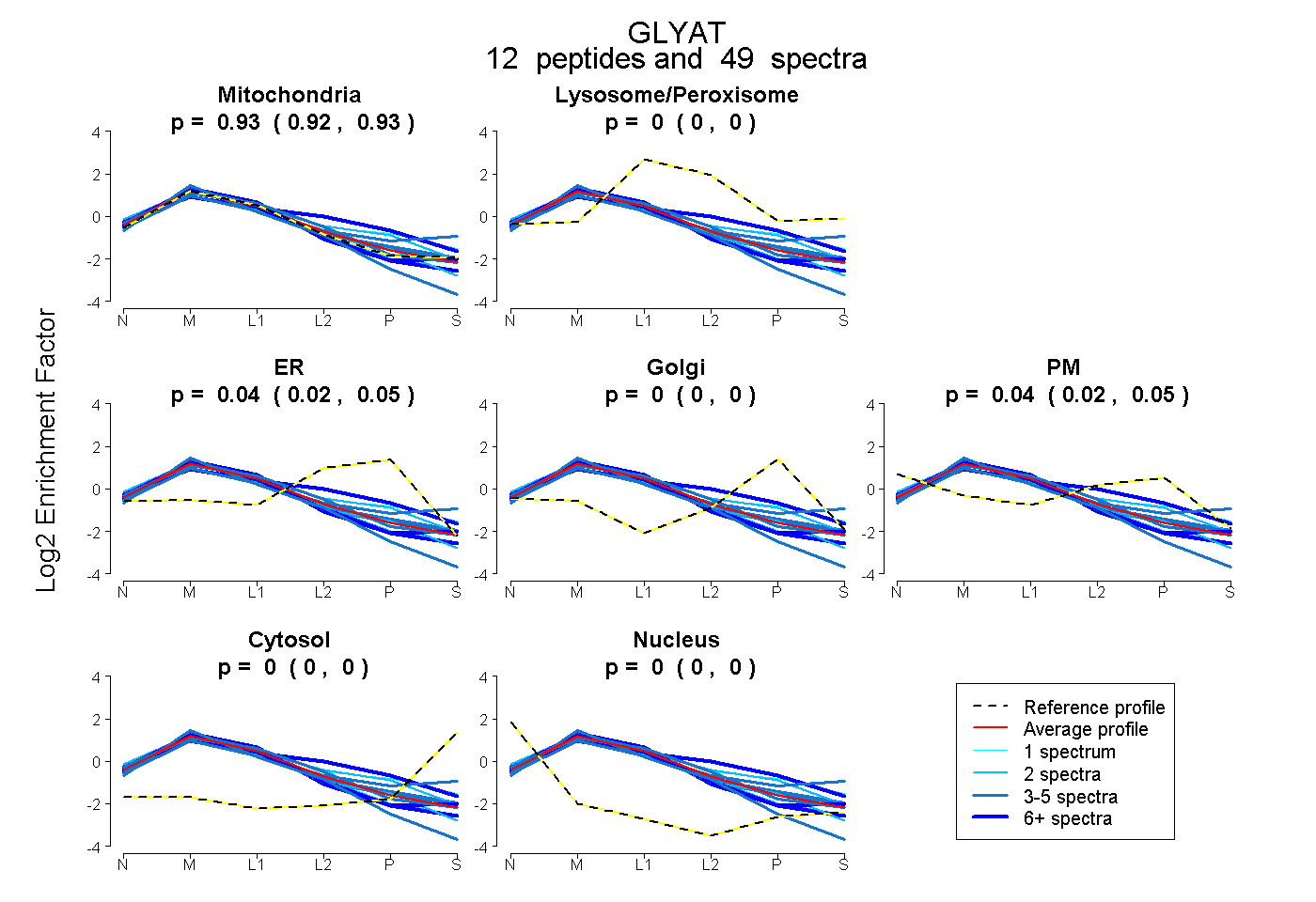
0.917 | 0.933
0.000 | 0.000
0.024 | 0.051
0.000 | 0.000
0.024 | 0.047
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
85 spectra |
 |
0.956 0.951 | 0.959 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.015 0.010 | 0.019 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.029 0.027 | 0.031 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
49 spectra |
 |
0.926 0.917 | 0.933 |
0.000 0.000 | 0.000 |
0.038 0.024 | 0.051 |
0.000 0.000 | 0.000 |
0.036 0.024 | 0.047 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 5 spectra, MGGTVPQYR | 0.967 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.033 | |||
| 8 spectra, FWLFGGNER | 0.987 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.013 | |||
| 3 spectra, VYGTIYHVNHGNPFNLK | 0.913 | 0.031 | 0.000 | 0.000 | 0.057 | 0.000 | 0.000 | |||
| 3 spectra, AINQEMFK | 0.902 | 0.013 | 0.000 | 0.000 | 0.086 | 0.000 | 0.000 | |||
| 4 spectra, GFPVYSHTDK | 0.961 | 0.000 | 0.000 | 0.039 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, AQGLVSFVIYSQDQIMK | 0.778 | 0.011 | 0.211 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, LSSLDVTHAALVNK | 0.966 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.034 | |||
| 1 spectrum, AIQNLASIHSLQVK | 0.689 | 0.160 | 0.000 | 0.151 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, DPENCQEFLGSSEVINWK | 0.950 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.050 | |||
| 2 spectra, LFPSLLDTK | 0.907 | 0.000 | 0.046 | 0.012 | 0.000 | 0.000 | 0.036 | |||
| 6 spectra, HSENILYVVSETVR | 0.586 | 0.123 | 0.151 | 0.000 | 0.140 | 0.000 | 0.000 | |||
| 4 spectra, IVPLQGAQMLQMLEK | 0.660 | 0.143 | 0.000 | 0.077 | 0.000 | 0.121 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
360 spectra |
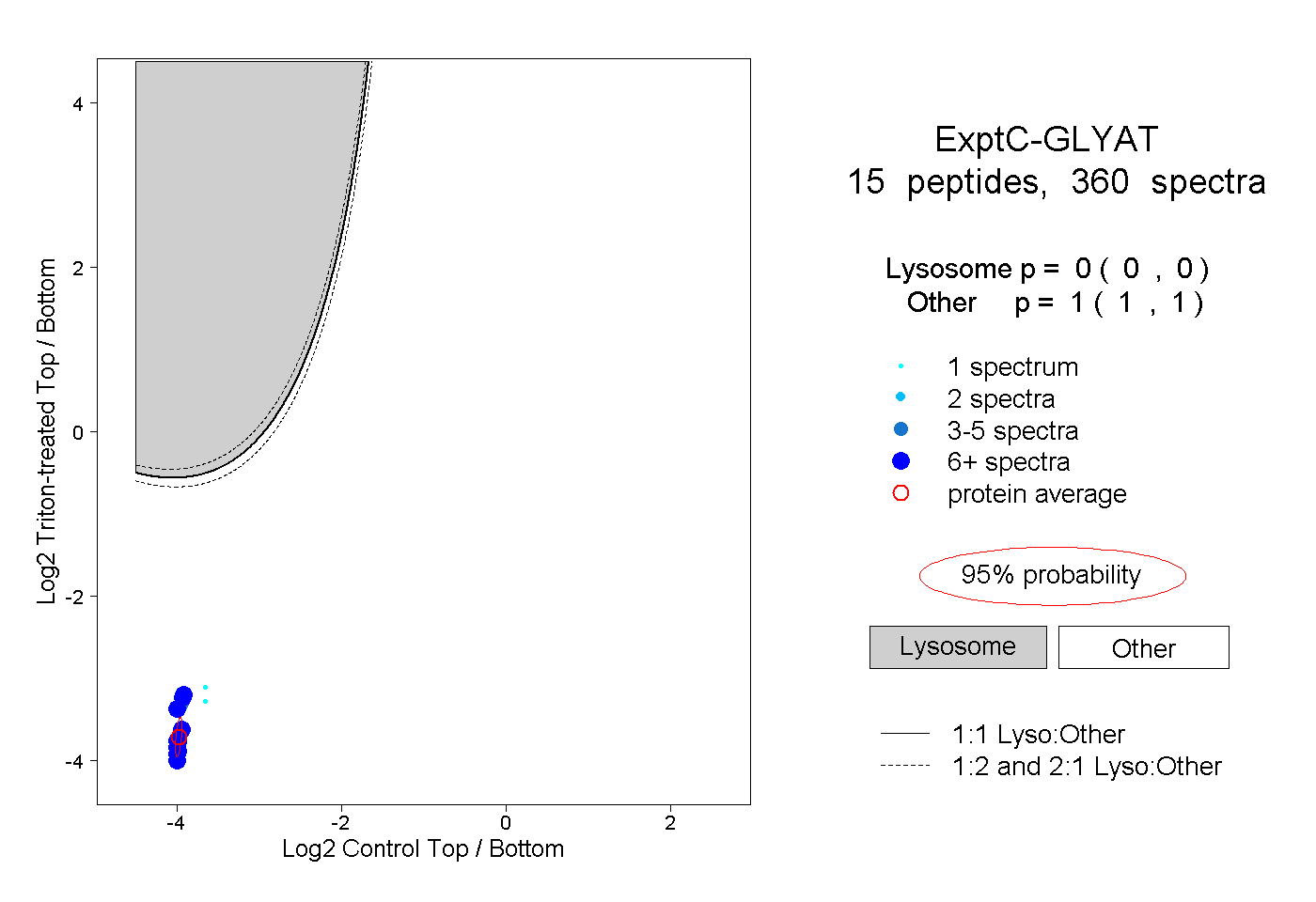 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
18 spectra |
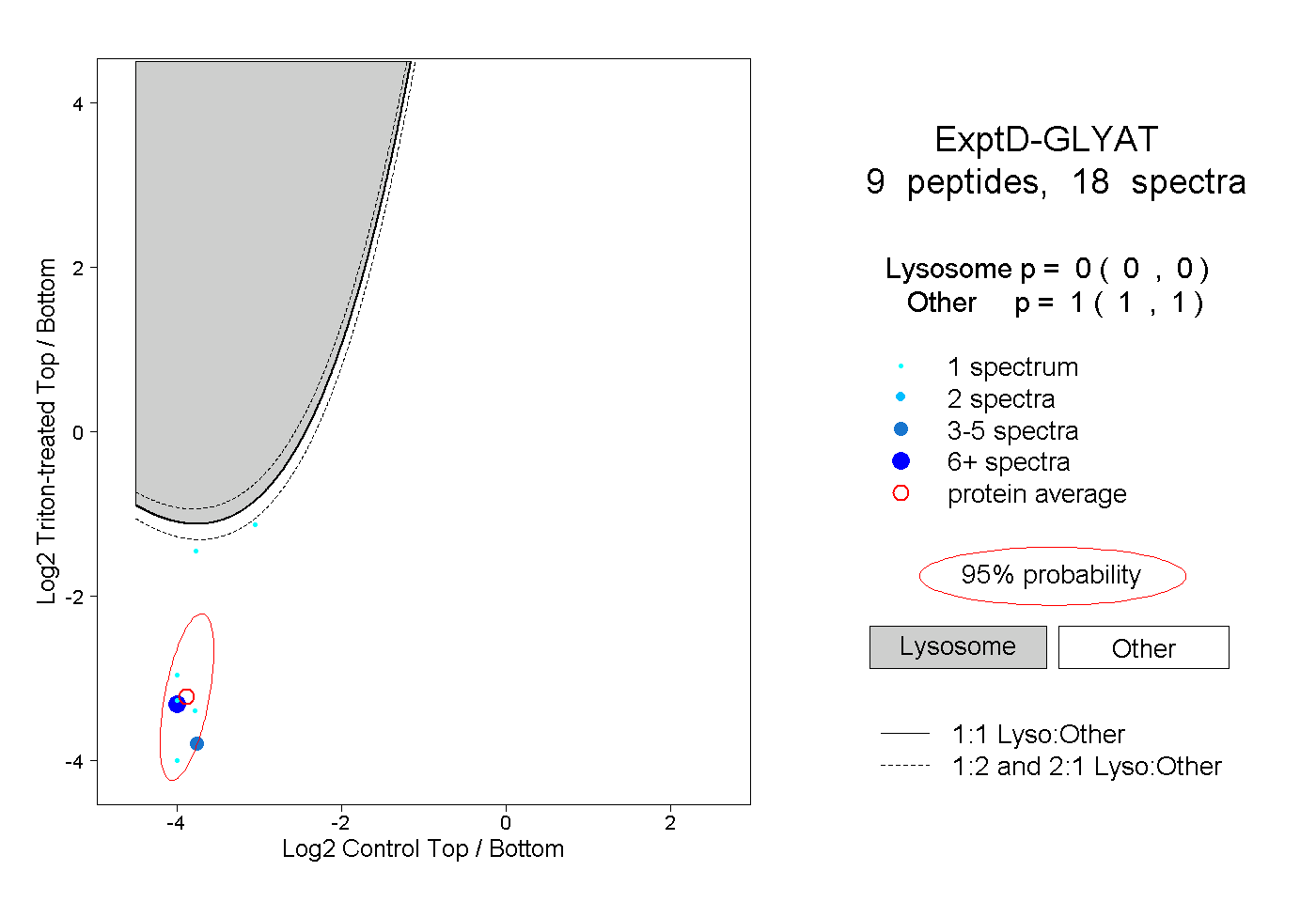 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |