peptides
spectra
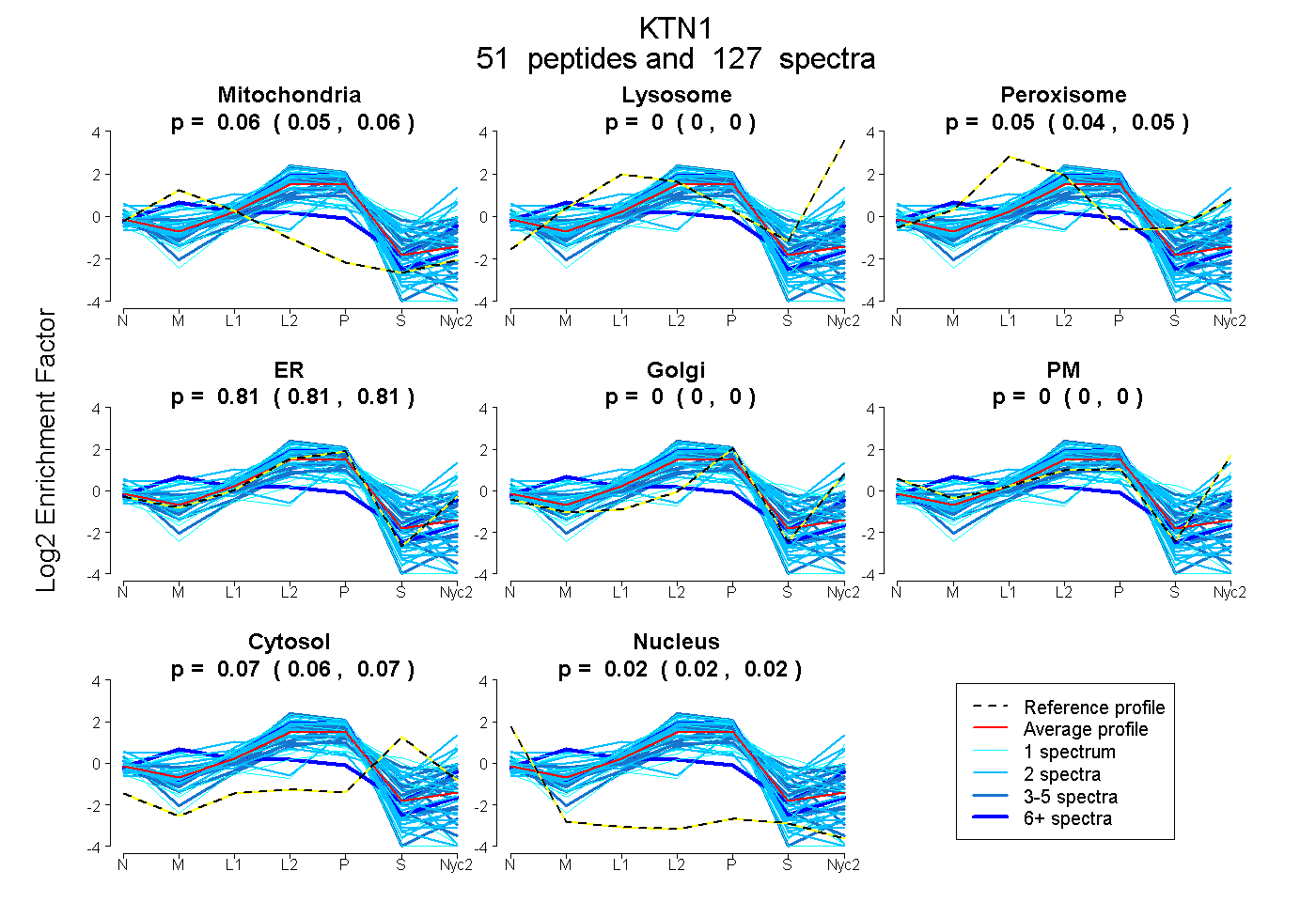
0.051 | 0.060
0.000 | 0.000
0.041 | 0.050
0.808 | 0.815
0.000 | 0.000
0.000 | 0.000
0.063 | 0.071
0.015 | 0.022
peptides
spectra
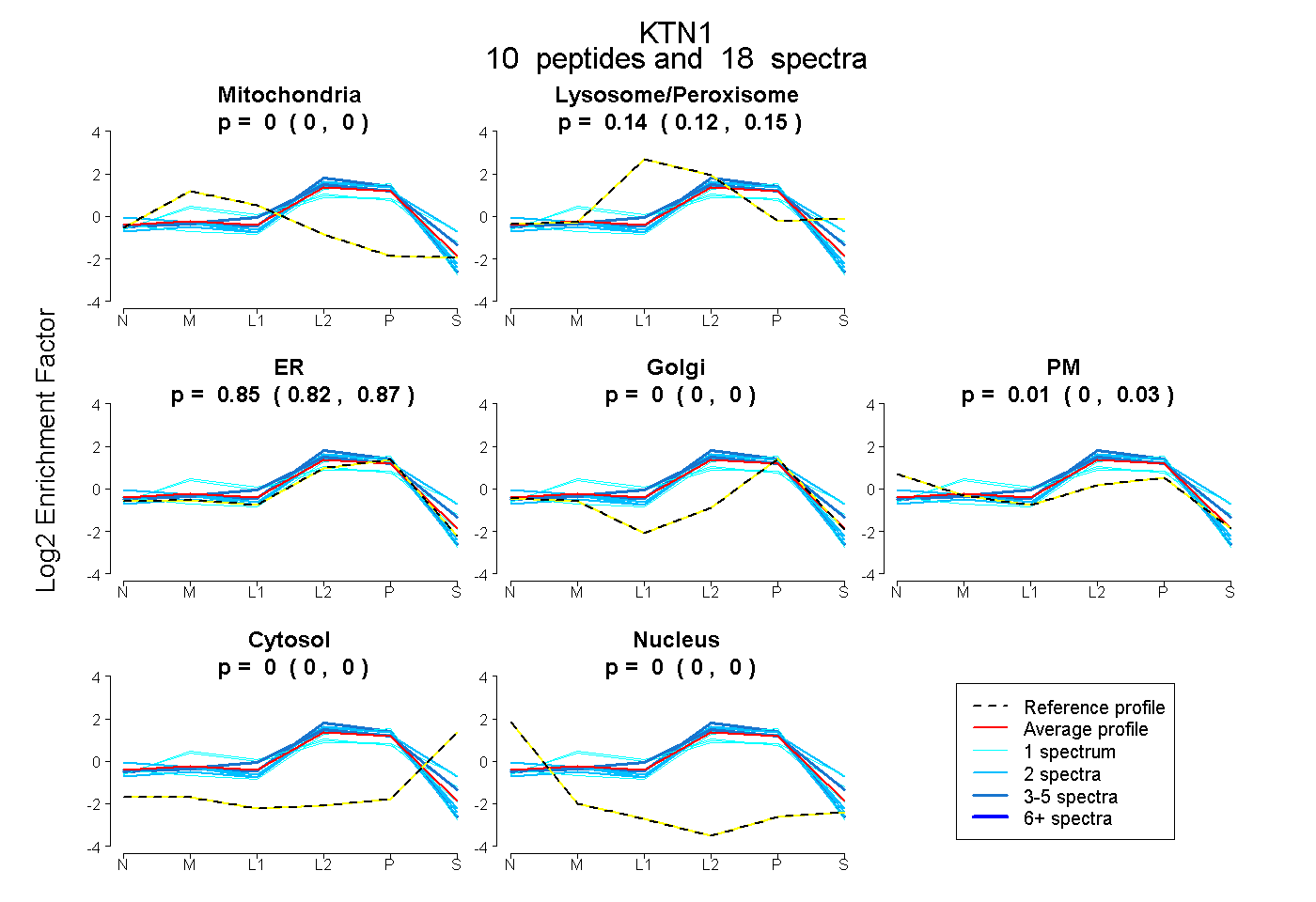
0.000 | 0.000
0.124 | 0.153
0.824 | 0.870
0.000 | 0.000
0.000 | 0.025
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
127 spectra |
 |
0.056 0.051 | 0.060 |
0.000 0.000 | 0.000 |
0.046 0.041 | 0.050 |
0.812 0.808 | 0.815 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.067 0.063 | 0.071 |
0.019 0.015 | 0.022 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
18 spectra |
 |
0.000 0.000 | 0.000 |
0.140 0.124 | 0.153 |
0.853 0.824 | 0.870 |
0.000 0.000 | 0.000 |
0.007 0.000 | 0.025 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, EEELNAIR | 0.000 | 0.174 | 0.727 | 0.000 | 0.000 | 0.099 | 0.000 | |||
| 2 spectra, AALEDLTGR | 0.000 | 0.068 | 0.932 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, VADDLHK | 0.000 | 0.023 | 0.873 | 0.000 | 0.103 | 0.000 | 0.000 | |||
| 1 spectrum, TQLNETHSK | 0.180 | 0.150 | 0.670 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, FEELENVLK | 0.000 | 0.054 | 0.946 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, SVLAETEGILQK | 0.000 | 0.039 | 0.961 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, AQQSLNFIHSK | 0.110 | 0.283 | 0.490 | 0.117 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LQNEQTER | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, VQLQEAER | 0.000 | 0.256 | 0.744 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, ILNDQNK | 0.000 | 0.423 | 0.081 | 0.351 | 0.138 | 0.007 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
357 spectra |
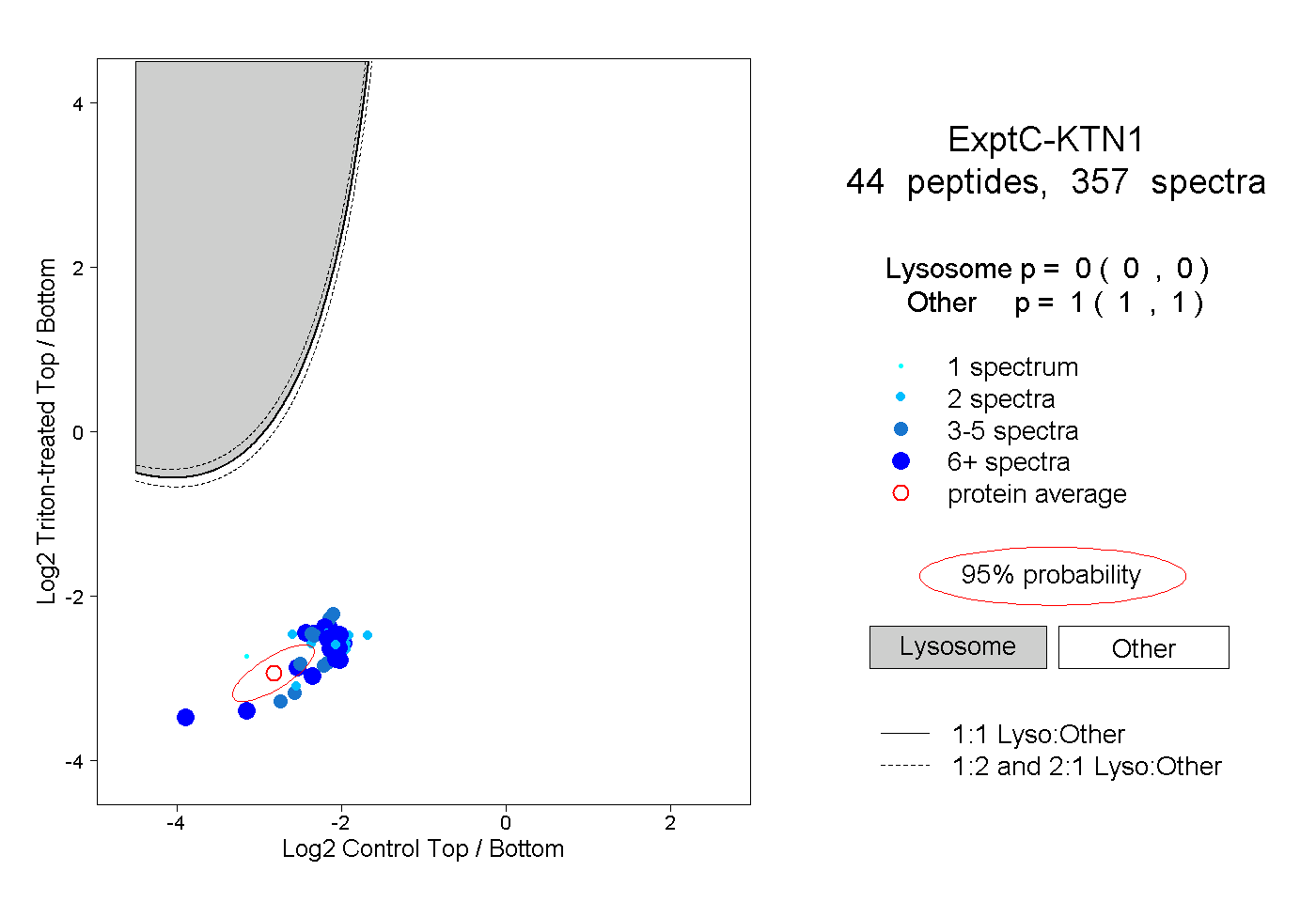 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
32 spectra |
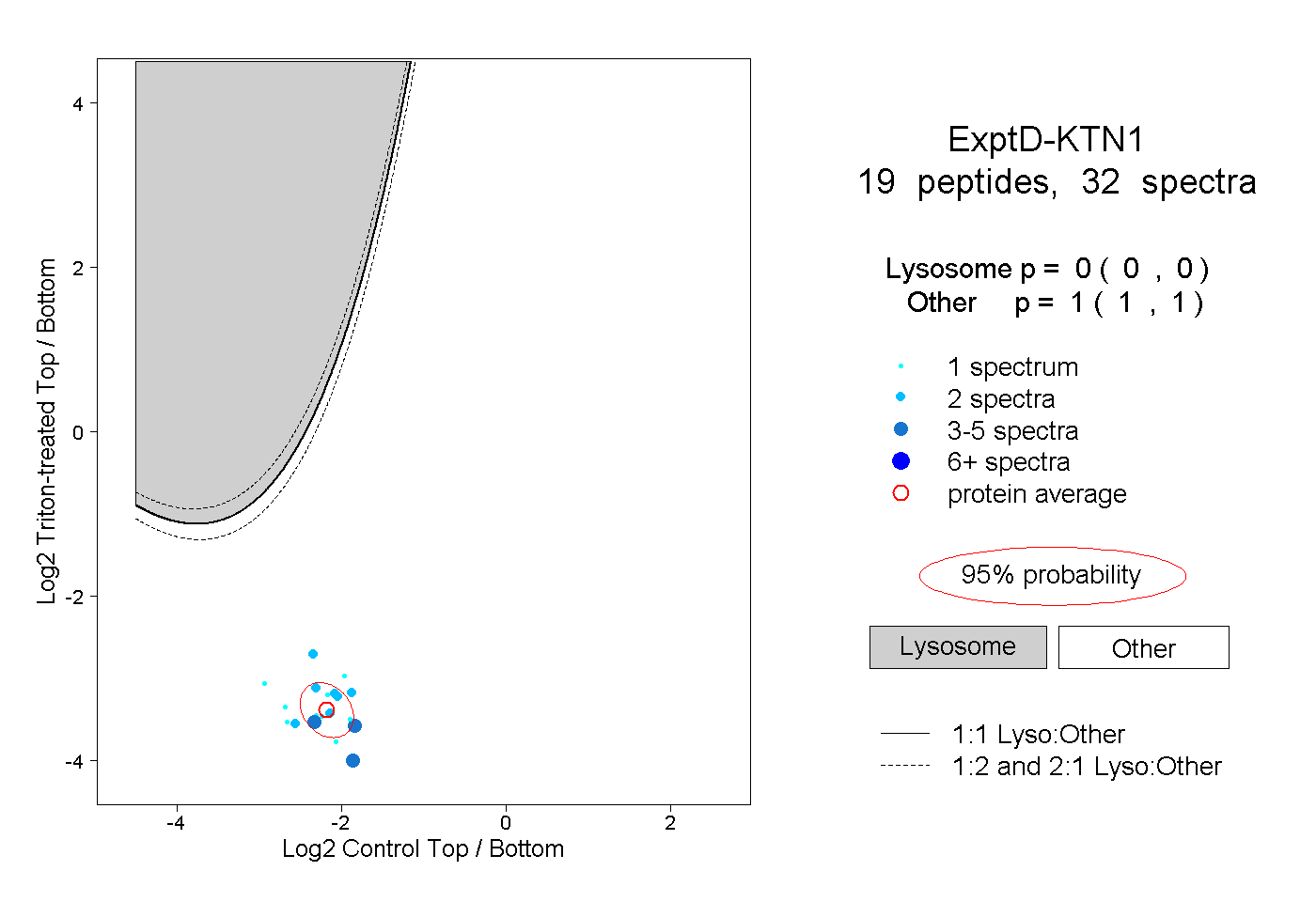 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |