peptides
spectra
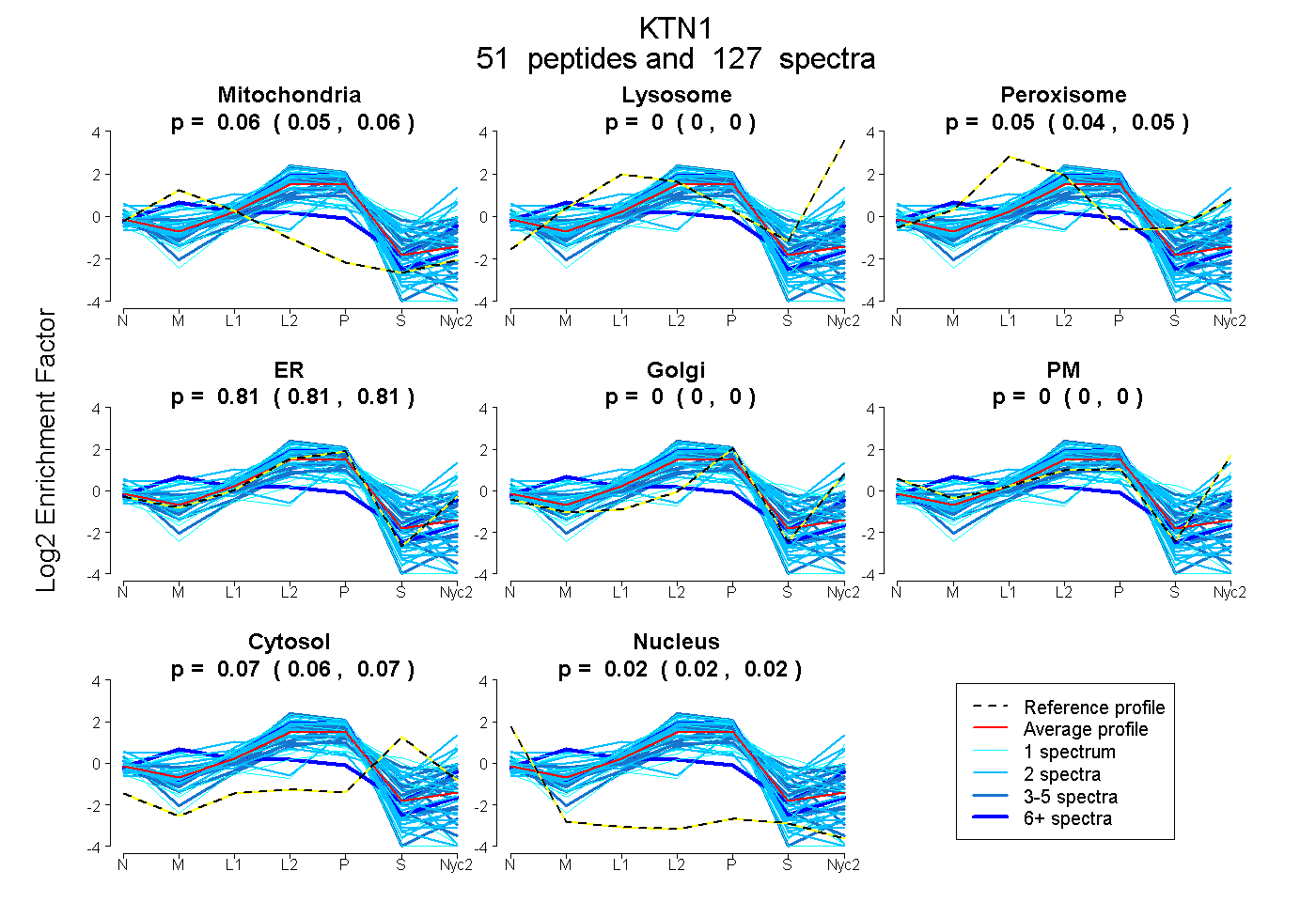
0.051 | 0.060
0.000 | 0.000
0.041 | 0.050
0.808 | 0.815
0.000 | 0.000
0.000 | 0.000
0.063 | 0.071
0.015 | 0.022
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
127 spectra |
 |
0.056 0.051 | 0.060 |
0.000 0.000 | 0.000 |
0.046 0.041 | 0.050 |
0.812 0.808 | 0.815 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.067 0.063 | 0.071 |
0.019 0.015 | 0.022 |
| 1 spectrum, ETLYDDVLAK | 0.000 | 0.000 | 0.101 | 0.384 | 0.224 | 0.000 | 0.290 | 0.000 | ||
| 1 spectrum, ELALAK | 0.084 | 0.000 | 0.365 | 0.000 | 0.355 | 0.065 | 0.130 | 0.000 | ||
| 3 spectra, ENEVQSLHSK | 0.000 | 0.000 | 0.143 | 0.522 | 0.000 | 0.129 | 0.206 | 0.000 | ||
| 2 spectra, ESDASK | 0.000 | 0.000 | 0.140 | 0.031 | 0.623 | 0.000 | 0.136 | 0.070 | ||
| 2 spectra, TENSSLTK | 0.000 | 0.207 | 0.300 | 0.032 | 0.237 | 0.173 | 0.052 | 0.000 | ||
| 4 spectra, NAEQAAAQLK | 0.000 | 0.000 | 0.176 | 0.717 | 0.000 | 0.000 | 0.106 | 0.000 | ||
| 3 spectra, TLQQLR | 0.140 | 0.000 | 0.083 | 0.644 | 0.000 | 0.012 | 0.121 | 0.000 | ||
| 2 spectra, EVQDENK | 0.000 | 0.152 | 0.125 | 0.705 | 0.000 | 0.008 | 0.011 | 0.000 | ||
| 7 spectra, SSVVMAR | 0.020 | 0.000 | 0.000 | 0.964 | 0.000 | 0.000 | 0.000 | 0.016 | ||
| 4 spectra, LVSELNEK | 0.015 | 0.000 | 0.000 | 0.907 | 0.000 | 0.000 | 0.000 | 0.078 | ||
| 1 spectrum, QSAELNK | 0.220 | 0.000 | 0.178 | 0.558 | 0.000 | 0.036 | 0.009 | 0.000 | ||
| 1 spectrum, QEGGPGK | 0.000 | 0.000 | 0.000 | 0.188 | 0.536 | 0.000 | 0.195 | 0.081 | ||
| 5 spectra, EEIGNAQLEK | 0.000 | 0.000 | 0.152 | 0.726 | 0.000 | 0.000 | 0.121 | 0.000 | ||
| 2 spectra, VQLQEAER | 0.000 | 0.000 | 0.123 | 0.664 | 0.000 | 0.000 | 0.213 | 0.000 | ||
| 1 spectrum, TVEELLETGLIQVATR | 0.090 | 0.000 | 0.000 | 0.836 | 0.000 | 0.000 | 0.000 | 0.075 | ||
| 1 spectrum, ILNDQNK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, LTDTLVSK | 0.052 | 0.000 | 0.000 | 0.932 | 0.000 | 0.000 | 0.000 | 0.015 | ||
| 1 spectrum, DVQNVNFLLK | 0.000 | 0.075 | 0.000 | 0.690 | 0.000 | 0.235 | 0.000 | 0.000 | ||
| 3 spectra, EEELNAIR | 0.012 | 0.000 | 0.106 | 0.740 | 0.000 | 0.000 | 0.142 | 0.000 | ||
| 2 spectra, STYVMEVR | 0.000 | 0.035 | 0.010 | 0.955 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, AALEDLTGR | 0.011 | 0.000 | 0.000 | 0.947 | 0.000 | 0.000 | 0.000 | 0.042 | ||
| 2 spectra, VADDLHK | 0.064 | 0.000 | 0.000 | 0.828 | 0.000 | 0.000 | 0.000 | 0.108 | ||
| 1 spectrum, EVQEIK | 0.258 | 0.000 | 0.147 | 0.485 | 0.000 | 0.000 | 0.110 | 0.000 | ||
| 1 spectrum, EHNIFQNK | 0.000 | 0.000 | 0.110 | 0.827 | 0.000 | 0.000 | 0.048 | 0.014 | ||
| 1 spectrum, DLLTELQK | 0.057 | 0.000 | 0.137 | 0.806 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, NFLLSLK | 0.021 | 0.000 | 0.000 | 0.883 | 0.000 | 0.000 | 0.000 | 0.096 | ||
| 2 spectra, SVLAETEGILQK | 0.019 | 0.000 | 0.000 | 0.899 | 0.000 | 0.000 | 0.017 | 0.064 | ||
| 4 spectra, LQNEQTER | 0.000 | 0.000 | 0.102 | 0.844 | 0.000 | 0.000 | 0.035 | 0.019 | ||
| 3 spectra, DAVSNTTNQLESK | 0.000 | 0.000 | 0.000 | 0.552 | 0.000 | 0.048 | 0.400 | 0.000 | ||
| 2 spectra, EQMEAEIAHLK | 0.089 | 0.000 | 0.000 | 0.911 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, QNEELNLLK | 0.000 | 0.237 | 0.081 | 0.545 | 0.000 | 0.000 | 0.137 | 0.000 | ||
| 3 spectra, ALQLEVQK | 0.000 | 0.000 | 0.000 | 0.666 | 0.000 | 0.000 | 0.250 | 0.084 | ||
| 2 spectra, TMMFSEDEALCVVDLLK | 0.226 | 0.000 | 0.011 | 0.763 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, TIQQMQSSFTASEQELER | 0.000 | 0.000 | 0.060 | 0.341 | 0.000 | 0.100 | 0.498 | 0.000 | ||
| 2 spectra, LLEEQLQR | 0.000 | 0.000 | 0.136 | 0.672 | 0.000 | 0.000 | 0.192 | 0.000 | ||
| 1 spectrum, TVQALK | 0.000 | 0.000 | 0.136 | 0.727 | 0.000 | 0.000 | 0.137 | 0.000 | ||
| 5 spectra, FEELENVLK | 0.003 | 0.000 | 0.000 | 0.909 | 0.000 | 0.000 | 0.000 | 0.088 | ||
| 2 spectra, ACMAGPSDTEAVK | 0.276 | 0.000 | 0.153 | 0.339 | 0.000 | 0.231 | 0.000 | 0.000 | ||
| 2 spectra, EHLEIELEK | 0.116 | 0.000 | 0.000 | 0.749 | 0.000 | 0.000 | 0.091 | 0.044 | ||
| 2 spectra, LMQLMESEQK | 0.106 | 0.000 | 0.000 | 0.891 | 0.000 | 0.000 | 0.002 | 0.000 | ||
| 2 spectra, QQQVEAVELESK | 0.062 | 0.000 | 0.000 | 0.890 | 0.000 | 0.000 | 0.000 | 0.048 | ||
| 4 spectra, CTQVCSTPR | 0.051 | 0.000 | 0.000 | 0.938 | 0.000 | 0.000 | 0.000 | 0.011 | ||
| 3 spectra, AQQSLNFIHSK | 0.015 | 0.000 | 0.013 | 0.888 | 0.000 | 0.000 | 0.071 | 0.014 | ||
| 2 spectra, EQAAAAHEVEK | 0.144 | 0.000 | 0.000 | 0.843 | 0.000 | 0.000 | 0.000 | 0.013 | ||
| 1 spectrum, EANEMHTLLQLECEK | 0.000 | 0.000 | 0.149 | 0.564 | 0.000 | 0.000 | 0.287 | 0.000 | ||
| 1 spectrum, GELSGLLHQLQEK | 0.078 | 0.000 | 0.000 | 0.777 | 0.000 | 0.000 | 0.000 | 0.145 | ||
| 2 spectra, TQLNETHSK | 0.001 | 0.000 | 0.000 | 0.880 | 0.000 | 0.000 | 0.000 | 0.119 | ||
| 2 spectra, QLTQEMMTEK | 0.000 | 0.000 | 0.284 | 0.377 | 0.000 | 0.000 | 0.211 | 0.128 | ||
| 12 spectra, LQALAK | 0.416 | 0.000 | 0.188 | 0.058 | 0.267 | 0.071 | 0.000 | 0.000 | ||
| 2 spectra, AMENLR | 0.000 | 0.000 | 0.115 | 0.609 | 0.000 | 0.000 | 0.275 | 0.000 | ||
| 4 spectra, LQQEGVQK | 0.000 | 0.000 | 0.055 | 0.799 | 0.000 | 0.000 | 0.146 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
18 spectra |
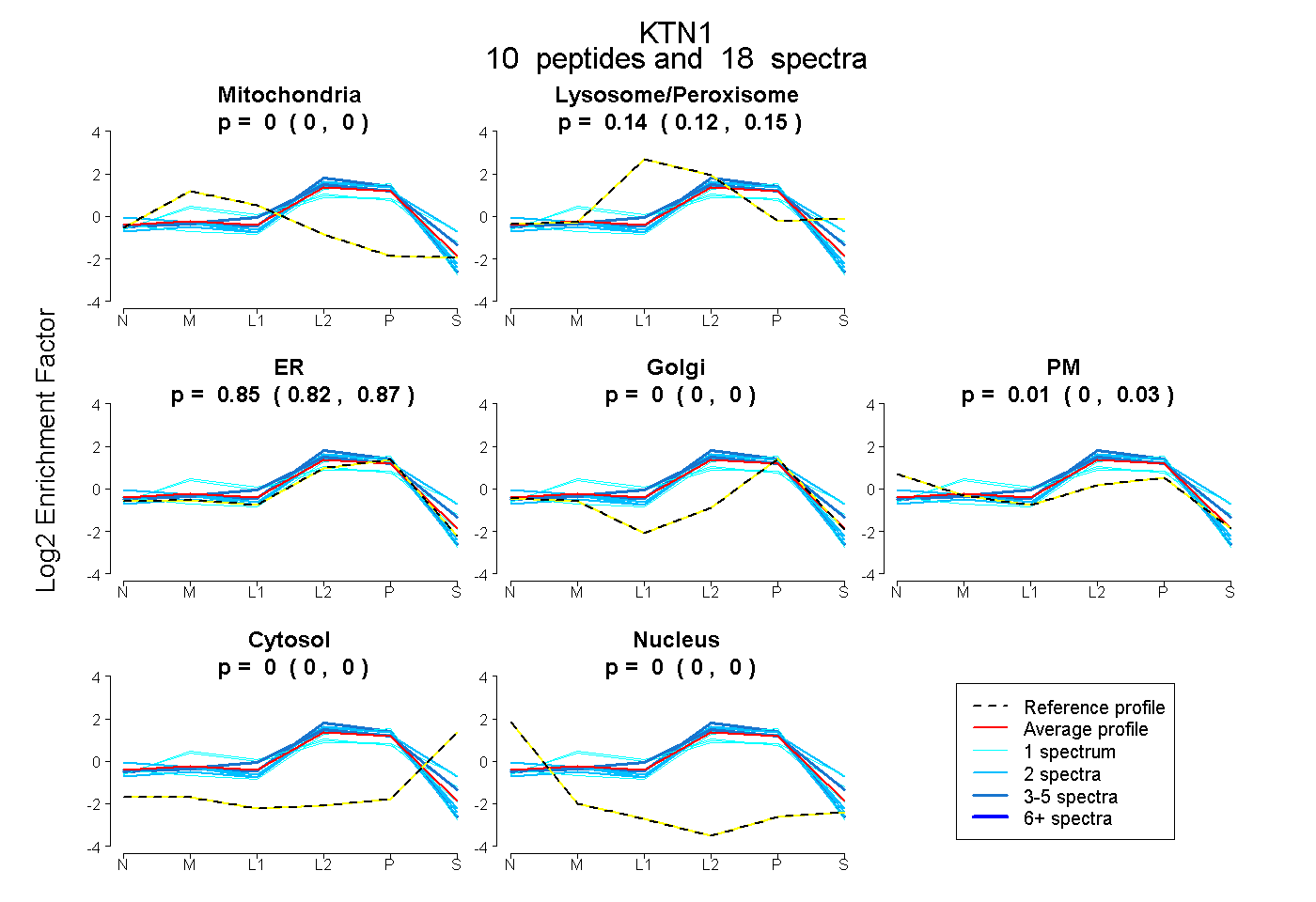 |
0.000 0.000 | 0.000 |
0.140 0.124 | 0.153 |
0.853 0.824 | 0.870 |
0.000 0.000 | 0.000 |
0.007 0.000 | 0.025 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
357 spectra |
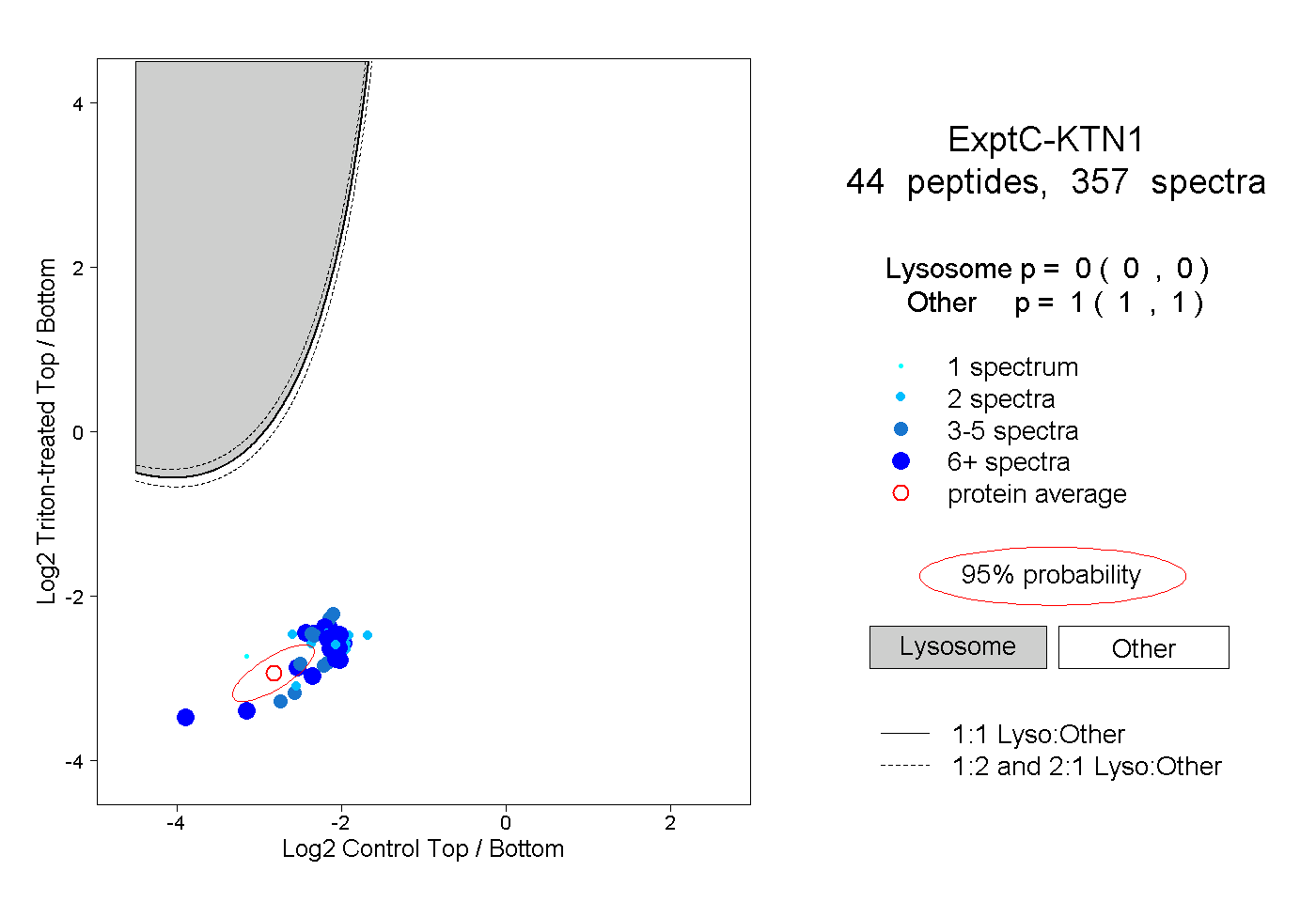 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
32 spectra |
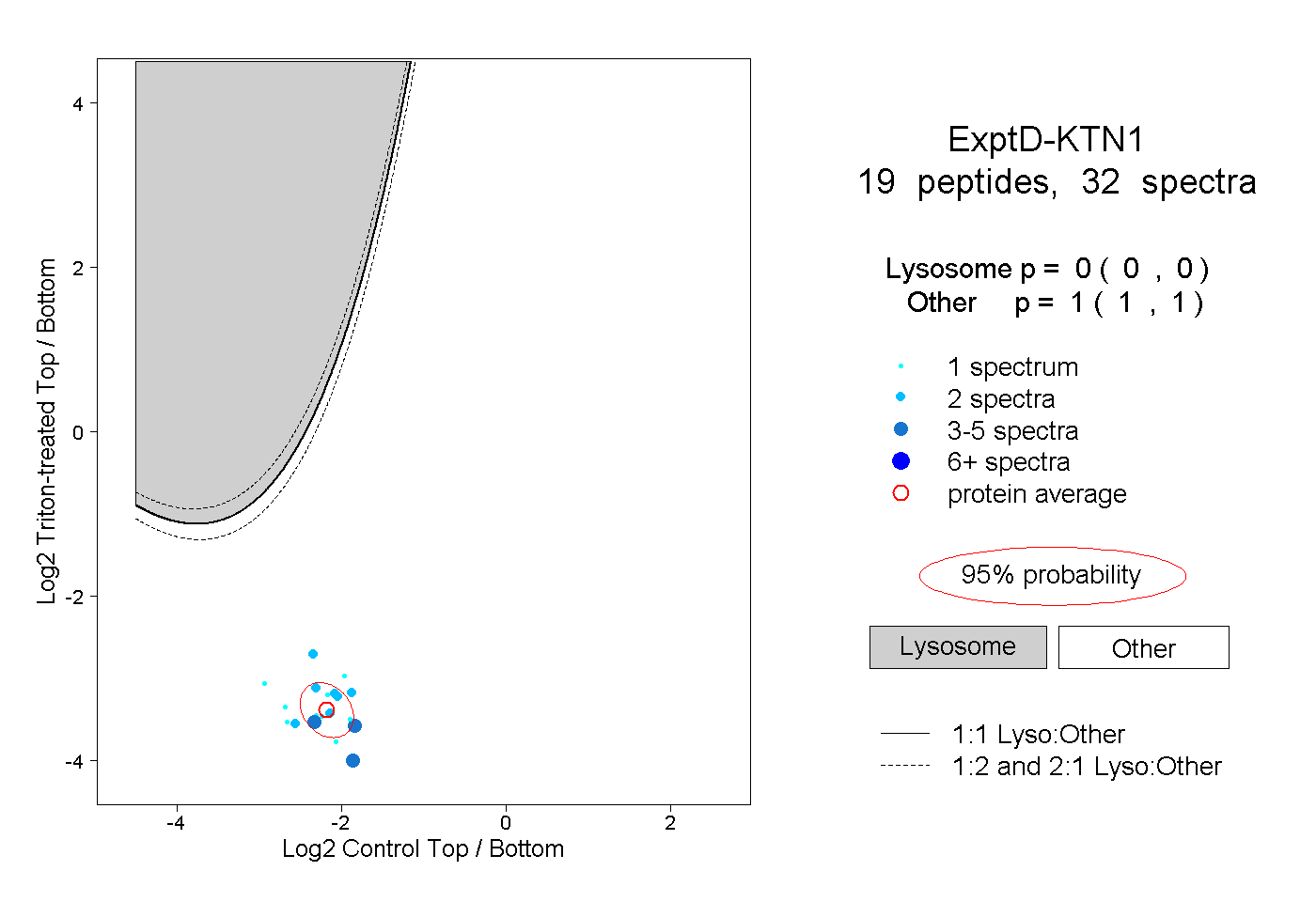 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |