peptides
spectra
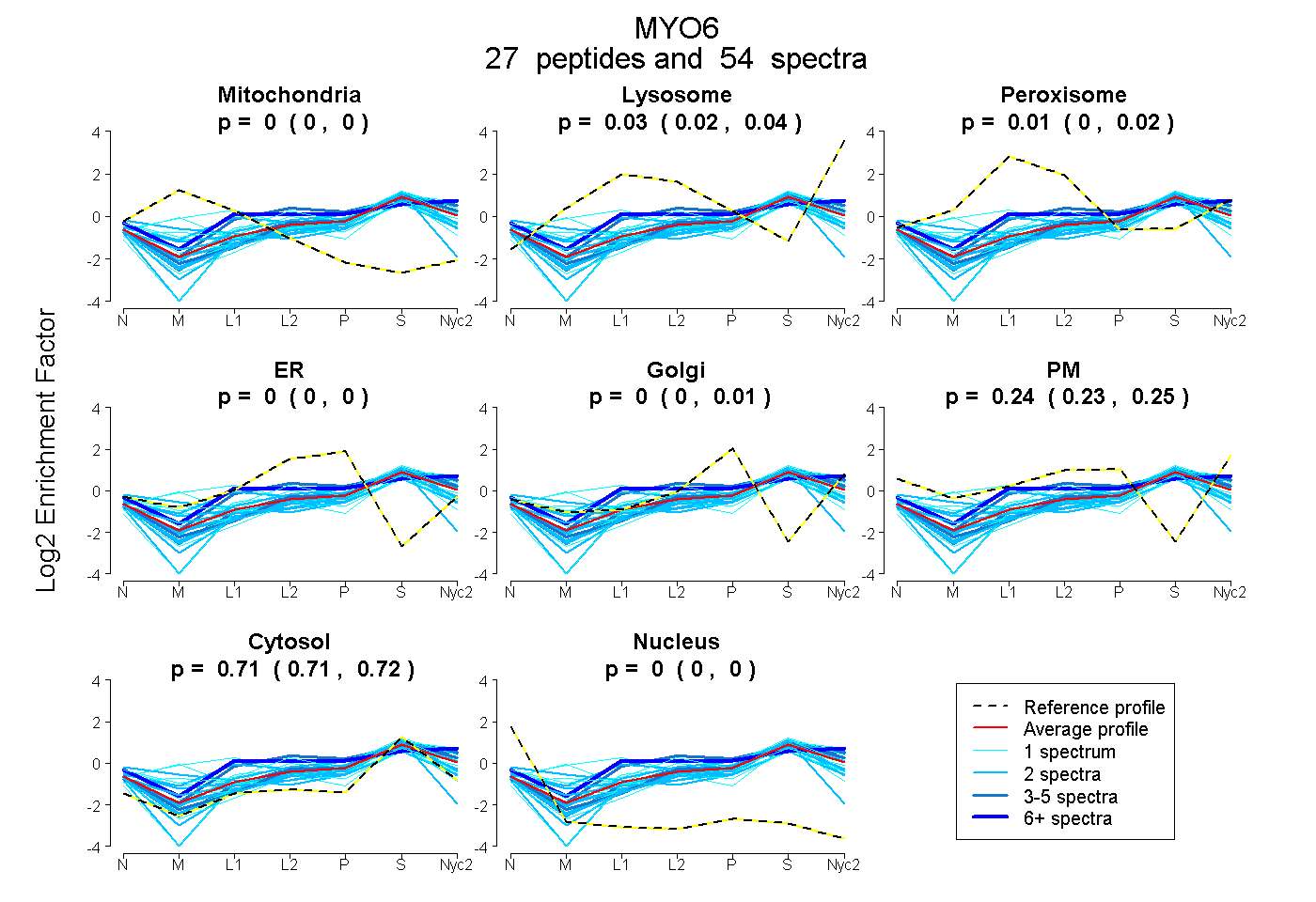
0.000 | 0.000
0.020 | 0.037
0.005 | 0.024
0.000 | 0.004
0.000 | 0.008
0.233 | 0.247
0.707 | 0.715
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
54 spectra |
 |
0.000 0.000 | 0.000 |
0.029 0.020 | 0.037 |
0.014 0.005 | 0.024 |
0.000 0.000 | 0.004 |
0.000 0.000 | 0.008 |
0.245 0.233 | 0.247 |
0.712 0.707 | 0.715 |
0.000 0.000 | 0.000 |
| 2 spectra, VEQANSAR | 0.000 | 0.179 | 0.101 | 0.000 | 0.000 | 0.173 | 0.546 | 0.000 | ||
| 2 spectra, FAEFDQIMK | 0.000 | 0.044 | 0.000 | 0.000 | 0.000 | 0.196 | 0.760 | 0.000 | ||
| 2 spectra, EYDALVK | 0.178 | 0.000 | 0.029 | 0.000 | 0.000 | 0.196 | 0.597 | 0.000 | ||
| 5 spectra, DPLLDDHGDFIR | 0.000 | 0.083 | 0.000 | 0.000 | 0.029 | 0.170 | 0.718 | 0.000 | ||
| 2 spectra, DLEISIDALMAK | 0.000 | 0.000 | 0.000 | 0.046 | 0.015 | 0.125 | 0.814 | 0.000 | ||
| 1 spectrum, ICVQGK | 0.000 | 0.000 | 0.042 | 0.159 | 0.000 | 0.054 | 0.717 | 0.028 | ||
| 3 spectra, NYHIFYR | 0.000 | 0.218 | 0.056 | 0.163 | 0.000 | 0.000 | 0.563 | 0.000 | ||
| 4 spectra, VFFRPGK | 0.000 | 0.008 | 0.000 | 0.000 | 0.032 | 0.226 | 0.734 | 0.000 | ||
| 1 spectrum, IVEANPLLEAFGNAK | 0.000 | 0.030 | 0.000 | 0.000 | 0.000 | 0.206 | 0.764 | 0.000 | ||
| 1 spectrum, VMLTTAGGTK | 0.000 | 0.006 | 0.000 | 0.000 | 0.171 | 0.021 | 0.802 | 0.000 | ||
| 1 spectrum, IDGLVK | 0.227 | 0.115 | 0.000 | 0.000 | 0.000 | 0.093 | 0.566 | 0.000 | ||
| 2 spectra, VYHAWK | 0.000 | 0.048 | 0.000 | 0.000 | 0.037 | 0.187 | 0.728 | 0.000 | ||
| 1 spectrum, DPLLDPWR | 0.122 | 0.063 | 0.118 | 0.000 | 0.000 | 0.025 | 0.673 | 0.000 | ||
| 1 spectrum, FNEVVSALK | 0.000 | 0.090 | 0.033 | 0.000 | 0.000 | 0.195 | 0.682 | 0.000 | ||
| 2 spectra, QFEEIWER | 0.000 | 0.093 | 0.000 | 0.104 | 0.007 | 0.113 | 0.682 | 0.000 | ||
| 1 spectrum, TVYSHLFDHVVDR | 0.000 | 0.055 | 0.000 | 0.000 | 0.139 | 0.000 | 0.806 | 0.000 | ||
| 2 spectra, VNLWLVCSR | 0.000 | 0.000 | 0.000 | 0.140 | 0.000 | 0.000 | 0.797 | 0.063 | ||
| 1 spectrum, YLTESYGTGQDIDDR | 0.000 | 0.000 | 0.180 | 0.000 | 0.000 | 0.258 | 0.562 | 0.000 | ||
| 7 spectra, VLLVR | 0.000 | 0.116 | 0.135 | 0.000 | 0.000 | 0.245 | 0.503 | 0.000 | ||
| 2 spectra, FVEIHFNEK | 0.000 | 0.029 | 0.000 | 0.000 | 0.064 | 0.151 | 0.756 | 0.000 | ||
| 2 spectra, GAEILPR | 0.000 | 0.014 | 0.000 | 0.000 | 0.112 | 0.051 | 0.823 | 0.000 | ||
| 1 spectrum, IQEEMEK | 0.120 | 0.059 | 0.318 | 0.000 | 0.070 | 0.000 | 0.433 | 0.000 | ||
| 1 spectrum, LVGILDILDEENR | 0.000 | 0.154 | 0.000 | 0.000 | 0.018 | 0.131 | 0.697 | 0.000 | ||
| 2 spectra, SSEDLLSALQK | 0.002 | 0.000 | 0.077 | 0.000 | 0.074 | 0.183 | 0.663 | 0.000 | ||
| 2 spectra, STGASFIR | 0.000 | 0.007 | 0.000 | 0.000 | 0.184 | 0.093 | 0.716 | 0.000 | ||
| 2 spectra, EEFHR | 0.000 | 0.000 | 0.000 | 0.052 | 0.103 | 0.020 | 0.825 | 0.000 | ||
| 1 spectrum, IQAEVEAQLAR | 0.000 | 0.148 | 0.000 | 0.000 | 0.000 | 0.259 | 0.594 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
14 spectra |
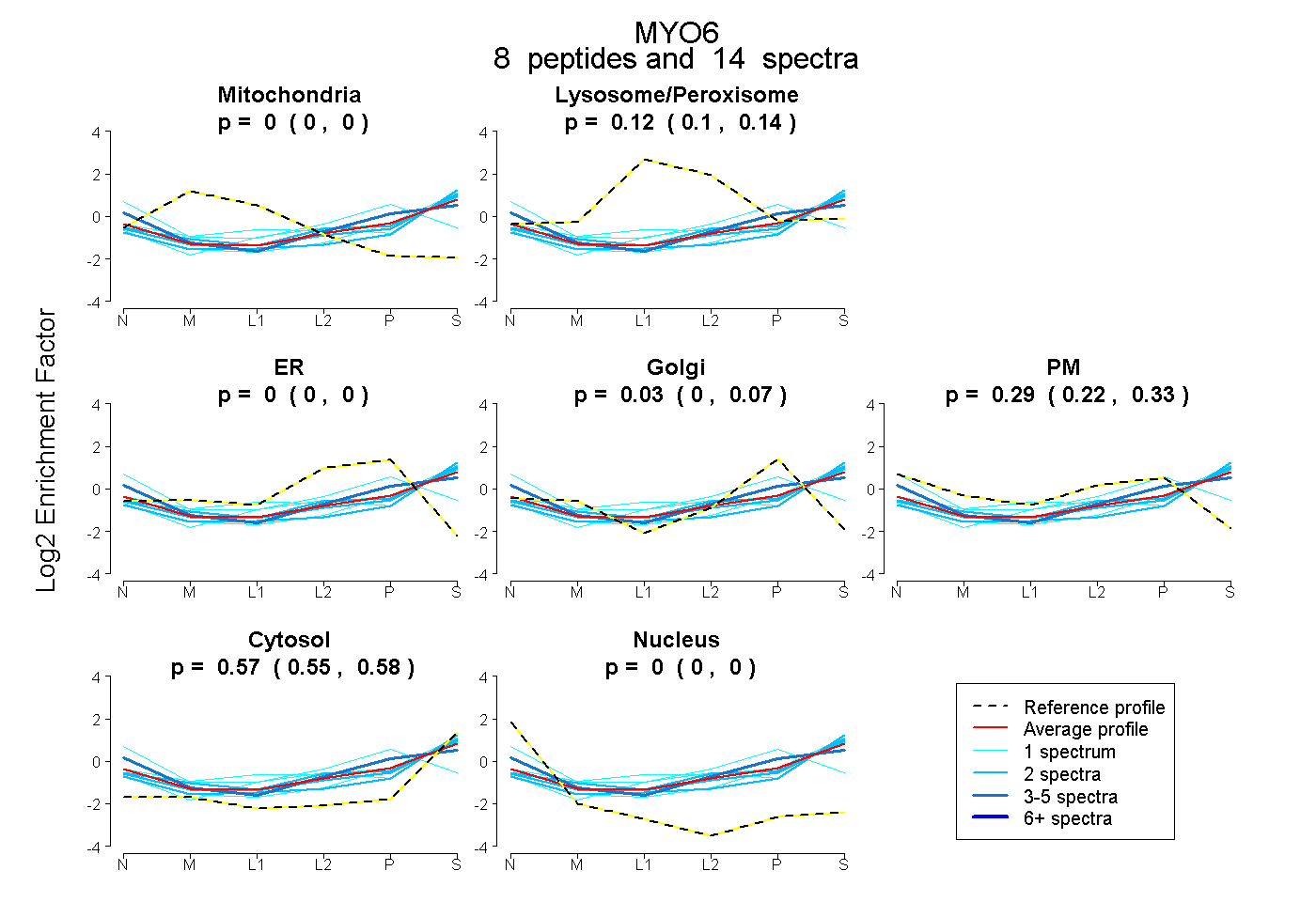 |
0.000 0.000 | 0.000 |
0.120 0.100 | 0.140 |
0.000 0.000 | 0.000 |
0.027 0.000 | 0.074 |
0.288 0.219 | 0.329 |
0.565 0.545 | 0.579 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
60 spectra |
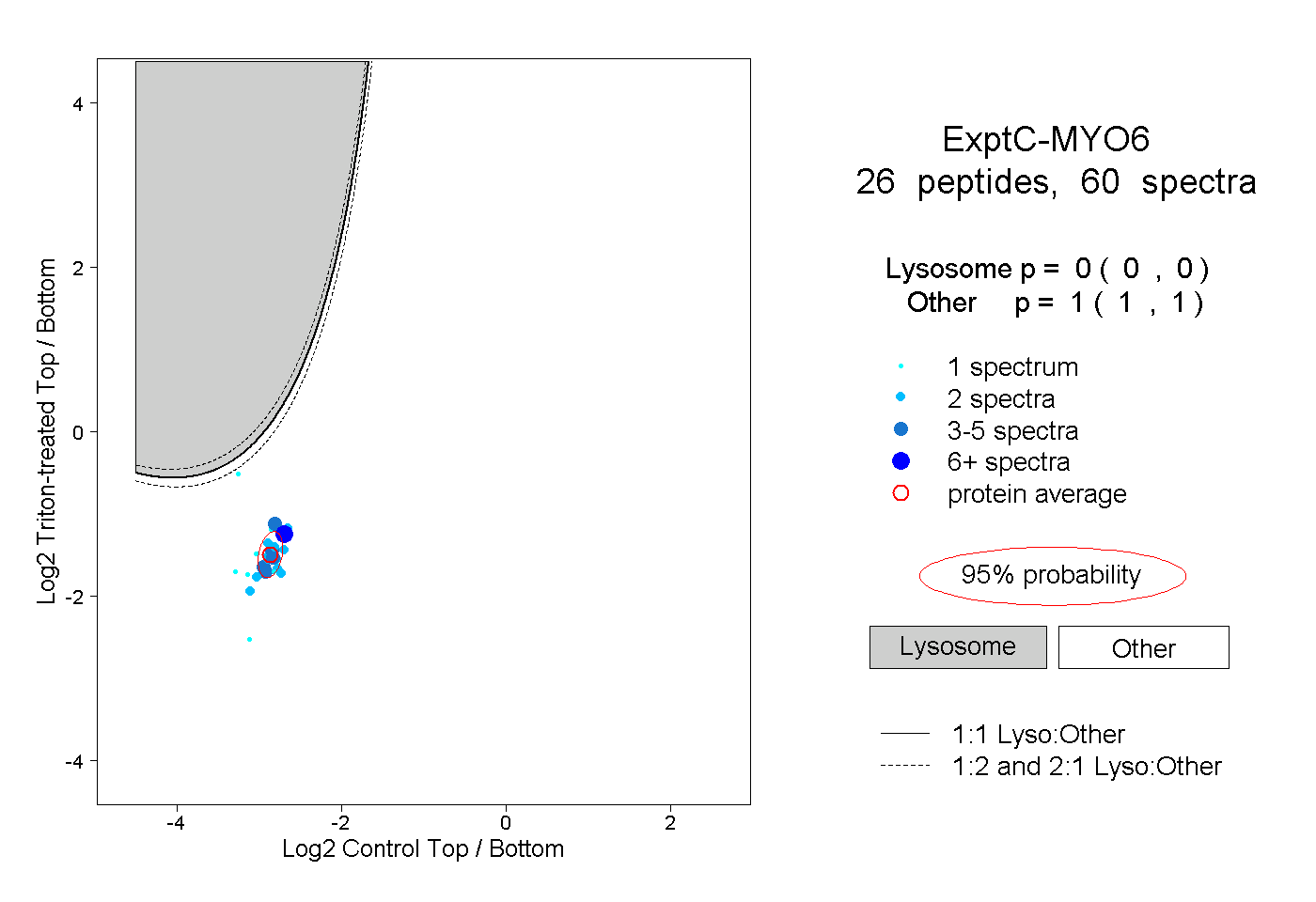 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
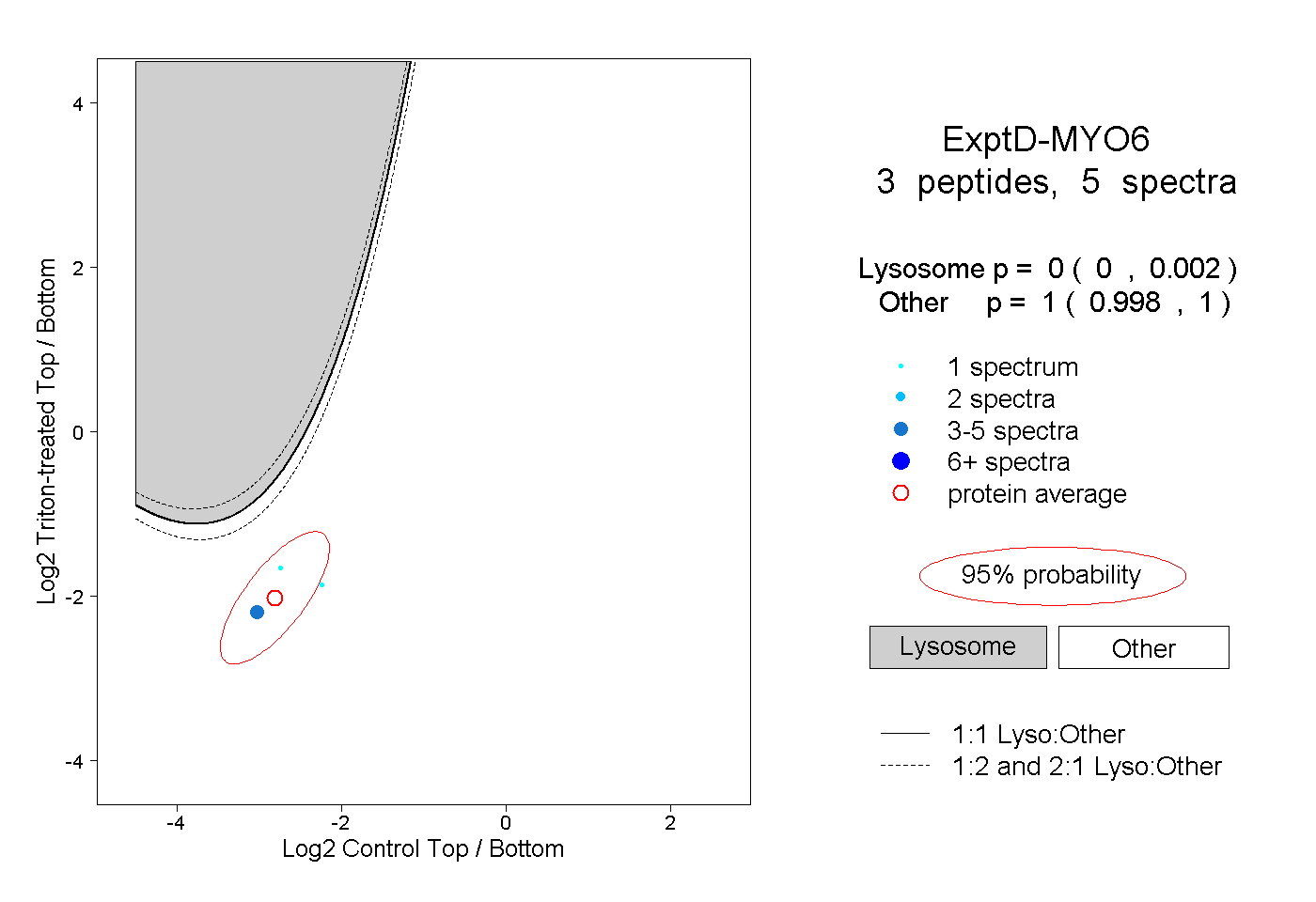 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |