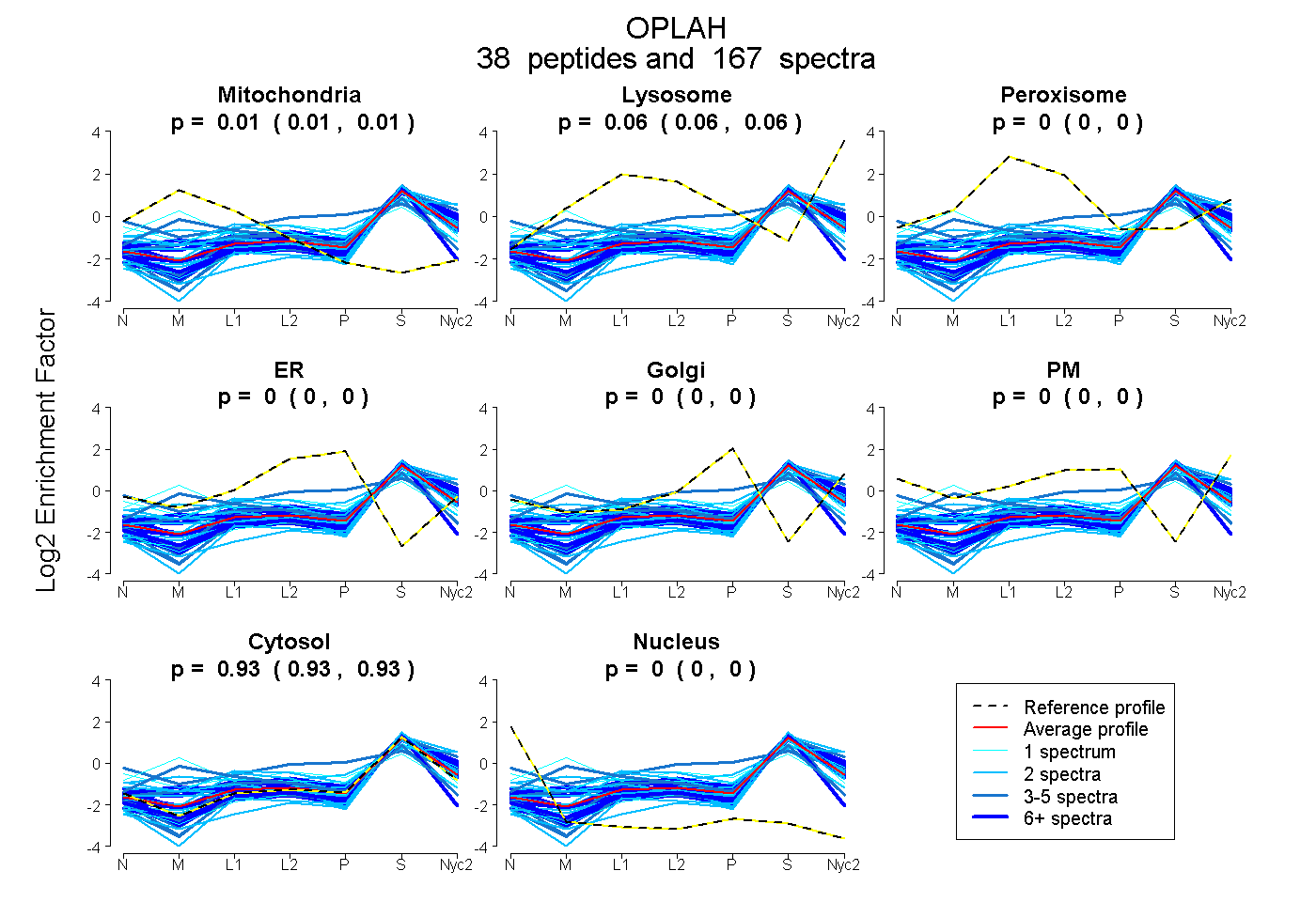
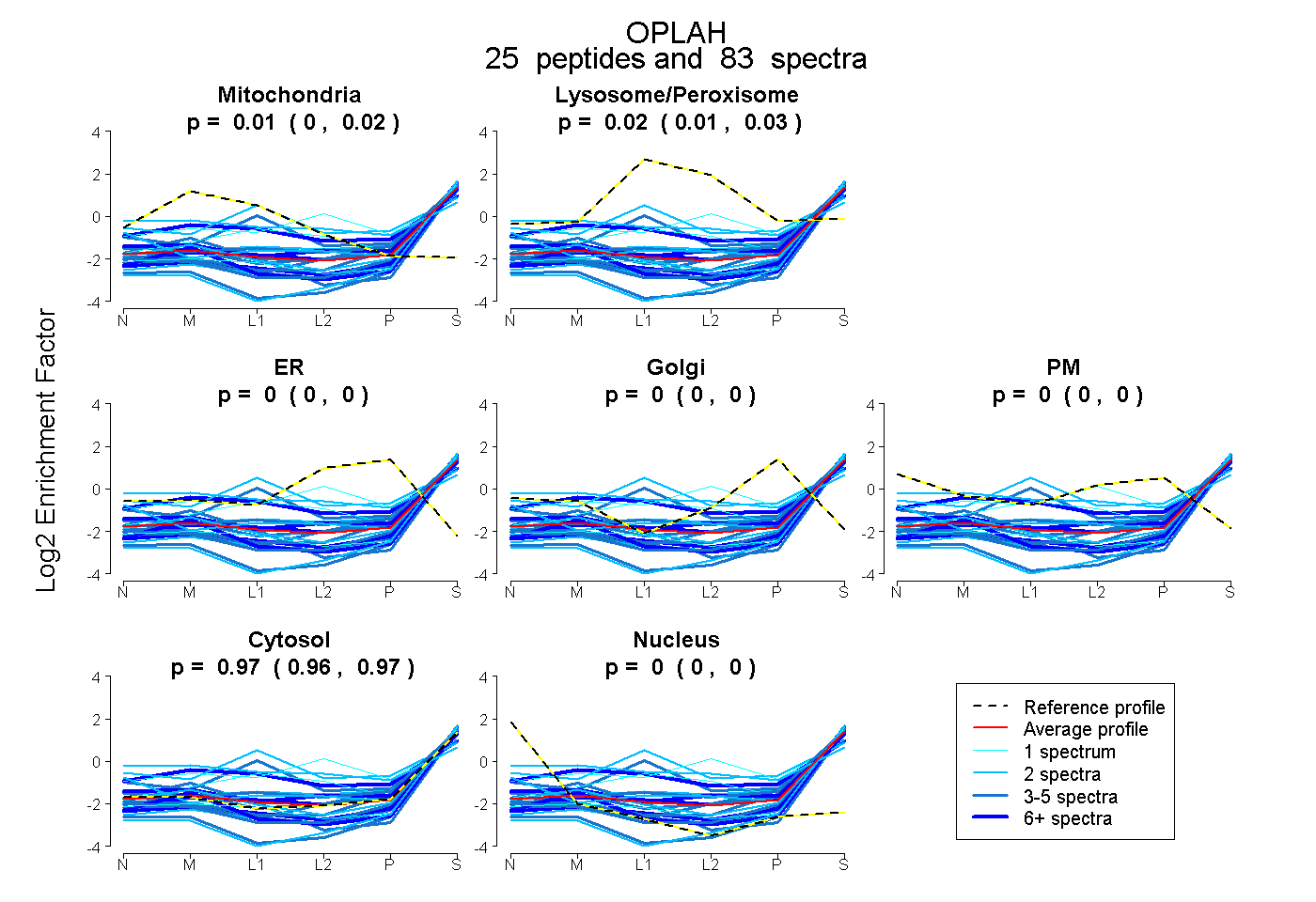
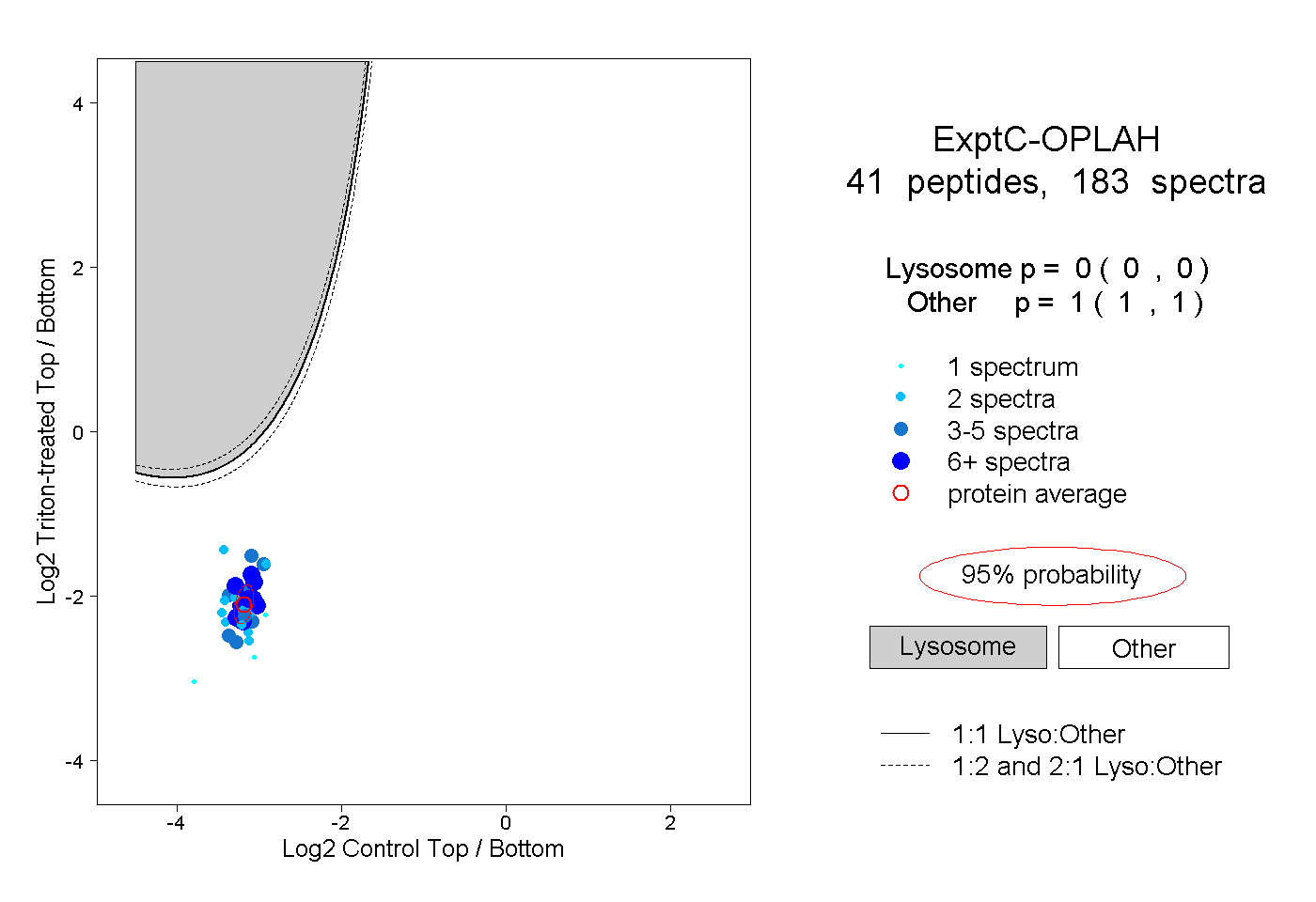
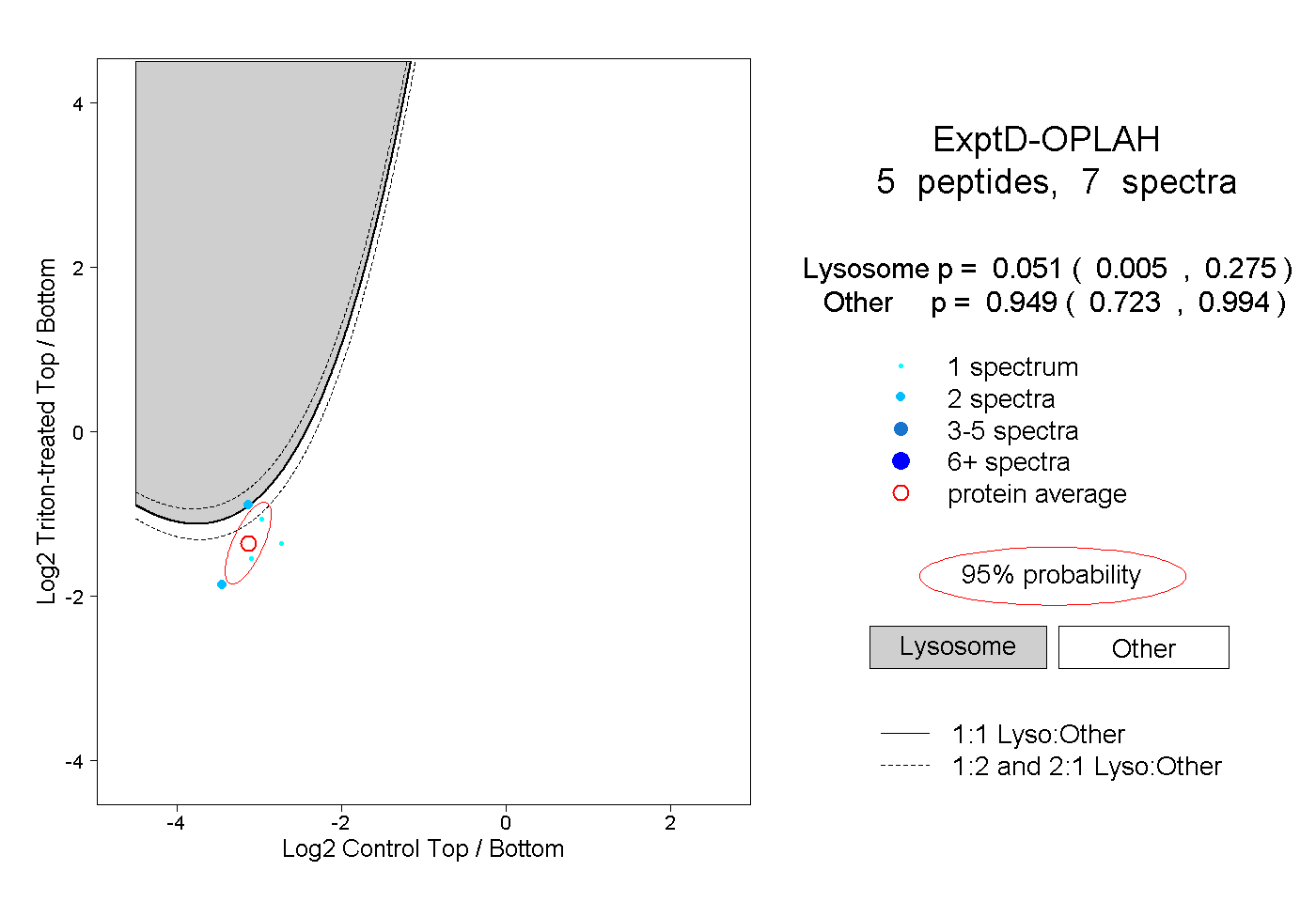
| 1 spectrum, LEEQCVDALQVQGFPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LDPIQLSIFSHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, NVQVLFMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, MGYYETVAGGAGAGPGWHGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, SDGGLAPMDAFSGSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GSVFEYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EEALLSVLTER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, ISVGAEGPSMADTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, GRPLDTSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YVQGFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SGLFVVGPESAGAHPGPACYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TAISTNIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GGTFTDVFAQCPGGHVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, AFQPYGLHGGEPGAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, AGDFGAAFVER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, EFGFIIPERPVVVDDVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TGDLLEIQQPVDLEALR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, IQTGPPHVEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, VANEAMCRPIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, VALLVTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, AQVAANQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, ALTQAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GHTACADAYLTPTIQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, ILEQEEGVLLPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, GFQGQLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, FELRPGSGGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ITDPEILESR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FMSIAEQMGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, NLHDNLSDLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LVQGGVFQEEAVTEALR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GLNLLIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, MGTTVATNALLER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, DIPLNQGCLAPVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, SGLQLEDTPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, GEPGAGSPVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, YPVILR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, AFGTSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, TVNLGGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GGPVTVTDANLVLGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, FHFAIDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, ISGCSGTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |