peptides
spectra
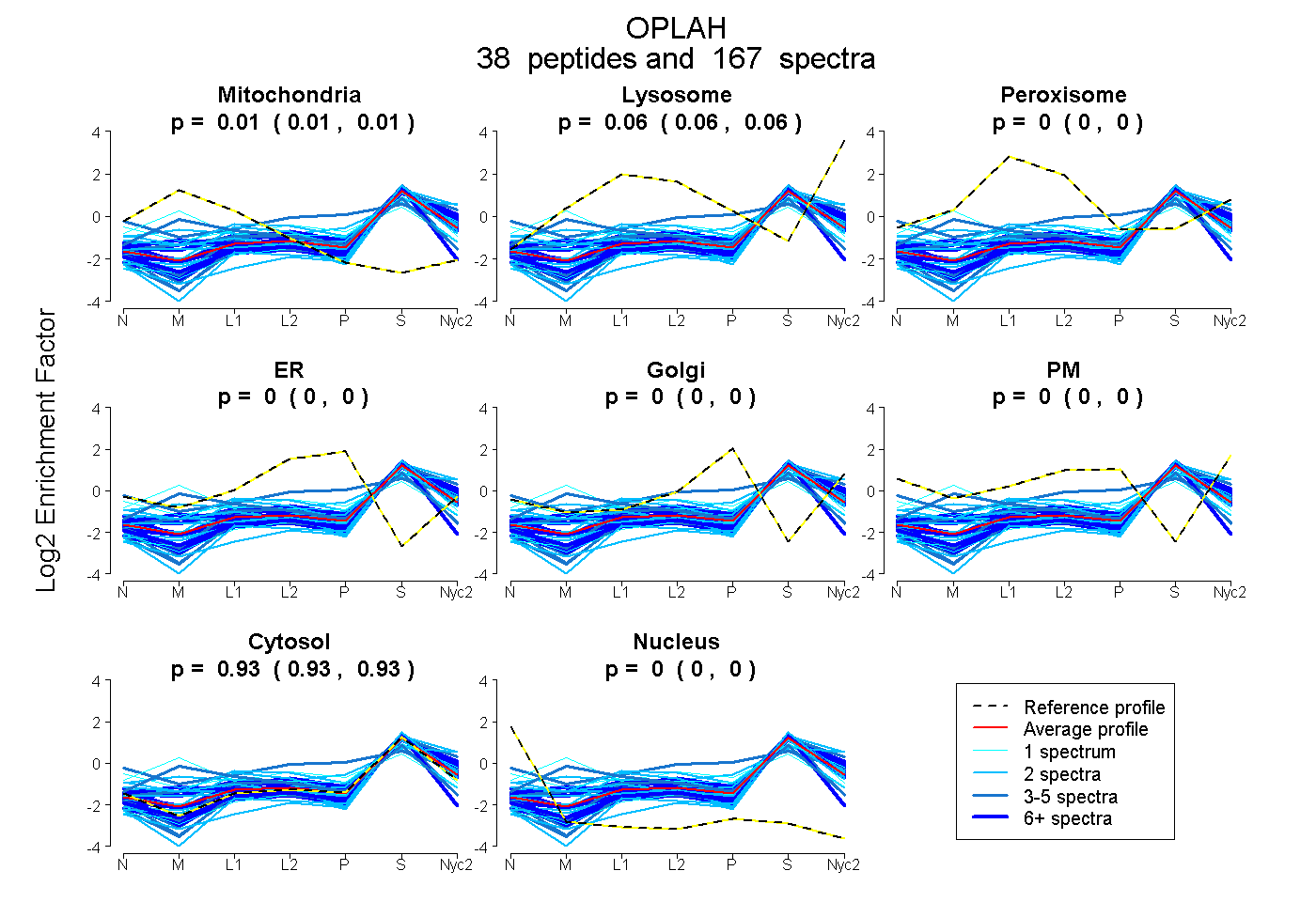
0.010 | 0.015
0.055 | 0.059
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.928 | 0.933
0.000 | 0.000
peptides
spectra
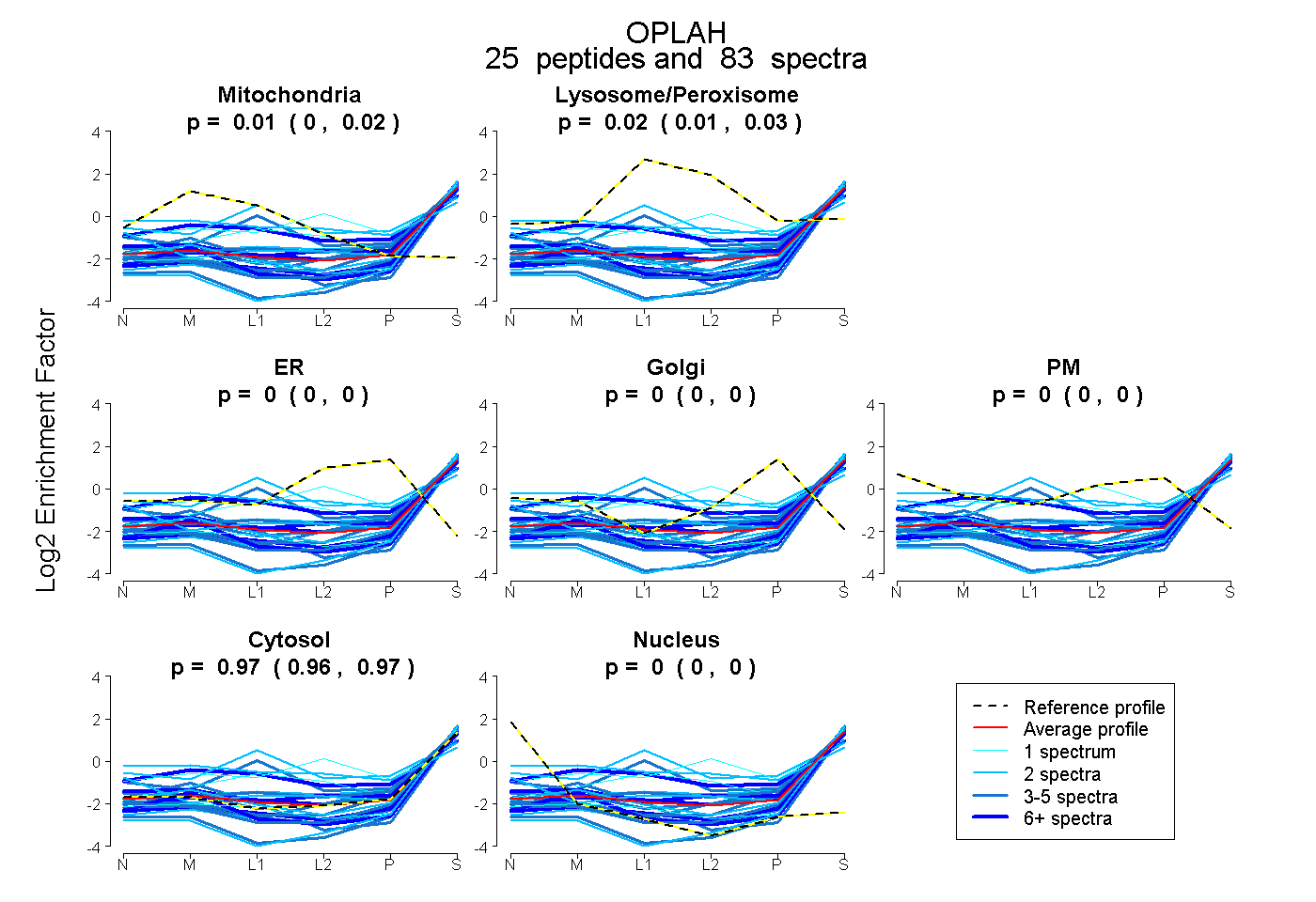
0.005 | 0.017
0.014 | 0.029
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.960 | 0.971
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
167 spectra |
 |
0.012 0.010 | 0.015 |
0.057 0.055 | 0.059 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.931 0.928 | 0.933 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
83 spectra |
 |
0.011 0.005 | 0.017 |
0.023 0.014 | 0.029 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.966 0.960 | 0.971 |
0.000 0.000 | 0.000 |
| 7 spectra, LDPIQLSIFSHR | 0.004 | 0.073 | 0.000 | 0.000 | 0.030 | 0.893 | 0.000 | |||
| 6 spectra, NVQVLFMR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, FELRPGSGGR | 0.000 | 0.135 | 0.000 | 0.000 | 0.000 | 0.865 | 0.000 | |||
| 2 spectra, SDGGLAPMDAFSGSR | 0.101 | 0.257 | 0.000 | 0.000 | 0.188 | 0.454 | 0.000 | |||
| 3 spectra, ITDPEILESR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 3 spectra, GSVFEYR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 3 spectra, NLHDNLSDLR | 0.000 | 0.115 | 0.000 | 0.000 | 0.000 | 0.885 | 0.000 | |||
| 1 spectrum, ISVGAEGPSMADTR | 0.000 | 0.363 | 0.073 | 0.000 | 0.018 | 0.546 | 0.000 | |||
| 2 spectra, GHDPSAHVLACFGGAGGQHACAIAR | 0.000 | 0.488 | 0.000 | 0.000 | 0.000 | 0.465 | 0.048 | |||
| 2 spectra, YVQGFR | 0.016 | 0.000 | 0.000 | 0.000 | 0.000 | 0.984 | 0.000 | |||
| 2 spectra, LEGLLSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, SGLFVVGPESAGAHPGPACYR | 0.000 | 0.114 | 0.000 | 0.000 | 0.000 | 0.802 | 0.084 | |||
| 3 spectra, ALGMDTVHIHR | 0.000 | 0.027 | 0.000 | 0.000 | 0.000 | 0.973 | 0.000 | |||
| 7 spectra, GGTFTDVFAQCPGGHVR | 0.147 | 0.245 | 0.000 | 0.008 | 0.000 | 0.601 | 0.000 | |||
| 3 spectra, GLNLLIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 3 spectra, AFQPYGLHGGEPGAR | 0.000 | 0.337 | 0.000 | 0.000 | 0.000 | 0.647 | 0.016 | |||
| 4 spectra, AGDFGAAFVER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 4 spectra, DIPLNQGCLAPVR | 0.013 | 0.000 | 0.000 | 0.000 | 0.000 | 0.931 | 0.056 | |||
| 6 spectra, EFGFIIPERPVVVDDVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, VANEAMCRPIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 4 spectra, VALLVTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.997 | 0.003 | |||
| 2 spectra, YPVILR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 3 spectra, ALTQAR | 0.000 | 0.005 | 0.000 | 0.069 | 0.000 | 0.925 | 0.000 | |||
| 1 spectrum, GHTACADAYLTPTIQR | 0.000 | 0.278 | 0.000 | 0.000 | 0.000 | 0.722 | 0.000 | |||
| 7 spectra, FHFAIDR | 0.000 | 0.021 | 0.000 | 0.000 | 0.000 | 0.979 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
183 spectra |
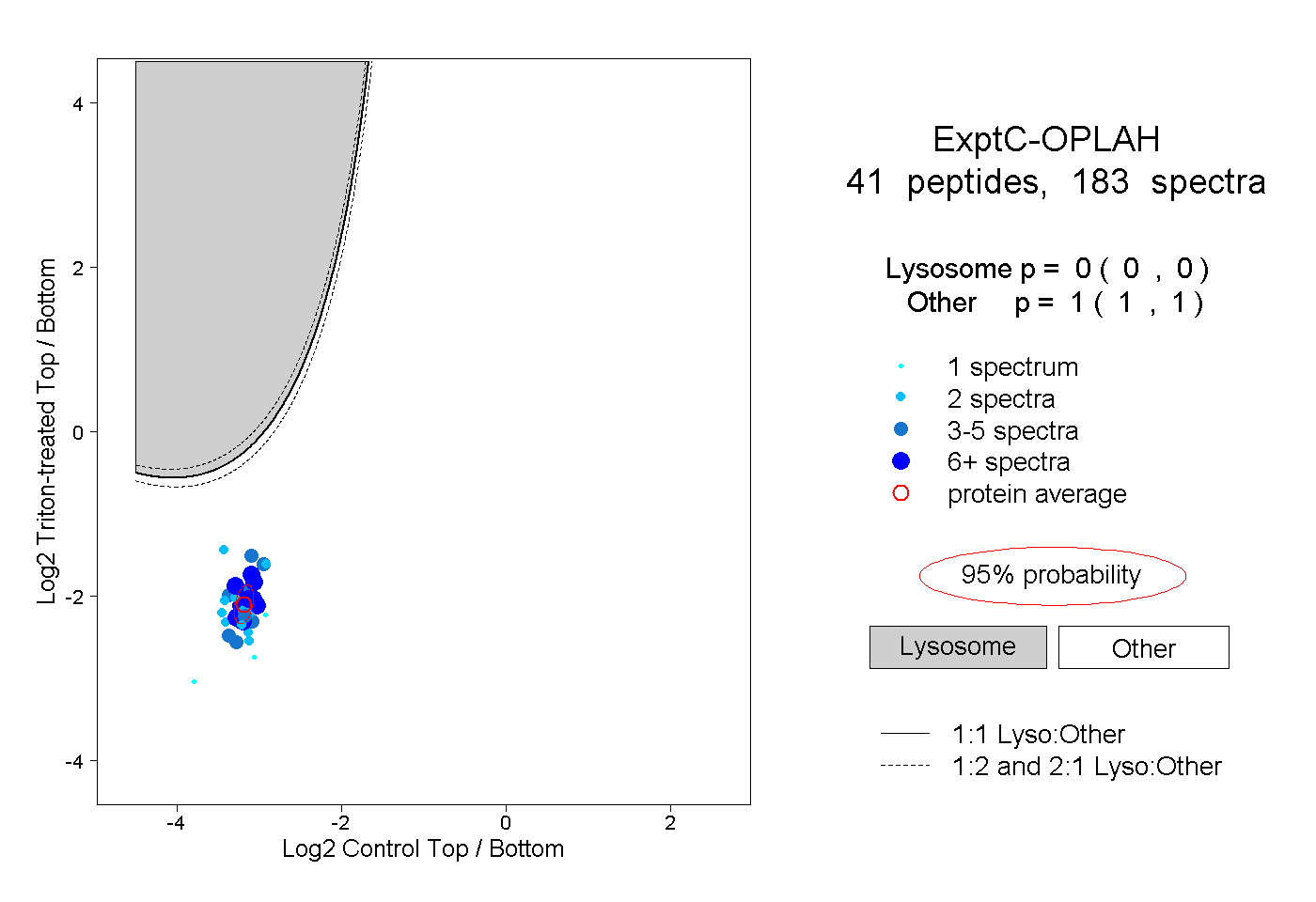 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
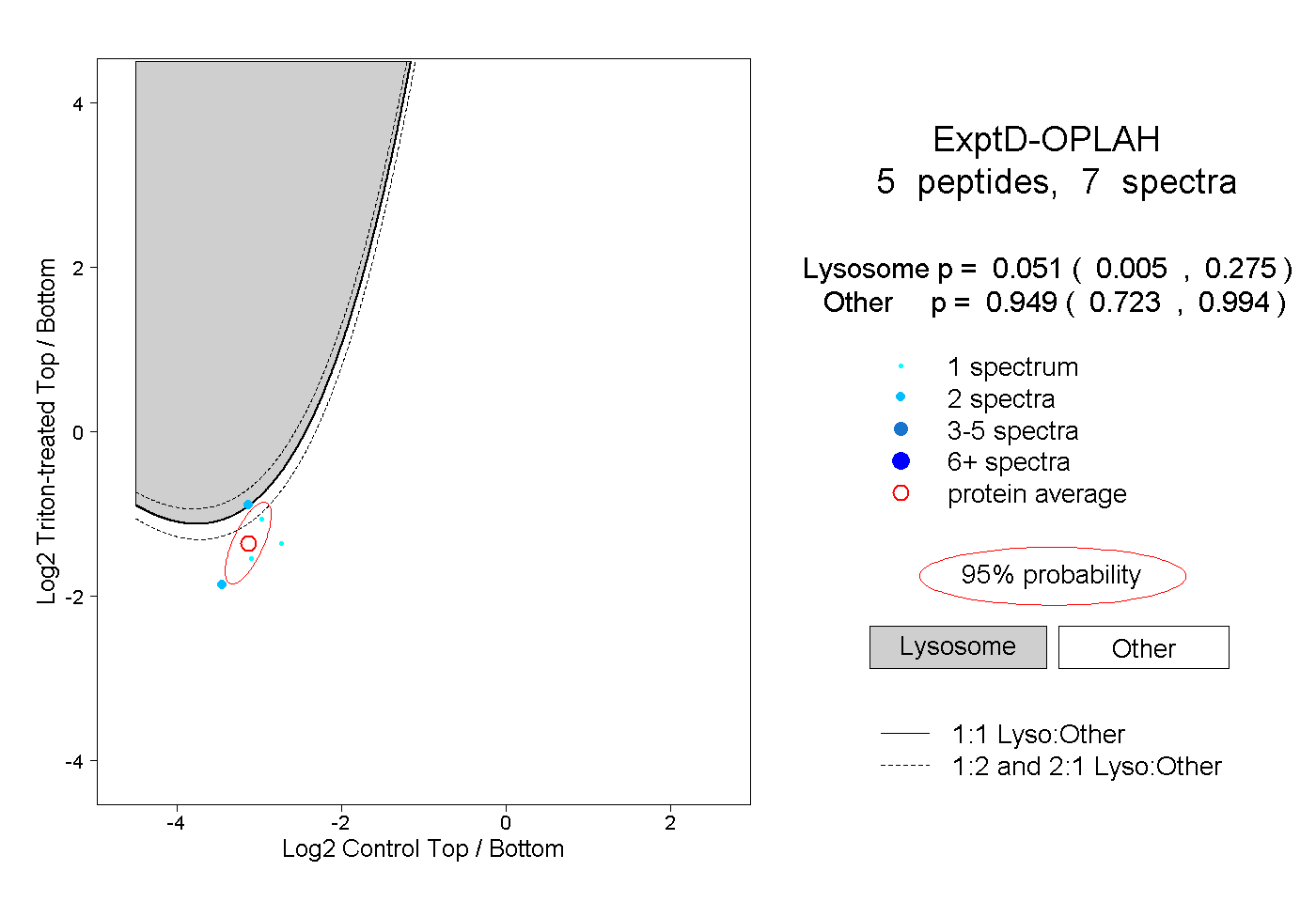 |
0.051 0.005 | 0.275 |
0.949 0.723 | 0.994 |