peptides
spectra
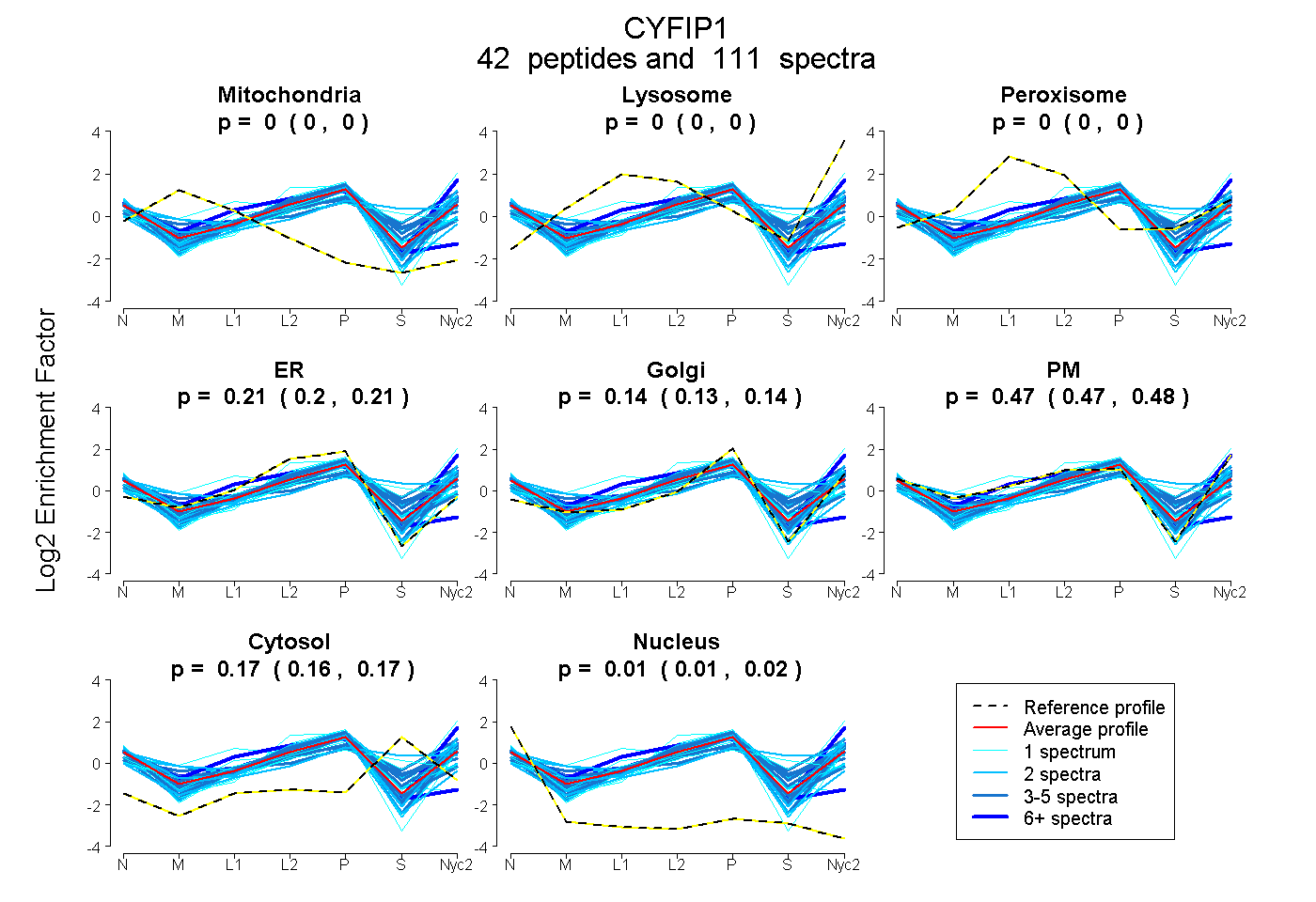
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.201 | 0.214
0.133 | 0.143
0.469 | 0.479
0.162 | 0.169
0.011 | 0.015
peptides
spectra
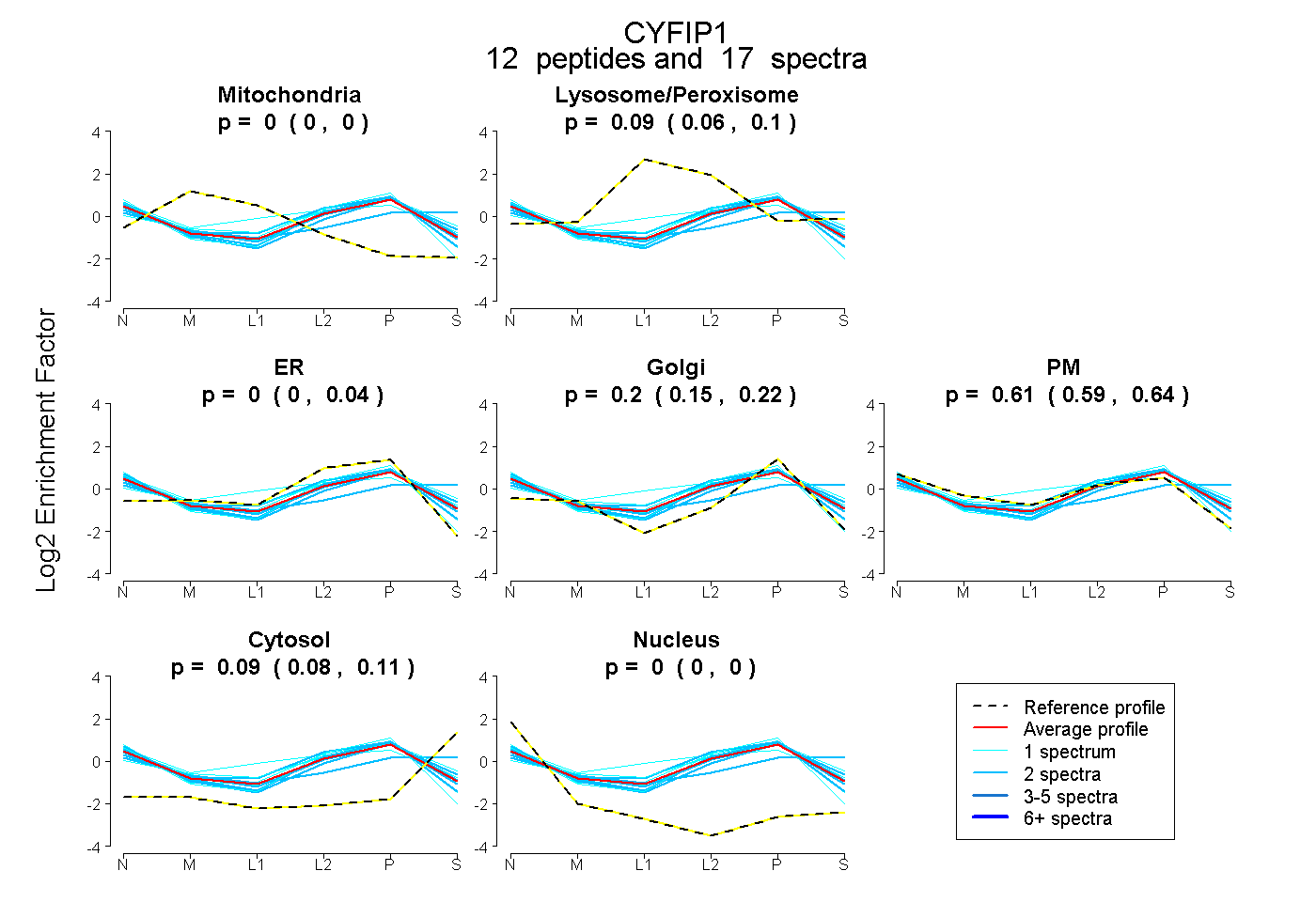
0.000 | 0.000
0.062 | 0.098
0.000 | 0.042
0.150 | 0.218
0.588 | 0.639
0.084 | 0.105
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
111 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.208 0.201 | 0.214 |
0.138 0.133 | 0.143 |
0.474 0.469 | 0.479 |
0.166 0.162 | 0.169 |
0.013 0.011 | 0.015 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
17 spectra |
 |
0.000 0.000 | 0.000 |
0.087 0.062 | 0.098 |
0.003 0.000 | 0.042 |
0.200 0.150 | 0.218 |
0.615 0.588 | 0.639 |
0.094 0.084 | 0.105 |
0.000 0.000 | 0.000 |
| 2 spectra, NAFVTGIAR | 0.000 | 0.066 | 0.136 | 0.092 | 0.688 | 0.018 | 0.000 | |||
| 1 spectrum, YAPLHLVPLIER | 0.000 | 0.000 | 0.310 | 0.154 | 0.490 | 0.000 | 0.046 | |||
| 2 spectra, SSLEGPTILDIEK | 0.000 | 0.115 | 0.000 | 0.280 | 0.468 | 0.137 | 0.000 | |||
| 2 spectra, SLLQGTILQYVK | 0.000 | 0.000 | 0.000 | 0.216 | 0.675 | 0.109 | 0.000 | |||
| 1 spectrum, SGFDIK | 0.000 | 0.276 | 0.000 | 0.411 | 0.204 | 0.108 | 0.000 | |||
| 1 spectrum, EGDLLTK | 0.000 | 0.078 | 0.000 | 0.149 | 0.648 | 0.126 | 0.000 | |||
| 2 spectra, NFVGPPHFQVICR | 0.000 | 0.112 | 0.000 | 0.030 | 0.502 | 0.355 | 0.000 | |||
| 1 spectrum, EANHNVSAPYGR | 0.000 | 0.240 | 0.000 | 0.011 | 0.665 | 0.084 | 0.000 | |||
| 2 spectra, SLELAIGR | 0.000 | 0.000 | 0.158 | 0.111 | 0.600 | 0.131 | 0.000 | |||
| 1 spectrum, HVQLLGR | 0.000 | 0.165 | 0.000 | 0.306 | 0.494 | 0.035 | 0.000 | |||
| 1 spectrum, LADQIFAYYK | 0.000 | 0.000 | 0.124 | 0.010 | 0.826 | 0.040 | 0.000 | |||
| 1 spectrum, AAQFLR | 0.000 | 0.046 | 0.014 | 0.230 | 0.682 | 0.028 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
108 spectra |
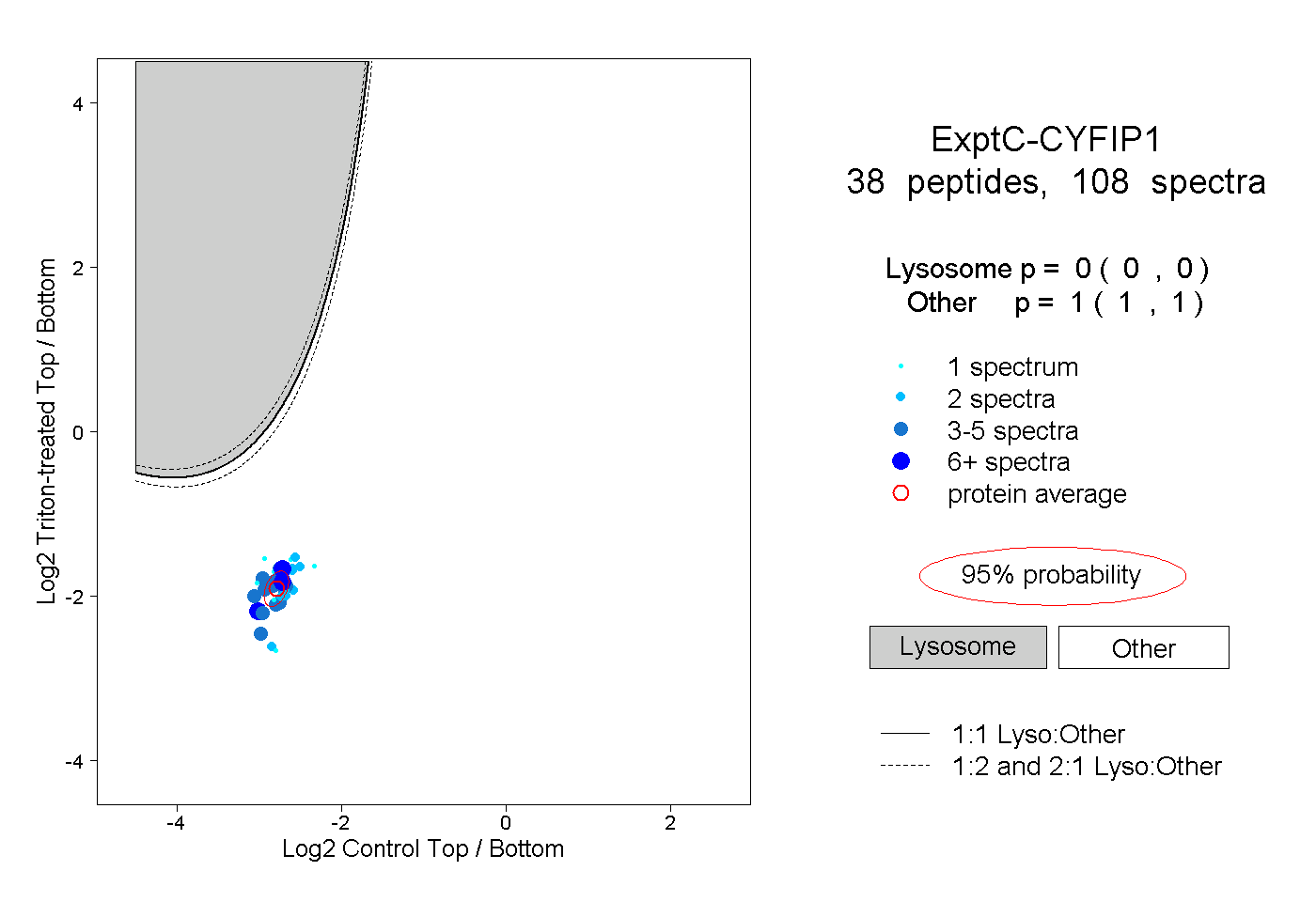 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
25 spectra |
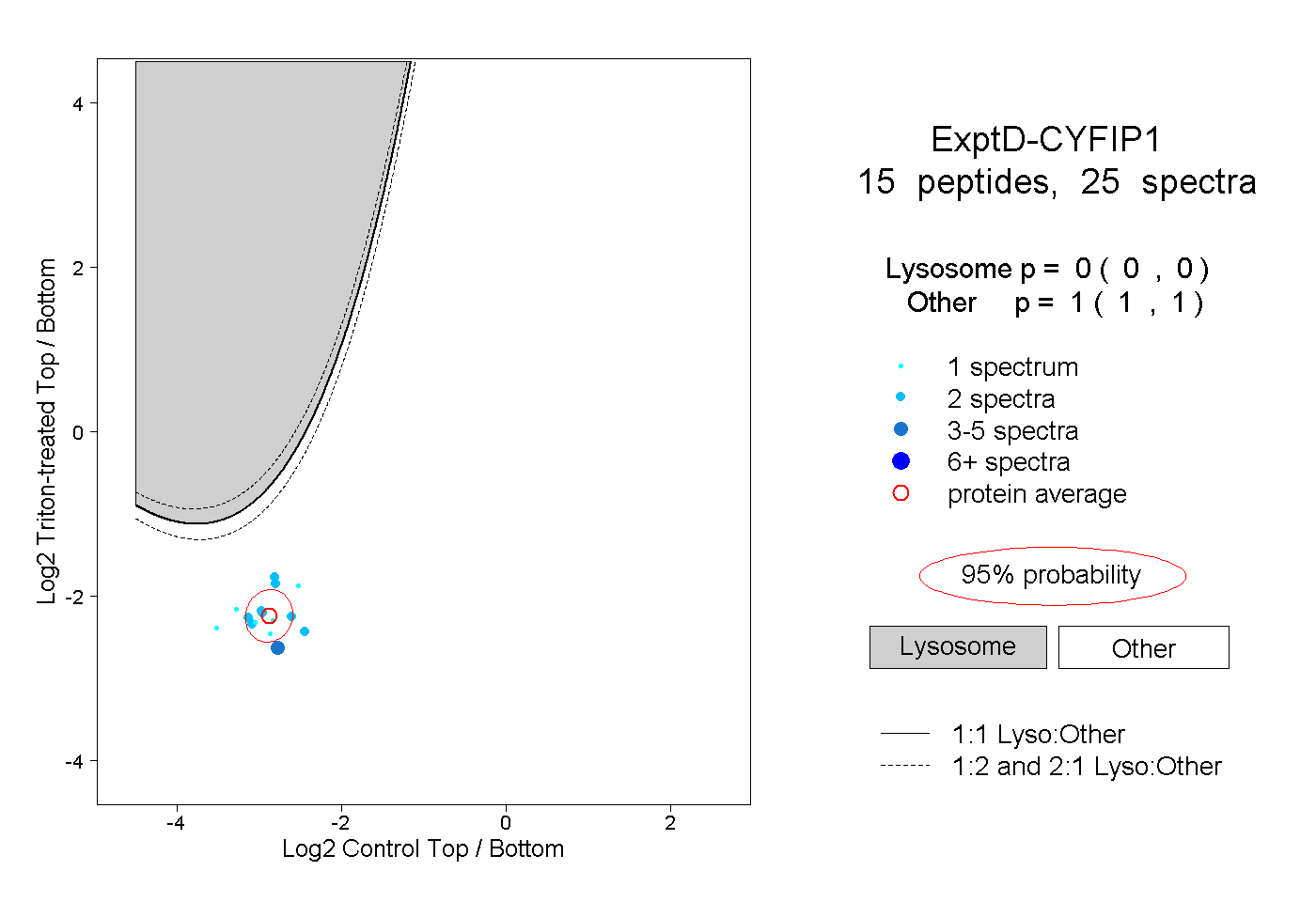 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |