peptides
spectra
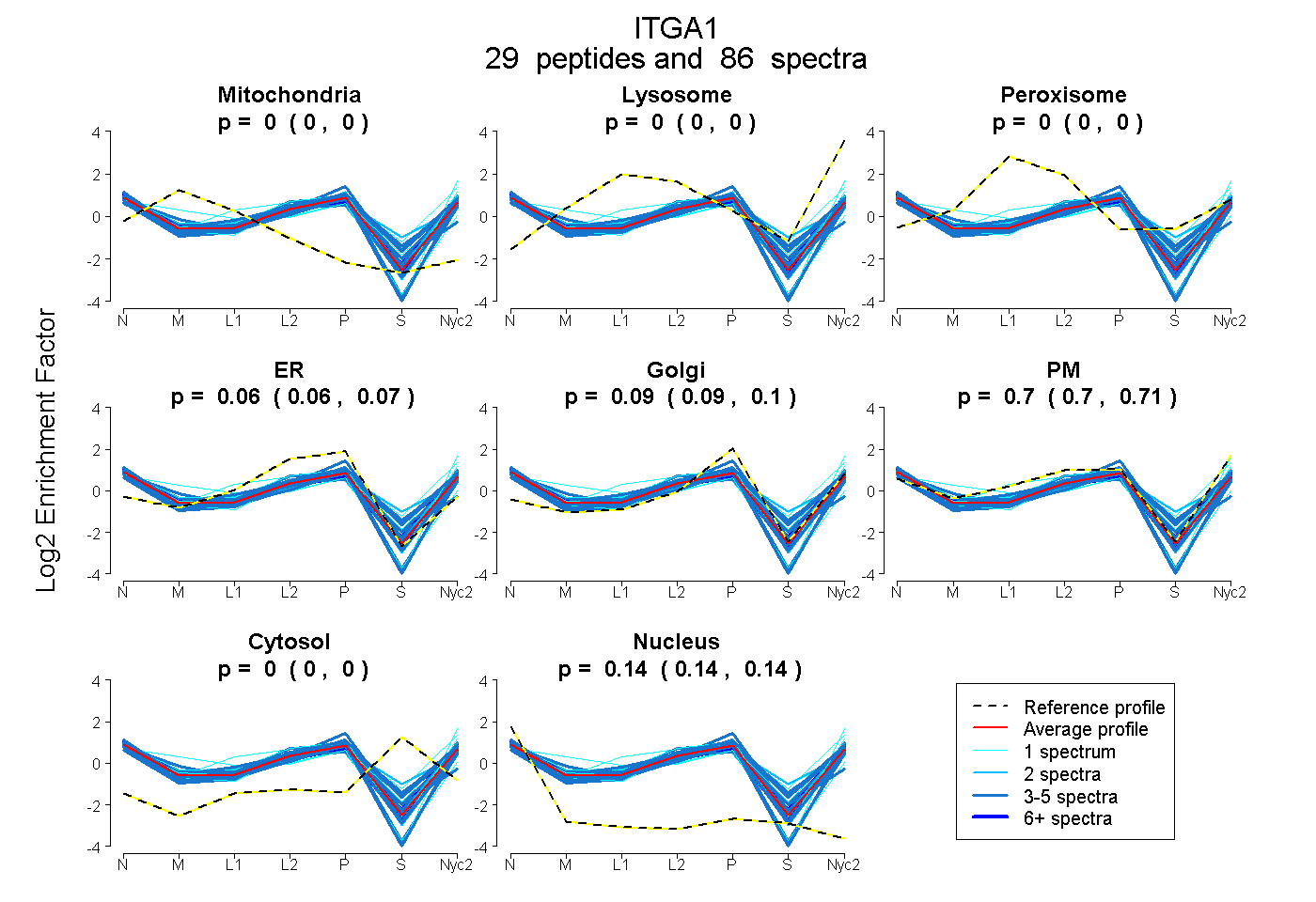
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.055 | 0.066
0.088 | 0.096
0.699 | 0.707
0.000 | 0.000
0.142 | 0.144
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
86 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.061 0.055 | 0.066 |
0.092 0.088 | 0.096 |
0.703 0.699 | 0.707 |
0.000 0.000 | 0.000 |
0.143 0.142 | 0.144 |
| 1 spectrum, TVVQHSPNLIFSGIEEIQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.947 | 0.000 | 0.053 | ||
| 1 spectrum, SLEDPFGINSGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.103 | 0.720 | 0.070 | 0.107 | ||
| 3 spectra, YSSTEEVLVAANK | 0.000 | 0.000 | 0.000 | 0.074 | 0.061 | 0.699 | 0.000 | 0.166 | ||
| 4 spectra, FGTAIAAVK | 0.012 | 0.000 | 0.000 | 0.170 | 0.000 | 0.703 | 0.000 | 0.116 | ||
| 2 spectra, ELAIQISK | 0.020 | 0.000 | 0.000 | 0.000 | 0.000 | 0.846 | 0.000 | 0.134 | ||
| 2 spectra, SILLVK | 0.000 | 0.000 | 0.000 | 0.044 | 0.245 | 0.572 | 0.000 | 0.139 | ||
| 5 spectra, SIASEPTEK | 0.000 | 0.000 | 0.000 | 0.034 | 0.228 | 0.572 | 0.000 | 0.166 | ||
| 1 spectrum, QTCCSSLK | 0.270 | 0.000 | 0.000 | 0.122 | 0.081 | 0.475 | 0.000 | 0.052 | ||
| 4 spectra, ESECLR | 0.000 | 0.000 | 0.000 | 0.143 | 0.000 | 0.719 | 0.000 | 0.138 | ||
| 3 spectra, VTLDSLR | 0.000 | 0.000 | 0.000 | 0.040 | 0.082 | 0.729 | 0.000 | 0.149 | ||
| 1 spectrum, VTMNFEPNK | 0.000 | 0.000 | 0.000 | 0.000 | 0.181 | 0.735 | 0.000 | 0.085 | ||
| 3 spectra, IPSGGDGK | 0.000 | 0.000 | 0.000 | 0.199 | 0.000 | 0.636 | 0.000 | 0.165 | ||
| 2 spectra, SFFSGTQER | 0.000 | 0.000 | 0.000 | 0.000 | 0.092 | 0.770 | 0.000 | 0.138 | ||
| 3 spectra, QVIQDCEDENIQR | 0.000 | 0.000 | 0.053 | 0.375 | 0.000 | 0.374 | 0.020 | 0.177 | ||
| 3 spectra, TGDVYK | 0.000 | 0.000 | 0.000 | 0.083 | 0.027 | 0.646 | 0.166 | 0.078 | ||
| 1 spectrum, AGETVTFK | 0.043 | 0.000 | 0.004 | 0.000 | 0.073 | 0.775 | 0.000 | 0.105 | ||
| 4 spectra, VMVIVTDGESHDNYR | 0.018 | 0.000 | 0.000 | 0.108 | 0.010 | 0.685 | 0.138 | 0.041 | ||
| 4 spectra, HDFQDSVR | 0.088 | 0.000 | 0.000 | 0.004 | 0.045 | 0.716 | 0.050 | 0.097 | ||
| 6 spectra, FEYQMSLEPIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.077 | 0.778 | 0.000 | 0.145 | ||
| 3 spectra, FSIAILGHYNR | 0.000 | 0.000 | 0.000 | 0.148 | 0.381 | 0.362 | 0.000 | 0.109 | ||
| 4 spectra, EAFTEAR | 0.000 | 0.000 | 0.000 | 0.090 | 0.037 | 0.709 | 0.000 | 0.164 | ||
| 4 spectra, NEPCGAR | 0.000 | 0.000 | 0.000 | 0.128 | 0.188 | 0.538 | 0.000 | 0.145 | ||
| 3 spectra, WVLIGSPLVGQPK | 0.000 | 0.000 | 0.000 | 0.026 | 0.151 | 0.643 | 0.132 | 0.047 | ||
| 1 spectrum, EAYAQR | 0.000 | 0.000 | 0.003 | 0.042 | 0.000 | 0.639 | 0.231 | 0.085 | ||
| 1 spectrum, DVAVVK | 0.000 | 0.000 | 0.093 | 0.000 | 0.000 | 0.760 | 0.147 | 0.000 | ||
| 8 spectra, FVEEIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.097 | 0.739 | 0.000 | 0.164 | ||
| 3 spectra, QGGLQTMTALGIDTAR | 0.000 | 0.000 | 0.000 | 0.012 | 0.068 | 0.799 | 0.000 | 0.121 | ||
| 4 spectra, VGYPFLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.096 | 0.732 | 0.000 | 0.172 | ||
| 2 spectra, EDSIYEADLQYR | 0.000 | 0.000 | 0.063 | 0.091 | 0.000 | 0.580 | 0.218 | 0.048 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
18 spectra |
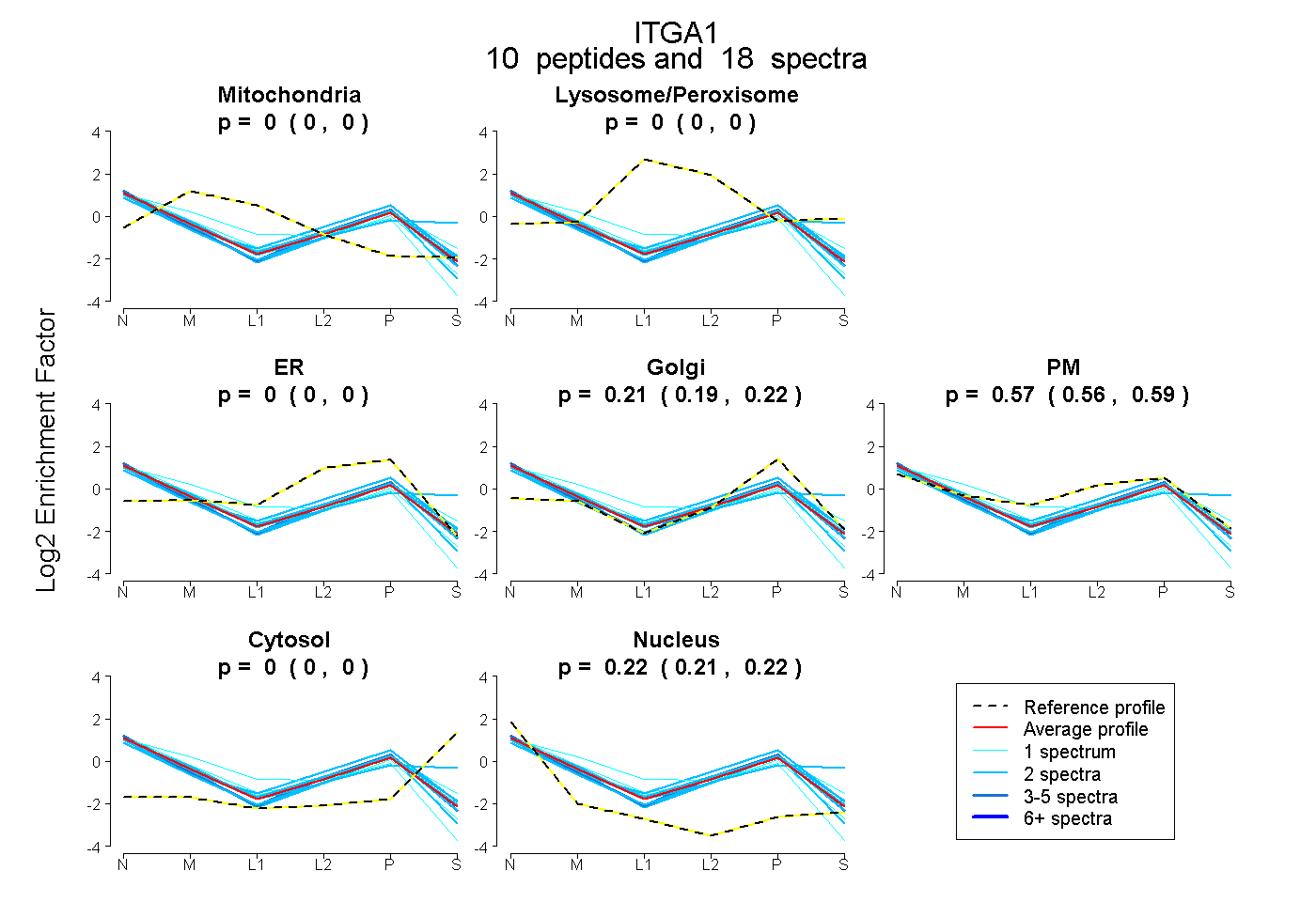 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.207 0.193 | 0.220 |
0.575 0.559 | 0.588 |
0.000 0.000 | 0.000 |
0.218 0.212 | 0.223 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
94 spectra |
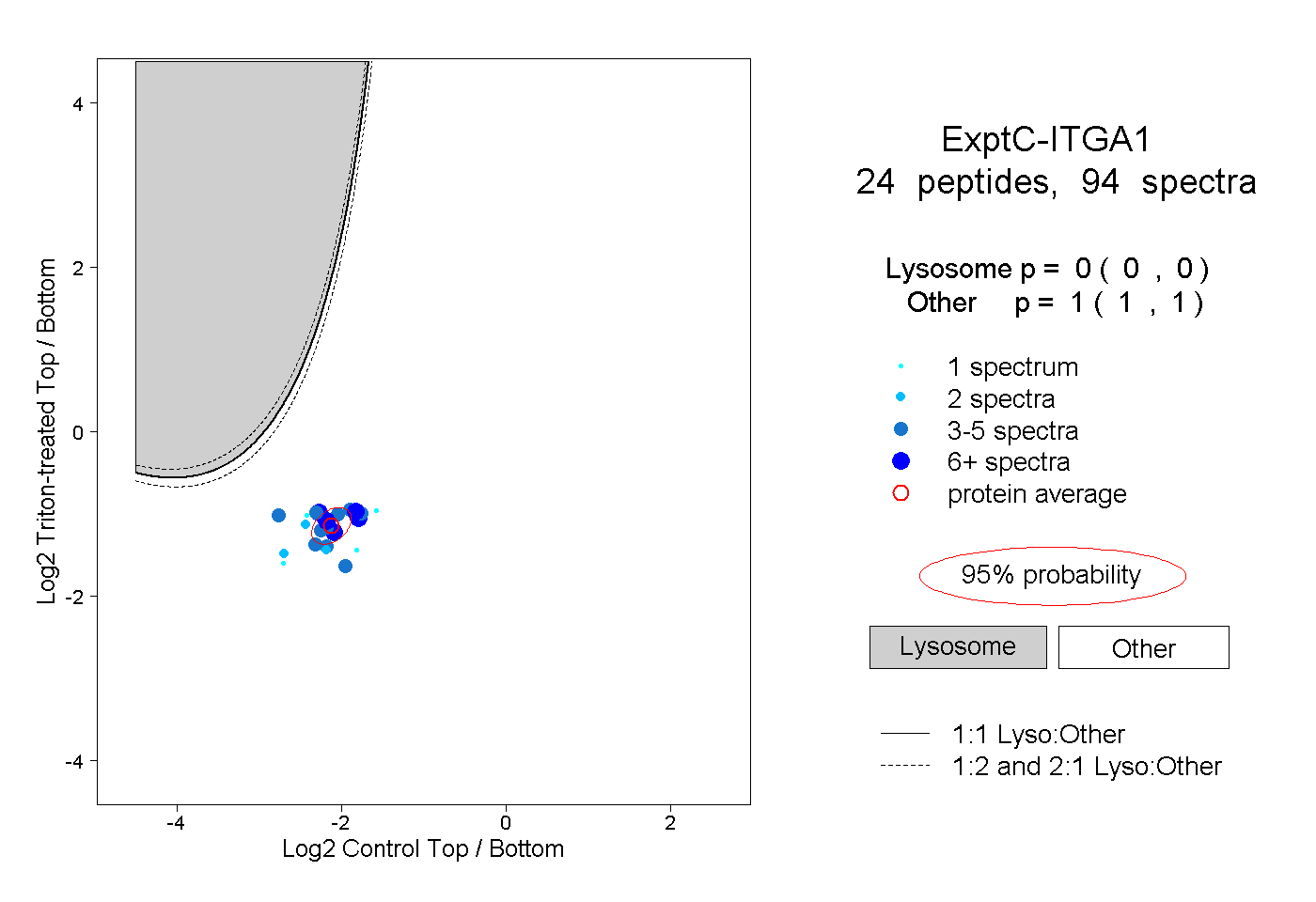 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
10 spectra |
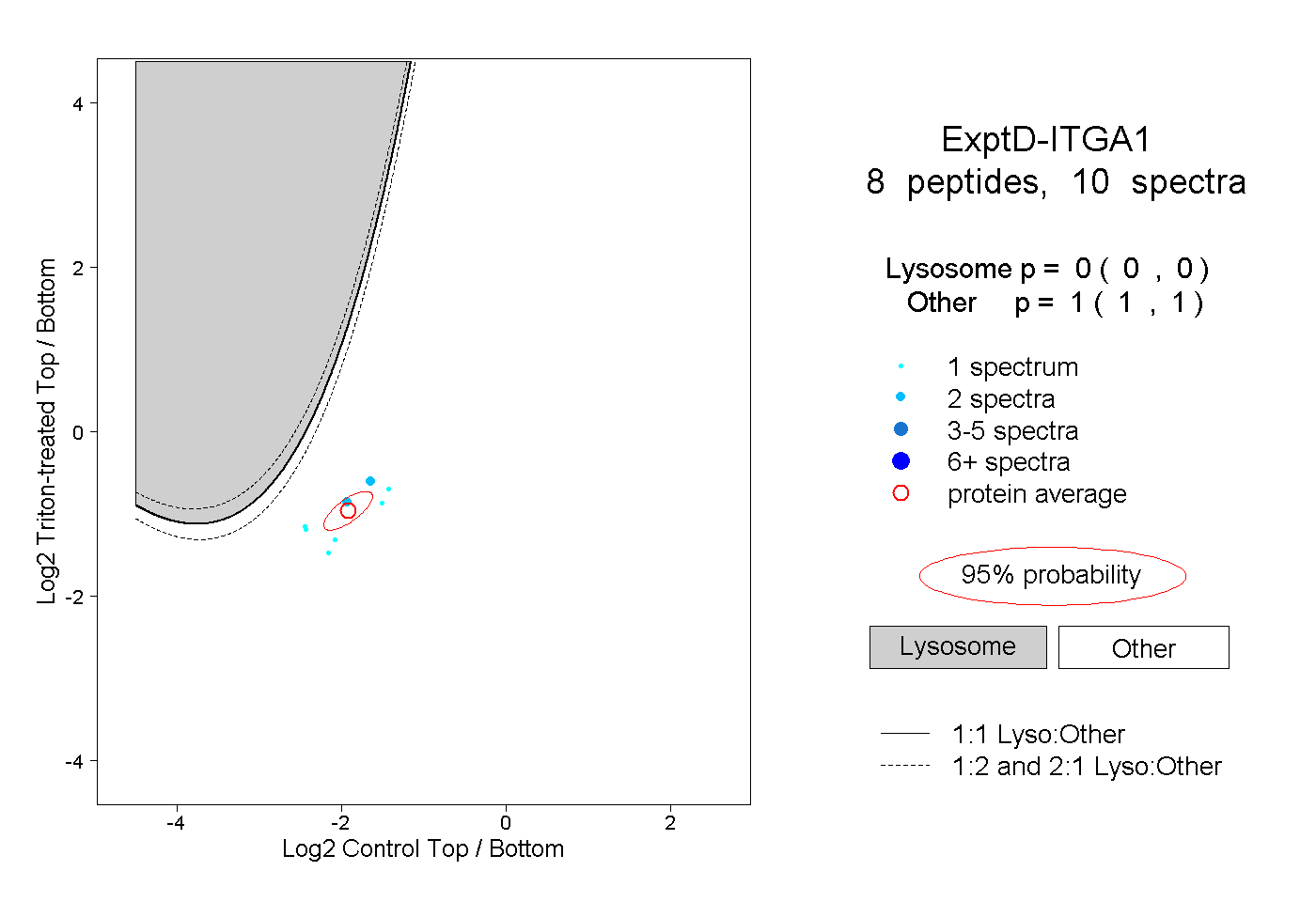 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |