peptides
spectra
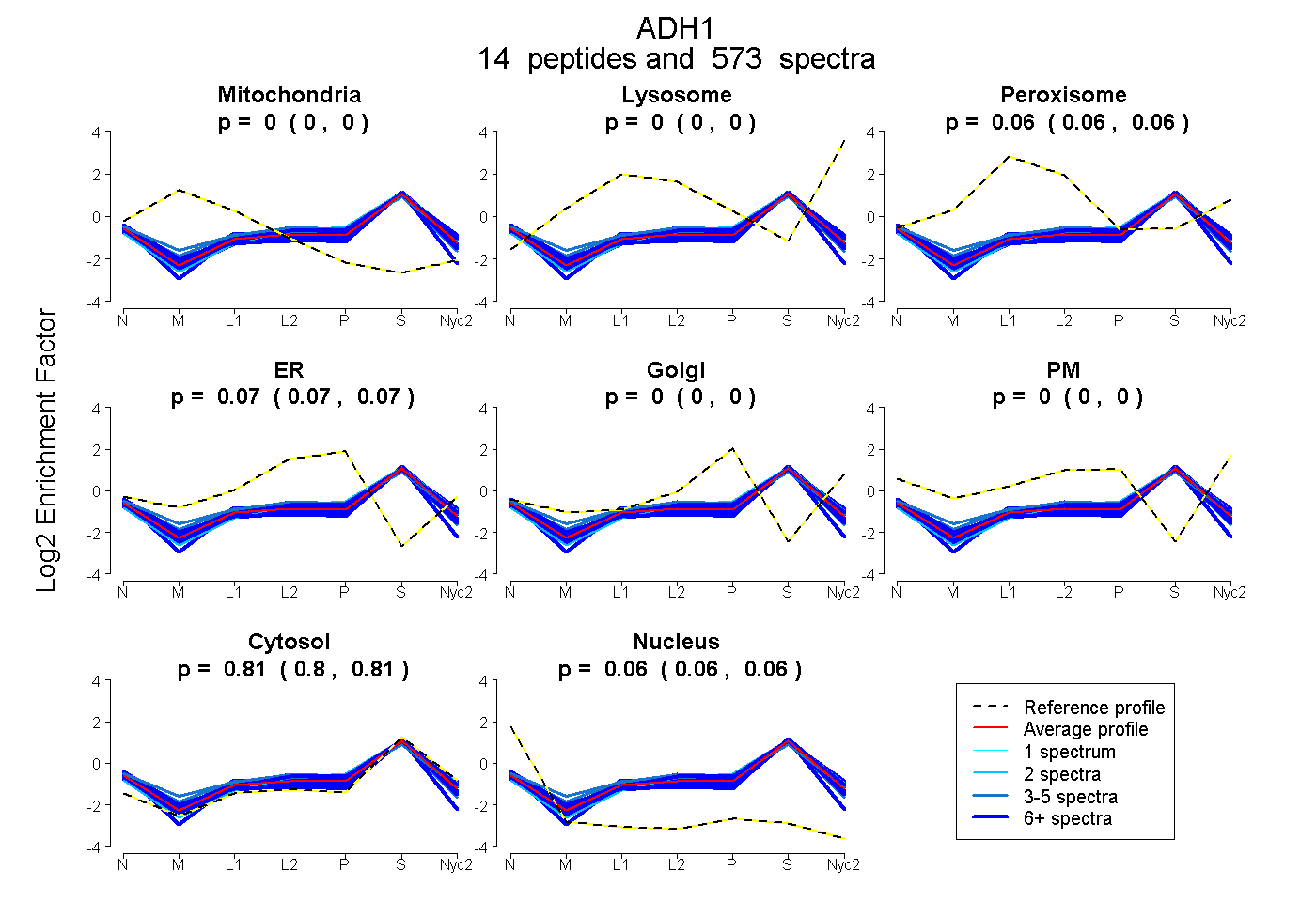
0.000 | 0.000
0.000 | 0.000
0.063 | 0.065
0.070 | 0.071
0.000 | 0.000
0.000 | 0.000
0.804 | 0.806
0.060 | 0.061
peptides
spectra
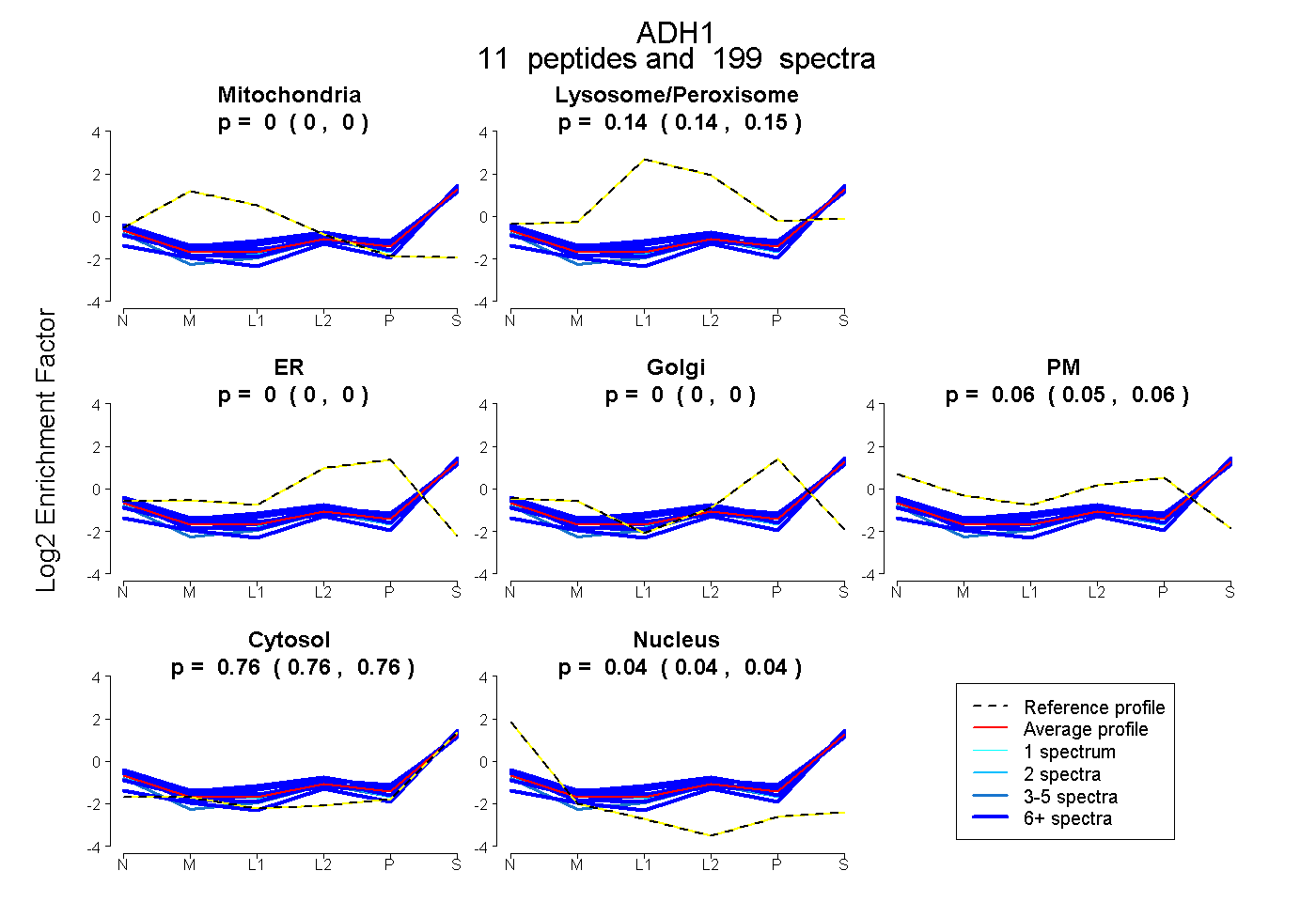
0.000 | 0.000
0.139 | 0.146
0.000 | 0.000
0.000 | 0.000
0.050 | 0.060
0.760 | 0.765
0.036 | 0.042
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
573 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.064 0.063 | 0.065 |
0.071 0.070 | 0.071 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.805 0.804 | 0.806 |
0.061 0.060 | 0.061 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
199 spectra |
 |
0.000 0.000 | 0.000 |
0.143 0.139 | 0.146 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.055 0.050 | 0.060 |
0.763 0.760 | 0.765 |
0.039 0.036 | 0.042 |
| 5 spectra, IDAAAPLDK | 0.000 | 0.116 | 0.000 | 0.000 | 0.000 | 0.832 | 0.052 | |||
| 10 spectra, LVADFMAK | 0.000 | 0.132 | 0.000 | 0.000 | 0.059 | 0.795 | 0.015 | |||
| 49 spectra, INEAFDLLR | 0.000 | 0.141 | 0.000 | 0.000 | 0.098 | 0.713 | 0.048 | |||
| 6 spectra, HPESNLCCQTK | 0.000 | 0.248 | 0.000 | 0.000 | 0.046 | 0.658 | 0.047 | |||
| 6 spectra, VCLIGCGFSTGYGSAVQVAK | 0.000 | 0.188 | 0.000 | 0.000 | 0.000 | 0.738 | 0.074 | |||
| 2 spectra, IIAVDINK | 0.000 | 0.160 | 0.000 | 0.000 | 0.000 | 0.754 | 0.086 | |||
| 2 spectra, FPLEPLITHVLPFEK | 0.000 | 0.101 | 0.000 | 0.000 | 0.106 | 0.793 | 0.000 | |||
| 6 spectra, VIPLFSPQCGK | 0.000 | 0.095 | 0.000 | 0.000 | 0.106 | 0.767 | 0.032 | |||
| 7 spectra, GAIFGGFK | 0.000 | 0.147 | 0.000 | 0.000 | 0.084 | 0.724 | 0.045 | |||
| 43 spectra, GALLDGTSR | 0.000 | 0.178 | 0.000 | 0.000 | 0.133 | 0.666 | 0.024 | |||
| 63 spectra, MVATGVCR | 0.000 | 0.050 | 0.000 | 0.000 | 0.000 | 0.950 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1242 spectra |
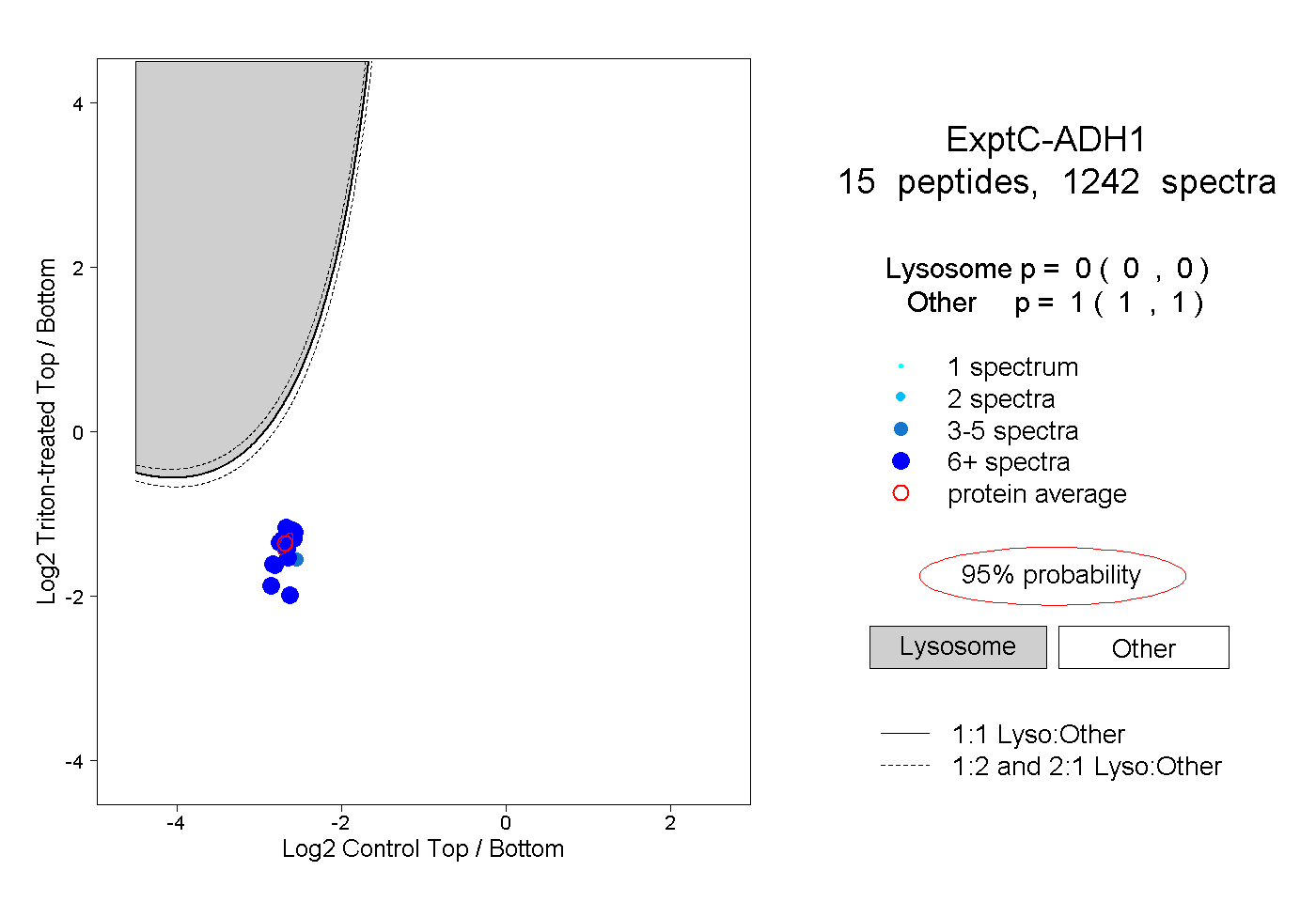 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
94 spectra |
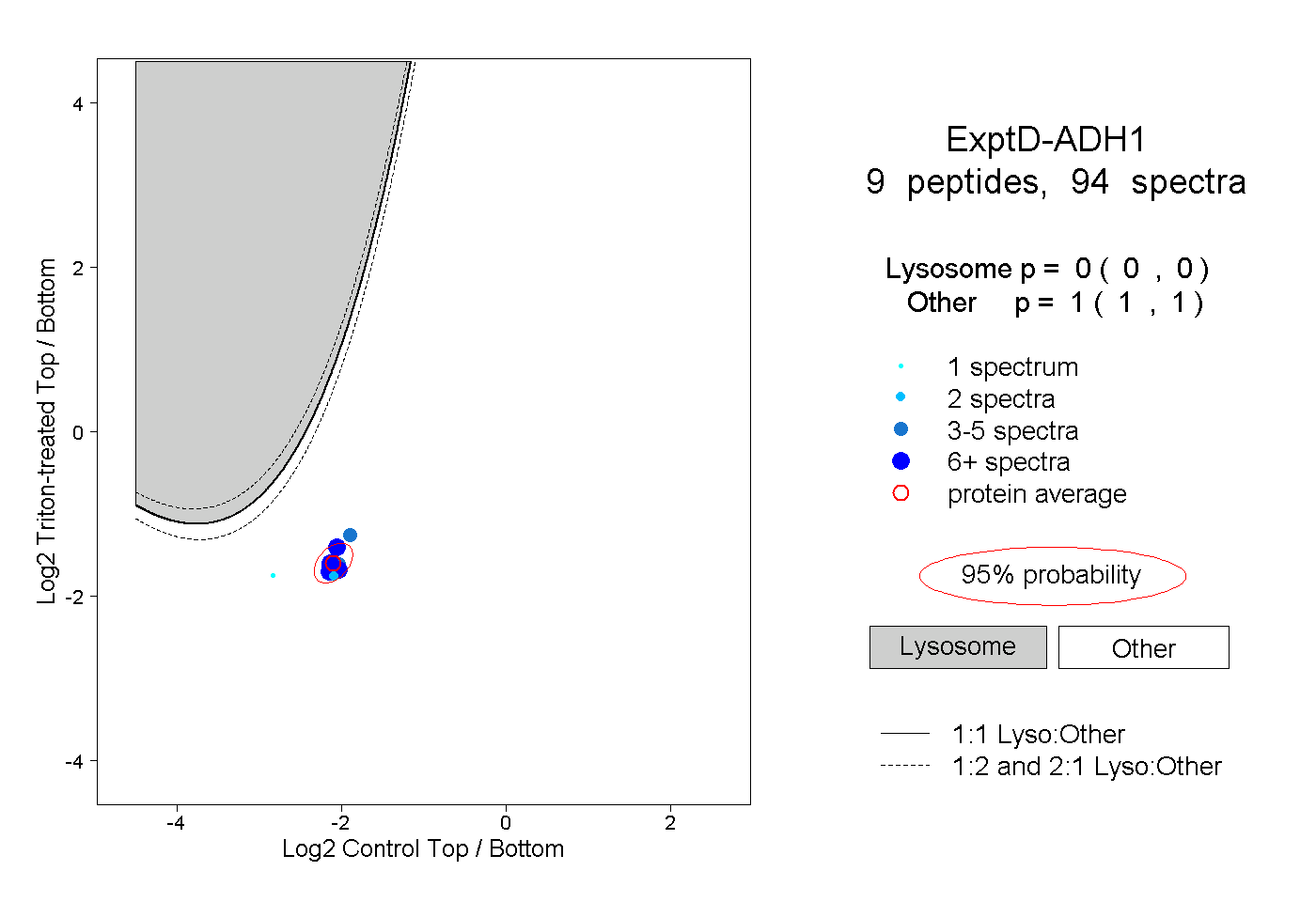 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |