peptides
spectra
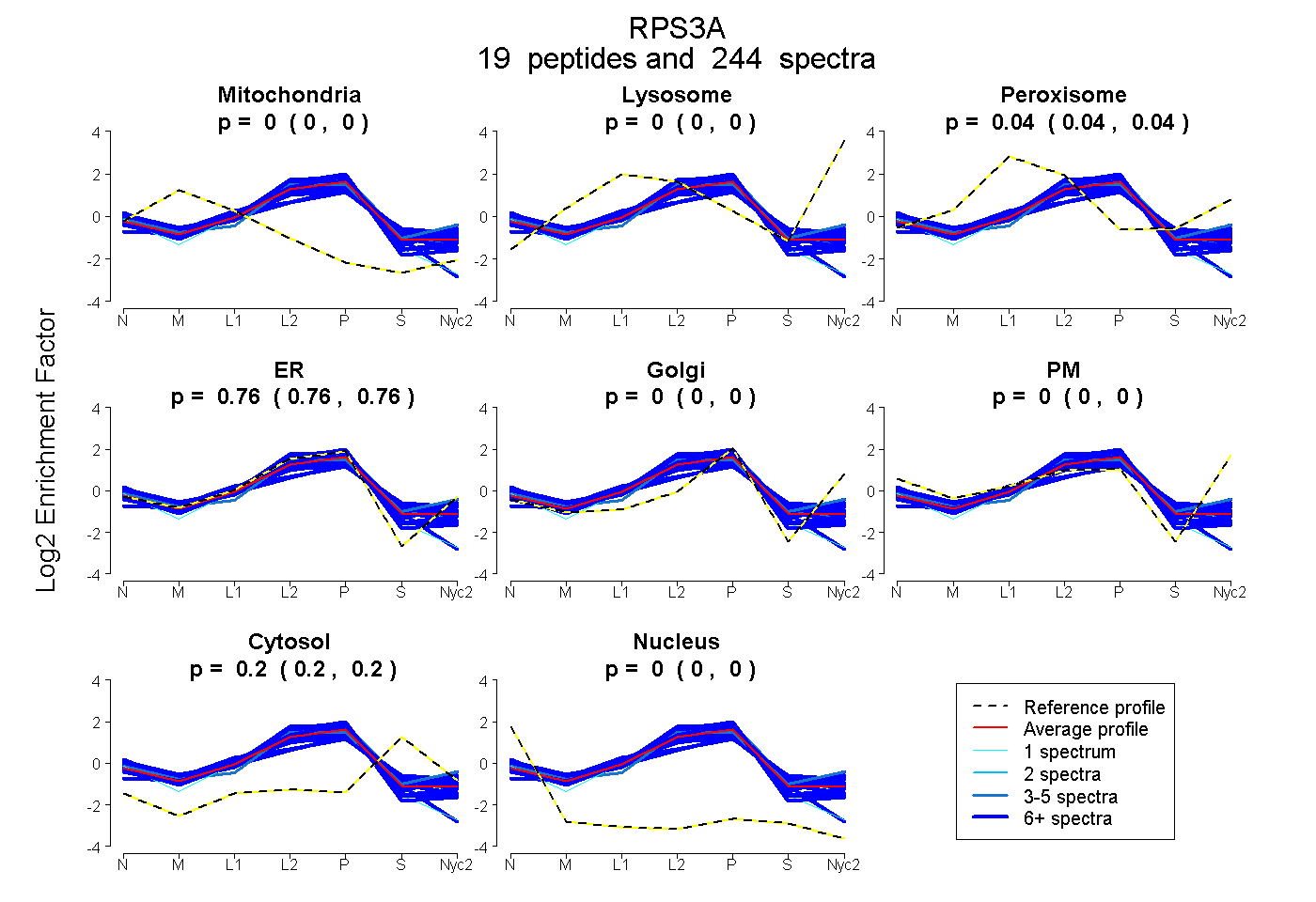
0.000 | 0.000
0.000 | 0.000
0.040 | 0.043
0.757 | 0.761
0.000 | 0.000
0.000 | 0.000
0.198 | 0.201
0.000 | 0.000
peptides
spectra
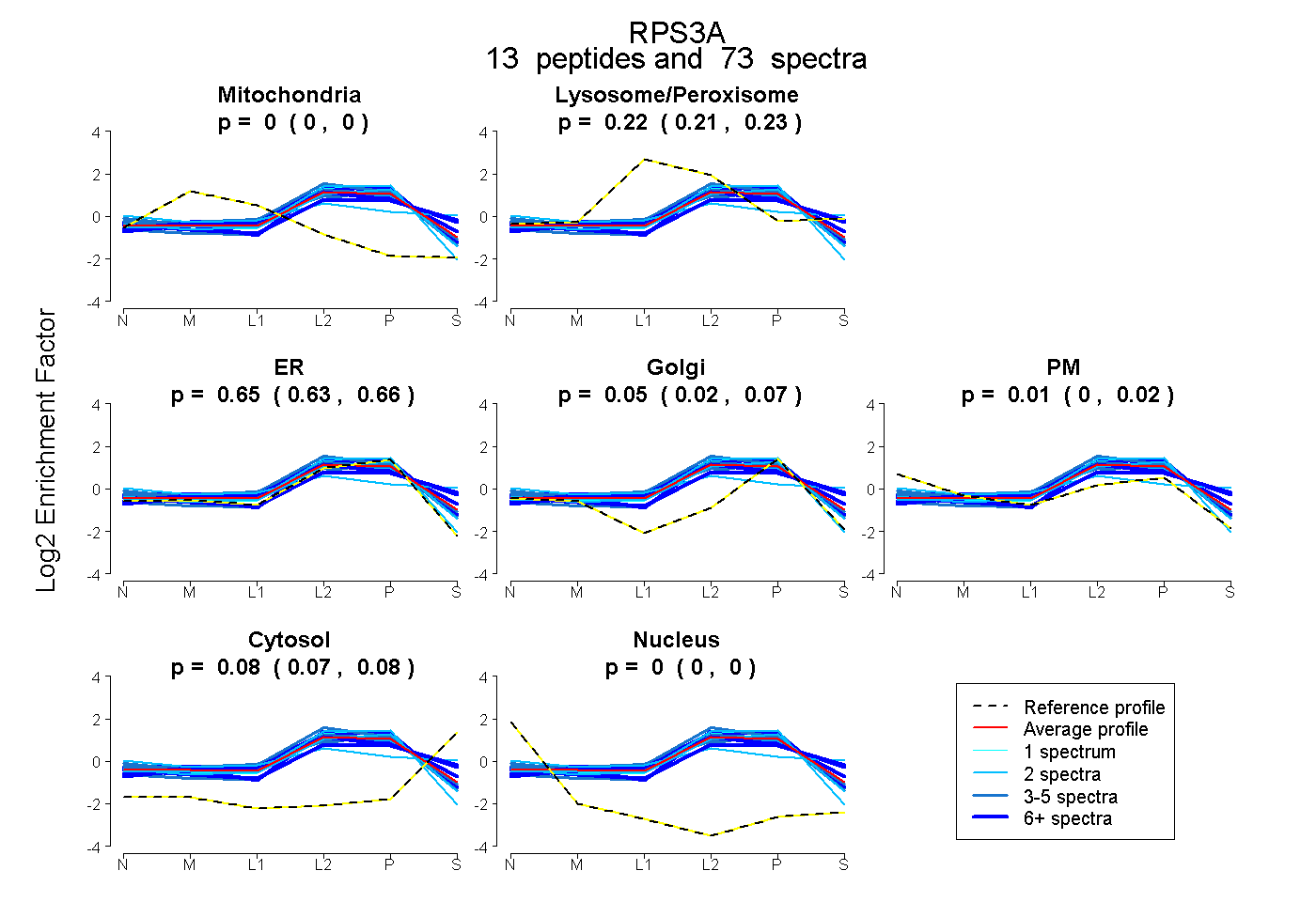
0.000 | 0.000
0.206 | 0.226
0.627 | 0.664
0.022 | 0.065
0.000 | 0.022
0.073 | 0.085
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
244 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.041 0.040 | 0.043 |
0.759 0.757 | 0.761 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.200 0.198 | 0.201 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
73 spectra |
 |
0.000 0.000 | 0.000 |
0.218 0.206 | 0.226 |
0.647 0.627 | 0.664 |
0.047 0.022 | 0.065 |
0.010 0.000 | 0.022 |
0.079 0.073 | 0.085 |
0.000 0.000 | 0.000 |
| 10 spectra, NCLTNFHGMDLTR | 0.000 | 0.313 | 0.524 | 0.000 | 0.000 | 0.163 | 0.000 | |||
| 3 spectra, IASDGLK | 0.000 | 0.333 | 0.346 | 0.267 | 0.054 | 0.000 | 0.000 | |||
| 3 spectra, ADGYEPPVQESV | 0.000 | 0.063 | 0.796 | 0.042 | 0.000 | 0.099 | 0.000 | |||
| 2 spectra, TTGDETGAK | 0.000 | 0.154 | 0.739 | 0.073 | 0.000 | 0.033 | 0.000 | |||
| 17 spectra, TTDGYLLR | 0.000 | 0.217 | 0.477 | 0.059 | 0.022 | 0.225 | 0.000 | |||
| 13 spectra, ACQSIYPLHDVFVR | 0.000 | 0.284 | 0.569 | 0.000 | 0.068 | 0.079 | 0.000 | |||
| 1 spectrum, EVQTNDLK | 0.000 | 0.063 | 0.937 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, TSYAQHQQVR | 0.000 | 0.372 | 0.000 | 0.079 | 0.356 | 0.193 | 0.000 | |||
| 4 spectra, LFCVGFTK | 0.000 | 0.238 | 0.681 | 0.000 | 0.081 | 0.000 | 0.000 | |||
| 11 spectra, APAMFNIR | 0.000 | 0.100 | 0.834 | 0.000 | 0.000 | 0.067 | 0.000 | |||
| 3 spectra, LITEDVQGK | 0.000 | 0.222 | 0.663 | 0.027 | 0.041 | 0.048 | 0.000 | |||
| 2 spectra, DWYDVK | 0.000 | 0.283 | 0.505 | 0.115 | 0.052 | 0.045 | 0.000 | |||
| 2 spectra, VVDPFSK | 0.000 | 0.082 | 0.918 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
328 spectra |
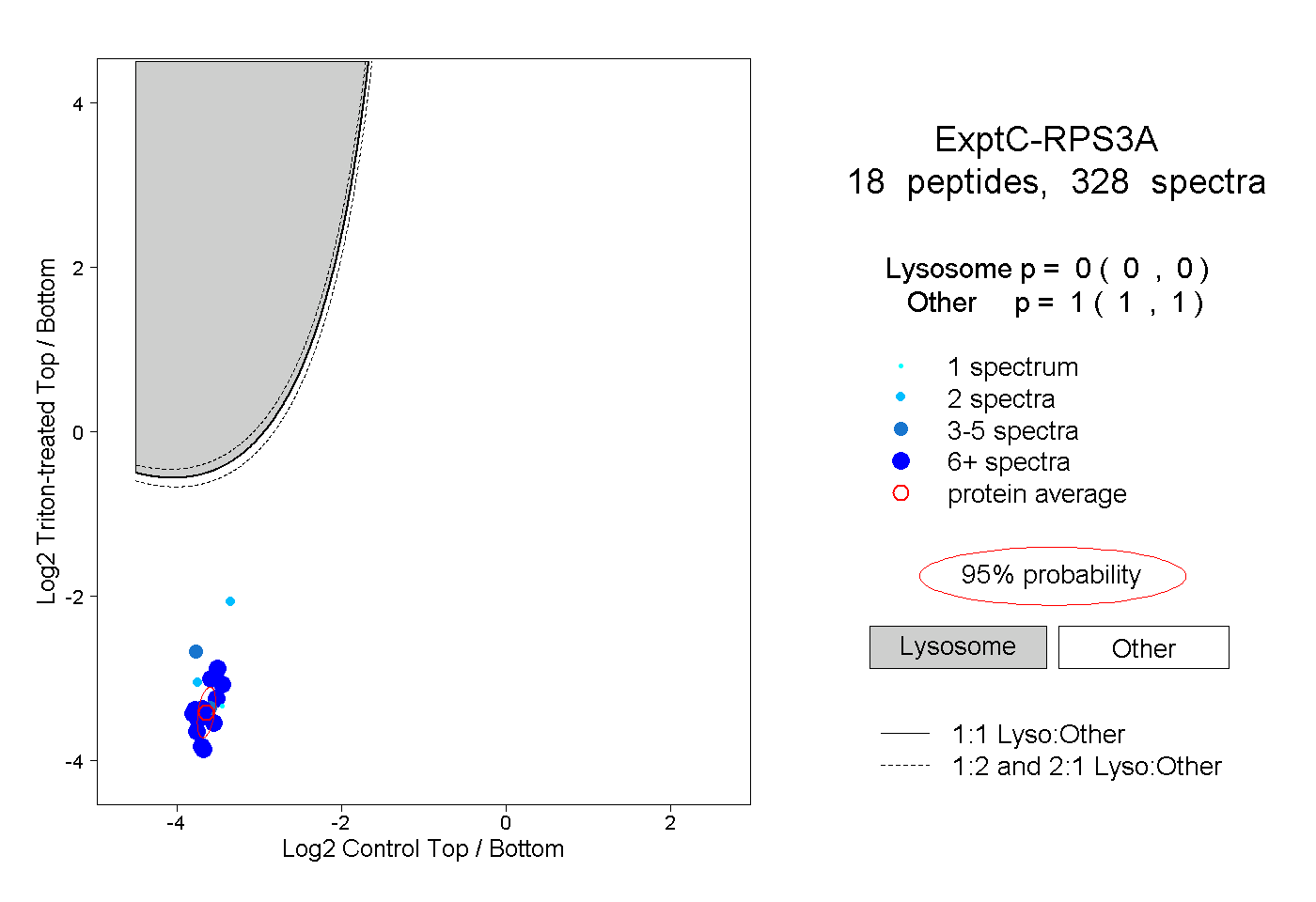 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
30 spectra |
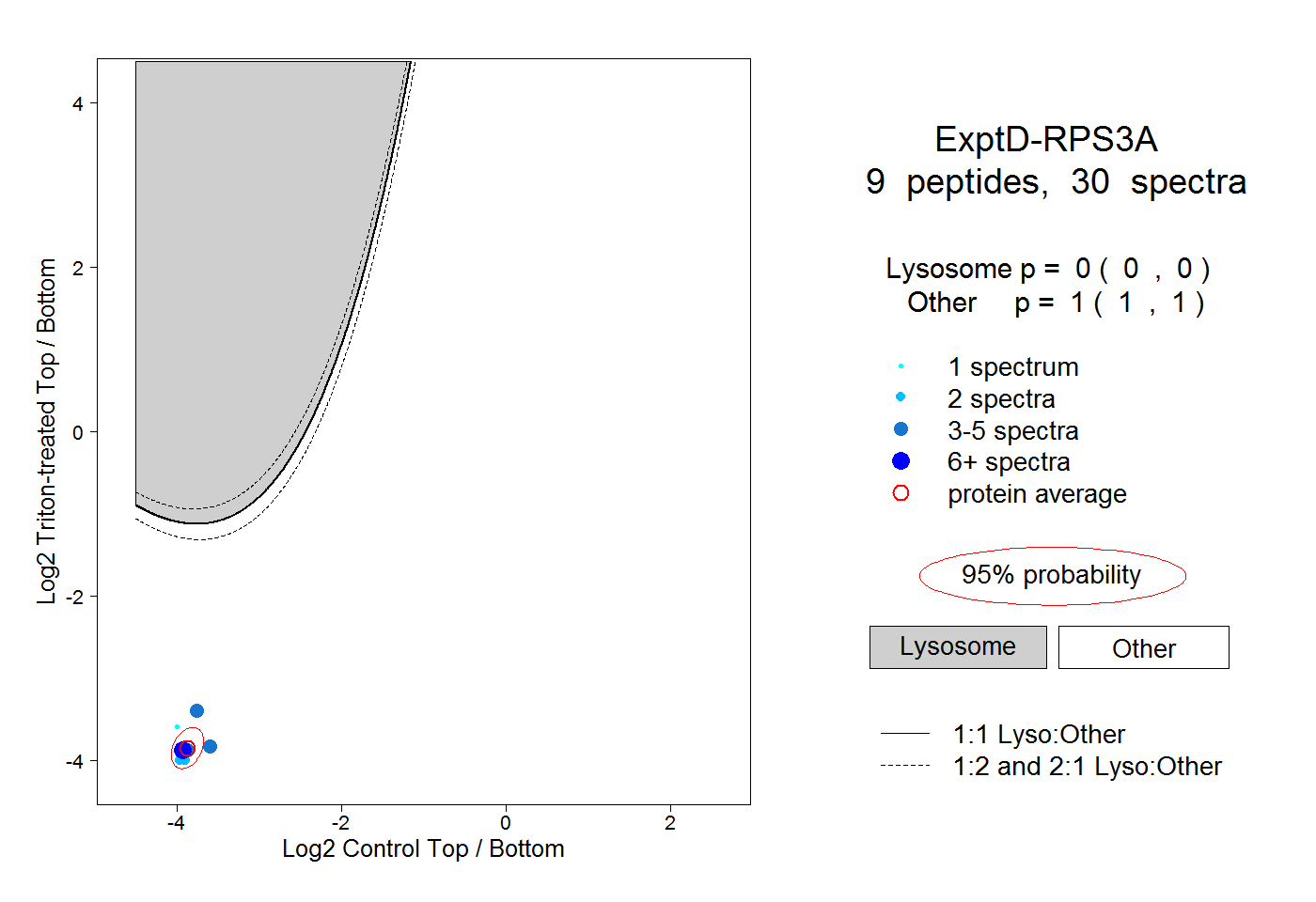 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |