UTRN
[ENSRNOP00000016273]
Main page
| | | Plot |
Mito |
Lyso |
|
Perox |
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt A |
 31
31
peptides |
54
spectra |
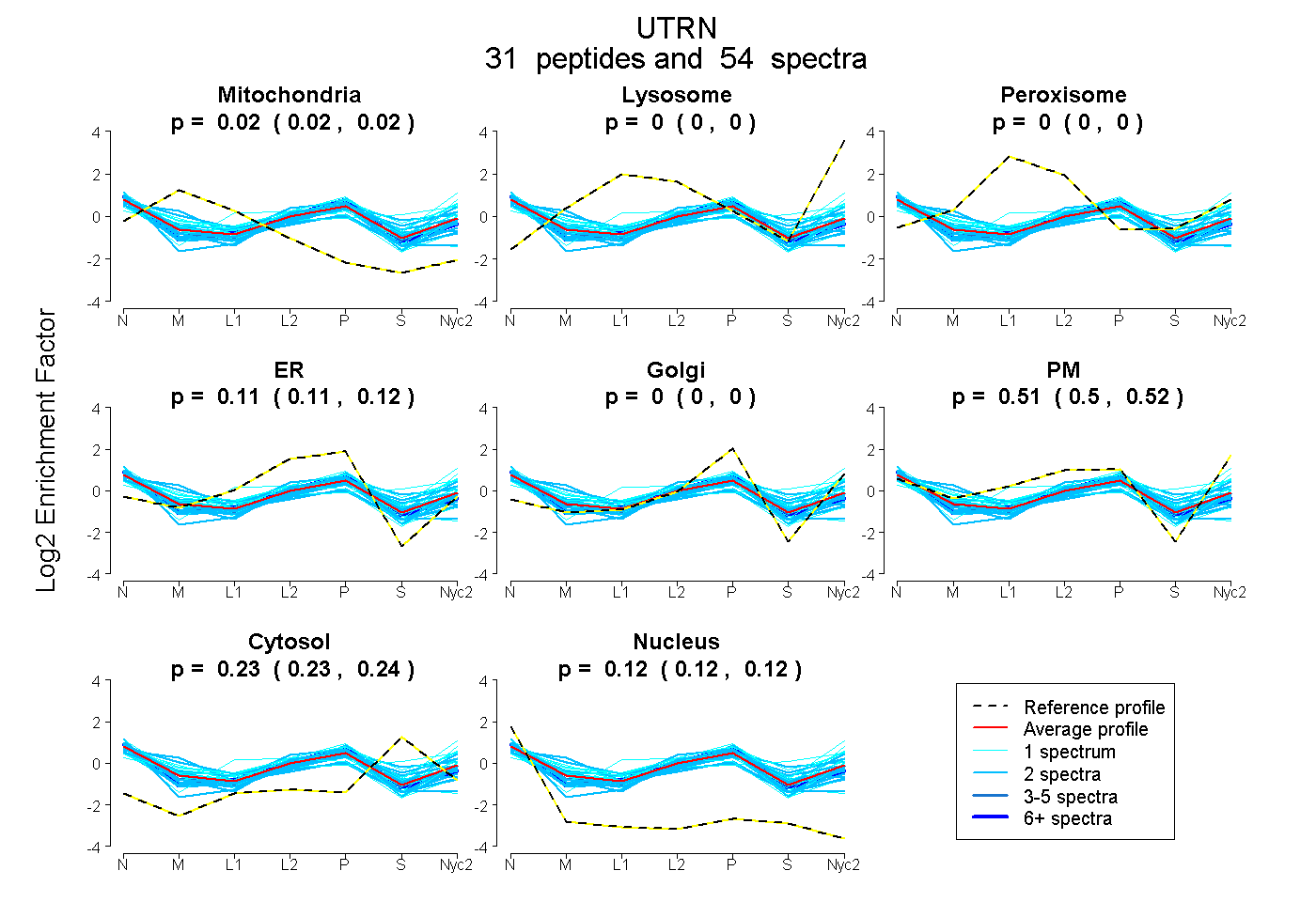 |
0.020
0.016 | 0.024 |
0.000
0.000 | 0.000 |
|
0.000
0.000 | 0.000 |
0.114
0.105 | 0.121 |
0.000
0.000 | 0.000 |
0.514
0.504 | 0.522 |
0.232
0.228 | 0.235 |
0.120
0.117 | 0.122 |
|
| | | Plot |
Mito |
|
Lyso or Perox |
|
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt B |
 2
2
peptides |
3
spectra |
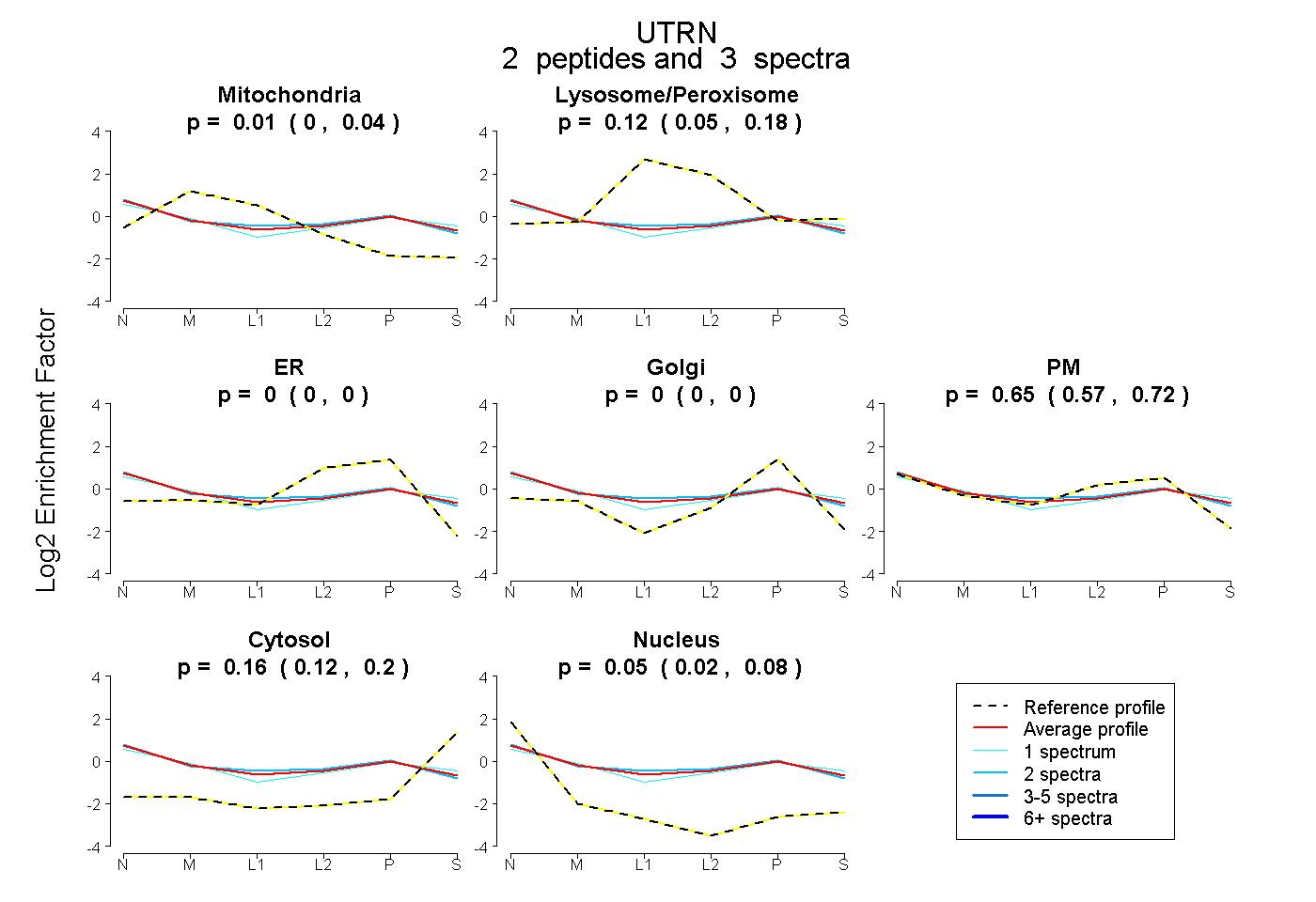 |
0.009
0.000 | 0.037 |
|
0.123
0.047 | 0.183 |
|
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.653
0.574 | 0.716 |
0.161
0.119 | 0.197 |
0.054
0.017 | 0.084 |
|
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
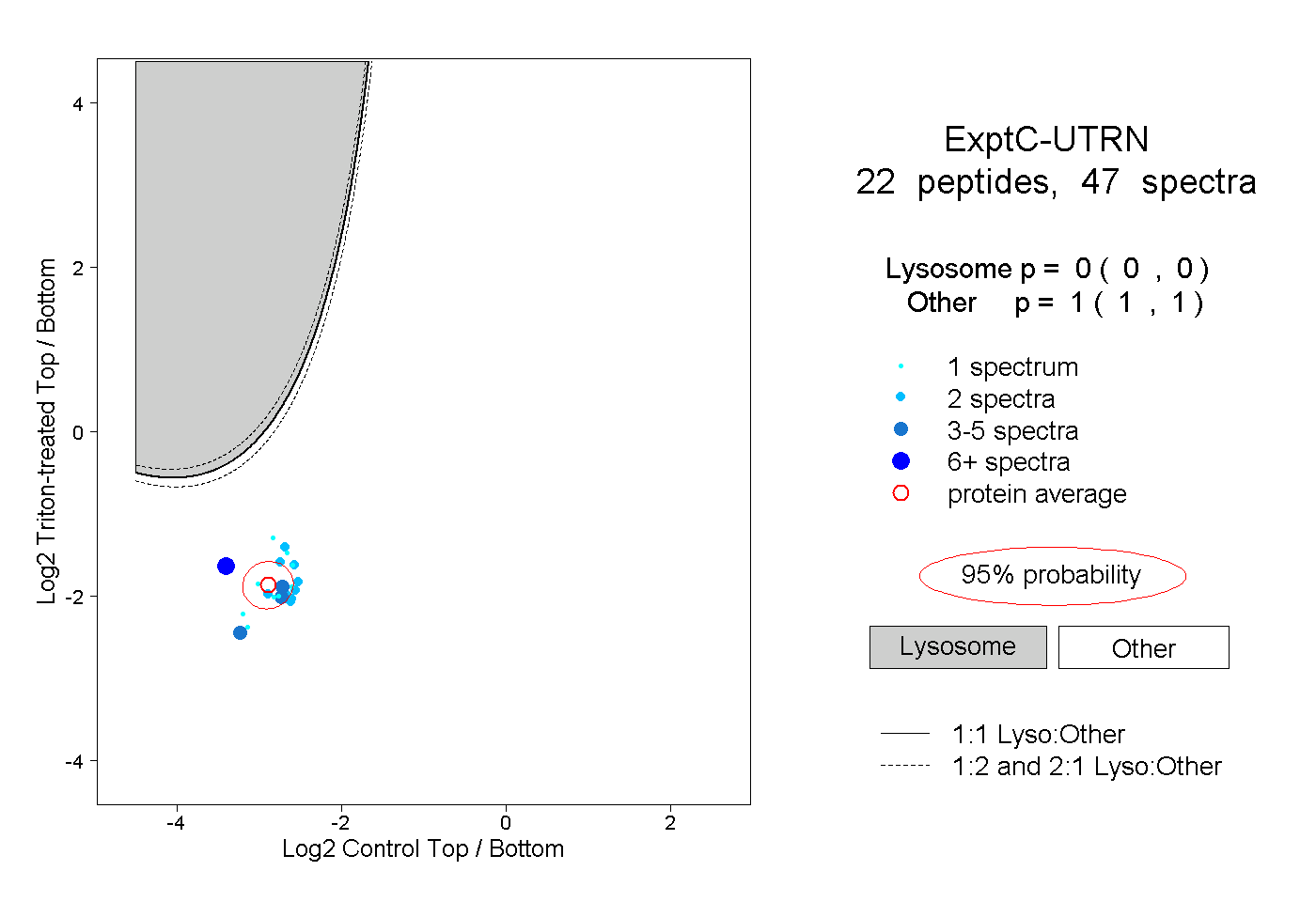
| Expt C |
 22
22
peptides |
47
spectra |
 |
|
0.000
0.000 | 0.000 |
|
|
|
|
|
|
|
1.000
1.000 | 1.000 |
| 3 spectra, LSEETK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EQAAQGDTTALQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ADSEVIEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VQTGNFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, QQTDNPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DNLSESLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TQDPCSAPQTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, QVSGYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, QEEIVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LRPSDASFLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, DLLETVHVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FQLFQKPANFEQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, LAELSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SLPSLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LLEEYSSDDTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EVETLPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SLQSDLEAEQVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, MQSTEALPER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SLEEIIPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ELTDLLGLHPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LSDSQEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, AQIEEVLQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
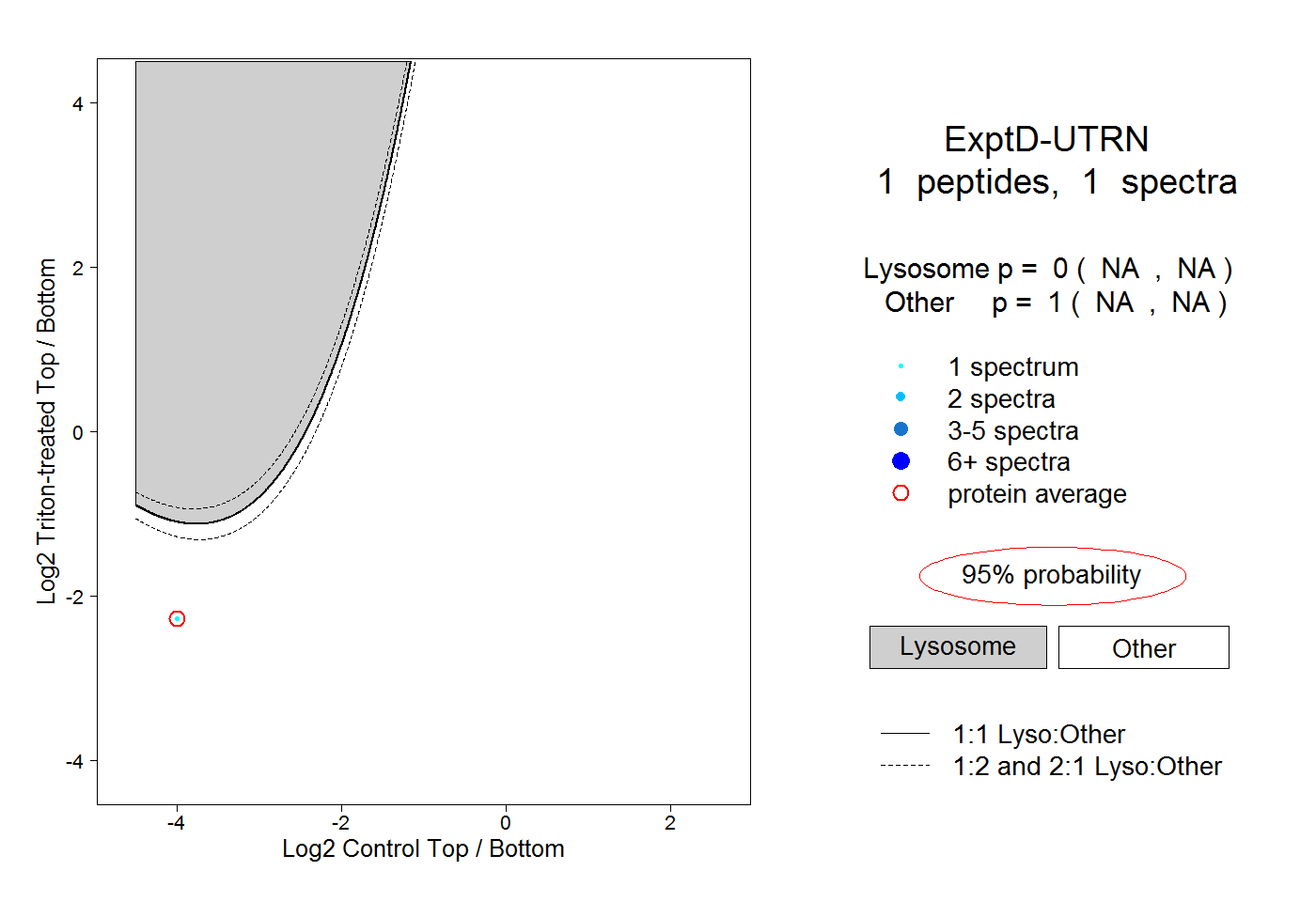
| Expt D |
 1
1
peptide |
1
spectrum |
 |
|
0.000
NA | NA |
|
|
|
|
|
|
|
1.000
NA | NA |



