peptides
spectra
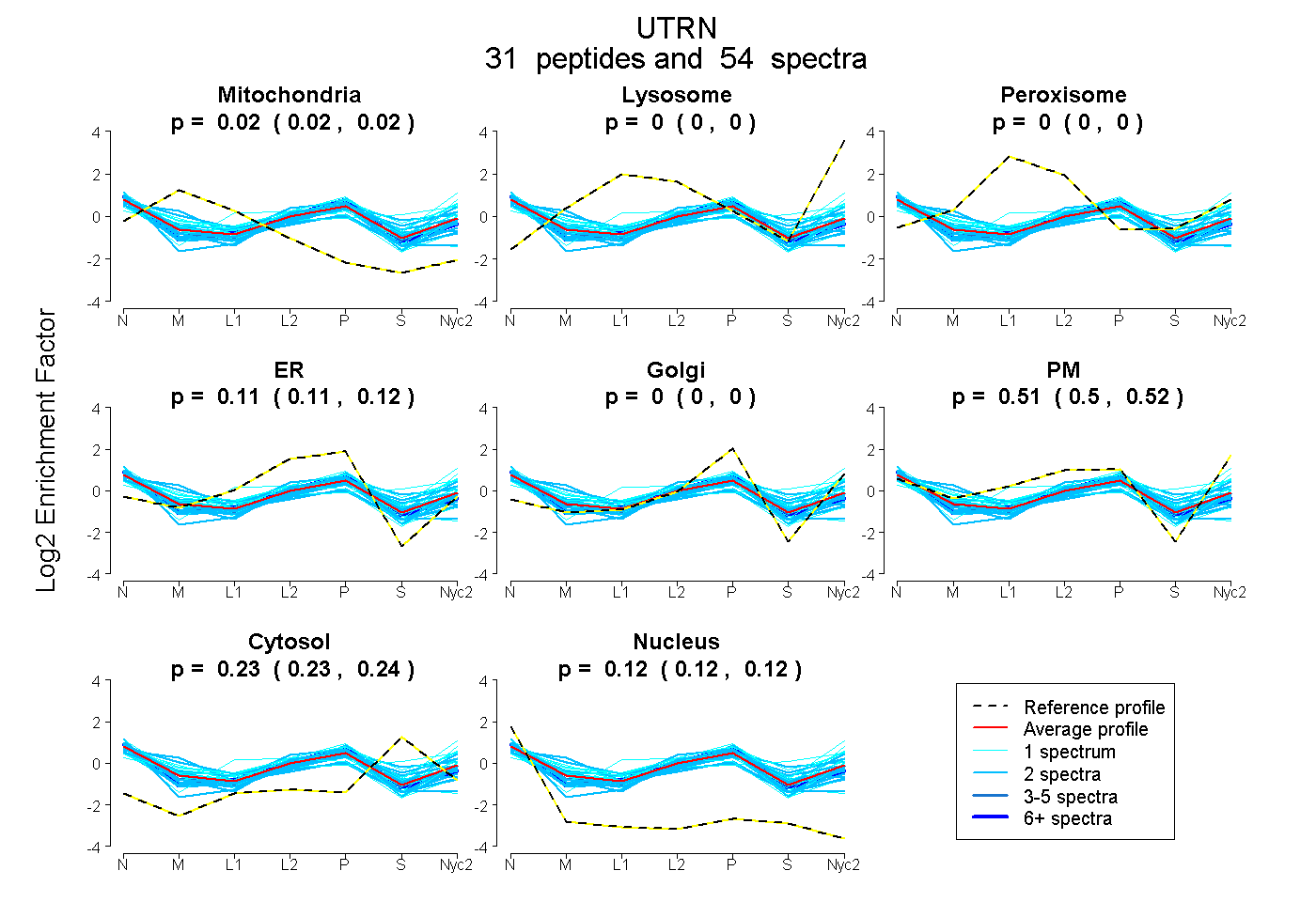
0.016 | 0.024
0.000 | 0.000
0.000 | 0.000
0.105 | 0.121
0.000 | 0.000
0.504 | 0.522
0.228 | 0.235
0.117 | 0.122
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
54 spectra |
 |
0.020 0.016 | 0.024 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.114 0.105 | 0.121 |
0.000 0.000 | 0.000 |
0.514 0.504 | 0.522 |
0.232 0.228 | 0.235 |
0.120 0.117 | 0.122 |
| 1 spectrum, WDSLVQR | 0.077 | 0.000 | 0.000 | 0.000 | 0.000 | 0.728 | 0.158 | 0.037 | ||
| 2 spectra, LEHAFSK | 0.263 | 0.000 | 0.000 | 0.047 | 0.000 | 0.454 | 0.142 | 0.093 | ||
| 1 spectrum, VHALNNVNR | 0.000 | 0.000 | 0.000 | 0.061 | 0.016 | 0.619 | 0.304 | 0.000 | ||
| 1 spectrum, MISQQLEDLGR | 0.127 | 0.000 | 0.000 | 0.000 | 0.052 | 0.560 | 0.211 | 0.050 | ||
| 2 spectra, QIHVDVEAK | 0.038 | 0.000 | 0.000 | 0.000 | 0.050 | 0.504 | 0.312 | 0.095 | ||
| 2 spectra, DVDPDVIQTHLDK | 0.324 | 0.000 | 0.000 | 0.040 | 0.191 | 0.242 | 0.123 | 0.080 | ||
| 1 spectrum, DNLSESLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.655 | 0.321 | 0.024 | ||
| 1 spectrum, FYMLQQAR | 0.209 | 0.000 | 0.000 | 0.000 | 0.090 | 0.511 | 0.136 | 0.053 | ||
| 1 spectrum, LAELSK | 0.076 | 0.000 | 0.000 | 0.000 | 0.021 | 0.691 | 0.167 | 0.044 | ||
| 1 spectrum, IAAHPNVQK | 0.000 | 0.000 | 0.000 | 0.045 | 0.033 | 0.545 | 0.377 | 0.000 | ||
| 8 spectra, AELEMLSDK | 0.000 | 0.000 | 0.000 | 0.273 | 0.000 | 0.380 | 0.196 | 0.150 | ||
| 2 spectra, TWTEDWR | 0.044 | 0.000 | 0.000 | 0.000 | 0.048 | 0.525 | 0.350 | 0.033 | ||
| 2 spectra, YEELSHLAESK | 0.000 | 0.000 | 0.000 | 0.343 | 0.000 | 0.299 | 0.138 | 0.219 | ||
| 2 spectra, NVEETTEYLK | 0.041 | 0.000 | 0.000 | 0.084 | 0.025 | 0.540 | 0.146 | 0.164 | ||
| 1 spectrum, DMLSQLNAK | 0.000 | 0.000 | 0.009 | 0.000 | 0.000 | 0.718 | 0.274 | 0.000 | ||
| 2 spectra, SQETSGVR | 0.000 | 0.000 | 0.000 | 0.112 | 0.009 | 0.459 | 0.245 | 0.176 | ||
| 2 spectra, DASFSESPQR | 0.000 | 0.000 | 0.000 | 0.269 | 0.116 | 0.207 | 0.272 | 0.136 | ||
| 1 spectrum, WSALVAEVK | 0.045 | 0.000 | 0.017 | 0.009 | 0.000 | 0.650 | 0.084 | 0.194 | ||
| 2 spectra, HKPDLFSWDR | 0.000 | 0.000 | 0.000 | 0.207 | 0.002 | 0.411 | 0.261 | 0.118 | ||
| 1 spectrum, FDATSAELQSWILR | 0.053 | 0.000 | 0.000 | 0.090 | 0.000 | 0.489 | 0.210 | 0.159 | ||
| 2 spectra, TQDPCSAPQTR | 0.000 | 0.000 | 0.000 | 0.527 | 0.000 | 0.056 | 0.149 | 0.267 | ||
| 1 spectrum, MLSESEK | 0.050 | 0.000 | 0.074 | 0.000 | 0.000 | 0.443 | 0.432 | 0.000 | ||
| 1 spectrum, LLSELSDASIQVENVR | 0.020 | 0.000 | 0.000 | 0.037 | 0.000 | 0.676 | 0.128 | 0.139 | ||
| 2 spectra, LLEEYSSDDTR | 0.038 | 0.000 | 0.000 | 0.083 | 0.079 | 0.498 | 0.102 | 0.199 | ||
| 3 spectra, ESLGELDK | 0.000 | 0.000 | 0.000 | 0.108 | 0.003 | 0.522 | 0.213 | 0.155 | ||
| 1 spectrum, FSQEIDIQK | 0.114 | 0.000 | 0.000 | 0.477 | 0.000 | 0.067 | 0.153 | 0.189 | ||
| 2 spectra, LEAFNSR | 0.044 | 0.000 | 0.000 | 0.000 | 0.000 | 0.667 | 0.244 | 0.045 | ||
| 1 spectrum, MNSDSEELTQR | 0.014 | 0.000 | 0.000 | 0.017 | 0.101 | 0.517 | 0.261 | 0.090 | ||
| 1 spectrum, ELTDLLGLHPR | 0.033 | 0.000 | 0.000 | 0.269 | 0.119 | 0.271 | 0.086 | 0.223 | ||
| 2 spectra, LGEQLAAVHEK | 0.000 | 0.000 | 0.000 | 0.255 | 0.000 | 0.386 | 0.265 | 0.094 | ||
| 2 spectra, AQIEEVLQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.114 | 0.426 | 0.412 | 0.047 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
3 spectra |
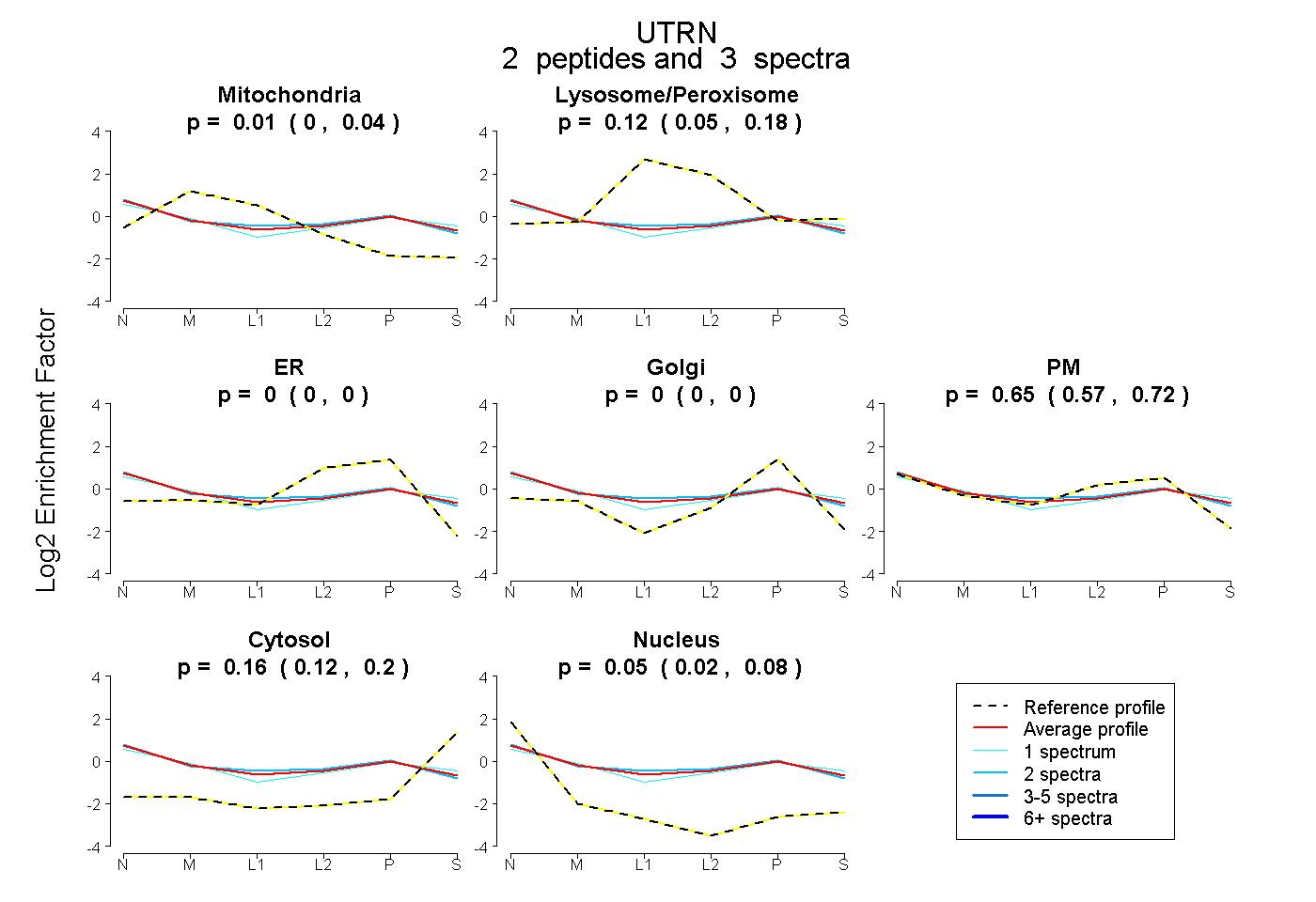 |
0.009 0.000 | 0.037 |
0.123 0.047 | 0.183 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.653 0.574 | 0.716 |
0.161 0.119 | 0.197 |
0.054 0.017 | 0.084 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
47 spectra |
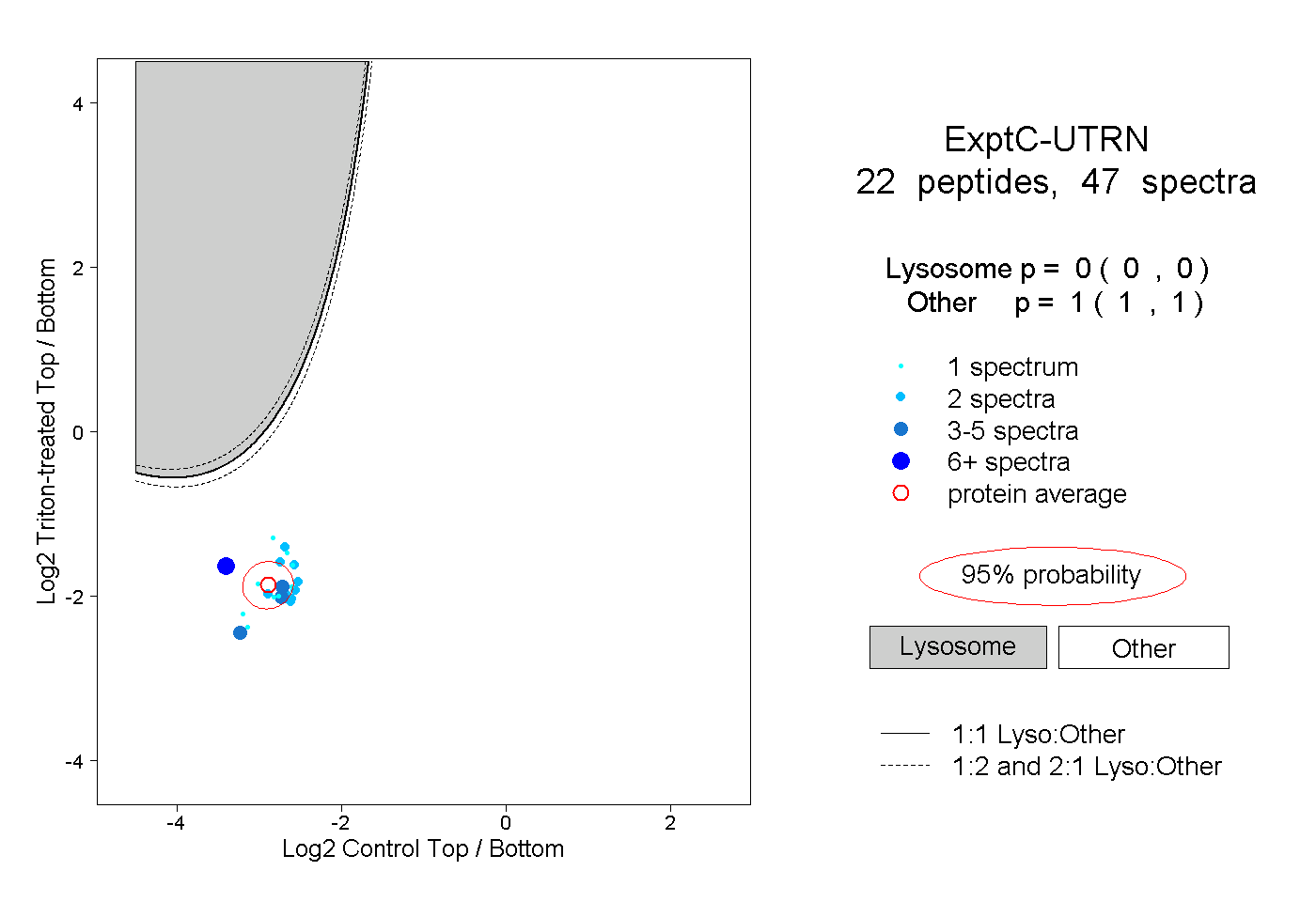 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
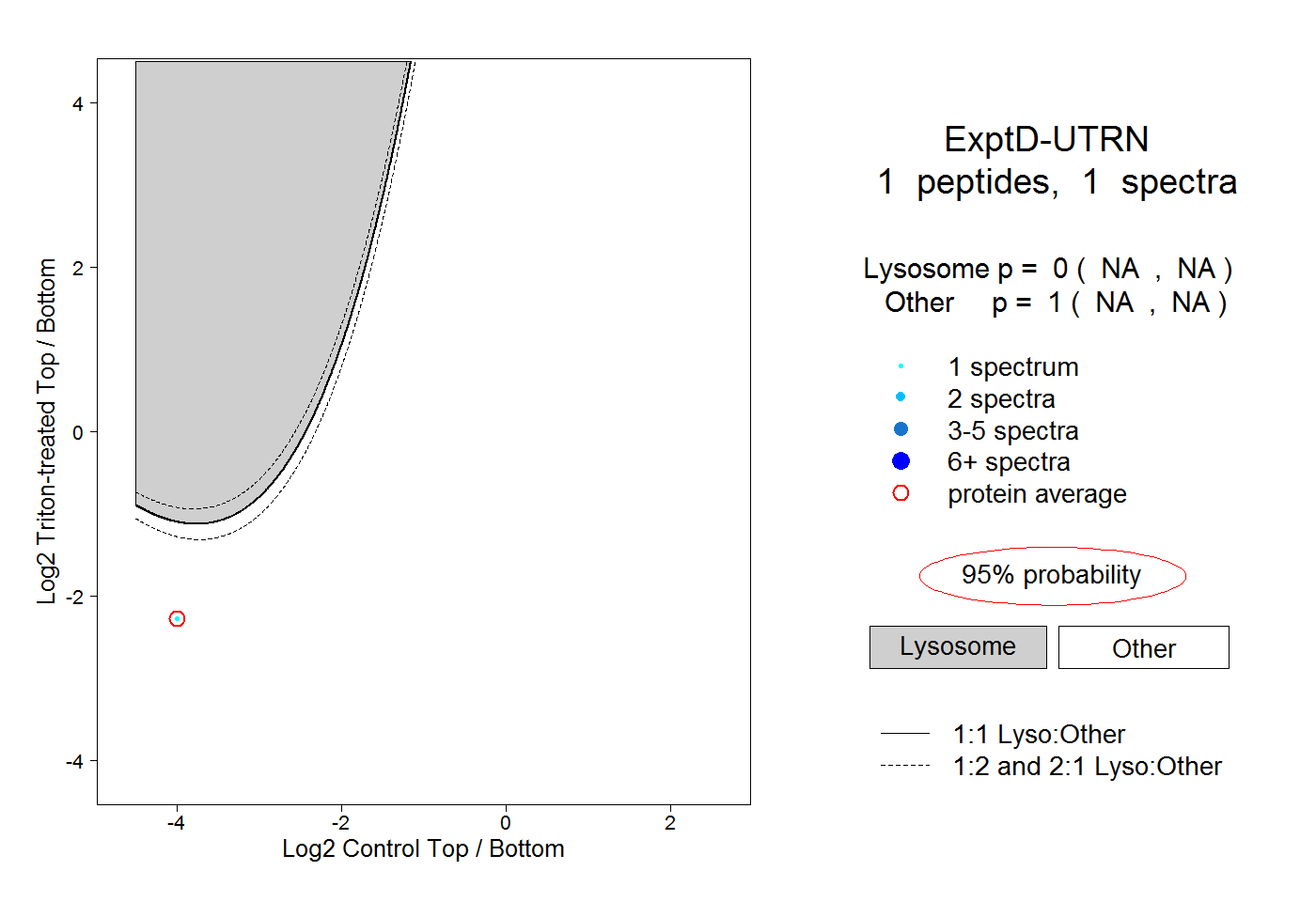 |
0.000 NA | NA |
1.000 NA | NA |