peptides
spectra
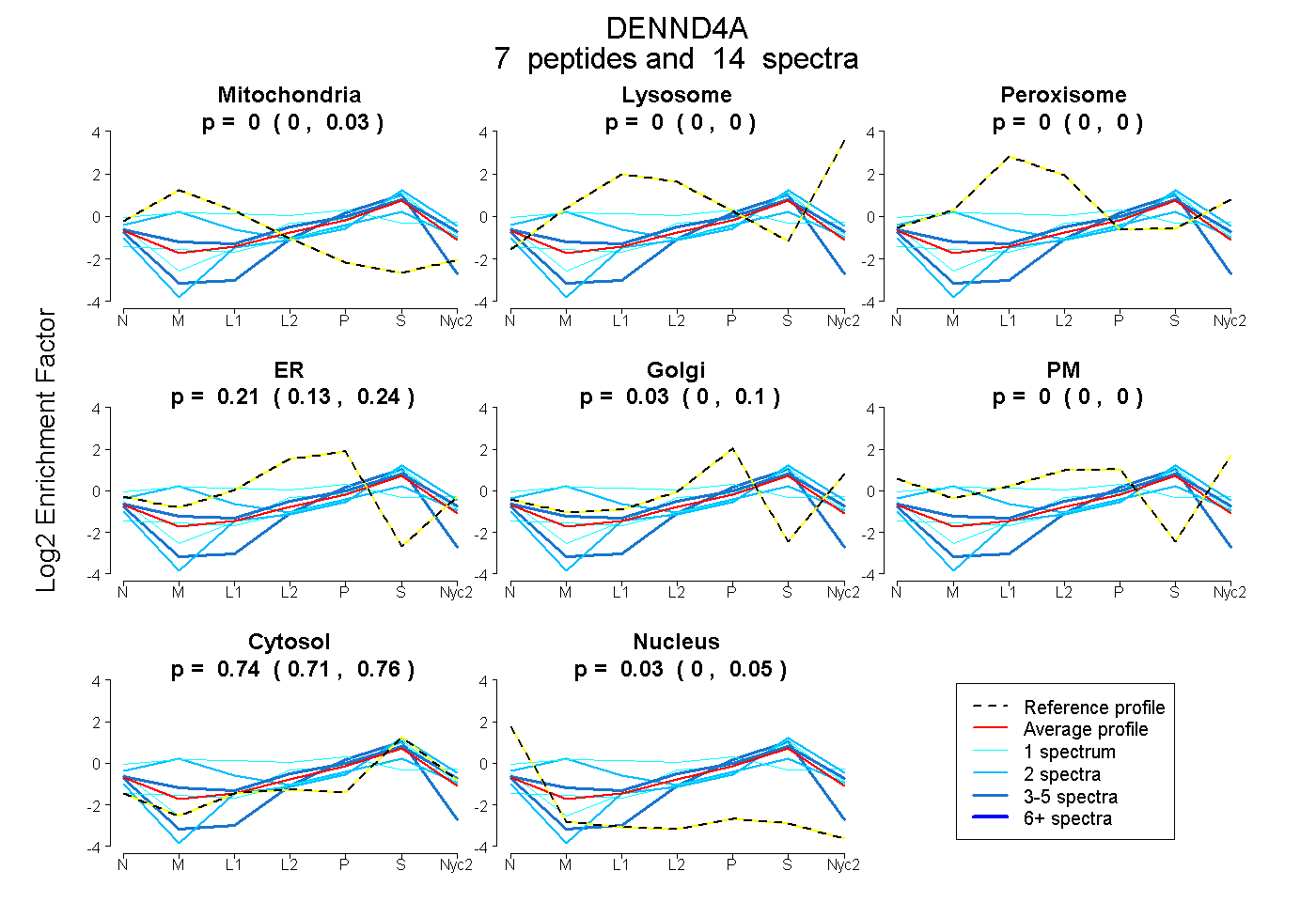
0.000 | 0.034
0.000 | 0.000
0.000 | 0.000
0.131 | 0.236
0.000 | 0.099
0.000 | 0.000
0.707 | 0.755
0.000 | 0.045
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
14 spectra |
 |
0.000 0.000 | 0.034 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.207 0.131 | 0.236 |
0.029 0.000 | 0.099 |
0.000 0.000 | 0.000 |
0.736 0.707 | 0.755 |
0.028 0.000 | 0.045 |
| 1 spectrum, SIQIPAHR | 0.166 | 0.000 | 0.307 | 0.000 | 0.298 | 0.011 | 0.219 | 0.000 | ||
| 3 spectra, LLLGLTSLVDGK | 0.000 | 0.000 | 0.000 | 0.042 | 0.000 | 0.000 | 0.758 | 0.199 | ||
| 2 spectra, SISTPSAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.067 | 0.000 | 0.933 | 0.000 | ||
| 2 spectra, LQENPCAR | 0.325 | 0.000 | 0.091 | 0.000 | 0.149 | 0.000 | 0.435 | 0.000 | ||
| 1 spectrum, LQQRPR | 0.000 | 0.000 | 0.000 | 0.212 | 0.000 | 0.000 | 0.788 | 0.000 | ||
| 1 spectrum, NNLFERPEGFLQAR | 0.022 | 0.000 | 0.000 | 0.035 | 0.098 | 0.000 | 0.846 | 0.000 | ||
| 4 spectra, VPFPSPQRPR | 0.010 | 0.000 | 0.027 | 0.176 | 0.095 | 0.008 | 0.683 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
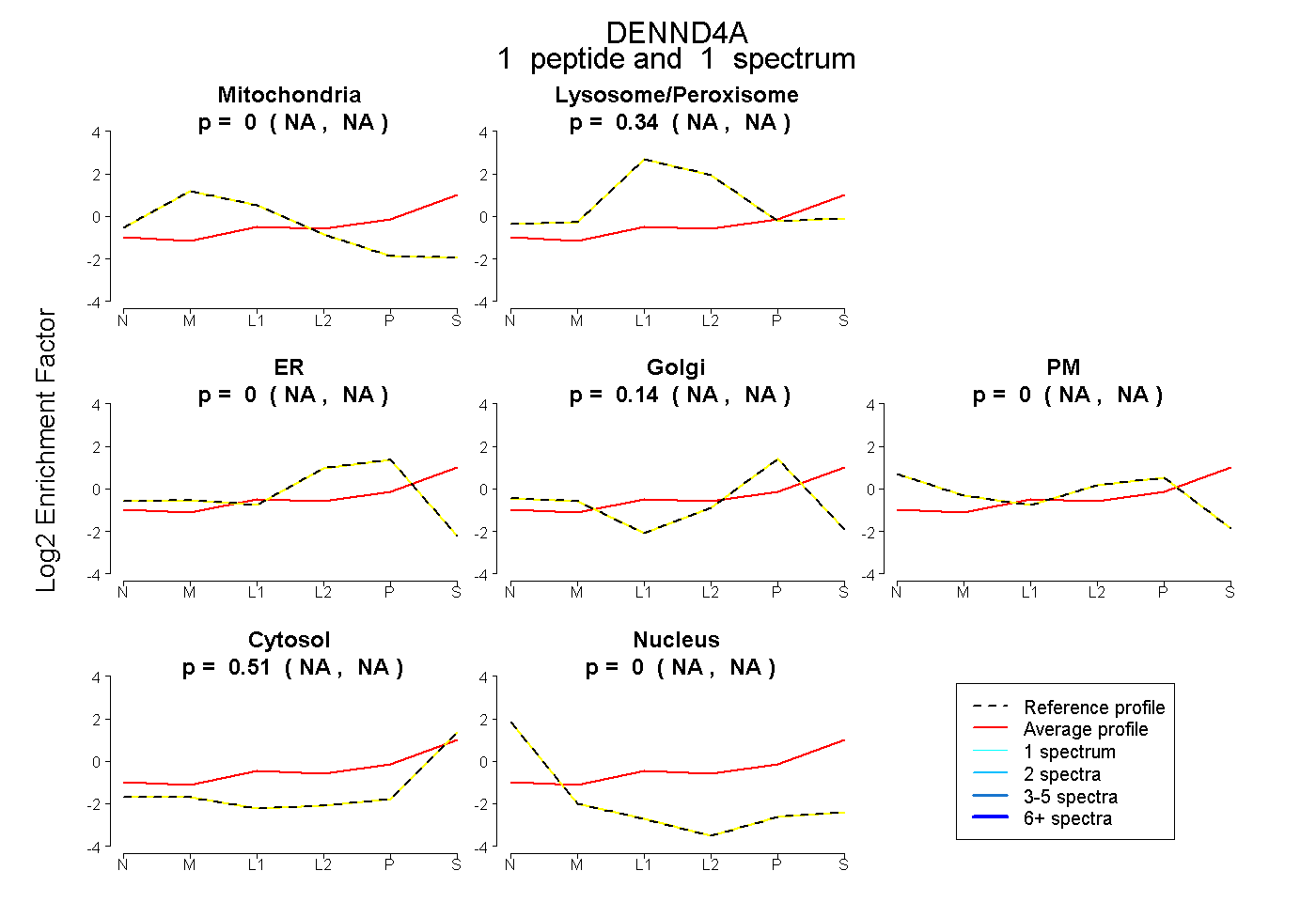 |
0.000 NA | NA |
0.345 NA | NA |
0.000 NA | NA |
0.143 NA | NA |
0.000 NA | NA |
0.513 NA | NA |
0.000 NA | NA |