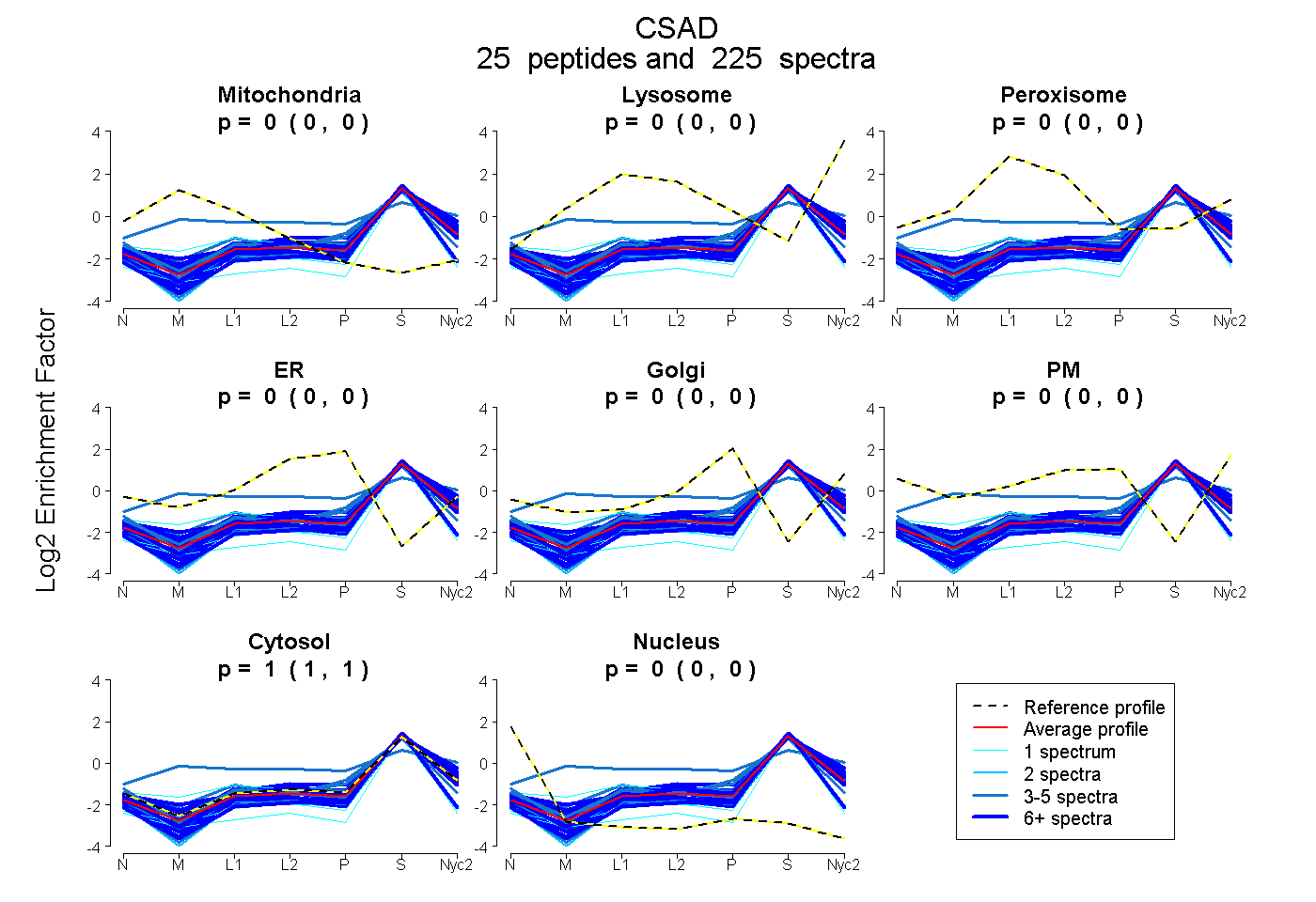
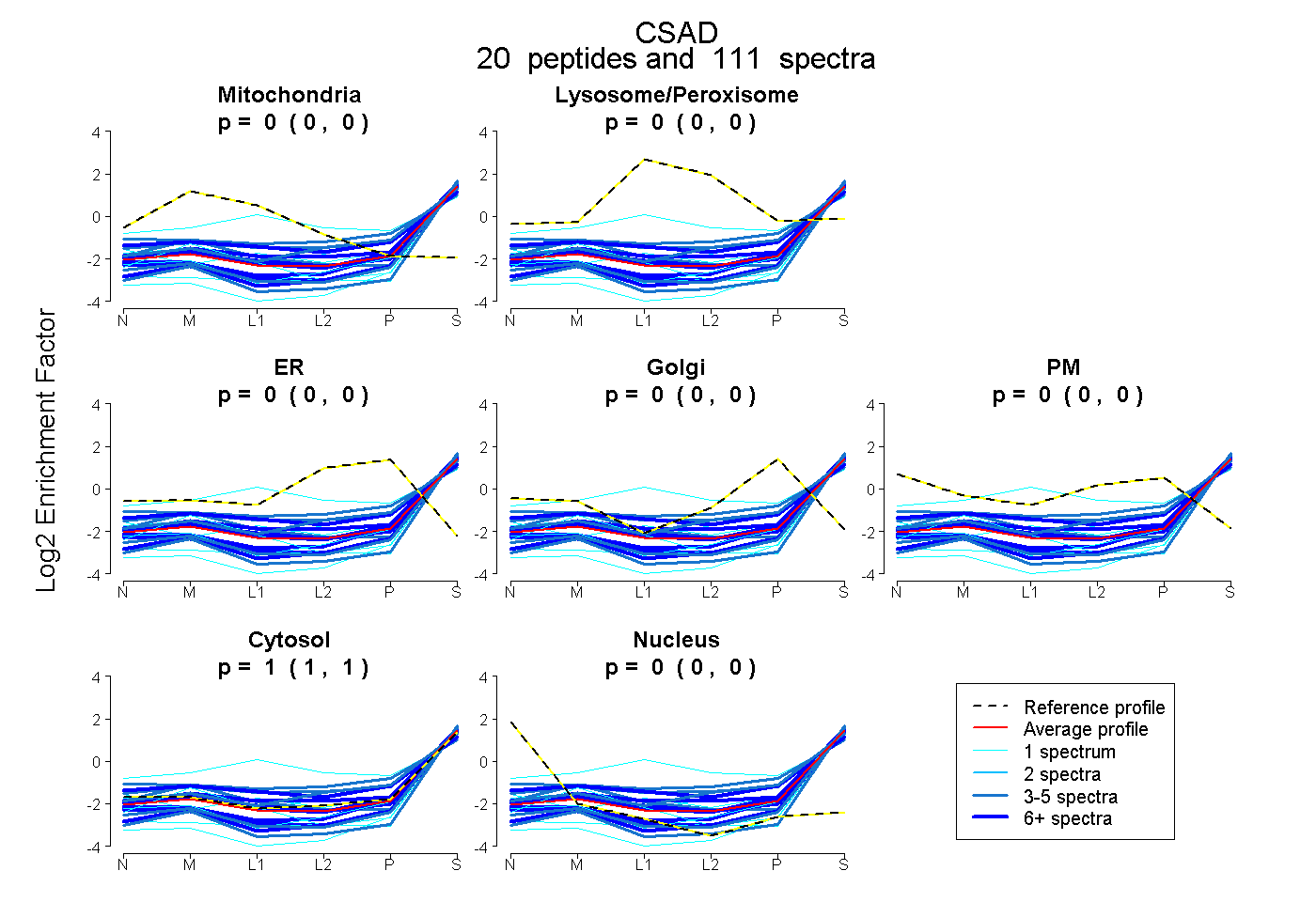
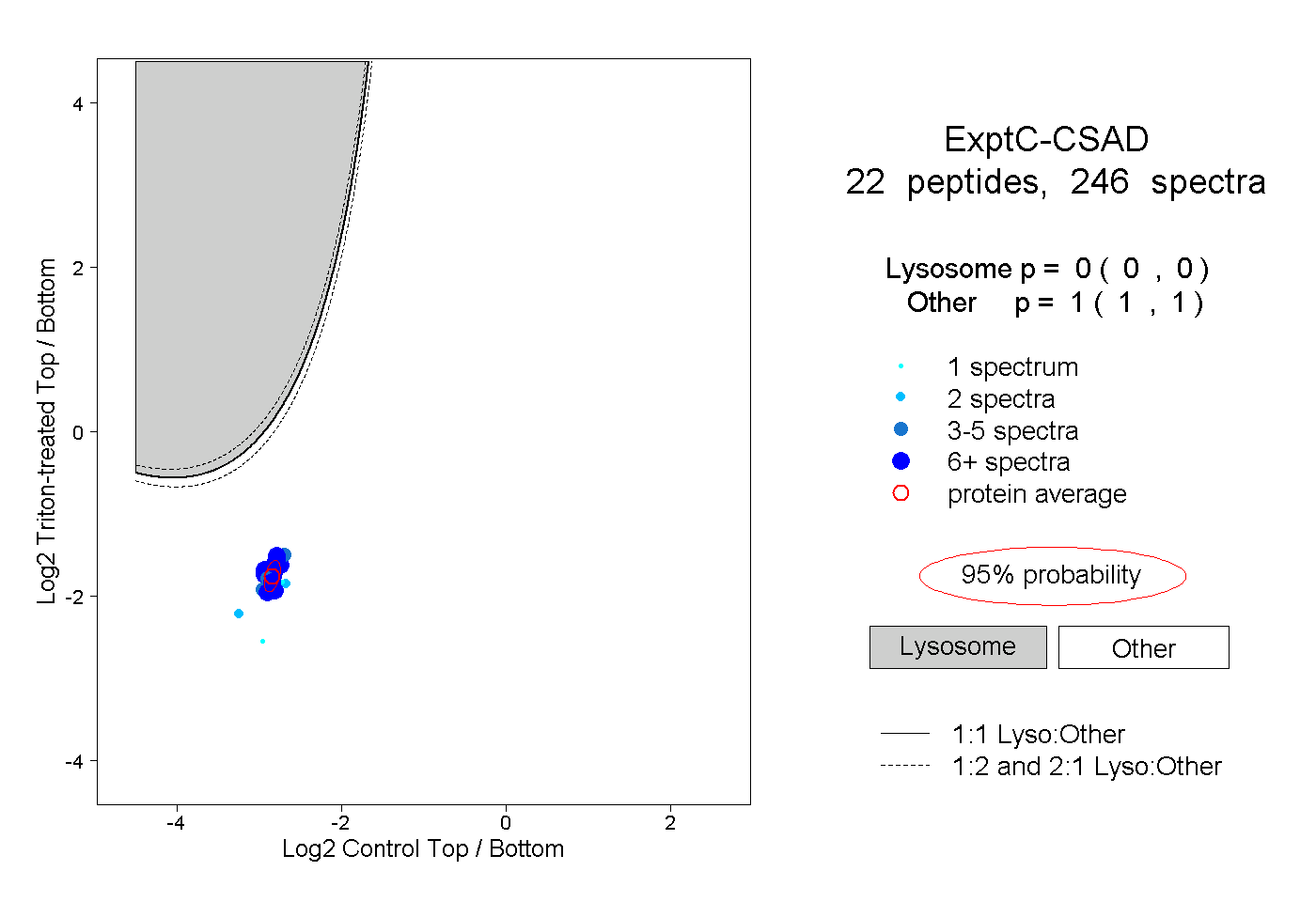
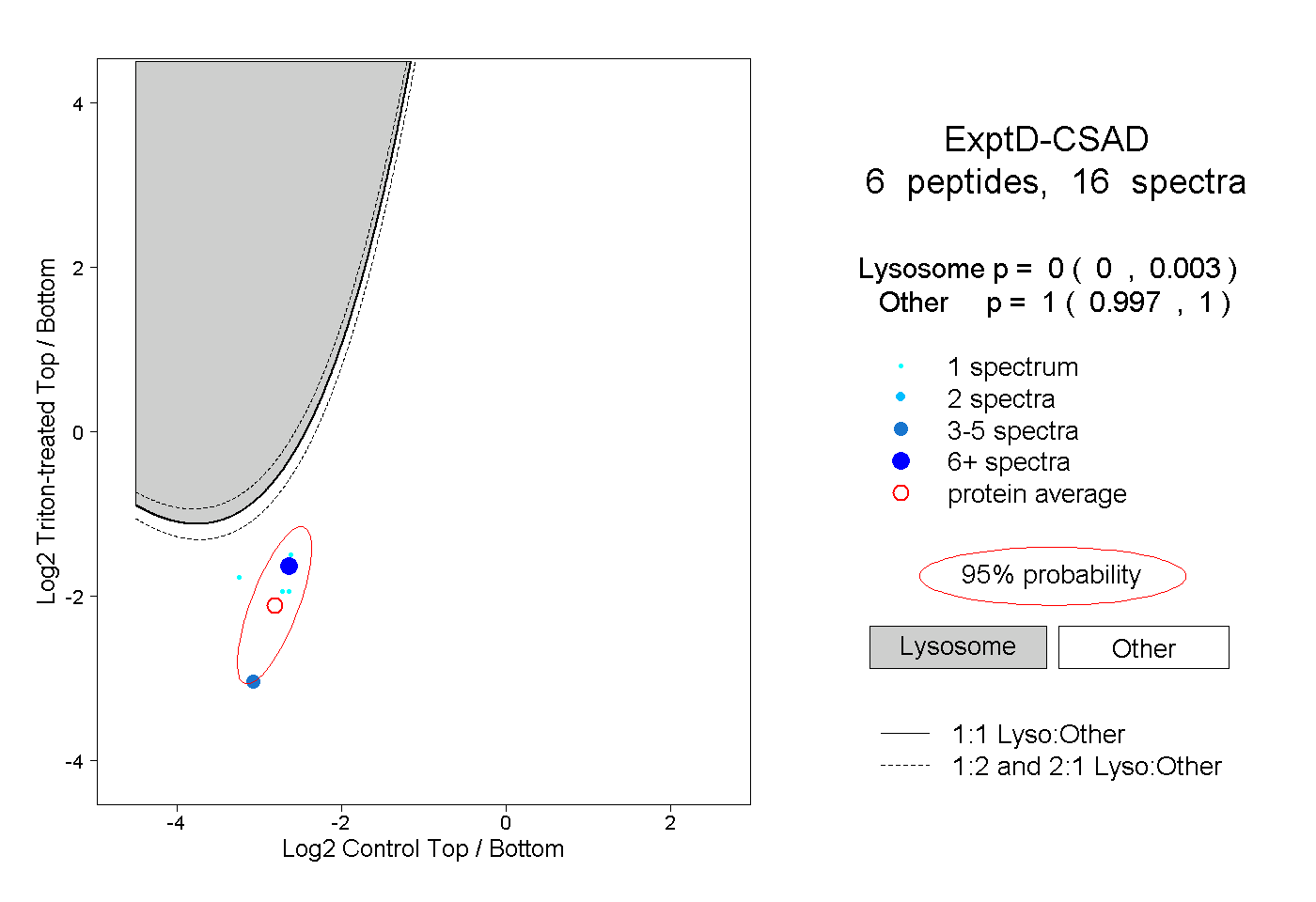
| 5 spectra, VVQCGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, HLLDGIQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, LLAAGLQCSALLLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, DVFGIVVDEAIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, IDQAFALTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, GAAFLGLGTDSVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, ESPDYSQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, QLLDLELQSQGESR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, GTNASEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 31 spectra, MIPEDLER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GTMMIGYQPHGTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FFNQLFSGLDPHALAGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, EPEELK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FYNVALDTGDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, DTSNLLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, AQGGQGLEWR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, AVIHYSVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, YLVEEIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, LSQVAPVLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, ALPPLALFTSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, TLDGDPVAVEALLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, ADSVAWNPHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |