peptides
spectra
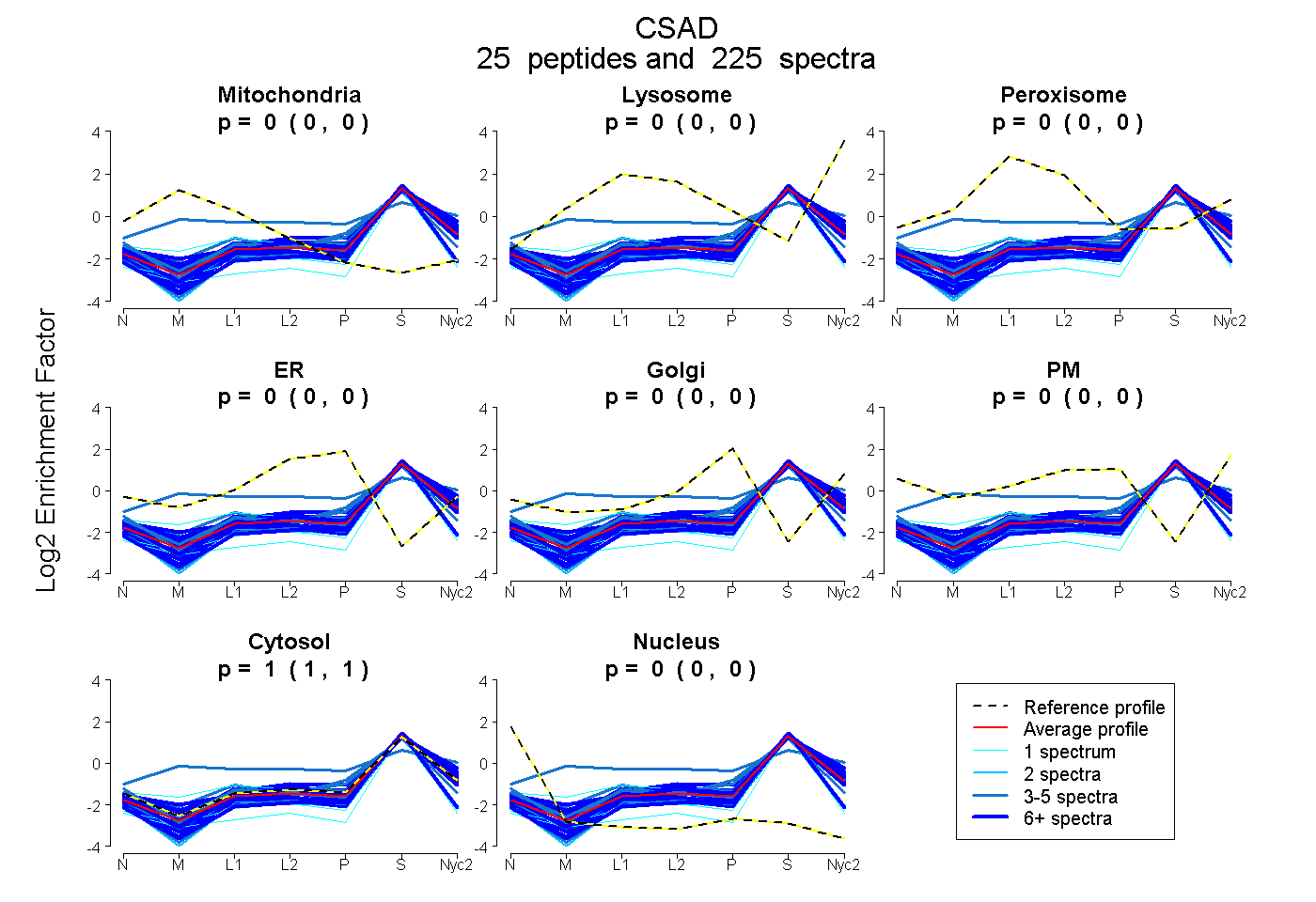
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
225 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
| 12 spectra, VVQCGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.914 | 0.086 | ||
| 16 spectra, HLLDGIQR | 0.020 | 0.014 | 0.000 | 0.000 | 0.000 | 0.000 | 0.966 | 0.000 | ||
| 1 spectrum, LLAAGLQCSALLLR | 0.168 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.826 | 0.006 | ||
| 13 spectra, DVFGIVVDEAIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 10 spectra, IDQAFALTR | 0.000 | 0.059 | 0.000 | 0.000 | 0.000 | 0.000 | 0.941 | 0.000 | ||
| 13 spectra, GAAFLGLGTDSVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 15 spectra, ESPDYSQR | 0.000 | 0.003 | 0.000 | 0.000 | 0.002 | 0.000 | 0.995 | 0.000 | ||
| 4 spectra, ECHYSITK | 0.061 | 0.000 | 0.000 | 0.026 | 0.000 | 0.000 | 0.912 | 0.000 | ||
| 4 spectra, QLLDLELQSQGESR | 0.000 | 0.000 | 0.000 | 0.000 | 0.038 | 0.000 | 0.962 | 0.000 | ||
| 5 spectra, GTNASEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 35 spectra, MIPEDLER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 3 spectra, GTMMIGYQPHGTR | 0.109 | 0.166 | 0.160 | 0.000 | 0.065 | 0.000 | 0.500 | 0.000 | ||
| 1 spectrum, FFNQLFSGLDPHALAGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.848 | 0.152 | ||
| 3 spectra, EPEELK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, FYNVALDTGDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, DTSNLLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.994 | 0.006 | ||
| 12 spectra, AQGGQGLEWR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.988 | 0.012 | ||
| 9 spectra, AVIHYSVK | 0.000 | 0.000 | 0.000 | 0.045 | 0.000 | 0.000 | 0.955 | 0.000 | ||
| 17 spectra, YLVEEIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 9 spectra, CHGSQASYLFQQDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 6 spectra, LSQVAPVLK | 0.000 | 0.040 | 0.000 | 0.000 | 0.000 | 0.000 | 0.960 | 0.000 | ||
| 21 spectra, ALPPLALFTSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 5 spectra, TLDGDPVAVEALLR | 0.001 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.990 | 0.009 | ||
| 6 spectra, LWLMWK | 0.000 | 0.006 | 0.000 | 0.000 | 0.000 | 0.000 | 0.994 | 0.000 | ||
| 2 spectra, ADSVAWNPHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.976 | 0.024 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
111 spectra |
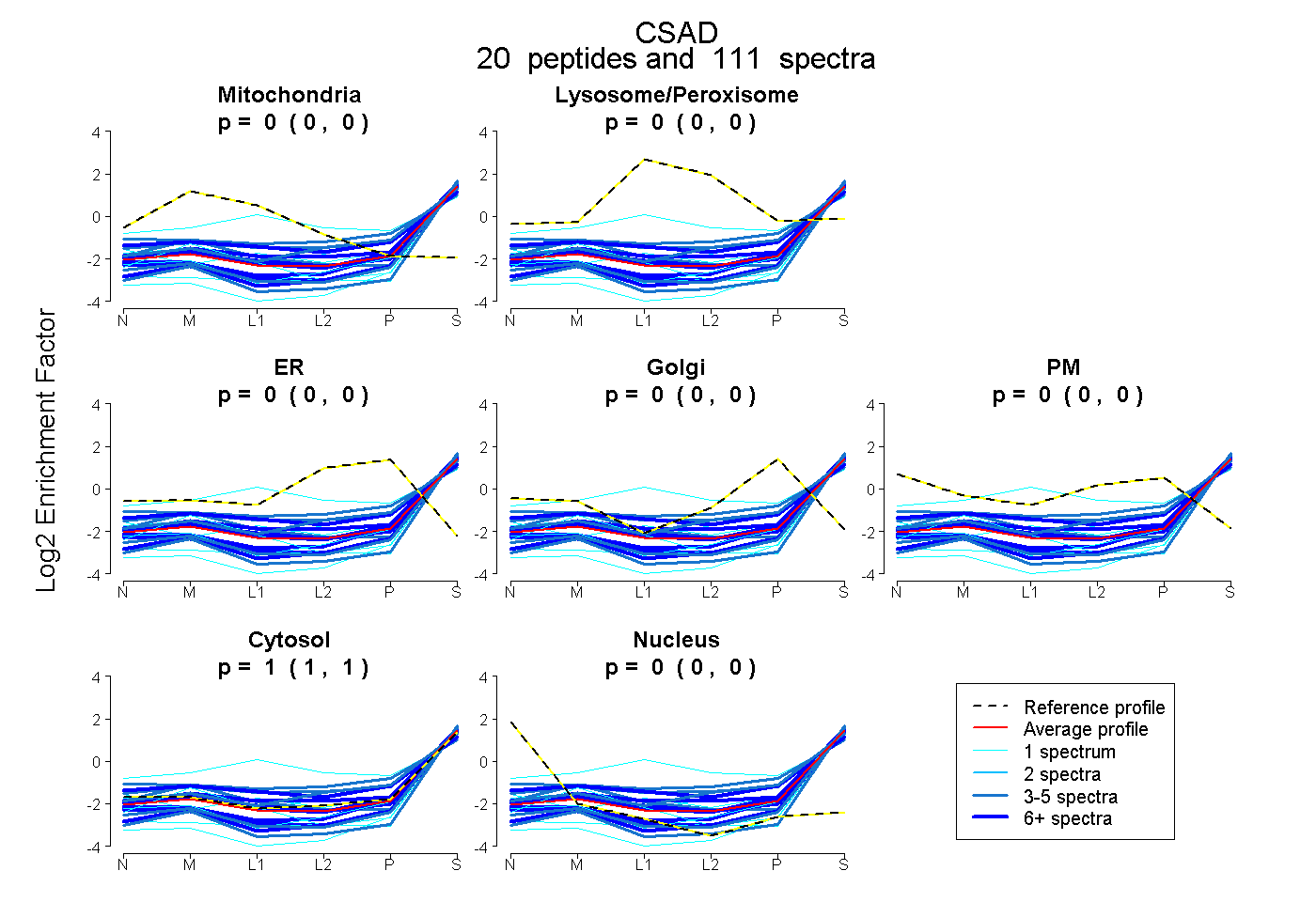 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
246 spectra |
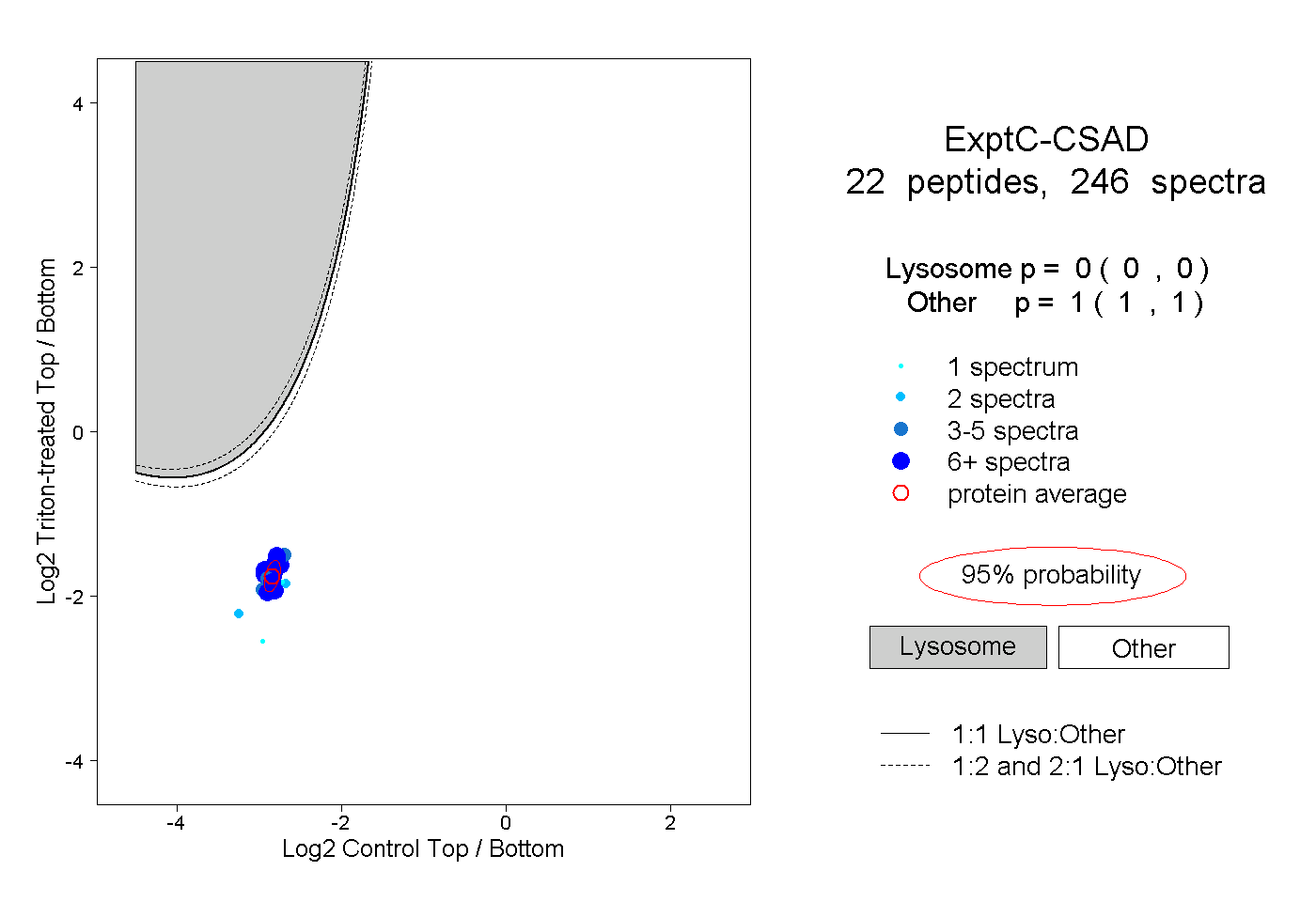 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
16 spectra |
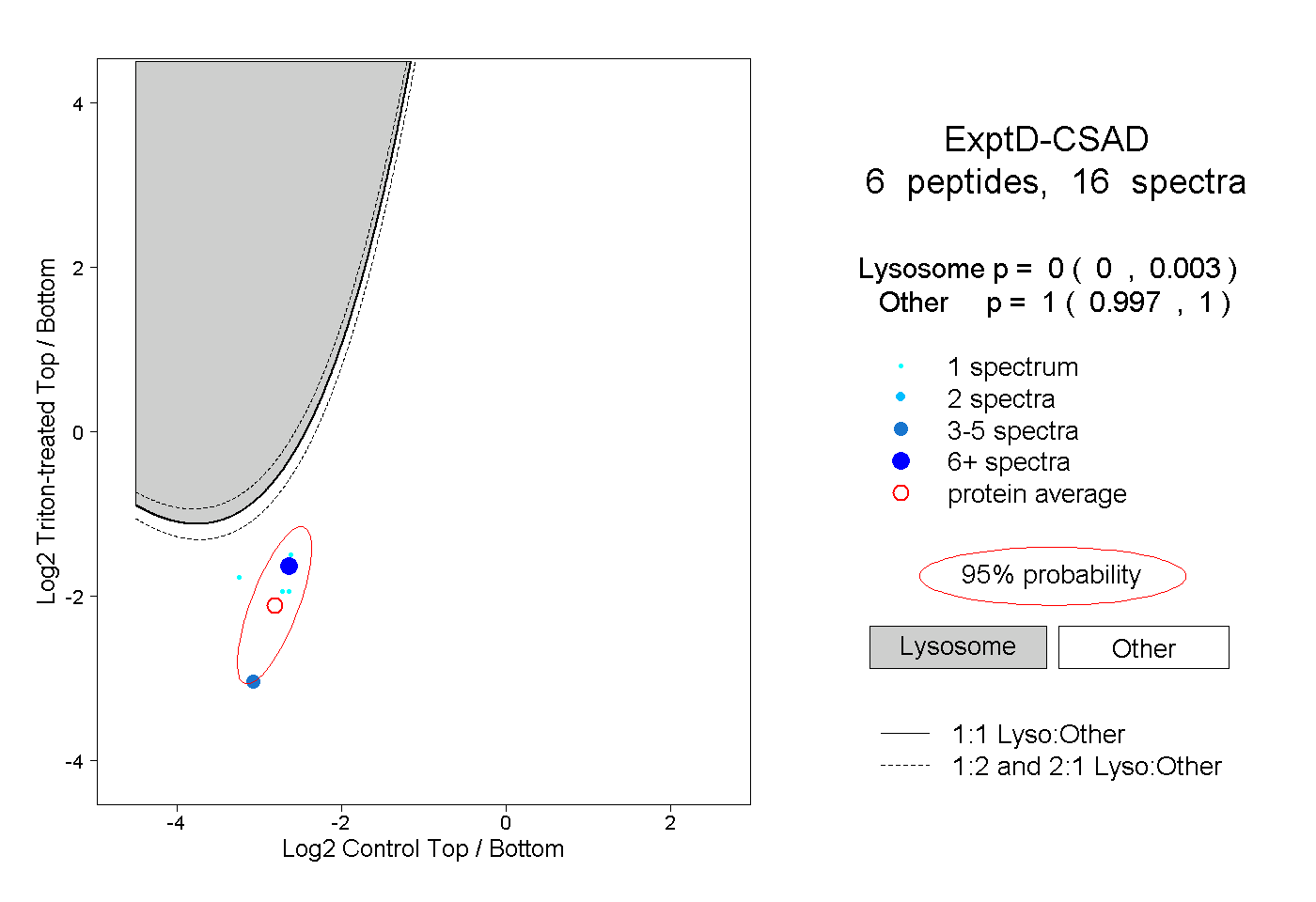 |
0.000 0.000 | 0.003 |
1.000 0.997 | 1.000 |