peptides
spectra
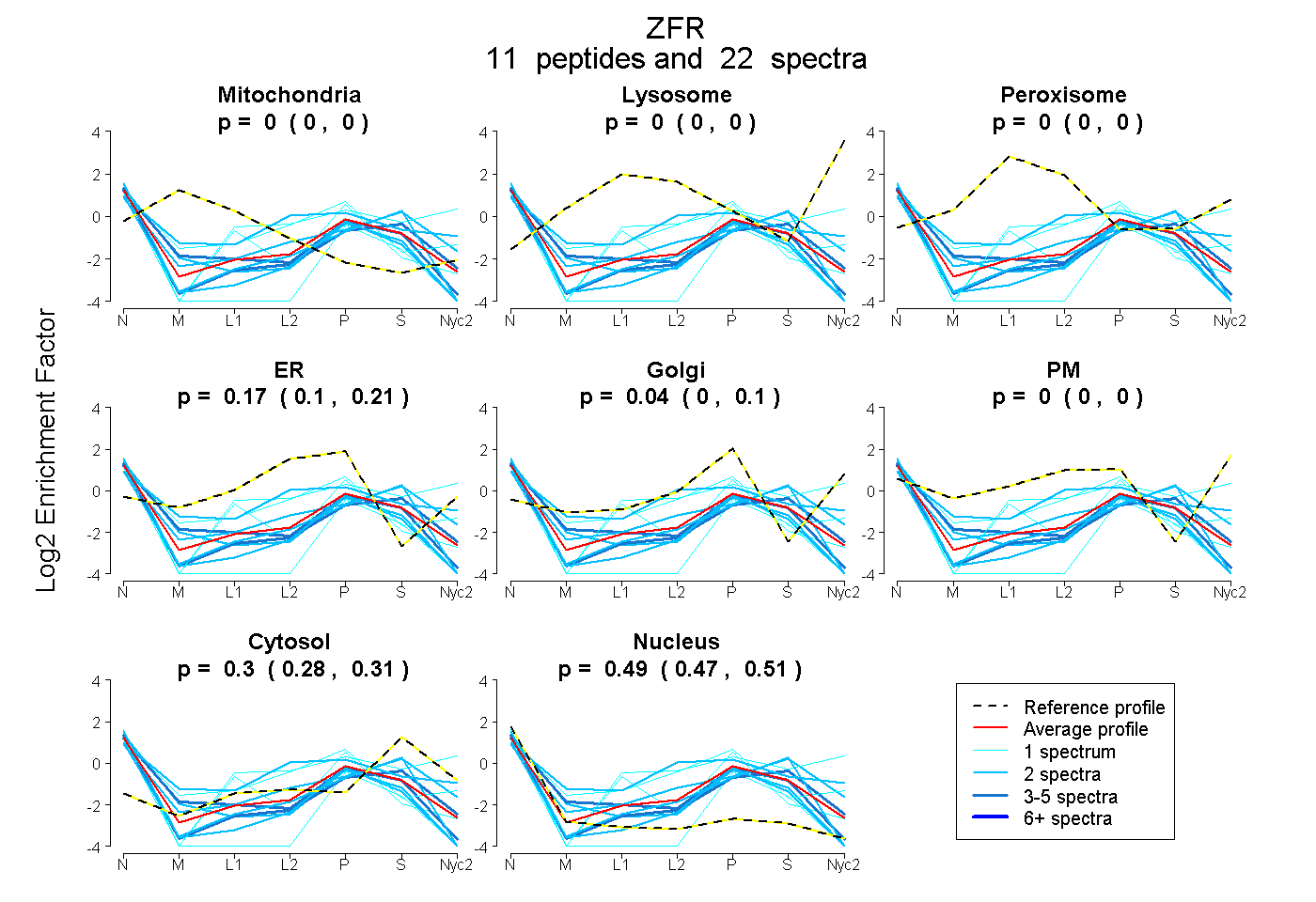
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.103 | 0.214
0.000 | 0.103
0.000 | 0.000
0.280 | 0.312
0.472 | 0.506
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.174 0.103 | 0.214 |
0.038 0.000 | 0.103 |
0.000 0.000 | 0.000 |
0.298 0.280 | 0.312 |
0.491 0.472 | 0.506 |
| 5 spectra, DPPDVLDR | 0.000 | 0.000 | 0.000 | 0.186 | 0.000 | 0.000 | 0.238 | 0.576 | ||
| 2 spectra, CLDALAALR | 0.000 | 0.000 | 0.000 | 0.155 | 0.000 | 0.000 | 0.160 | 0.685 | ||
| 1 spectrum, QPPKPPQIHYCDVCK | 0.000 | 0.000 | 0.000 | 0.412 | 0.111 | 0.073 | 0.088 | 0.317 | ||
| 1 spectrum, NNPAASAVQIPEVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.002 | 0.420 | 0.480 | 0.099 | ||
| 1 spectrum, AGYSQGATQYTQAQQAR | 0.000 | 0.000 | 0.000 | 0.202 | 0.147 | 0.000 | 0.084 | 0.567 | ||
| 2 spectra, STAPAVAYDSK | 0.000 | 0.000 | 0.000 | 0.276 | 0.000 | 0.231 | 0.302 | 0.191 | ||
| 3 spectra, DSDGVDGFEAEGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.060 | 0.000 | 0.412 | 0.527 | ||
| 2 spectra, RPDSSDDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.471 | 0.529 | ||
| 1 spectrum, AISSASSPQSPGDALR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.102 | 0.898 | ||
| 2 spectra, EDITSSAQFALR | 0.000 | 0.000 | 0.000 | 0.087 | 0.000 | 0.000 | 0.161 | 0.751 | ||
| 2 spectra, FNIHNNR | 0.000 | 0.000 | 0.000 | 0.098 | 0.000 | 0.070 | 0.531 | 0.301 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
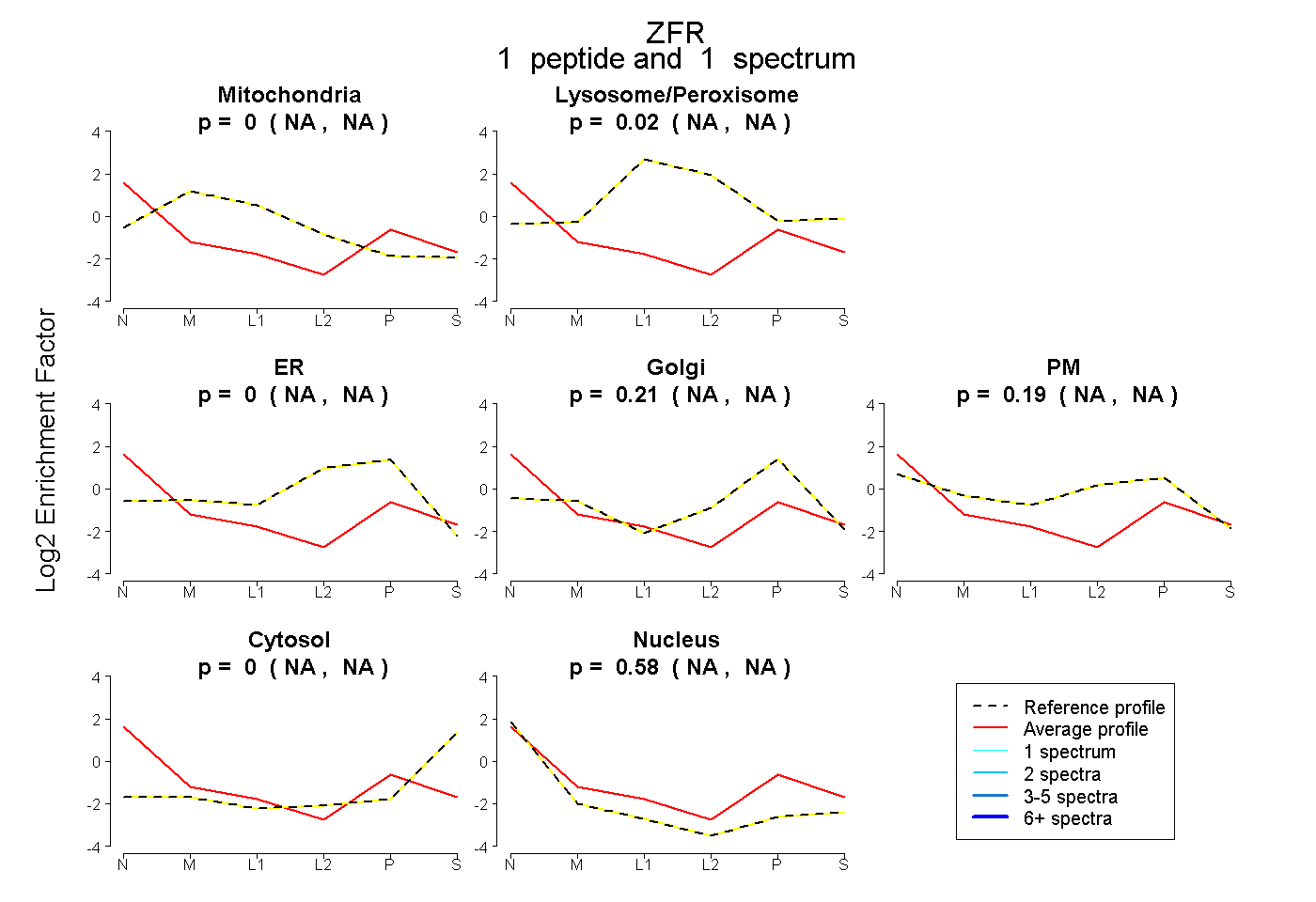 |
0.000 NA | NA |
0.022 NA | NA |
0.000 NA | NA |
0.208 NA | NA |
0.186 NA | NA |
0.000 NA | NA |
0.585 NA | NA |