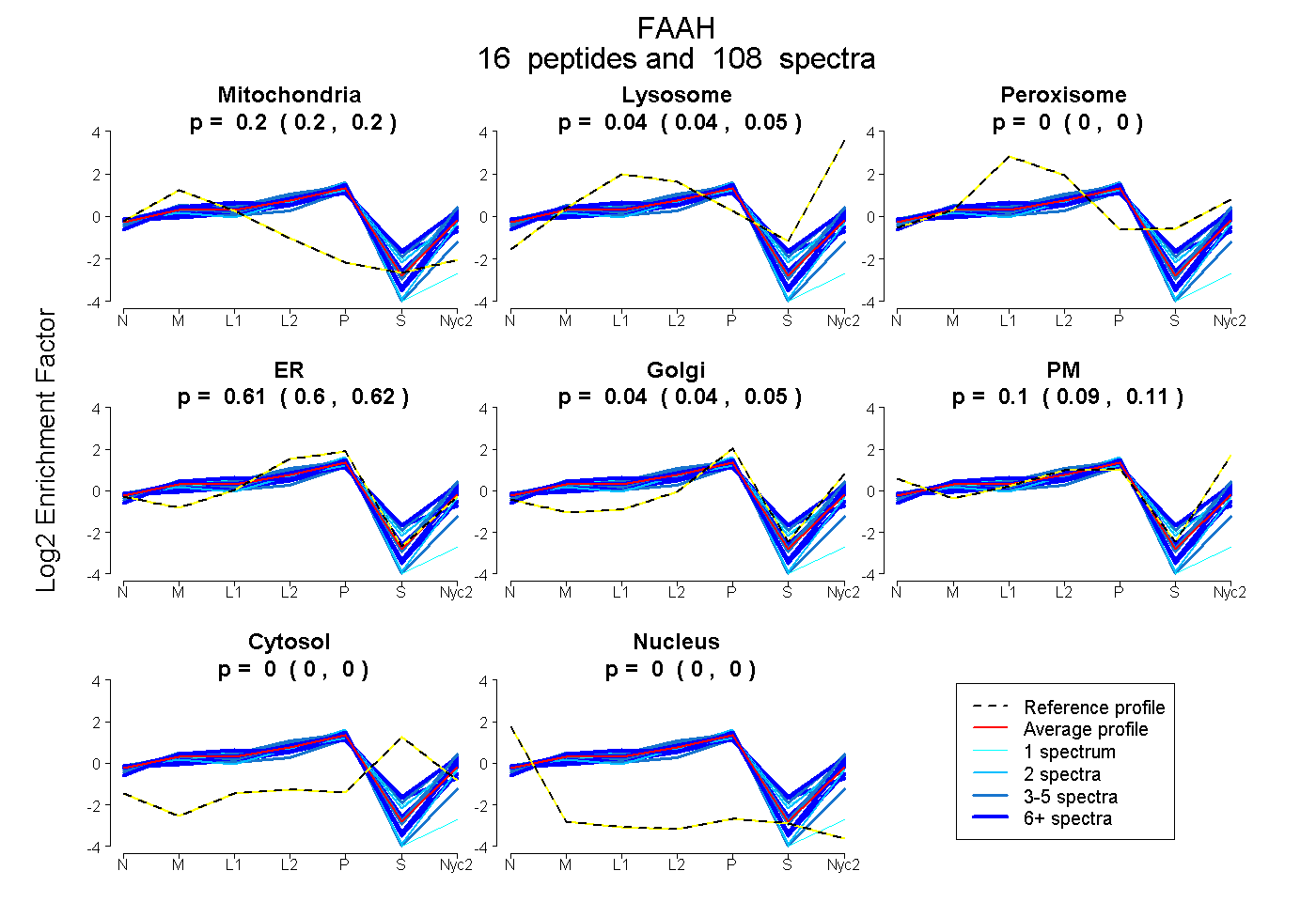
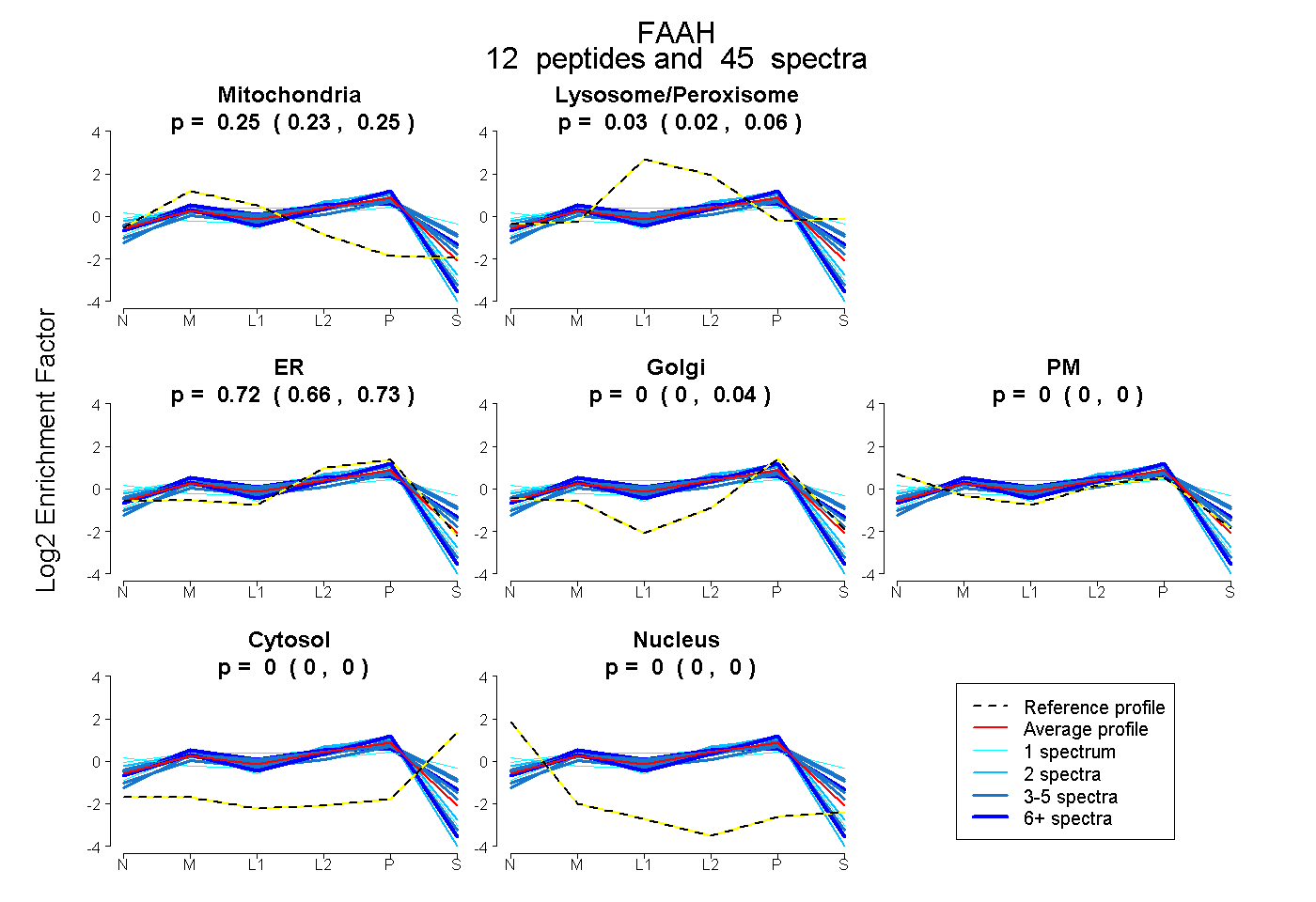
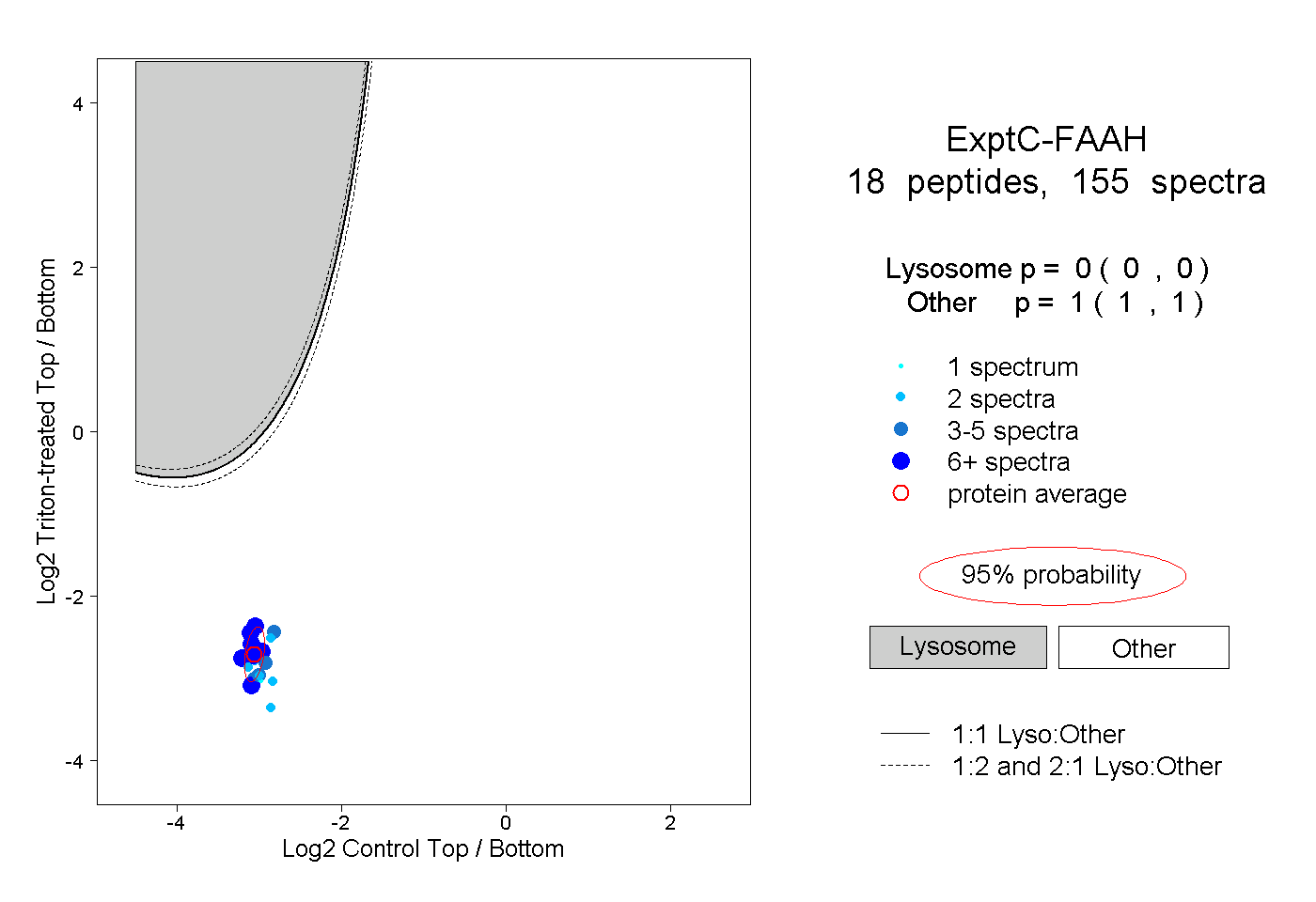
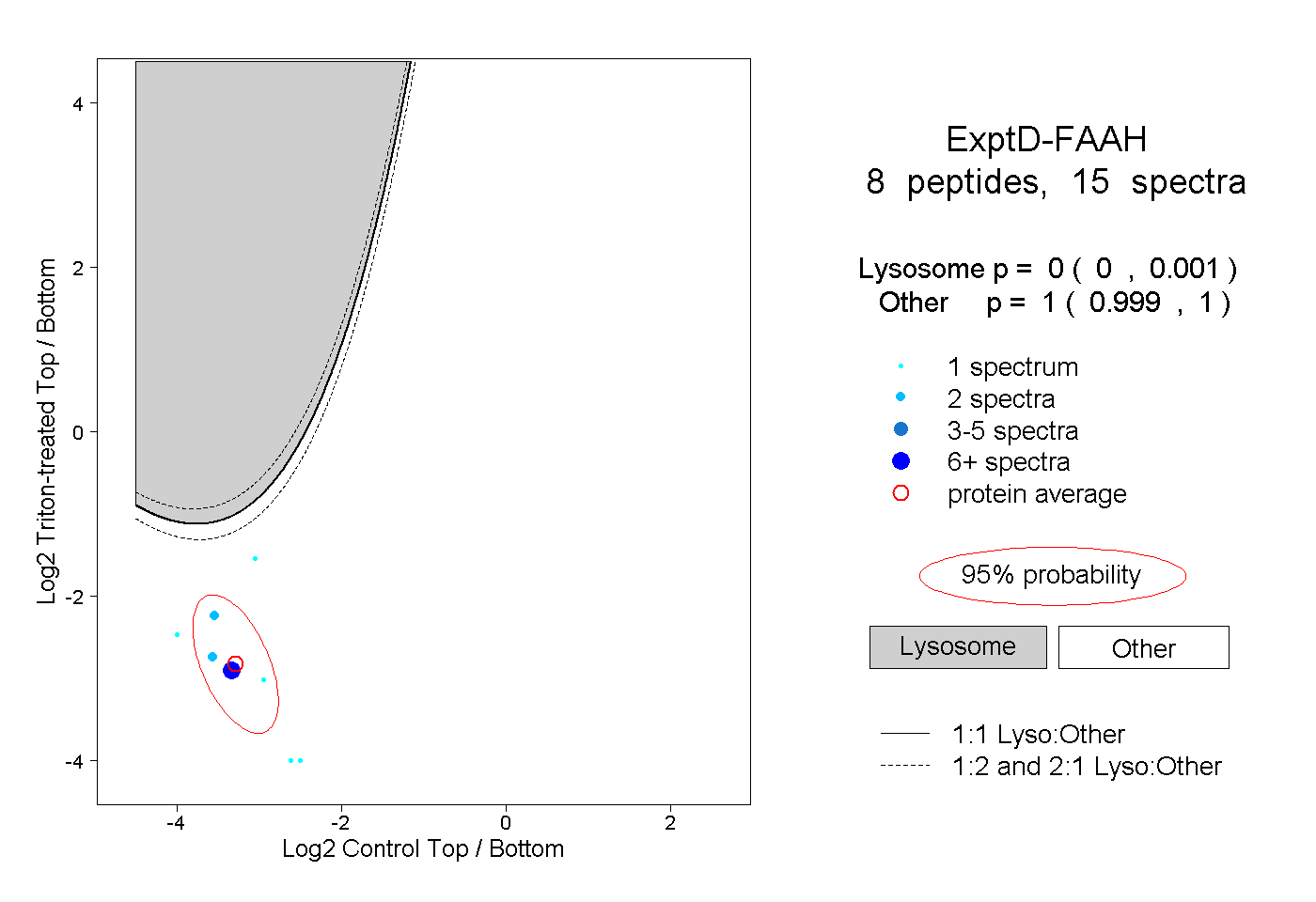
| 3 spectra, GCVYGQTAVQLSLGPMAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 37 spectra, ASLETMDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 28 spectra, SFLQNFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, ECFSYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, FPSAFCGICGLKPTGNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QGLLYGVPVSLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GDFVDPCLGDLILILR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SSRPLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, DVESLALCLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, LPSWFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, LQHEIEMYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LQSGELSPEAVFFTYLGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QSVIAQWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VGYYETDNYTMPSPAMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, AWEVNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, GYFGDIWDIILK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, LAAFLNSMRPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ALLCEHLFTLDPTVPPLPFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |