peptides
spectra
0.000 | 0.000
0.020 | 0.030
0.000 | 0.000
0.000 | 0.000
0.023 | 0.032
0.000 | 0.000
0.943 | 0.950
0.000 | 0.000
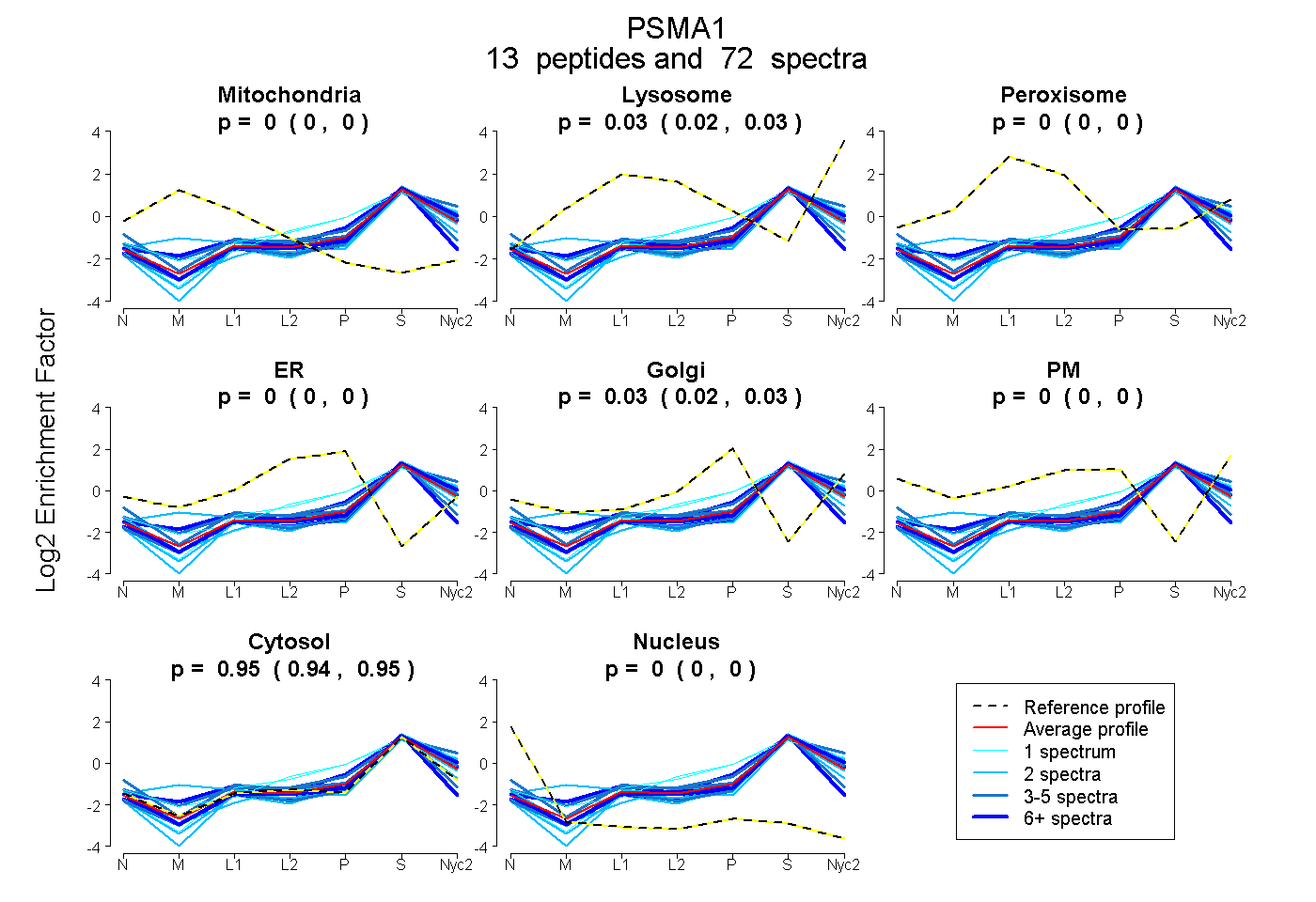
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
72 spectra |
 |
0.000 0.000 | 0.000 |
0.025 0.020 | 0.030 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.028 0.023 | 0.032 |
0.000 0.000 | 0.000 |
0.947 0.943 | 0.950 |
0.000 0.000 | 0.000 |
| 2 spectra, AQPSQAADEPAEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.982 | 0.017 | ||
| 2 spectra, ETLPAEQDLTTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 3 spectra, IHQIEYAMEAVK | 0.000 | 0.022 | 0.000 | 0.000 | 0.000 | 0.098 | 0.880 | 0.000 | ||
| 13 spectra, FVFDRPLPVSR | 0.000 | 0.020 | 0.000 | 0.000 | 0.077 | 0.000 | 0.904 | 0.000 | ||
| 2 spectra, AQSELAAHQK | 0.125 | 0.067 | 0.000 | 0.000 | 0.000 | 0.000 | 0.808 | 0.000 | ||
| 1 spectrum, THAVLVALK | 0.000 | 0.070 | 0.000 | 0.000 | 0.188 | 0.000 | 0.741 | 0.000 | ||
| 1 spectrum, NVSIGIVGK | 0.000 | 0.004 | 0.000 | 0.000 | 0.144 | 0.000 | 0.852 | 0.000 | ||
| 2 spectra, NQYDNDVTVWSPQGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 11 spectra, LLCNFMR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.967 | 0.033 | ||
| 4 spectra, QECLDSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.996 | 0.004 | ||
| 16 spectra, TQIPTQR | 0.000 | 0.040 | 0.000 | 0.000 | 0.000 | 0.000 | 0.960 | 0.000 | ||
| 10 spectra, AMSIGAR | 0.000 | 0.107 | 0.000 | 0.000 | 0.000 | 0.000 | 0.893 | 0.000 | ||
| 5 spectra, LVSLIGSK | 0.000 | 0.148 | 0.000 | 0.000 | 0.045 | 0.000 | 0.807 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
25 spectra |
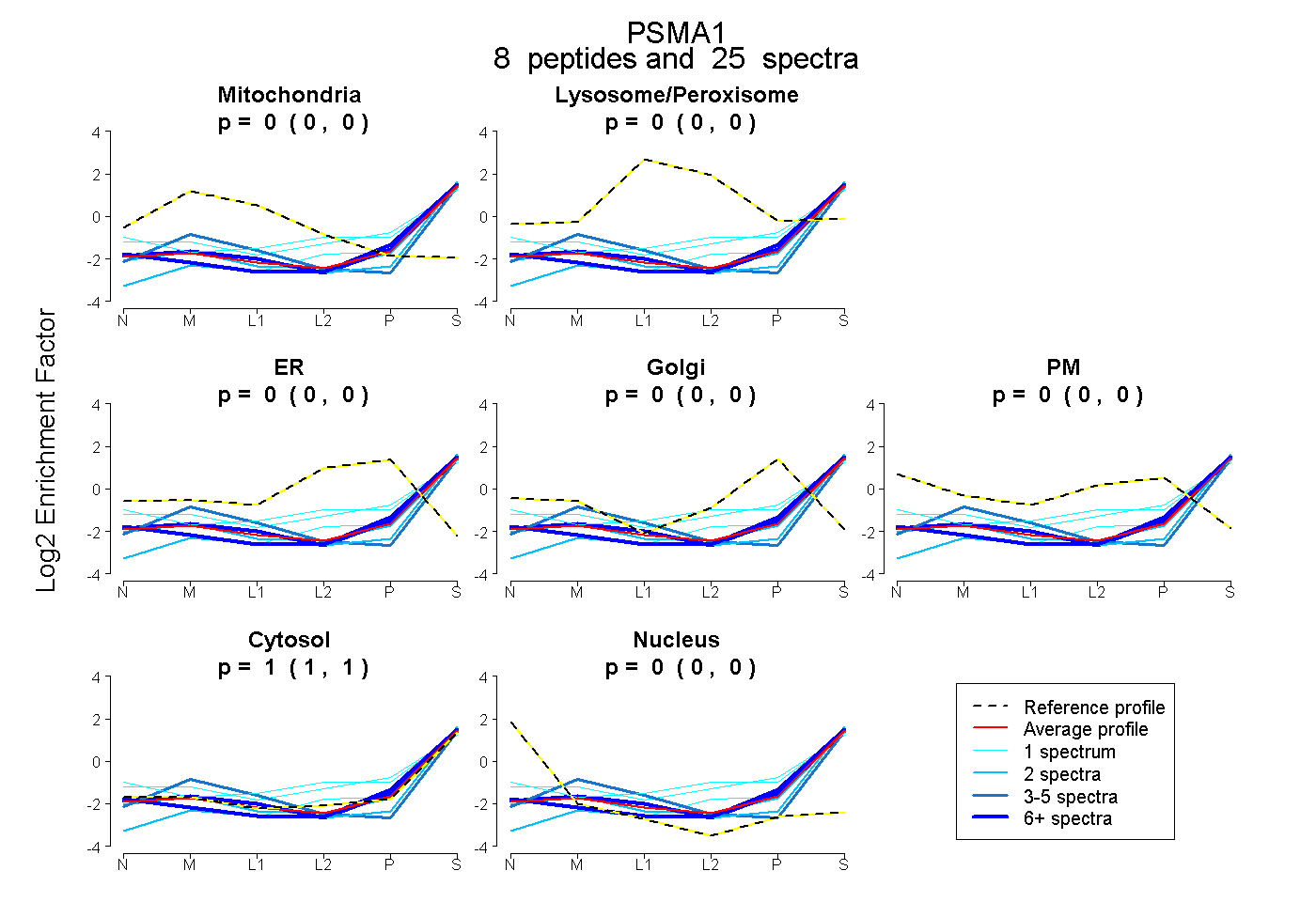 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
77 spectra |
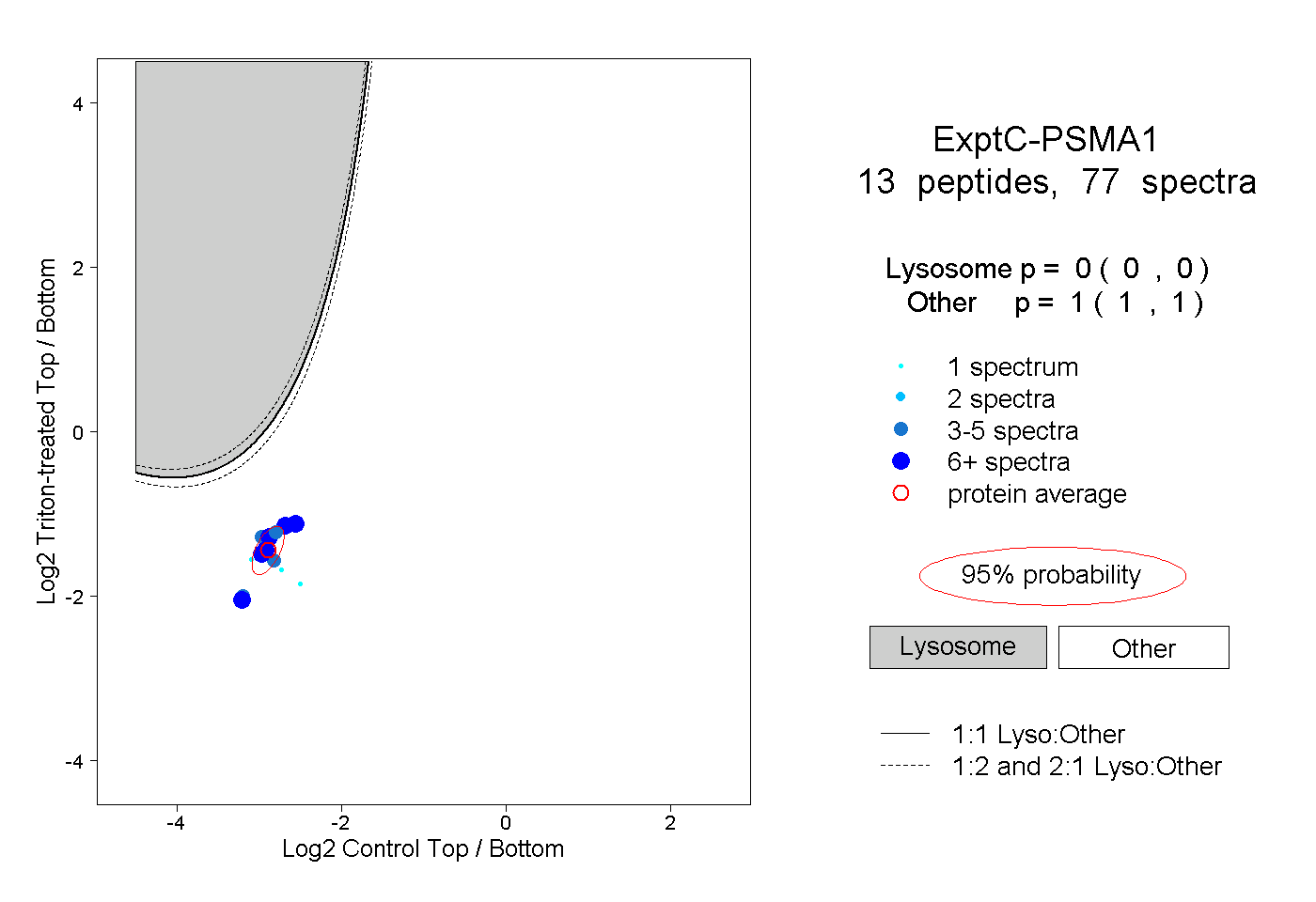 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
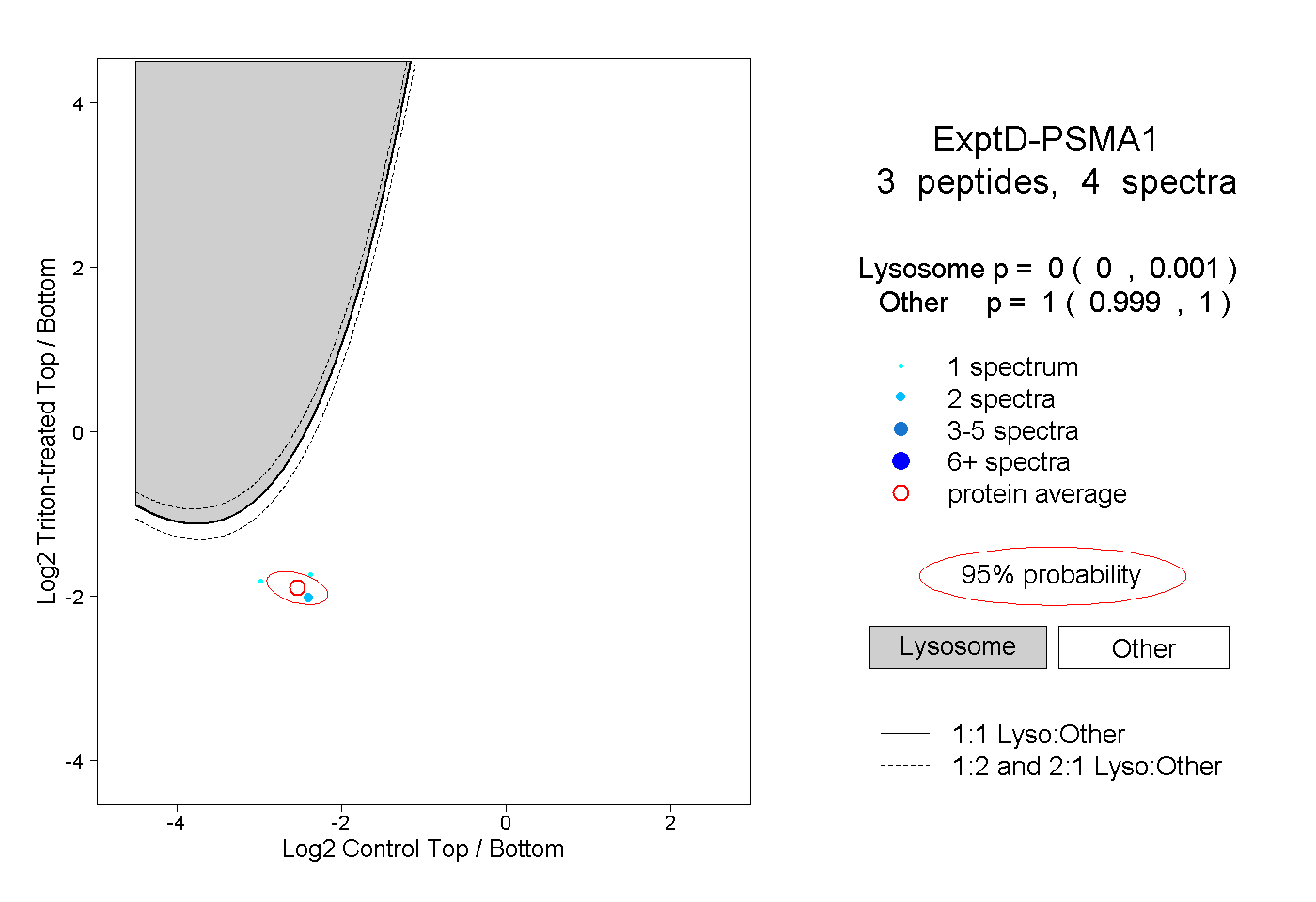 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |